Clear Sky Science · it
Integrazione, allineamento e annotazione multi-specie di dati single-cell RNA-seq con CAMEX
Perché questa ricerca è importante
Ogni corpo animale è composto da un ricco insieme di tipi cellulari, eppure non disponiamo ancora di una mappa chiara di come queste cellule si confrontino tra specie o cambino nel corso dell'evoluzione. Questo studio presenta CAMEX, uno strumento computazionale che unisce dati di attività genica a singola cellula provenienti da molte specie diverse in un quadro condiviso. Per il lettore non specialista, è una notizia entusiasmante perché ci avvicina a rispondere a domande come quali tipi cellulari siano veramente universali, quali siano unici negli esseri umani e come organi come cervello, fegato e testicolo si siano formati nel tempo evolutivo.
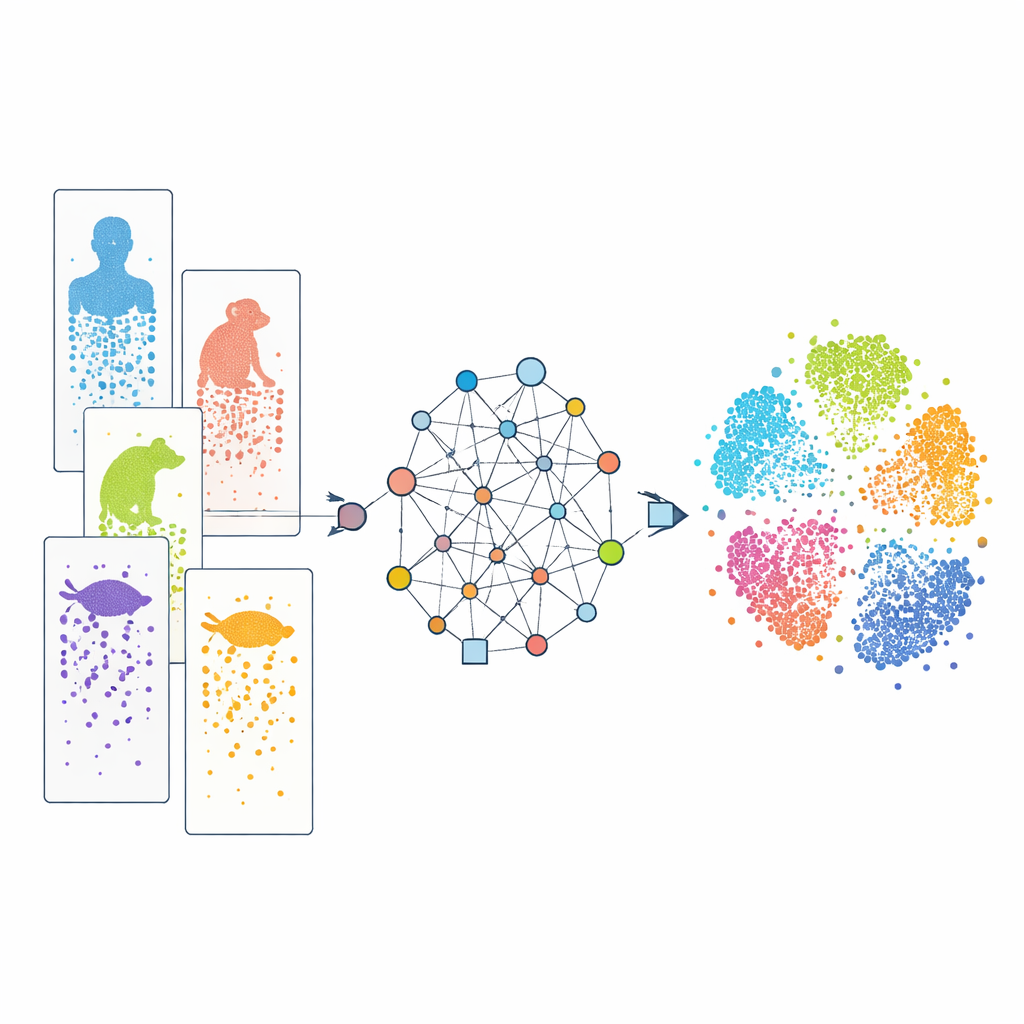
Osservare le cellule una per una
Il moderno sequenziamento dell'RNA a singola cellula permette agli scienziati di leggere quali geni sono attivi in migliaia fino a milioni di cellule individuali in un singolo esperimento. Confrontando questi pattern, i ricercatori possono raggruppare le cellule in tipi e seguire il loro sviluppo. Esistono ormai molti dataset per umani, scimmie, topi, pesci, rettili e altri. Tuttavia, ogni studio spesso utilizza tecnologie sperimentali diverse, e le specie variano nei loro repertori genici. Inoltre, la nostra conoscenza dei geni è disomogenea: gli animali da laboratorio ben studiati sono molto meglio annotati rispetto a specie meno studiate. Queste differenze agiscono come “batch effect” e dizionari incompleti, rendendo difficile allineare cellule simili tra specie e determinare quali caratteristiche siano veramente condivise o specifiche di una specie.
Un approccio basato sui grafi per connettere le specie
CAMEX affronta questi ostacoli trasformando tutti i dati in un unico grande network che include sia cellule sia geni. In questa rete, le cellule sono connesse ai geni che esprimono, ai loro vicini cellulari più simili, e i geni sono collegati tra specie se vengono giudicati correlati dall'evoluzione, anche quando la relazione è molti-a-molti anziché un semplice rapporto uno-a-uno. Un tipo specializzato di modello di apprendimento automatico, una rete neurale su grafo eterogeneo, trasmette informazioni lungo queste connessioni e impara una rappresentazione compatta (embedding) per ogni cellula e gene in uno spazio condiviso a bassa dimensionalità. Per l'integrazione dei dati, il modello viene addestrato a ricostruire sia la struttura della rete sia i pattern di attività genica originali senza che i tipi cellulari gli vengano comunicati a priori. Per l'annotazione cellulare, lo stesso encoder alimenta un classificatore basato sull'attenzione che può trasferire etichette note da una specie di riferimento a specie meno studiate.
Rivelare tipi cellulari e sviluppi condivisi
Gli autori mostrano che CAMEX surclassa una serie di strumenti popolari quando è messo alla prova su dataset reali e impegnativi. Nei dati di fegato, ovaio e pancreas che coprono fino a quattro specie e più piattaforme sperimentali, CAMEX ha trovato il miglior equilibrio tra due obiettivi contrastanti: rimuovere differenze di batch artificiali mantenendo le vere distinzioni biologiche tra tipi cellulari. Ha allineato con precisione popolazioni cellulari comuni come epatociti e cellule immunitarie e, cosa importante, ha preservato tipi cellulari rari che altri metodi tendevano a sfumare. In un test di grande impatto, CAMEX ha integrato dati di testicolo provenienti da 11 specie, dai primati all'ornitorinco e al pollo. Ha ricostruito il percorso continuo con cui le cellule germinali maturano fino agli spermatozoi e ha mostrato che l'uso di relazioni geniche molti-a-molti è cruciale per mantenere le prestazioni man mano che le specie diventano più distanti. Il modello ha anche allineato con successo stadi dello sviluppo degli organi in sette specie, estendendo l'idea dei classici stadi di Carnegie oltre il ristretto insieme di organismi modello per i quali erano stati definiti originariamente.
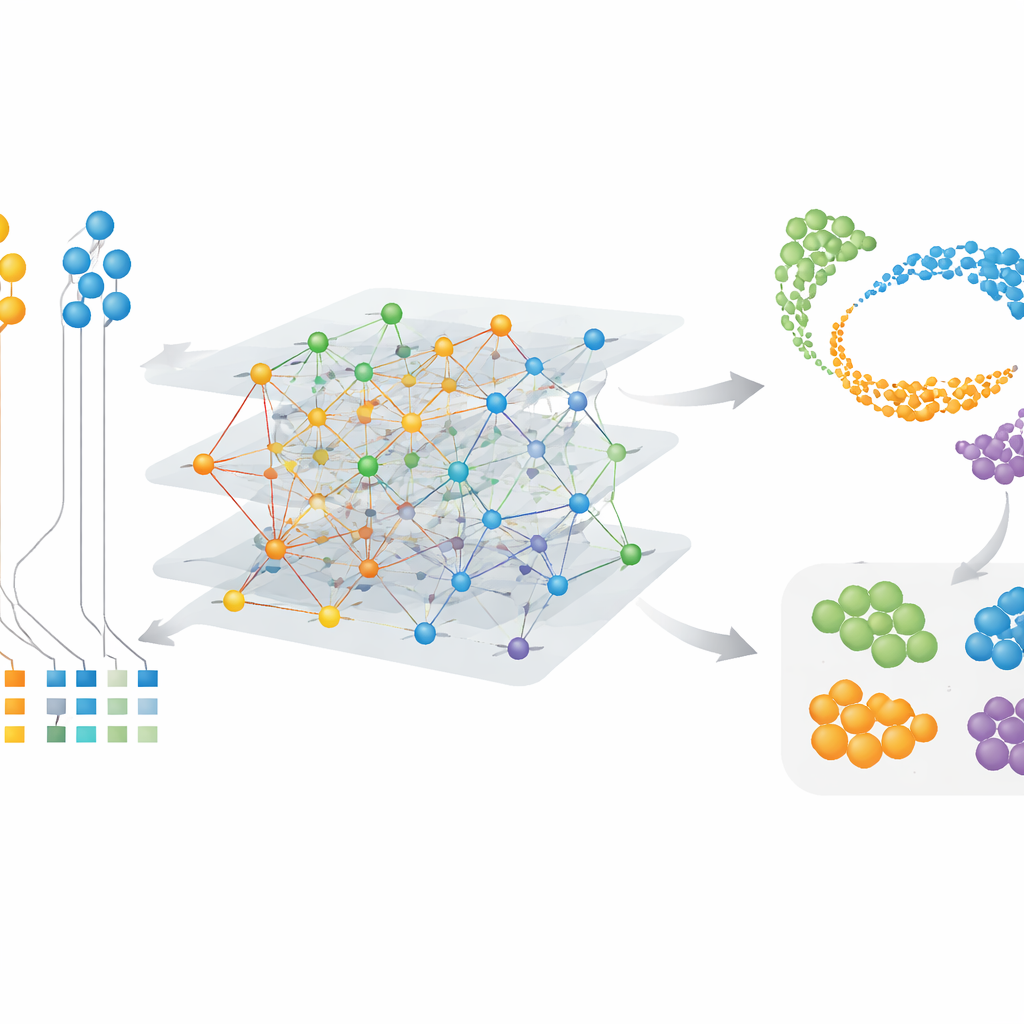
Individuare cellule e moduli genici specifici per specie
Poiché CAMEX apprende embedding sia per cellule sia per geni, può evidenziare caratteristiche speciali oltre a quelle condivise. In dataset cerebrali che includevano uomo, topo, lucertola e tartaruga, CAMEX ha integrato i dati e, usando le etichette umane come guida, ha annotato con precisione i tipi cellulari nelle altre specie, anche sottogruppi piccoli come i periciti cerebrali nella tartaruga. Applicando il metodo a una mappa dettagliata della corteccia prefrontale dorsolaterale dei primati, gli autori sono stati in grado di isolare sottotipi specifici di microglia — le cellule immunitarie del cervello — presenti solo negli esseri umani o condivise con gli scimpanzé. Raggruppando gli embedding genici, hanno anche individuato gruppi di geni legati a funzioni chiave: ad esempio moduli attivi nelle cellule di supporto somatiche nel testicolo e altri associati alla meiosi, il processo di divisione cellulare che produce gli spermatozoi. Questi risultati indicano sia programmi conservati sia adattamenti specifici di specie nel comportamento cellulare.
Cosa significa per il quadro più ampio
In termini semplici, CAMEX è un nuovo e potente “motore di traduzione” per i dati single-cell attraverso l'albero della vita. Aiuta gli scienziati a capire quando cellule di animali diversi svolgono essenzialmente lo stesso ruolo, quando si sono diverte e come le tempistiche dello sviluppo si confrontano tra specie. Pur avendo ancora limiti — come la dipendenza dalle mappe di omologia esistenti e le sfide generali nell'interpretare modelli basati su grafi — consente già confronti evolutivi più ricchi rispetto a quanto era possibile in precedenza. Con il tempo, strumenti come CAMEX potrebbero contribuire a costruire un vero e proprio albero dei tipi cellulari, affinare i nostri modelli dello sviluppo degli organi e guidare la ricerca di tipi cellulari rilevanti per le malattie e di bersagli farmacologici sia negli umani sia nei modelli animali.
Citazione: Guo, ZH., Huang, DS. & Zhang, S. Multi-species integration, alignment and annotation of single-cell RNA-seq data with CAMEX. Nat Commun 17, 3017 (2026). https://doi.org/10.1038/s41467-026-69696-3
Parole chiave: sequenziamento dell'RNA a singola cellula, integrazione tra specie, reti neurali su grafi, evoluzione dei tipi cellulari, genomica comparativa