Clear Sky Science · sv
Fullständigt genomsekvensering av Sphingomonas sp. gentR, en bakterie med hög gentamicinresistens
Varför en laboratoriemikrob spelar roll för vardagsmedicin
Antibiotika som gentamicin är arbetsmyror inom sjukvård och jordbruk, men bakterier lär sig stadigt att överleva dem. Denna studie zoomar in på en enskild, ovanligt tålig mikroorganism kallad Sphingomonas sp. gentR som kan stå emot mycket höga doser gentamicin. Genom att avkoda dess hela genetiska ritning avslöjar forskarna var dess resistensmekanismer döljer sig och gör dessa data fritt tillgängliga så att andra kan följa, förstå och kanske desarmera liknande mikrober innan deras försvar sprids till sjukdomsframkallande bakterier.
En tålig mikroorganism från en antibiotikalösning
Berättelsen börjar i ett vanligt laboratorium, där en arbetslösning av gentamicin—ett antibiotikum som används för att behandla allvarliga infektioner—hade förvarats kallt. Från just den lösningen isolerade teamet oväntat en gul, stavformig bakterie som tillhör Sphingomonas-gruppen. När de testade hur mycket gentamicin den kunde tåla växte mikroben även vid koncentrationer ungefär tusen gånger högre än de som stoppar många bakterier, vilket gjorde den till en extrem överlevare. Sphingomonas-arter är redan kända för att leva i hårda miljöer såsom ökensand, glaciäris, djupa bergarter och till och med rymdfarkoster, men denna nivå av gentamicinresistens hade inte setts i gruppen tidigare.
Att läsa mikrobernas hela instruktionsbok
För att ta reda på vad som gjorde denna stam så motståndskraftig extraherade forskarna dess DNA och använde två kompletterande sekvenseringstekniker. Den ena gav många korta, precisa DNA-fragment, medan den andra genererade färre men mycket långa fragment. Genom att kombinera dessa data monterade de ett komplett, gapfritt genom för bakterien: en huvudcirkulär kromosom och två mindre cirkulära DNA-bitar kallade plasmider. Därefter använde de en uppsättning specialiserade datorverktyg och referensdatabaser för att förutsäga gener, lokalisera rörliga element som virus och genomöar, och tilldela sannolika funktioner till nästan varje del av genomet, från grundläggande metabolism till stressresponser.
Var resistensen gömmer sig
Med det fullständiga genomet i handen sökte teamet igenom det mot kuraterade samlingar av kända antibiotikaresistensgener. De fann en liten uppsättning gener tydligt kopplade till resistens mot flera läkemedelsklasser. Mest anmärkningsvärt ligger tre bekräftade resistensgener—två som kan inaktivera aminoglykosidantibiotika såsom gentamicin och streptomycin, och en som skyddar mot sulfonamider—samlade på en distinkt DNA-sträcka inbäddad i en av plasmiderna. Denna region, känd som en genomö, är den molekylära motsvarigheten till en plug-and-play-modul: ett genkluster som kan flytta mellan DNA-molekyler och potentiellt mellan bakterier. Genomet bär också många gener som finjusterar hur cellen känner av sin omgivning, pumpar ut giftiga föreningar och upprätthåller sina membran, allt som kan stärka överlevnad under antibiotikastress.
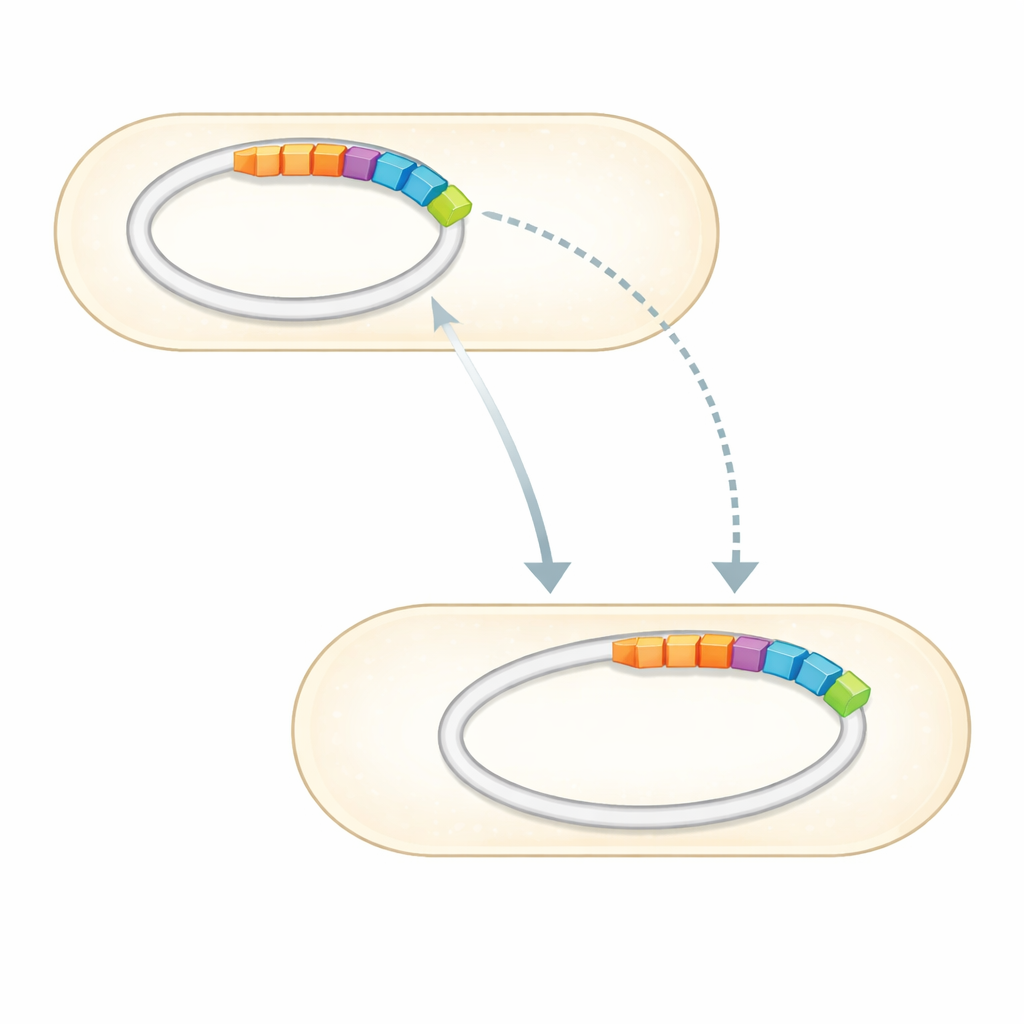
En mångsidig verktygslåda för liv i svåra miljöer
Utöver resistensen i sig målar genkatalogen upp Sphingomonas sp. gentR som en metabolisk generalist väl anpassad för liv i näringsfattiga eller förorenade miljöer. Många av dess gener stödjer energiproduktion, användning av aminosyror och nedbrytning eller transport av olika molekyler, vilket tyder på att den kan utnyttja ovanliga näringskällor. Andra antyder förmåga att tåla olika påfrestningar och kanske bryta ner främmande kemikalier. Denna mångsidighet hjälper till att förklara varför Sphingomonas-arter undersöks både som växtvänliga partners och som rengöringsagenter för industriella föroreningar, och varför en enskild stam kan frodas i en antibiotikarik nisch som en läkemedelslösning.
Vad detta genom betyder för hälsa och miljö
Genom att fullständigt kartlägga DNA hos en exceptionellt gentamicinresistent Sphingomonas-stam och lokalisera dess nyckelresistensgener till en mobil ö på en plasmid ger studien en detaljerad referens för forskare världen över. För folkhälsa belyser den en möjlig väg genom vilken kraftfulla resistensegenskaper kan hoppa från ofarliga miljöbakterier till patogener som infekterar människor, djur eller grödor. För miljövetenskap och bioteknik erbjuder den en genetisk verktygslåda som kan användas för att sanera förorenade platser där antibiotika eller andra kemikalier ansamlas. I enkla termer visar arbetet både hur tåliga vissa bakgrundsmikrober har blivit och ger forskare instruktionerna de behöver för att övervaka och hantera den tåligheten.
Citering: Liu, Y., Jiang, L., Zhang, J. et al. Complete genome sequence of Sphingomonas sp. gentR, a high-level gentamicin-resistant bacterium. Sci Data 13, 672 (2026). https://doi.org/10.1038/s41597-026-06723-4
Nyckelord: antibiotikaresistens, gentamicin, Sphingomonas, bakteriegenom, plasmidgener