Clear Sky Science · sv
4polar3D enkelmolekylavbildning av 3D-orientering i täta aktinnätverk med ratiometrisk polarisationsuppdelning
En ny metod för att se cellers dolda ordning
Inne i varje levande cell bildar långa, tunna proteinfilament ett skelett som ger cellen form och hjälper den att röra sig. Dessa fibrer är trånga och intrasslade, så även avancerade mikroskop ser ofta bara en suddig massa av fläckar. Denna studie introducerar en ny avbildningsmetod som kan avslöja inte bara var dessa små molekyler befinner sig, utan också hur de är orienterade i tre dimensioner, vilket gör det möjligt för forskare att kartlägga den dolda arkitekturen i detta inre skelett i intakta celler.
Varför riktningen spelar roll
Många proteiner i celler beter sig som små pilar: deras riktning i rummet påverkar hur de interagerar, bygger upp strukturer och genererar krafter. Traditionella superupplösningsmikroskop kan lokalisera enskilda fluorescerande molekyler med hög precision men förbiser i regel hur dessa är tilta eller roterade. För tätt packade strukturer, såsom aktinfilament vid cellkanten, räcker inte positionsinformation för att förstå hur fibrerna är ordnade eller hur de trycker och drar i cellmembranet. En teknik som fångar både position och orientering samtidigt, över stora ytor, kan överbrygga glappet mellan detaljrika strukturella metoder som elektronmikroskopi och snabbare optiska metoder som används i levande celler.
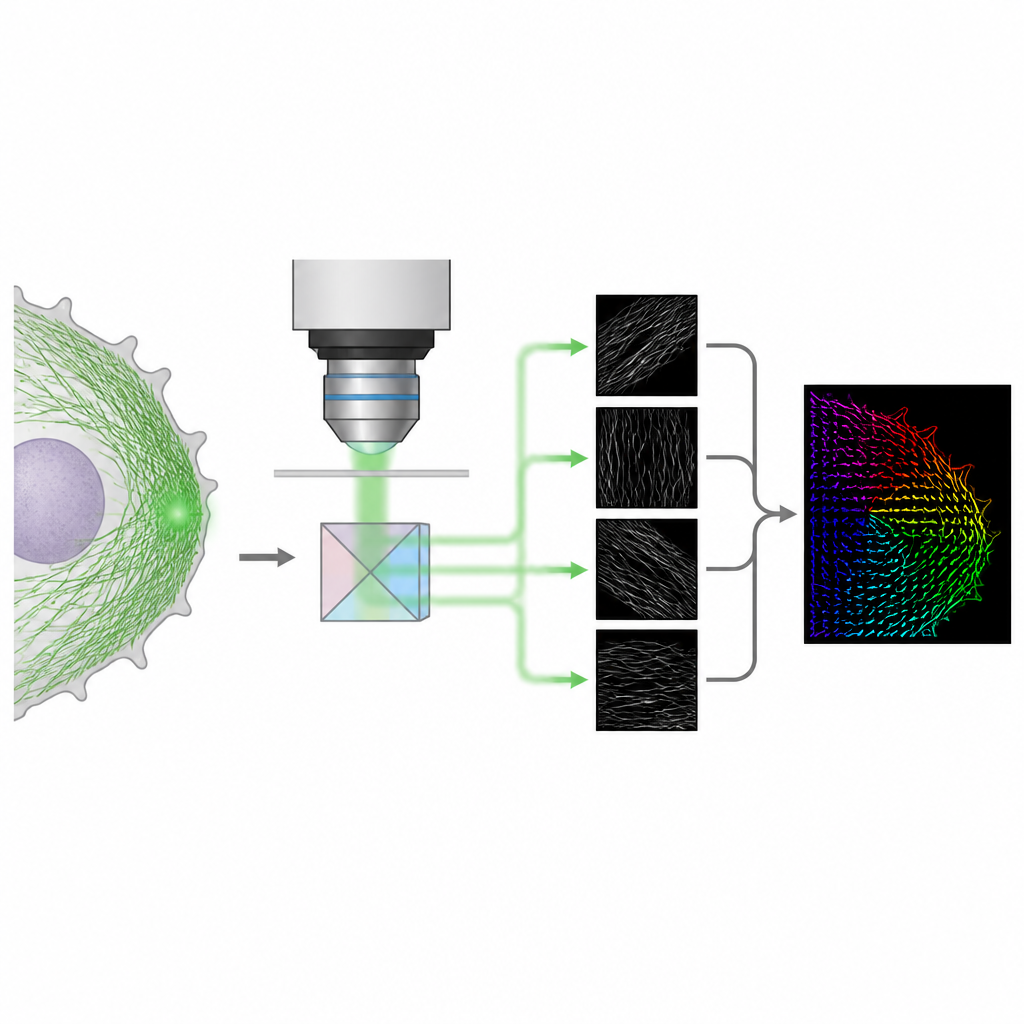
En enklare optisk lösning för 3D-orientering
Författarna presenterar en metod kallad 4polar3D som mäter hur enskilda fluorescerande molekyler är orienterade och hur mycket de fladdrar, samtidigt som den lokaliserar dem i cellen. Istället för att omforma ljusmönstret från varje molekyl med komplexa optiska element delar systemet upp det emitterade ljuset i fyra strålar, vardera filtrerad av en annan polarisationsriktning och numerisk apertur. Genom att jämföra hur starkt samma molekyl framträder i dessa fyra kanaler extraherar metoden tre nyckelparametrar: riktningen i planet i mikroskopets bildyta, hur mycket den är tiltat ut ur detta plan, och hur fritt den kan rotera. Eftersom metoden bara förlitar sig på integrerad ljusstyrka snarare än detaljerad mönsterpassning, är dataanalysen snabb och robust, även när många molekyler lyser samtidigt.
Försök på modellmembran
För att kontrollera att 4polar3D fungerar som avsett testade teamet först metoden på enkla lipidmembran märkta med en fluorescerande färg som tenderar att alignera med fettsyrakedjorna. På plana stödda membran mätte metoden en föredragen tilt hos färgmolekylerna och en bred fladdring, i överensstämmelse med tidigare, mer komplexa tillvägagångssätt. När samma membran sveptes runt små kiseldioxidkulor följde de uppmätta orienteringarna sfärens krökning: molekyler nära botten pekade mer mot mikroskopet, medan de vid sidorna blev mer parallella med ytan. Dessa tester visade att 4polar3D noggrant kan återvinna ett brett spektrum av tilt-vinklar och skilja mellan in-plan och off-plan-orienteringar.
Avslöjande av 3D-aktinarkitektur i cell-liknande miljöer
Forskarna vände sig sedan till de täta aktinnätverk som driver cellrörelse och adhesion. I snabbt rörliga melanomceller är det tunna skiktet i cellens främre del, kallat lamellipodium, packat med aktinfilament. Med en fluorescerande markör som binder längs dessa filament registrerade 4polar3D miljontals enkelmolekylhändelser och rekonstruerade en detaljerad karta över filamentens riktningar. Nära själva kanten visade aktinnätverket en blandning av in-plan grenade filament med ett karakteristiskt par av föredragna riktningar, och en andra population filament som var tilta ut ur planet med mer varierade orienteringar. Längre bak, i övergångsregionen och i tjocka stressfibrer, blev filamenten mestadels in-plan och riktade längs tydliga axlar.
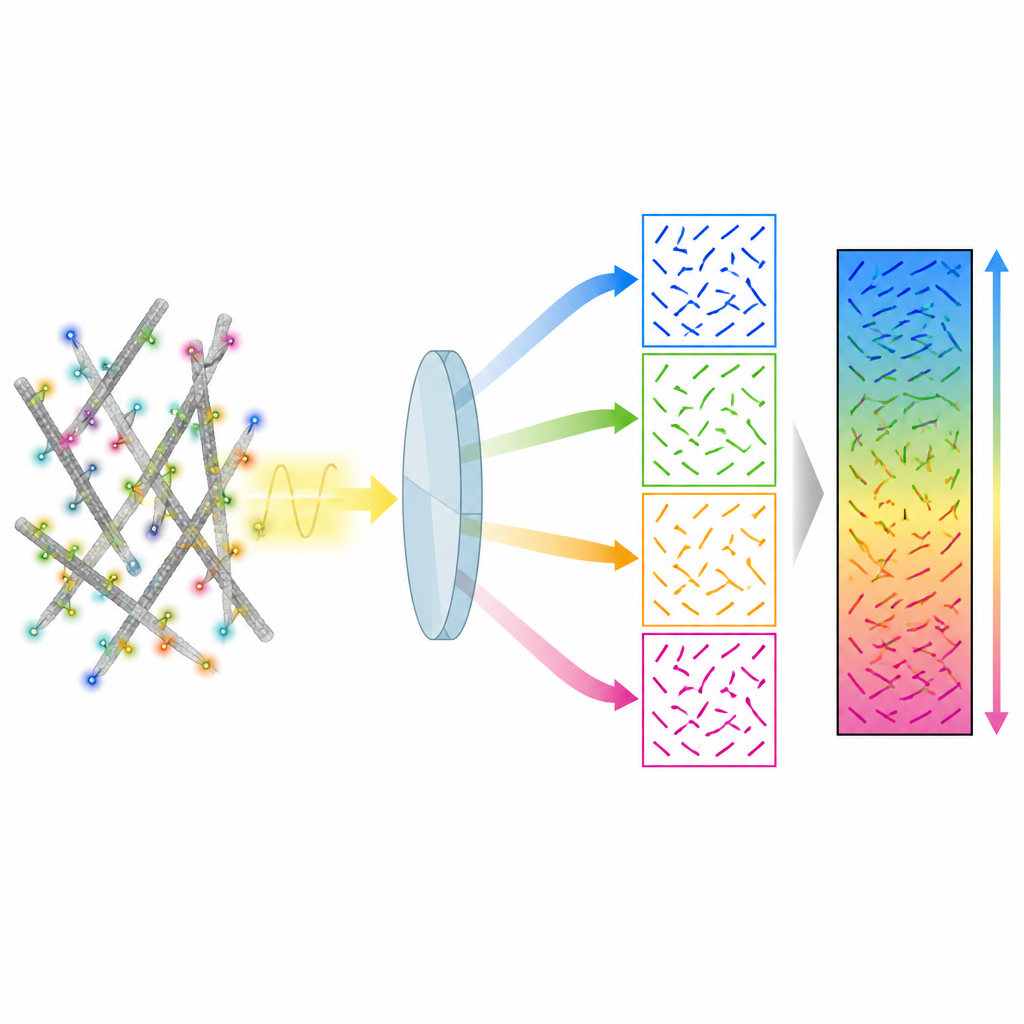
Avslöja 3D-struktur i små adhesionsorganeller
Metoden undersökte också podosomer, små adhesionsstrukturer i immunceller som är mindre än diffraktionsgränsen för ljus. Genom att sammanfatta data från hundratals podosomer fann författarna ett tydligt mönster: i centrum var många aktinfilament tilta ut ur planet och sträckte sig sannolikt uppåt, medan runt kanterna bildade in-plan filament en radiell ring som pekade utåt från varje kärna. Mellan närliggande podosomer gick detta ordnade radiella mönster till stor del förlorat. Mätningar av den uppenbara fokalhöjden hos de fluorescerande fläckarna antydde att off-plan-filamenten i kärnan sitter högre ovanför glasyta än den omgivande in-plan-ringen, vilket stöder bilden av ett lager-på-lager, tredimensionellt aktinskelett.
Vad detta betyder för cellbiologin
Sammanfattningsvis erbjuder 4polar3D ett praktiskt sätt att kartlägga hur molekyler pekar i tre dimensioner över stora områden av en cell, med en relativt enkel optisk uppsättning och snabba beräkningar. Även om metoden är mindre exakt vid extrema tilt-vinklar än vissa mer invecklade tekniker, fungerar den väl för de flesta orienteringar och kan, vilket är avgörande, hantera täta, biologiskt relevanta prover. Genom att avslöja hur aktinfilament väver in och ut ur cellplanet i lamellipodia och podosomer öppnar detta tillvägagångssätt dörren för rutinmässiga studier som kopplar nanoskalig fiberorganisation till cellrörelse, kraftgenerering och signalering.
Citering: Senthil Kumar, C.S., Valades Cruz, C.A., Sison, M. et al. 4polar3D single molecule imaging of 3D orientation in dense actin networks using ratiometric polarization splitting. Nat Commun 17, 4246 (2026). https://doi.org/10.1038/s41467-026-70852-y
Nyckelord: enkelmolekylavbildning, aktin cytoskelett, polarisationsmikroskopi, superupplösning, cellmekanik