Clear Sky Science · pt
Mapas de acessibilidade da cromatina definem identidades de células estromais entre tecidos
Por que o código oculto de nossos tecidos importa
Cada órgão do corpo sabe o que fazer porque suas células leem o genoma de formas ligeiramente diferentes. Este estudo faz uma pergunta simples, porém poderosa: podemos identificar que tipo de célula estamos observando — e de qual órgão ela veio — apenas vendo quais partes de seu DNA estão abertas e prontas para serem lidas? Os autores constroem um mapa detalhado dessa paisagem de “DNA aberto” em diversos órgãos de camundongo e mostram que ela registra silenciosamente tanto a identidade celular quanto o tecido de origem, com usos potenciais em diagnóstico, rastreamento de câncer e medicina regenerativa.
Espiando o DNA aberto pelo corpo
Para explorar esse código oculto, os pesquisadores usaram uma técnica chamada single-cell ATAC-seq, que marca os trechos de DNA fisicamente acessíveis dentro de cada núcleo. Trabalhando com amostras congeladas de nove órgãos de camundongo — incluindo cérebro, coração, pulmão, fígado, rim, intestino, pâncreas, cólon e baço — eles isolaram os núcleos e perfilizaram mais de 51.000 células individuais. Ajustes cuidadosos foram necessários para cada tecido, de modo que núcleos frágeis de órgãos moles como pulmão e cérebro, bem como tecidos densos como o coração, pudessem ser capturados com alta qualidade. Após o sequenciamento, ferramentas computacionais avançadas agruparam as células pela semelhança de suas regiões de DNA acessível e então projetaram esses grupos em “mapas” bidimensionais onde células relacionadas se agrupam. 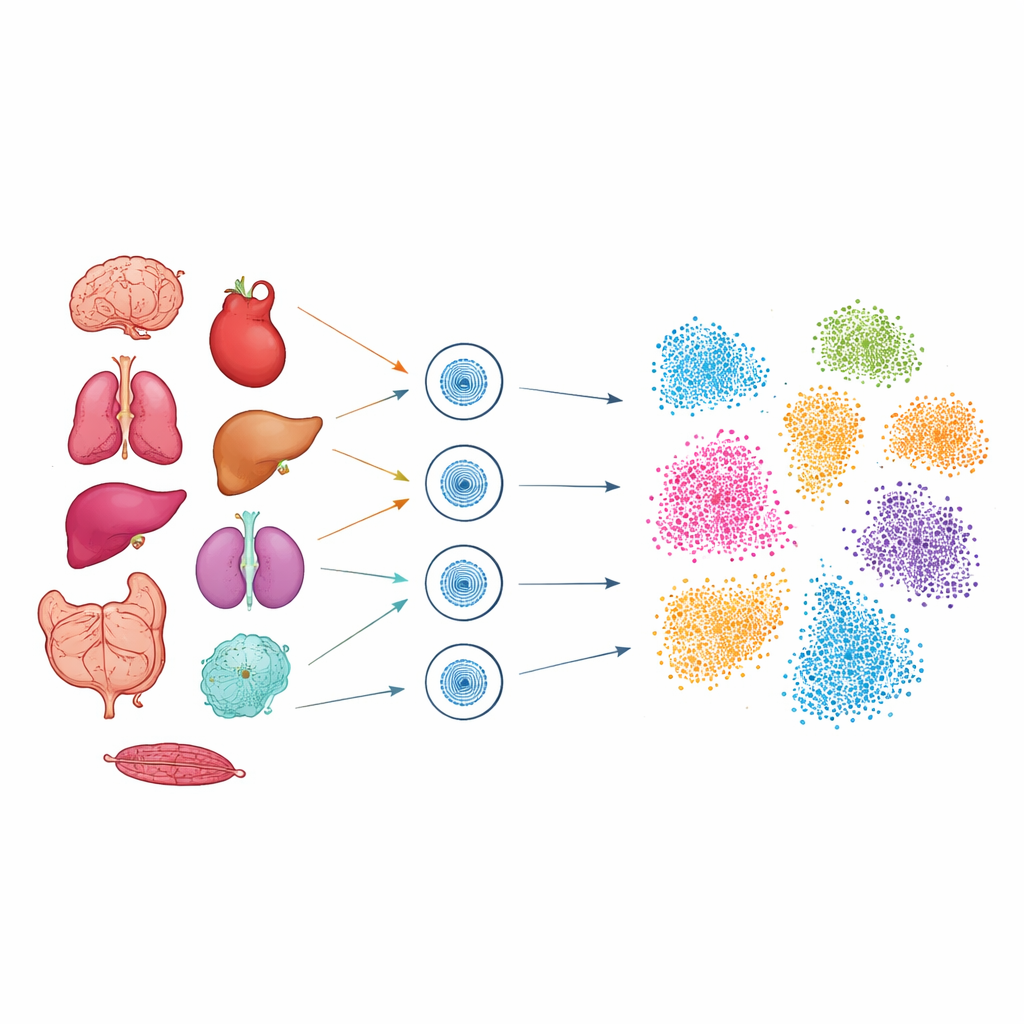
Reconhecendo tipos celulares a partir do DNA aberto
Nesses mapas, a equipe identificou 28 tipos celulares principais distribuídos pelos nove órgãos, como neurônios, cardiomiócitos, células imunes e várias células do intestino e do fígado. Mesmo sem medir o RNA diretamente, cada tipo celular exibiu um padrão característico de picos de DNA aberto em torno de genes conhecidos por serem importantes para sua função. Por exemplo, células T mostraram sítios abertos próximos a genes envolvidos na sinalização imune; neurônios, próximos a genes necessários para sinapses e atividade cerebral; e células do músculo cardíaco, próximos a genes ligados à contração e ao manejo de cálcio. Ao comparar seus resultados com grandes atlas públicos de referência, os autores confirmaram que os tipos celulares recuperados correspondiam bem a populações já descritas, mas agora com uma camada adicional de detalhe regulatório: onde no genoma estão os interruptores de controle dessas células.
Impressões digitais teciduais escritas na cromatina
Além dos tipos celulares distintos, o estudo revelou uma camada extra de organização: células do mesmo órgão tendiam a compartilhar padrões mais amplos de acessibilidade, mesmo quando pertenciam a tipos diferentes. Isso foi especialmente marcante nas células “estromais” — células de suporte como endoteliais, fibroblastos e macrófagos que existem em muitos órgãos. Embora um endotélio do coração e um do fígado compartilhem uma identidade central, suas regiões de DNA abertas divergem de maneiras que refletem o ambiente local e suas funções. No fígado, regiões acessíveis próximas a genes envolvidos em desintoxicação e metabolismo se destacaram; no endotélio pulmonar, regiões abertas apareceram próximas a genes ligados à troca gasosa e ao surfactante; no rim, a acessibilidade ressaltou genes importantes para filtração e equilíbrio iônico. Comparações estatísticas confirmaram que a similaridade geral nos padrões de cromatina era maior dentro de um mesmo órgão do que entre órgãos diferentes.
Detalhando as redes de controle
As regiões de DNA abertas não são aleatórias — servem como pontos de ancoragem para fatores de transcrição, as proteínas que ligam ou desligam genes. Ao buscar motivos de sequência recorrentes dentro das regiões acessíveis, os autores puderam inferir quais famílias de fatores de transcrição são mais ativas em diferentes contextos. Células pulmonares mostraram fortes assinaturas de fatores Nkx que ajudam a definir a identidade das vias aéreas; neurônios foram enriquecidos para fatores Rfx envolvidos no desenvolvimento cerebral; e células imunes carregaram motivos para reguladores como Runx1. Análises de footprinting, que observam como essas proteínas protegem o DNA da enzima do ATAC-seq, reforçaram que esses motivos correspondem a eventos reais de ligação. Em conjunto, os padrões de cromatina aberta e de atividade de fatores de transcrição delineiam programas regulatórios específicos de tipo celular que ajudam a consolidar o papel de cada célula.
Rastreando células estromais até seu órgão de origem
Para testar se padrões de cromatina sozinhos poderiam funcionar como um “endereço de retorno” para células estromais compartilhadas, os pesquisadores agruparam células únicas semelhantes em unidades compactas chamadas metacélulas. Entre macrófagos e fibroblastos encontrados em múltiplos órgãos, eles descobriram módulos de DNA acessível que se alinhavam de perto ao tecido de origem: macrófagos do baço diferiam de macrófagos do fígado, e fibroblastos do coração diferenciavam-se de fibroblastos do pulmão, mesmo que todos pertencessem à mesma classe celular ampla. Células endoteliais mostraram o mesmo princípio. Combinando uma região marcador endotelial geral com uma região acessível específica do fígado, a equipe pôde selecionar de forma limpa células endoteliais sinusoidais do fígado a partir do conjunto. 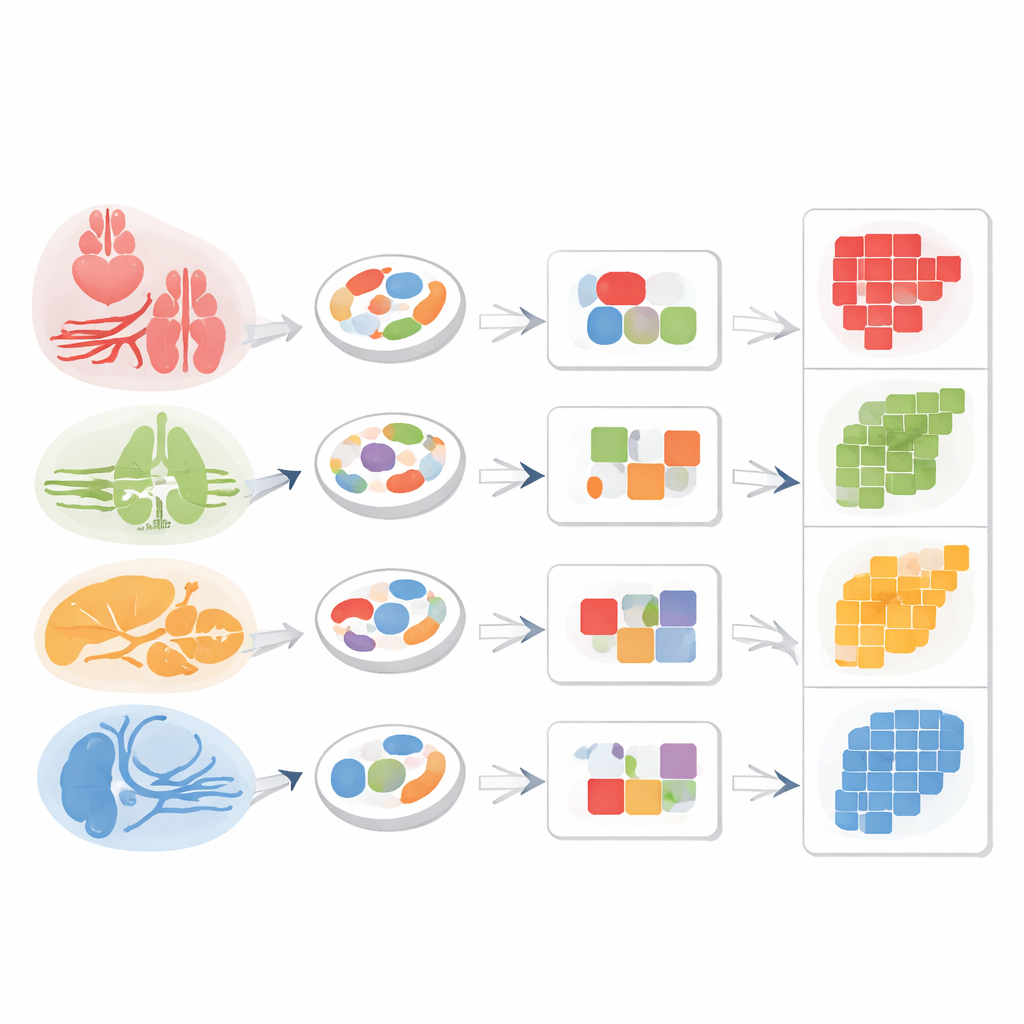
O que este atlas significa para a saúde e a doença
Em termos práticos, este trabalho mostra que as células não carregam apenas um rótulo genérico como “vaso sanguíneo” ou “célula de suporte”. Seu DNA é embalado de maneiras que lembram qual órgão elas servem e quais tarefas desempenham ali. Como estados de cromatina podem persistir quando células se movem ou se transformam — por exemplo, durante a disseminação do câncer — tais mapas poderiam, no futuro, ajudar a rastrear onde um tumor teve início ou distinguir estados celulares nocivos de saudáveis. O atlas fornecido pelos autores é uma referência para tecidos normais de camundongo, oferecendo uma linha de base com a qual células doentes ou experimentalmente manipuladas podem ser comparadas, e destacando como um genoma compartilhado é esculpido em órgãos diversos por meio da abertura e fechamento do DNA regulatório.
Citação: Nooranikhojasteh, A., Tavallaee, G., Khuu, N. et al. Chromatin accessibility landscapes define stromal cell identities across tissues. Commun Biol 9, 480 (2026). https://doi.org/10.1038/s42003-026-09720-w
Palavras-chave: acessibilidade da cromatina, células estromais, epigenômica de célula única, identidade tecidual, regulação gênica