Clear Sky Science · it
I paesaggi di accessibilità della cromatina definiscono le identità delle cellule stromali nei tessuti
Perché il codice nascosto dei nostri tessuti importa
Ogni organo del corpo sa cosa fare perché le sue cellule leggono il genoma in modi leggermente diversi. Questo studio pone una domanda semplice ma potente: possiamo capire che tipo di cellula stiamo osservando—e da quale organo proviene—solo osservando quali parti del suo DNA sono aperte e pronte per essere lette? Gli autori costruiscono una mappa dettagliata di questo paesaggio di “DNA aperto” attraverso molti organi del topo e mostrano che esso registra silenziosamente sia l’identità cellulare sia il tessuto di origine, con potenziali applicazioni in diagnosi, tracciamento del cancro e medicina rigenerativa.
Uno sguardo al DNA accessibile in tutto il corpo
Per esplorare questo codice nascosto, i ricercatori hanno usato una tecnica chiamata ATAC-seq a singola cellula, che segnala gli spezzoni di DNA fisicamente accessibili all’interno di ciascun nucleo. Lavorando con campioni congelati provenienti da nove organi del topo, tra cui cervello, cuore, polmone, fegato, rene, intestino, pancreas, colon e milza, hanno isolato i nuclei e profilato oltre 51.000 singole cellule. È stata necessaria una messa a punto accurata per ogni tessuto, in modo che i nuclei fragili di organi morbidi come polmone e cervello, così come i tessuti densi come il cuore, potessero tutti essere catturati con alta qualità. Dopo il sequenziamento, strumenti computazionali avanzati hanno raggruppato le cellule in base alla somiglianza delle regioni di DNA accessibile, quindi hanno proiettato questi gruppi in “mappe” bidimensionali dove le cellule correlate si raggruppano insieme. 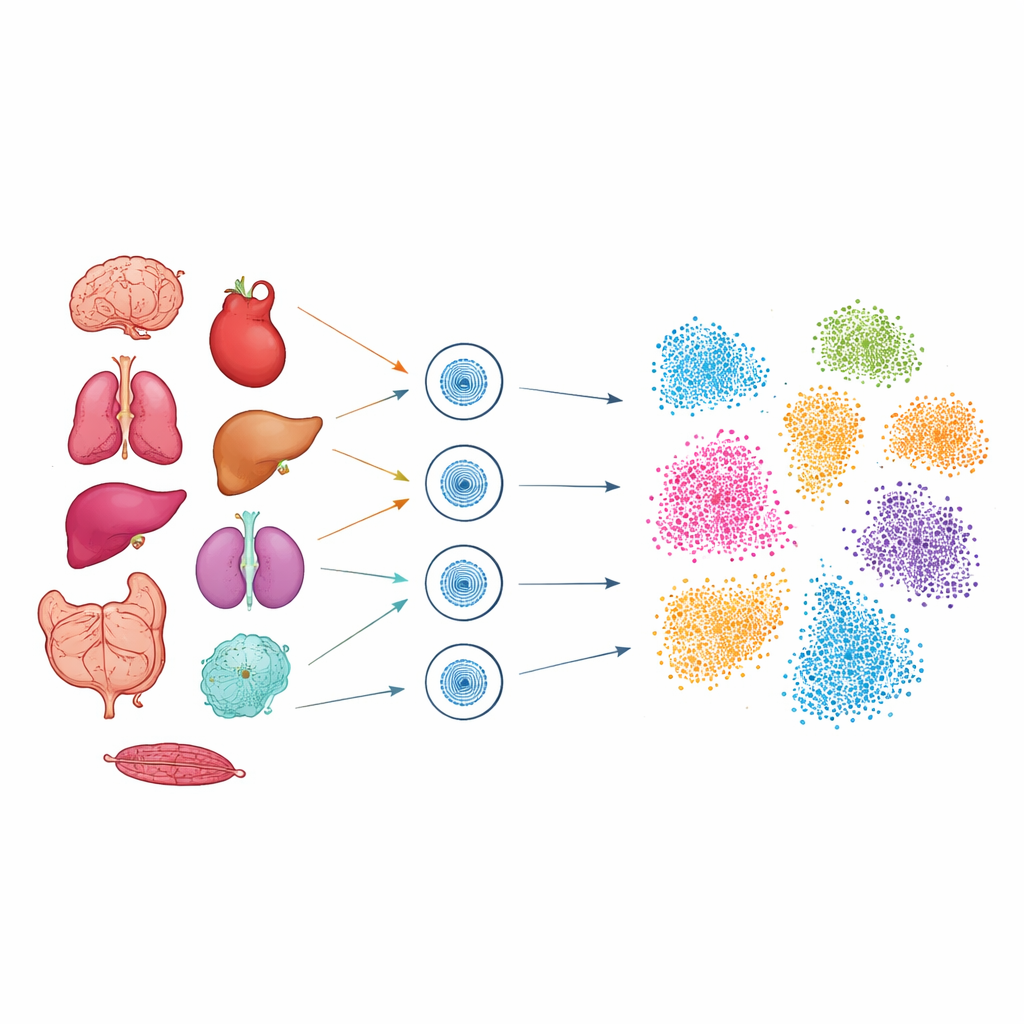
Riconoscere i tipi cellulari dal loro DNA accessibile
Dalle queste mappe, il gruppo ha identificato 28 tipi cellulari principali distribuiti nei nove organi, come neuroni, cardiomiociti, cellule immunitarie e varie cellule intestinali e epatiche. Anche senza misurare direttamente l’RNA, ogni tipo cellulare presentava un pattern caratteristico di picchi di DNA aperto attorno a geni noti per essere importanti per la sua funzione. Per esempio, le cellule T mostravano siti aperti vicino a geni coinvolti nella segnalazione immunitaria, i neuroni vicino a geni necessari per le sinapsi e l’attività cerebrale, e le cellule del muscolo cardiaco vicino a geni legati alla contrazione e alla gestione del calcio. Confrontando i loro risultati con grandi atlanti di riferimento pubblici, gli autori hanno confermato che i tipi cellulari recuperati corrispondono bene a popolazioni già descritte, ma ora con uno strato aggiuntivo di dettaglio regolatorio: dove nel genoma si trovano gli interruttori di controllo per quelle cellule.
Impronte tissutali scritte nella cromatina
Oltre ai tipi cellulari distinti, lo studio ha rivelato un ulteriore livello di organizzazione: le cellule dello stesso organo tendevano a condividere schemi più ampi di accessibilità, anche quando appartenevano a tipi diversi. Questo è stato particolarmente evidente nelle cellule “stromali”—cellule di supporto come cellule endoteliali, fibroblasti e macrofagi che esistono in molti organi. Sebbene un’endoteliale del cuore e una del fegato condividano un’identità di base, le loro regioni di DNA aperto divergono in modi che riflettono il loro ambiente locale e i compiti svolti. Nel fegato, regioni accessibili vicino a geni coinvolti nella detossificazione e nel metabolismo erano prominenti; nell’endotelio polmonare, le regioni aperte erano vicine a geni legati allo scambio gassoso e al surfattante; nel rene, l’accessibilità evidenziava geni importanti per la filtrazione e l’equilibrio ionico. Confronti statistici hanno confermato che la somiglianza complessiva nei modelli di cromatina era maggiore all’interno degli organi che tra organi diversi.
Ingrandire le reti di controllo
Le regioni di DNA aperto non sono casuali—servono come siti di aggancio per i fattori di trascrizione, le proteine che attivano o spengono i geni. Cercando motivi di sequenza ricorrenti all’interno delle regioni accessibili, gli autori hanno potuto inferire quali famiglie di fattori di trascrizione sono più attive in diversi contesti. Le cellule polmonari mostravano forti firme dei fattori Nkx che aiutano a definire l’identità delle vie aeree, i neuroni erano arricchiti per fattori Rfx coinvolti nello sviluppo cerebrale, e le cellule immunitarie portavano motivi per regolatori come Runx1. Analisi di footprinting, che osservano come queste proteine proteggono il DNA dall’enzima ATAC-seq, hanno rafforzato che questi motivi corrispondono a eventi di legame reali. Insieme, i pattern di cromatina aperta e l’attività dei fattori di trascrizione delineano programmi regolatori specifici per tipo cellulare che contribuiscono a consolidare il ruolo di ciascuna cellula.
Ricollegare le cellule stromali al loro organo di origine
Per verificare se i pattern di cromatina da soli potessero operare come un “indirizzo di ritorno” per cellule stromali condivise, i ricercatori hanno raggruppato singole cellule simili in unità compatte chiamate metacellule. Tra i macrofagi e i fibroblasti presenti in più organi, hanno scoperto moduli di DNA accessibile che si allineavano strettamente con il tessuto di origine: i macrofagi della milza differivano dai macrofagi del fegato, e i fibroblasti del cuore da quelli del polmone, nonostante appartenessero tutti alla stessa classe cellulare ampia. Le cellule endoteliali hanno mostrato lo stesso principio. Combinando una regione marker endoteliale generale con una regione accessibile specifica del fegato, il gruppo è riuscito a isolare con precisione le cellule endoteliali sinusoidali del fegato dal miscuglio. 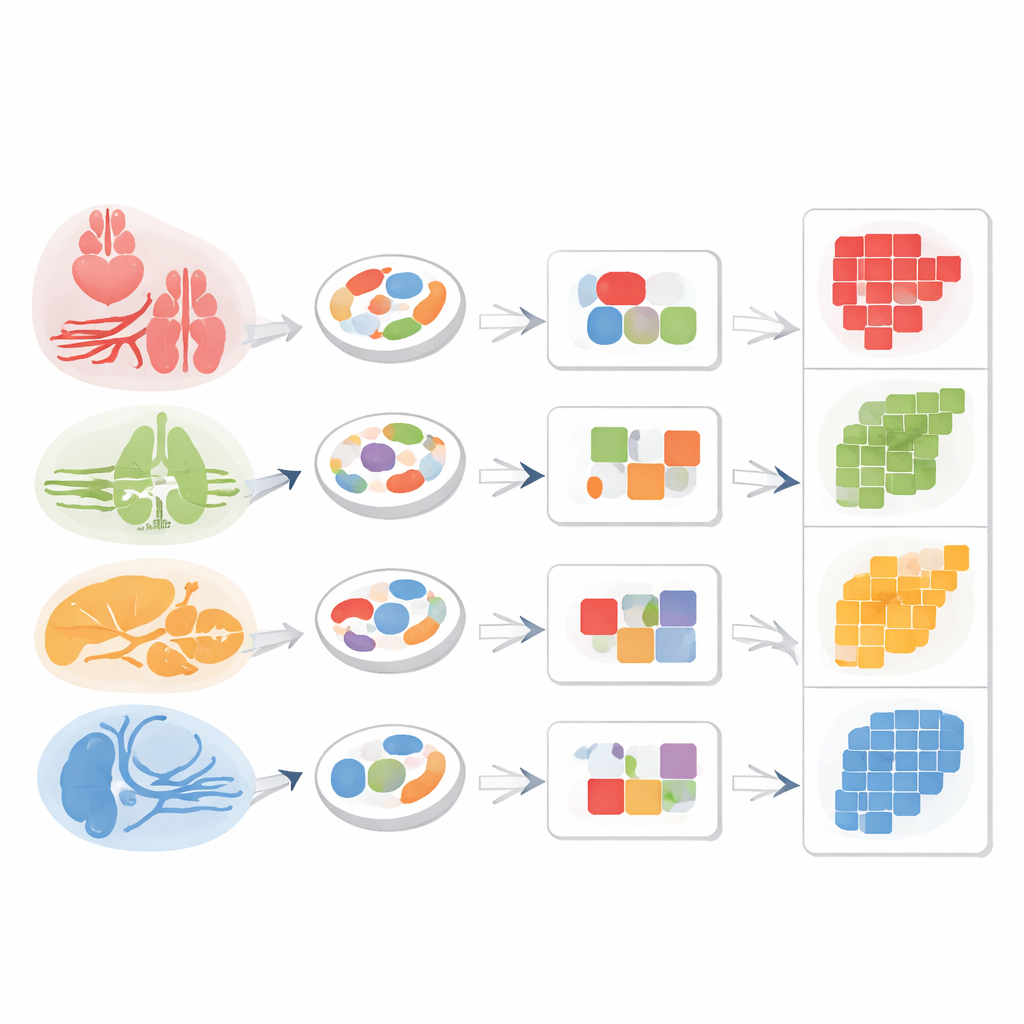
Cosa significa questo atlante per salute e malattia
In termini pratici, questo lavoro mostra che le cellule non portano semplicemente un’etichetta generica come “vasi sanguigni” o “cellula di supporto.” Il loro DNA è impacchettato in modi che ricordano quale organo servono e quali compiti svolgono lì. Poiché gli stati della cromatina possono persistere quando le cellule si spostano o si trasformano—per esempio durante la diffusione del cancro—tali mappe potrebbero infine aiutare a ricostruire dove è iniziato un tumore o a distinguere stati cellulari dannosi da quelli sani. L’atlas fornito dagli autori è un riferimento per i tessuti normali del topo, offrendo una baseline rispetto alla quale confrontare cellule malate o manipolate sperimentalmente e mettendo in evidenza come un genoma condiviso venga scolpito in organi diversi attraverso l’apertura e la chiusura del DNA regolatorio.
Citazione: Nooranikhojasteh, A., Tavallaee, G., Khuu, N. et al. Chromatin accessibility landscapes define stromal cell identities across tissues. Commun Biol 9, 480 (2026). https://doi.org/10.1038/s42003-026-09720-w
Parole chiave: accessibilità della cromatina, cellule stromali, epigenomica a singola cellula, identità tissutale, regolazione genica