Clear Sky Science · pl
Mapy dostępności chromatyny definiują tożsamości komórek stromalnych w różnych tkankach
Dlaczego ukryty kod naszych tkanek ma znaczenie
Każdy narząd w ciele wie, co ma robić, ponieważ jego komórki odczytują genom w nieco inny sposób. W tym badaniu zadano proste, lecz silne pytanie: czy potrafimy rozpoznać typ komórki — i z jakiego narządu pochodzi — tylko na podstawie tego, które fragmenty jej DNA są otwarte i gotowe do odczytu? Autorzy zbudowali szczegółową mapę tego „otwartego DNA” w wielu narządach myszy i pokazali, że cicho zapisuje ona zarówno tożsamość komórki, jak i organ pochodzenia, co ma potencjalne zastosowania w diagnostyce, śledzeniu raka i medycynie regeneracyjnej.
Zaglądanie w otwarte DNA w całym organizmie
Aby zbadać ten ukryty kod, badacze użyli techniki zwanej single-cell ATAC-seq, która oznacza odcinki DNA fizycznie dostępne w każdym jądrze. Pracując z zamrożonymi próbkami z dziewięciu narządów myszy — w tym mózgu, serca, płuc, wątroby, nerek, jelita, trzustki, okrężnicy i śledziony — wyizolowali jądra i przeanalizowali ponad 51 000 pojedynczych komórek. Każda tkanka wymagała starannego dostrojenia procedury, aby uchwycić kruche jądra z miękkich organów, takich jak płuca i mózg, a także gęstsze tkanki, jak serce, przy zachowaniu wysokiej jakości. Po sekwencjonowaniu zaawansowane narzędzia obliczeniowe pogrupowały komórki według podobieństwa regionów dostępnej chromatyny, a następnie odwzorowały te grupy na dwuwymiarowe „mapy”, gdzie powiązane komórki grupują się razem. 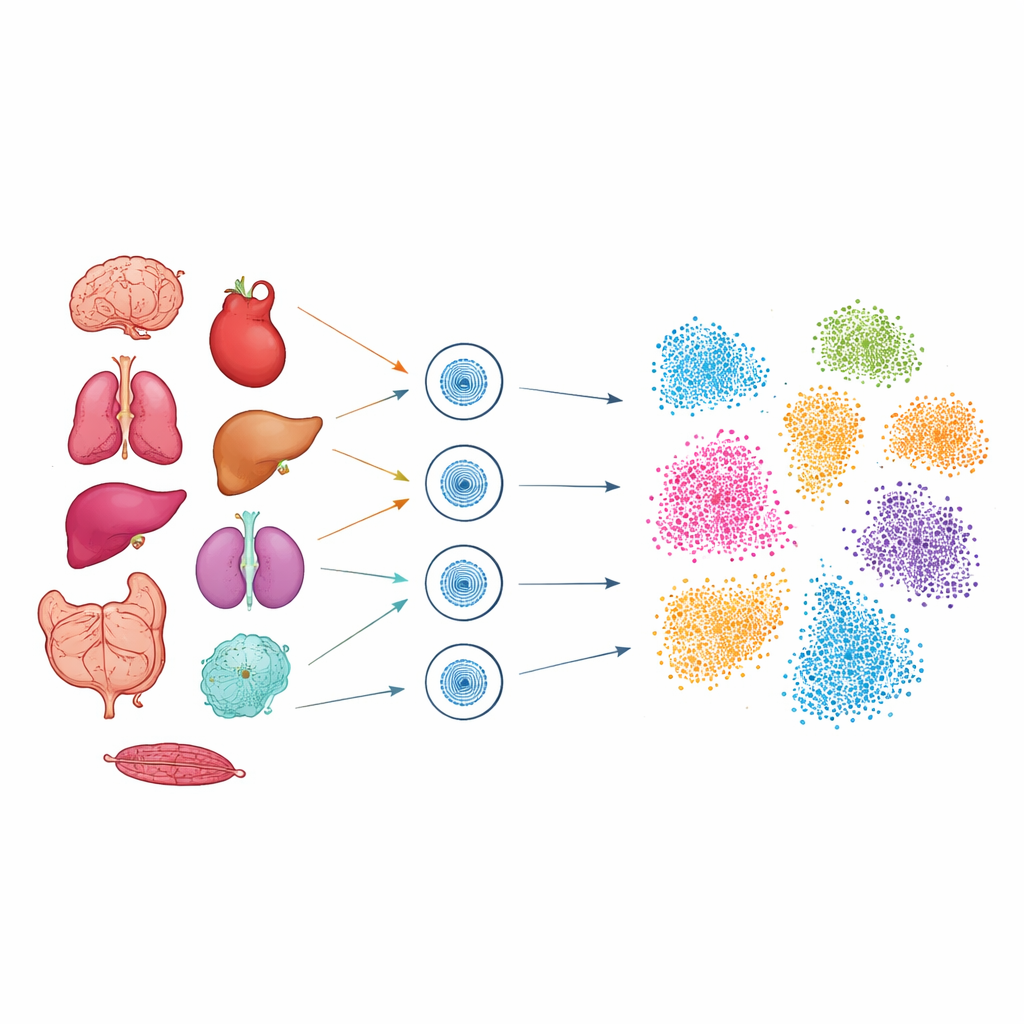
Rozpoznawanie typów komórek po ich otwartym DNA
Z tych map zespół zidentyfikował 28 głównych typów komórek rozmieszczonych w dziewięciu narządach, takich jak neurony, kardiomiocyty, komórki układu odpornościowego oraz różne komórki jelitowe i wątrobowe. Nawet bez bezpośredniego pomiaru RNA każdy typ komórki niósł charakterystyczny wzór otwartych pików chromatyny wokół genów znanych z istotnej roli w jego funkcji. Na przykład limfocyty T miały otwarte miejsca w pobliżu genów związanych z sygnalizacją odpornościową, neurony — przy genach niezbędnych dla synaps i aktywności mózgu, a kardiomiocyty — przy genach związanych ze skurczem i gospodarką wapniową. Porównanie wyników z dużymi publicznymi atlasami referencyjnymi potwierdziło, że wykryte typy komórek dobrze odpowiadają wcześniej opisanym populacjom, ale teraz z dodatkową warstwą informacji regulacyjnej: wskazaniem, gdzie w genomie znajdują się przełączniki kontrolujące te komórki.
Odciski palców tkanek zapisane w chromatynie
Ponad odrębnymi typami komórek, badanie ujawniło dodatkową warstwę organizacji: komórki z tego samego narządu miały tendencję do dzielenia szerszych wzorców dostępności, nawet gdy należały do różnych typów. Było to szczególnie widoczne w komórkach „stromalnych” — komórkach wspierających, takich jak komórki śródbłonka, fibroblasty i makrofagi, obecnych w wielu narządach. Chociaż komórka śródbłonka serca i śródbłonek wątroby dzielą podstawową tożsamość, ich otwarte regiony DNA różnicowały się w sposób odzwierciedlający lokalne środowisko i zadania. W wątrobie wyraźne były regiony otwarte przy genach związanych z detoksyfikacją i metabolizmem; w śródbłonku płuc — przy genach związanych z wymianą gazową i surfaktantem; w nerkach — przy genach ważnych dla filtracji i równowagi jonowej. Analizy statystyczne potwierdziły, że ogólne podobieństwo wzorców chromatyny było wyższe w obrębie jednego narządu niż między różnymi narządami.
Zbliżenie na sieci kontrolne
Regiony otwartego DNA nie są przypadkowe — służą jako miejsca dokowania dla czynników transkrypcyjnych, białek włączających lub wyłączających geny. Przez wyszukiwanie powtarzających się motywów sekwencji w dostępnych regionach autorzy mogli wnioskować, które rodziny czynników transkrypcyjnych są najbardziej aktywne w różnych kontekstach. Komórki płuc wykazały silne sygnatury czynników Nkx, które pomagają definiować tożsamość dróg oddechowych; neurony były wzbogacone w motywy Rfx związane z rozwojem mózgu; komórki odpornościowe nosiły motywy regulatorów takich jak Runx1. Analizy footprintingu, które badają, jak te białka chronią DNA przed enzymem ATAC-seq, wzmocniły przekonanie, że te motywy odpowiadają rzeczywistym zdarzeniom wiązania. Razem wzorce otwartej chromatyny i aktywności czynników transkrypcyjnych wyznaczają specyficzne dla typów komórek programy regulacyjne, które pomagają utrwalić rolę każdej komórki.
Śledzenie komórek stromalnych z powrotem do ich narządu macierzystego
Aby sprawdzić, czy same wzorce chromatyny mogą działać jako „adres zwrotny” dla wspólnych komórek stromalnych, badacze pogrupowali podobne pojedyncze komórki w zwarte jednostki zwane metakomórkami (metacells). Wśród makrofagów i fibroblastów występujących w wielu narządach odkryli moduły dostępnego DNA, które ściśle korelowały z tkanką pochodzenia: makrofagi śledziony różniły się od makrofagów wątroby, a fibroblasty serca od fibroblastów płuc, mimo że wszystkie należały do tej samej szerokiej klasy komórek. To samo zaobserwowano dla komórek śródbłonka. Łącząc ogólny region markera śródbłonka z regionem specyficznym dla wątroby, zespół był w stanie wyraźnie wyodrębnić wątrobowe komórki śródbłonka zatokowego z mieszaniny. 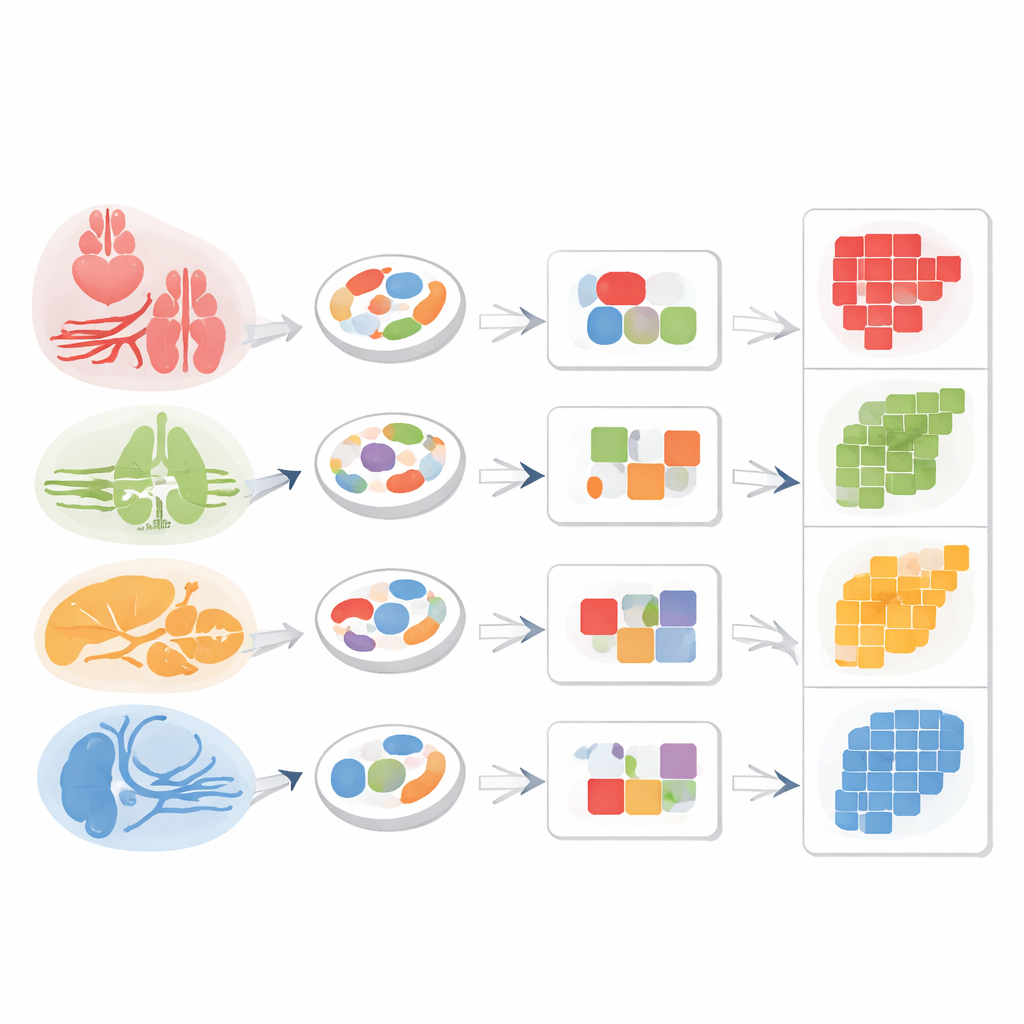
Co ten atlas oznacza dla zdrowia i chorób
Mówiąc prościej, praca ta pokazuje, że komórki nie noszą tylko ogólnej etykiety typu „naczynie krwionośne” czy „komórka wspierająca”. Ich DNA jest zapakowane w sposoby, które pamiętają, któremu organowi służą i jakie zadania tam wykonują. Ponieważ stany chromatyny mogą utrzymywać się, gdy komórki przemieszczają się lub przekształcają — na przykład podczas rozsiewu nowotworu — takie mapy mogą w przyszłości pomóc śledzić, skąd pochodzi guz lub odróżnić stany komórek szkodliwe od zdrowych. Atlas udostępniony przez autorów stanowi odniesienie dla prawidłowych tkanek myszy, oferując punkt odniesienia, wobec którego można porównywać komórki chore lub eksperymentalnie zmodyfikowane, i ukazując, jak wspólny genom jest rzeźbiony w różnorodne narządy przez otwieranie i zamykanie DNA regulacyjnego.
Cytowanie: Nooranikhojasteh, A., Tavallaee, G., Khuu, N. et al. Chromatin accessibility landscapes define stromal cell identities across tissues. Commun Biol 9, 480 (2026). https://doi.org/10.1038/s42003-026-09720-w
Słowa kluczowe: dostępność chromatyny, komórki stromalne, epigenomika pojedynczych komórek, tożsamość tkanki, regulacja genów