Clear Sky Science · nl
Chromatine-toegankelijkheidslandschappen definiëren stromale celidentiteiten doorweven weefsels
Waarom de verborgen code van onze weefsels ertoe doet
Elk orgaan in het lichaam weet wat het moet doen omdat zijn cellen het genoom op licht verschillende manieren aflezen. Deze studie stelt een eenvoudige maar krachtige vraag: kunnen we aan de hand van welke delen van het DNA open en leesbaar zijn bepalen wat voor soort cel we bekijken — en uit welk orgaan deze afkomstig is? De auteurs bouwen een gedetailleerde kaart van dit "open DNA"-landschap over vele muizenorganen en laten zien dat het stilletjes zowel celidentiteit als weefselherkomst vastlegt, met mogelijke toepassingen in diagnostiek, het opsporen van kanker en regeneratieve geneeskunde.
Gluurtocht in open DNA door het hele lichaam
Om deze verborgen code te onderzoeken, gebruikten de onderzoekers een techniek genaamd single-cell ATAC-seq, die de DNA-segmenten markeert die fysiek toegankelijk zijn in elke kern. Met bevroren monsters van negen muizenorganen — waaronder hersenen, hart, long, lever, nier, darm, alvleesklier, dikke darm en milt — isoleerden ze de kernen en profielen ze meer dan 51.000 individuele cellen. Zorgvuldige optimalisatie was nodig voor elk weefsel, zodat fragiele kernen uit zachte organen zoals long en hersenen, evenals dichte weefsels zoals het hart, allemaal met hoge kwaliteit konden worden vastgelegd. Na sequencing groepeerden geavanceerde computationele tools cellen op basis van hoe vergelijkbaar hun toegankelijke DNA-regio’s waren, en projecteerden die groepen vervolgens in tweedimensionale "kaarten" waar verwante cellen samenclusteren. 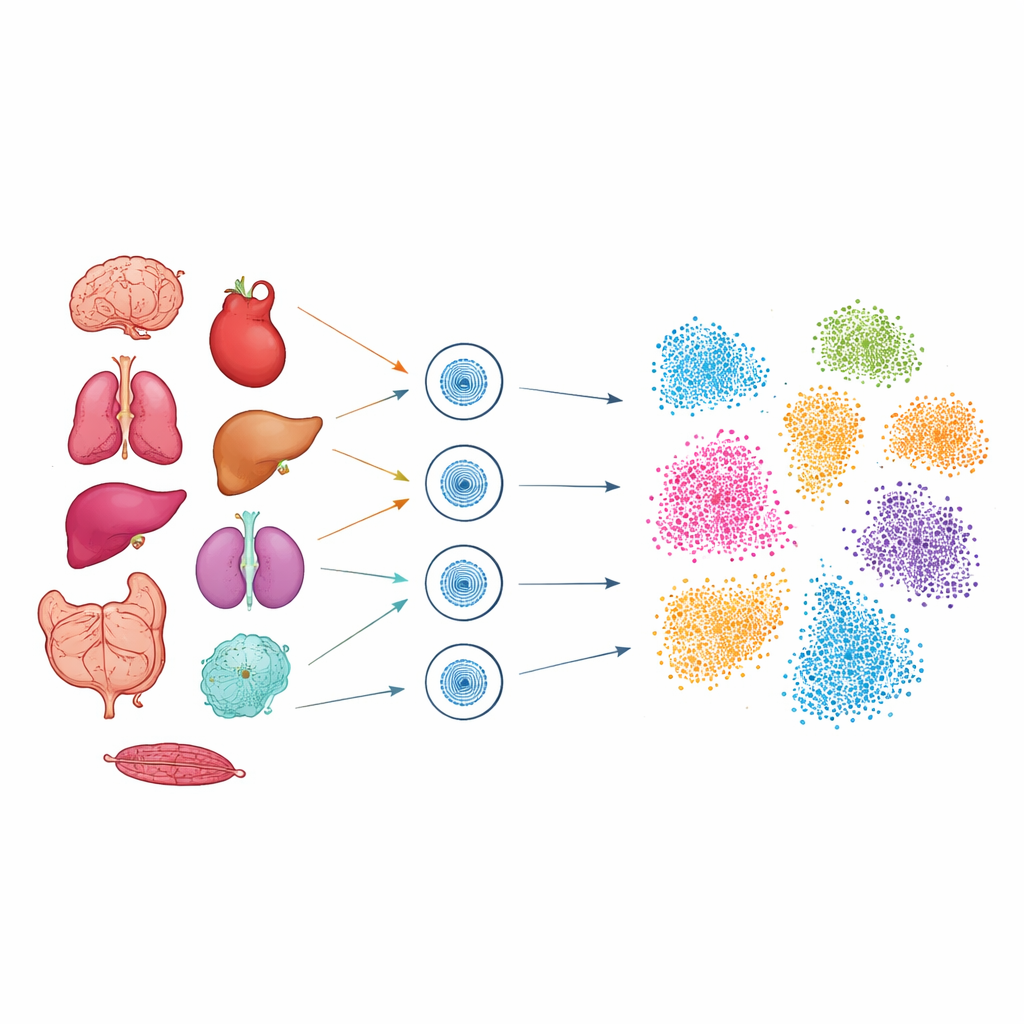
Celltypen herkennen aan hun open DNA
Uit deze kaarten identificeerde het team 28 grote celtypen verspreid over de negen organen, zoals neuronen, cardiomyocyten, immuuncellen en verschillende darms- en levercellen. Zelfs zonder direct RNA te meten, droeg elk celtype een karakteristiek patroon van open DNA-pieken rond genen die belangrijk zijn voor zijn functie. Zo toonden T-cellen open sites nabij genen betrokken bij immuuncommunicatie, neuronen nabij genen die nodig zijn voor synapsen en hersenactiviteit, en hartspiercellen nabij genen gekoppeld aan contractie en calciumhuishouding. Door hun resultaten te vergelijken met grote publieke referentieatlassen bevestigden de auteurs dat de teruggevonden celtypen goed overeenkwamen met eerder beschreven populaties, maar nu met een extra laag regulatoir detail: waar in het genoom de schakelaars voor die cellen liggen.
Weefselfingerafdrukken geschreven in chromatine
Voorbij de afzonderlijke celtypen onthulde de studie een extra organisatielaag: cellen uit hetzelfde orgaan deelden vaak bredere toegankelijkheidspatronen, zelfs wanneer ze tot verschillende typen behoorden. Dit was vooral opvallend bij "stromale" cellen — ondersteunende cellen zoals endotheelcellen, fibroblasten en macrofagen die in veel organen voorkomen. Hoewel een endotheelcel in het hart en een in de lever een kernidentiteit delen, wijken hun open DNA-regio’s af op manieren die hun lokale omgeving en taken weerspiegelen. In de lever waren toegankelijke regio’s nabij genen betrokken bij ontgifting en metabolisme prominent; in longendotheel lagen open regio’s nabij genen gekoppeld aan gasuitwisseling en surfactant; in de nier benadrukte toegankelijkheid genen belangrijk voor filtratie en ionenbalans. Statistische vergelijkingen bevestigden dat de algemene overeenkomst in chromatinepatronen binnen organen hoger was dan tussen organen.
Inzoomen op de regelnetwerken
De open DNA-regio’s zijn niet willekeurig — ze dienen als aanlegplaatsen voor transcriptiefactoren, de eiwitten die genen aan- of uitzetten. Door te zoeken naar terugkerende sequentiemotieven binnen toegankelijke regio’s konden de auteurs afleiden welke families transcriptiefactoren het meest actief zijn in verschillende contexten. Longcellen toonden sterke signaturen van Nkx-factoren die de luchtwegidentiteit helpen bepalen, neuronen waren verrijkt voor Rfx-factoren betrokken bij hersenontwikkeling, en immuuncellen droegen motieven voor regulatoren zoals Runx1. Footprinting-analyses, die bekijken hoe deze eiwitten het DNA beschermen tegen het ATAC-seq-enzym, versterkten dat deze motieven overeenkomen met daadwerkelijke bindingsgebeurtenissen. Samen schetsen de patronen van open chromatine en transcriptiefactoractiviteit celtype-specifieke regulatoire programma’s die helpen de rol van elke cel te verankeren.
Stromale cellen terugleiden naar hun thuisorgaan
Om te testen of chromatinepatronen op zichzelf als een "terugadres" voor gedeelde stromale cellen kunnen fungeren, groepeerden de onderzoekers vergelijkbare enkele cellen in compacte eenheden genaamd metacellen. Binnen macrofagen en fibroblasten die in meerdere organen werden gevonden, ontdekten ze modules van toegankelijk DNA die sterk overeenkwamen met het weefsel van herkomst: miltmacrofagen verschilden van levermacrofagen, en hartfibroblasten van longfibroblasten, ook al behoorden ze tot dezelfde brede celklasse. Endotheelcellen toonden hetzelfde principe. Door een algemeen endotheelmerkergebied te combineren met een lever-specifieke toegankelijke regio kon het team lever sinusoïdale endotheelcellen duidelijk uit de mix selecteren. 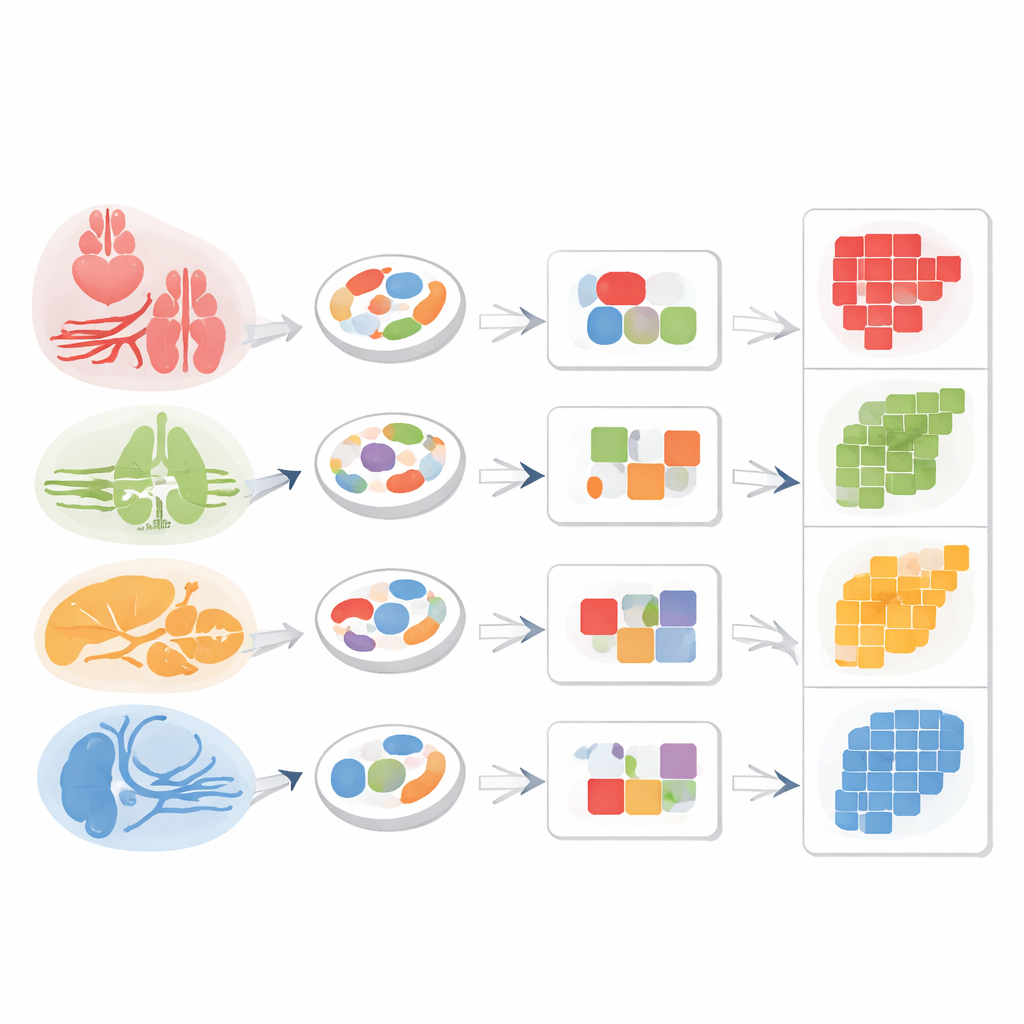
Wat deze atlas betekent voor gezondheid en ziekte
In gewone bewoordingen toont dit werk aan dat cellen niet slechts een generiek etiket dragen zoals "bloedvat" of "ondersteunende cel." Hun DNA is verpakt op wijzen die onthouden welk orgaan ze dienen en welke taken ze daar vervullen. Omdat chromatine-staten kunnen aanhouden terwijl cellen zich verplaatsen of transformeren — bijvoorbeeld tijdens het uitzaaien van kanker — zouden dergelijke kaarten uiteindelijk kunnen helpen te achterhalen waar een tumor is begonnen of schadelijke van gezonde celtoestanden te onderscheiden. De atlas die de auteurs bieden is een referentie voor normale muizenweefsels, en biedt een basislijn waarmee zieke of experimenteel gemanipuleerde cellen vergeleken kunnen worden, en toont hoe een gedeeld genoom wordt gevormd tot diverse organen door het openen en sluiten van regulatoir DNA.
Bronvermelding: Nooranikhojasteh, A., Tavallaee, G., Khuu, N. et al. Chromatin accessibility landscapes define stromal cell identities across tissues. Commun Biol 9, 480 (2026). https://doi.org/10.1038/s42003-026-09720-w
Trefwoorden: chromatine-toegankelijkheid, stromale cellen, eencellige epigenomica, weefselidentiteit, genregulatie