Clear Sky Science · pt
KIMMDY: um emulador de reações biomoleculares
Observando Moléculas Formarem e Quebrarem Ligações
A vida depende de inúmeros pequenas reações químicas dentro de nossas células, mas assistir a essas reações se desenrolando em detalhe é quase impossível. Experimentos mostram apenas médias borradas, e modelos computacionais têm dificuldade em acompanhar tanto o movimento de grandes moléculas biológicas quanto a formação e quebra de ligações químicas ao longo de tempos longos. Este artigo apresenta o KIMMDY, um novo tipo de simulador que não tenta rastrear cada detalhe quântico de uma reação, mas sim emular como as reações se desenrolariam em ambientes biológicos complexos. Ele abre uma janela sobre como tecidos envelhecem sob estresse, como o DNA é danificado pela luz e como vias reacionais concorrentes moldam a biologia.
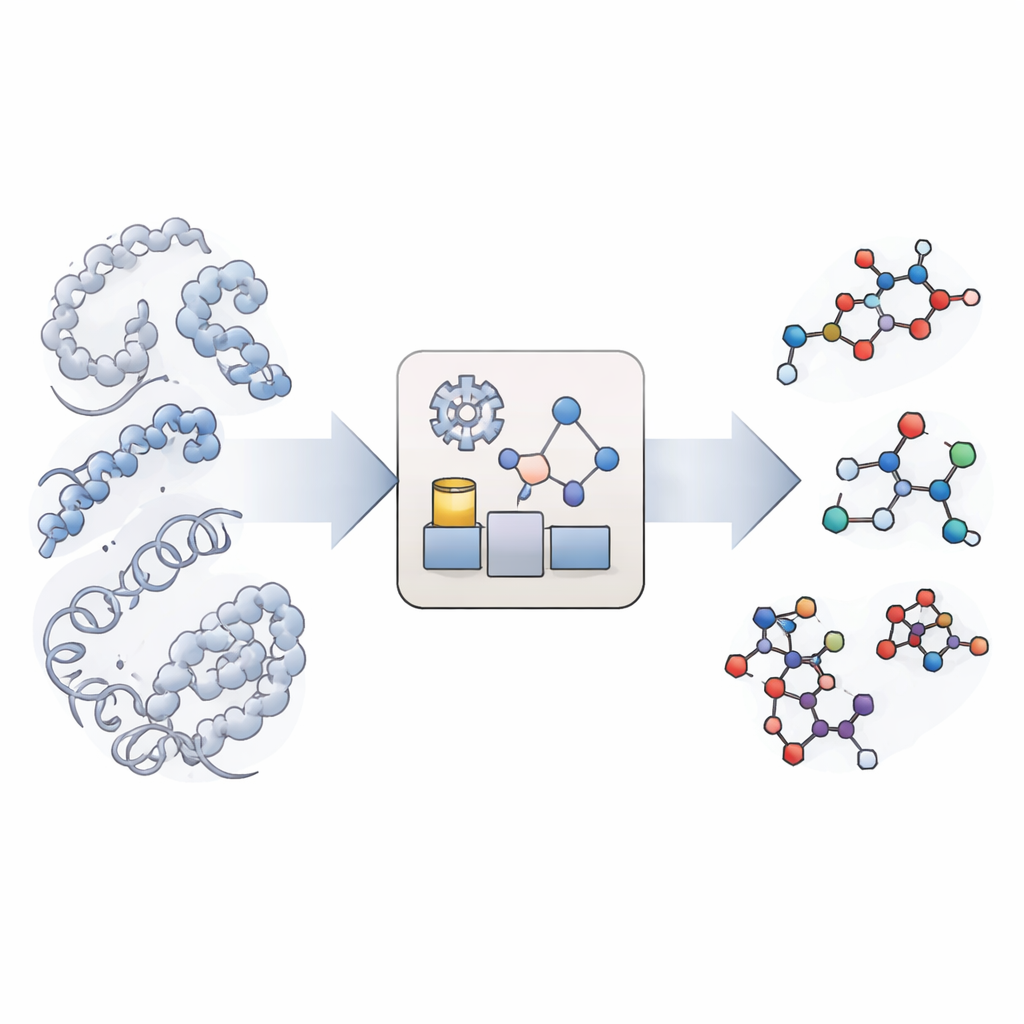
Uma Nova Maneira de Imitar Reações Químicas
Simulações moleculares tradicionais são excelentes para mostrar como grandes biomoléculas, como proteínas e DNA, se movem e se dobram, mas tratam ligações químicas como inquebráveis. Simulações verdadeiramente reativas existem, porém são tão exigentes computacionalmente que raramente alcançam as escalas de tempo relevantes para a biologia, especialmente quando muitos tipos e sítios de reação estão envolvidos. KIMMDY (abreviação de Kinetic Monte Carlo Molecular Dynamics) segue um caminho diferente. Ele permite que simulações convencionais lidem com o movimento molecular e, em seguida, usa um módulo adicional para buscar locais onde reações poderiam ocorrer, estimar com que rapidez aconteceriam e escolher aleatoriamente qual reação ocorre em seguida. Ao ciclar repetidamente movimento, busca de reações e escolha reacional, KIMMDY pode seguir cascatas reacionais complexas em tempos que vão de frações de segundo a muito mais longos, sem nunca calcular um caminho reacional completo em nível quântico.
Como o Emulador de Reações Funciona
No centro do KIMMDY está um "emulador de reações" que prevê taxas reacionais a partir das formas instantâneas das moléculas. Para cada instantâneo de uma simulação de dinâmica molecular, o KIMMDY identifica possíveis parceiros reagentes e usa diferentes modelos para estimar quão alta é a barreira para cada reação. Em muitos casos, ele emprega redes neurais gráficas — modelos de aprendizado de máquina que tratam átomos como nós e ligações como arestas — para estimar alturas de barreira com base em cálculos quânticos de alto nível anteriores. Em outros casos, recorre a fórmulas físicas mais simples ou regras heurísticas extraídas de experimentos. A partir dessas barreiras, calcula taxas e as alimenta em uma etapa de Monte Carlo cinético que escolhe aleatoriamente a próxima reação, avança o relógio simulado e então atualiza a estrutura molecular e o campo de forças antes da próxima rodada de movimento molecular.
Acompanhando Danos por Radicais em Estruturas Proteicas
Para verificar que o KIMMDY funciona conforme esperado, os autores primeiro o aplicaram a uma classe simples de reações em pequenos radicais orgânicos onde há dados experimentais disponíveis. O emulador reproduziu quais reações de deslocamento de hidrogênio são mais prováveis, mesmo subestimando suas velocidades absolutas. Em seguida, passaram para um caso muito mais complexo: o colágeno, a proteína fibrosa que dá força aos tecidos conjuntivos. Sob estresse mecânico, ligações no colágeno podem romper-se homoliticamente, criando radicais altamente reativos que saltam de um sítio para outro ao transferir átomos de hidrogênio ao longo de uma cadeia. Em um fibrila de colágeno com 2,6 milhões de átomos, o KIMMDY rastreou centenas desses saltos e mostrou que radicais podem migrar muitos nanômetros longe de sua origem. As simulações revelaram que uma cruzamento incomum (chamado PYD) e um aminoácido modificado (DOPA) atuam ambos como capturadores de radical excepcionalmente eficazes, uma conclusão apoiada por cálculos termodinâmicos e pela reinterpretação de espectros anteriores de ressonância paramagnética eletrônica.
Quando Diferentes Reações Competem
Muitos sistemas biológicos podem romper a mesma ligação de mais de uma maneira, levando tanto à formação de radicais quanto a produtos mais convencionais de "casca fechada". No colágeno, por exemplo, uma ligação peptídica pode tanto se partir simetricamente em dois radicais (homólise) quanto reagir com água e se dividir de forma desigual (hidrólise). Simulações quânticas diretas de ambas as opções em um ambiente realista seriam proibitivas. Com o KIMMDY, os autores combinaram um modelo físico para homólise assistida por força com um modelo heurístico, baseado em experimentos, para hidrólise e deixaram as duas reações competirem tanto em um peptídeo isolado quanto em uma fibrila densa de colágeno. Eles descobriram que, em uma cadeia isolada sob tração, a hidrólise domina claramente. Em uma fibrila lotada e reticulada, no entanto, o estresse mecânico se concentra em certas regiões de forma tão intensa que a homólise se torna competitiva ou até mais rápida, explicando por que a formação de radicais é observada em tecidos reais.
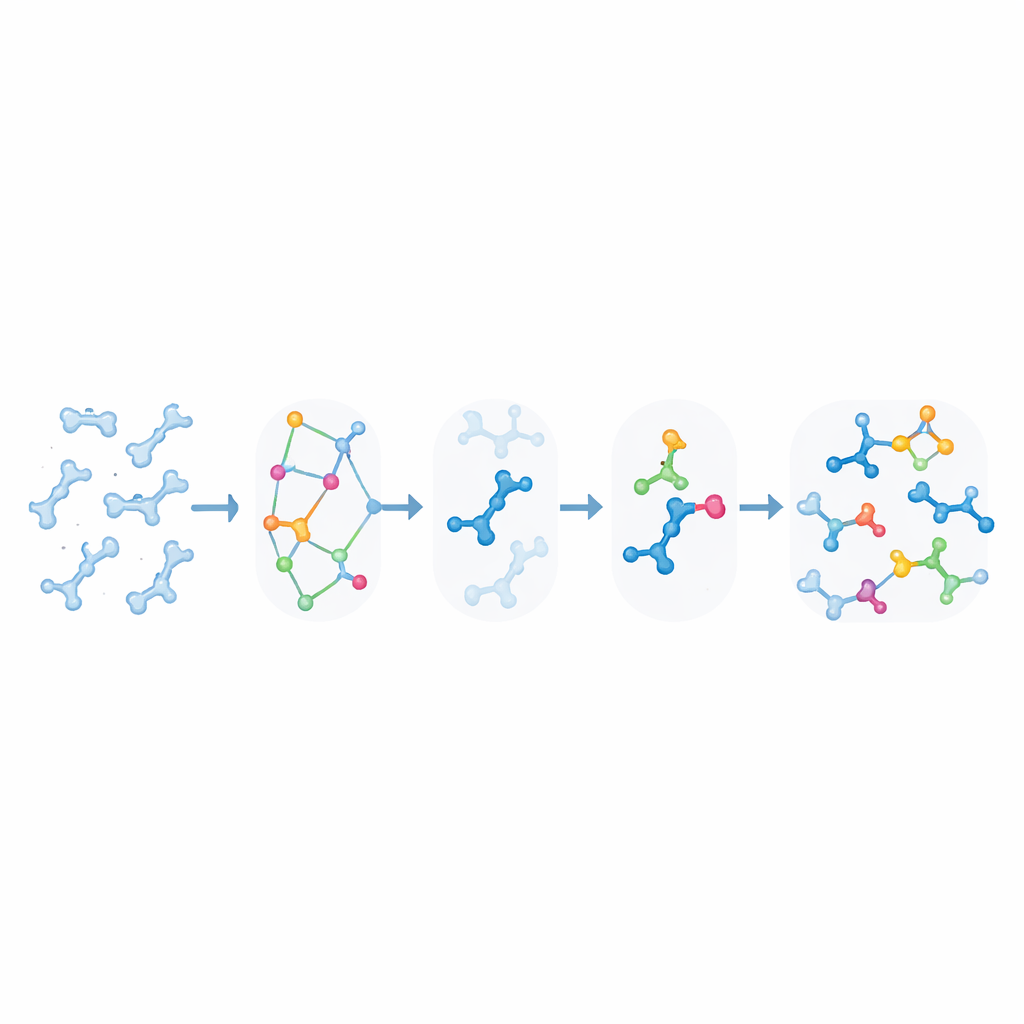
Danos Induzidos por Luz e Cruzamentos no DNA
O KIMMDY também ilumina como a luz ultravioleta altera o DNA. Quando duas timinas vizinhas absorvem UV, elas podem fundir-se em um dímero ciclobutano, uma lesão fortemente associada ao câncer de pele, mas também utilizada para reticular fitas em nanotecnologia de DNA. Usando uma regra geométrica simples que relaciona distância e ângulo entre ligações reativas à probabilidade de reação, ajustada para coincidir com experimentos de pequenas moléculas, os autores usaram o KIMMDY para estimar "rendimento quântico" — com que frequência um dímero se forma por fóton absorvido — para vários motivos de DNA. O emulador previu que alguns arranjos comumente usados em DNA origami, como saliências e cruzamentos, na verdade têm rendimentos surpreendentemente baixos em comparação com DNA padrão de fita dupla ou com falhas (nicks). Também sugeriu que formar um dímero não altera dramaticamente as chances de formar outro nas proximidades, implicando que danos prévios não necessariamente tornam o DNA mais propenso a novos dímeros.
Por Que Isso Importa para a Biologia e o Design
Em termos simples, o KIMMDY oferece uma maneira rápida e flexível de explorar cenários "e se" para a química dentro da matéria viva. Ao emular em vez de simular completamente as reações, ele consegue lidar com sistemas enormes e com escalas de tempo longas, ao mesmo tempo em que leva em conta como as formas em constante mudança das moléculas influenciam quais reações ocorrem, onde e quando. O método ajudou a descobrir um sítio de estabilização de radical até então negligenciado no colágeno, esclareceu como forças mecânicas deslocam o equilíbrio entre vias de quebra de ligações e levantou novas questões sobre como e onde cruzamentos no DNA se formam sob luz. À medida que o emulador é estendido a mais tipos de reações e modelos de taxas mais precisos, promete tornar-se uma ferramenta poderosa para entender como biomoléculas envelhecem, falham ou podem ser projetadas para medicina e nanotecnologia.
Citação: Hartmann, E., Buhr, J., Riedmiller, K. et al. KIMMDY: a biomolecular reaction emulator. Nat Commun 17, 3500 (2026). https://doi.org/10.1038/s41467-026-71955-2
Palavras-chave: simulações biomoleculares, cinética de reações, modelagem molecular, danos ao DNA, mecanoquímica