Clear Sky Science · pt
Comparação e otimização de métodos de preferência de vizinhança celular para análise quantitativa de tecidos
Por que os vizinhos celulares importam
Nossos corpos são formados por bairros movimentados de células, não por dispersões aleatórias. Que células ficam ao lado de quais pode influenciar como um tumor cresce, como uma ferida cicatriza ou como o coração se recupera após um infarto. Este artigo faz uma pergunta aparentemente simples: quando cientistas medem quais tipos celulares tendem a estar próximos uns dos outros em imagens de tecido, quão confiáveis são os diferentes métodos usados, e podemos melhorar isso?
Como os cientistas leem o mapa da cidade celular
Tecnologias modernas de imagem e genômica espacial podem registrar a posição exata e a identidade de milhares de células em uma lâmina de tecido. Uma forma popular de analisar esses dados é calcular “preferências de vizinhança”: para um dado tipo celular A, com que frequência ele tem o tipo B como vizinho próximo em comparação com o que seria esperado ao acaso? Muitos softwares já existem para essa tarefa, mas eles dependem de etapas sutilmente diferentes. Os autores as dividem em três escolhas centrais: como definir uma vizinhança ao redor de cada célula (por exemplo, desenhando arestas entre células próximas ou usando uma distância fixa), como contar vizinhos (tratando um par A–B igual a B–A, ou distinguindo a direção de A para B versus B para A), e como transformar essas contagens em uma pontuação final (contagens normalizadas simples, estatísticas baseadas em permutação ou medidas de aprendizado de máquina). Esse quadro comum permite uma comparação justa, lado a lado, entre métodos.
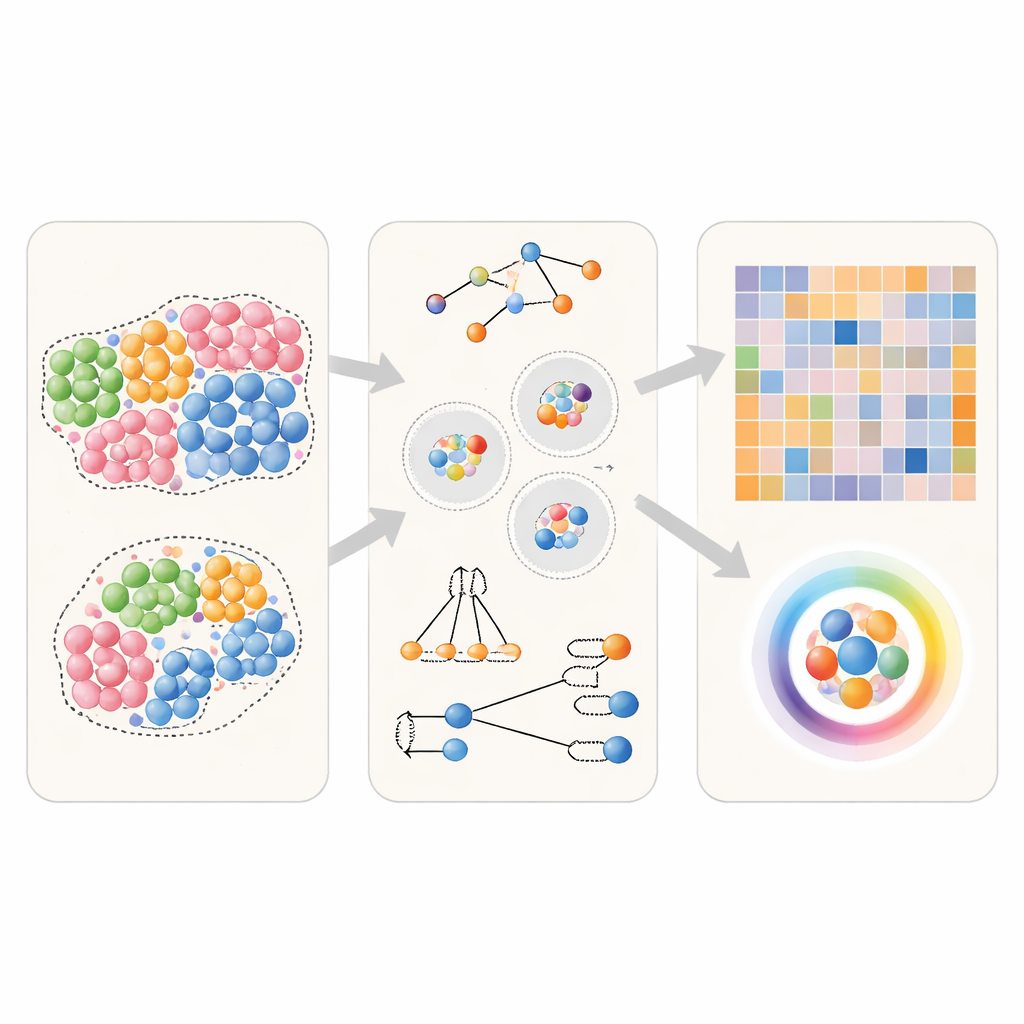
Testando métodos de vizinhança em tecidos virtuais
Para ver quão bem diferentes abordagens performam, a equipe primeiro usou tecidos gerados por computador nos quais as verdadeiras relações de vizinhança são conhecidas antecipadamente. Eles criaram cenários simples em que um determinado tipo celular ou não tem preferência especial, prefere levemente seu próprio tipo, ou se agrupa fortemente com sua própria espécie. Também simularam situações direcionais em que um tipo celular prefere se aproximar de outro, mas não o contrário. Usando esses tecidos virtuais, os autores forneceram dados idênticos a várias ferramentas amplamente usadas e então perguntaram: cada método consegue distinguir de forma confiável esses cenários, e pode recuperar corretamente qual tipo celular busca qual vizinho?
Por que direção e sutileza são difíceis de capturar
A comparação revelou que quase todos os métodos conseguem detectar diferenças grandes e óbvias na organização do tecido. Contudo, surgiram duas fraquezas principais. Primeiro, algumas ferramentas comprimem sua saída em pontuações grosseiras de três níveis (por exemplo, “abaixo do acaso”, “sem diferença” ou “acima do acaso”), o que dificulta distinguir uma preferência fraca de uma forte. Segundo, muitos métodos fazem a média das contagens de vizinhos sobre todas as células de um dado tipo, independentemente de uma célula particular ter ou não encontrado o outro tipo. Essa “média total” tende a borrar a direcionalidade, fazendo a relação de A para B parecer semelhante à de B para A, mesmo quando apenas uma direção mostra realmente preferência. Como resultado, ferramentas existentes podem subestimar ou até inverter a aparente direção da infiltração celular, especialmente quando um tipo celular é raro e o outro é abundante.
Uma nova forma de pontuar vizinhos direcionais
Para resolver essas questões, os autores introduzem um novo esquema de pontuação chamado escore z condicional, ou COZI. O COZI mantém a mesma ideia de comparar contagens observadas de vizinhos com muitas versões randomizadas do tecido, mas altera como as contagens são agregadas: considera apenas as células do tipo A que realmente tocam pelo menos uma célula do tipo B. Esse foco “condicional” mostra-se crucial para recuperar a direcionalidade. O COZI então converte o resultado em um z-score contínuo, que reflete quão fortemente o padrão observado se desvia da expectativa aleatória. Para tornar as pontuações mais fáceis de interpretar, os autores adicionam uma medida acompanhante, a razão condicional de células (CCR), que simplesmente informa que fração das células do tipo A participa da vizinhança A–B. Juntos, o z-score e a CCR revelam não apenas quão forte é uma relação espacial, mas também se ela é impulsionada por algumas células especializadas ou por uma mudança ampla na organização do tecido.
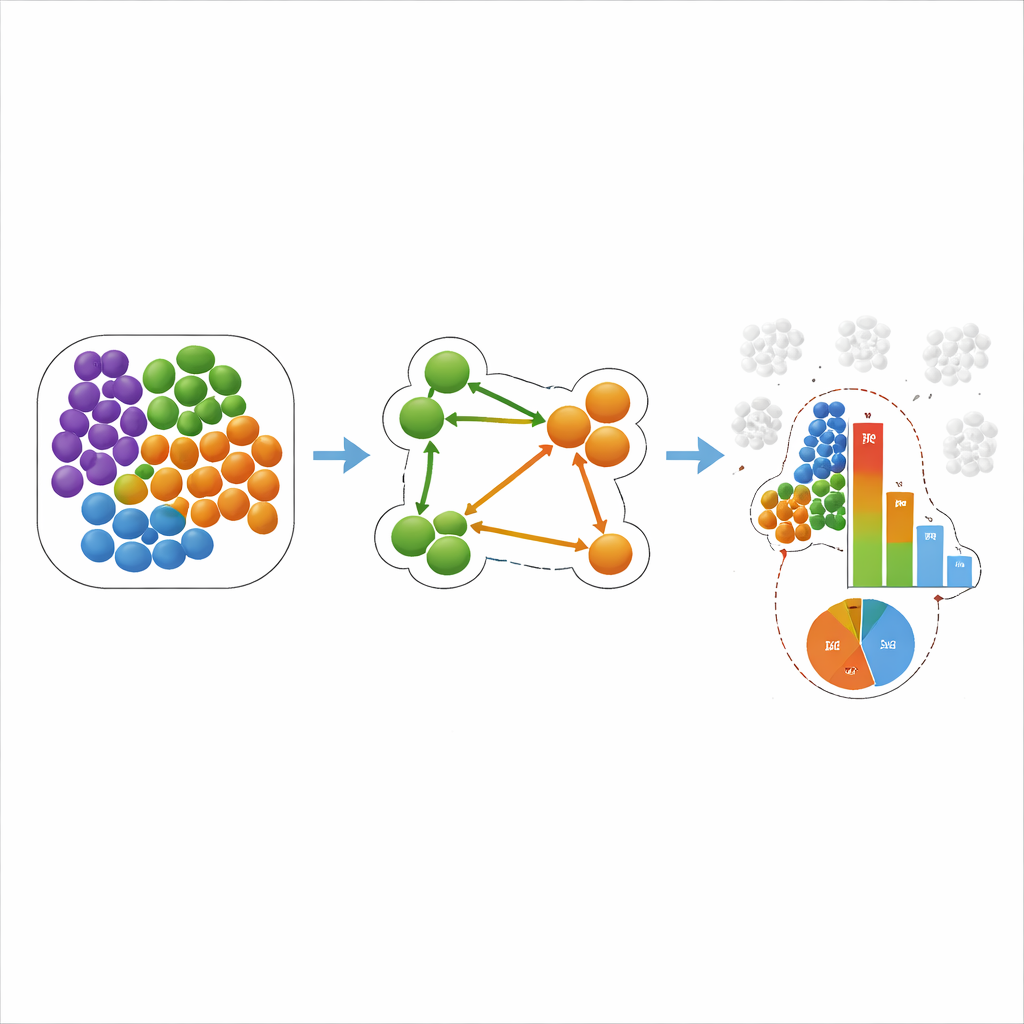
O que isso significa para câncer e doenças cardíacas
A equipe então aplicou COZI e outros métodos a dois conjuntos de dados do mundo real. Em um estudo de câncer de mama triple-negativo, trabalhos anteriores tinham agrupado tumores em “friO”, “mistos” e “compartimentalizados” com base em como células imunes e células tumorais se misturavam. O COZI não só reproduziu esses agrupamentos, mas também revelou padrões direcionais: por exemplo, em alguns tumores, células imunes tendiam a se agrupar entre si enquanto um subconjunto de células tumorais alcançava essas bolsas, enquanto em outros, eram as células imunes que infiltravam regiões tumorais. Em um modelo de camundongo de infarto do miocárdio, o COZI rastreou como neutrófilos e monócitos entraram progressivamente no músculo cardíaco danificado, primeiro pela camada interna do ventrículo e depois mais profundamente na zona lesionada. Importante, ele separou mudanças globais no número de células de alterações reais em quem é vizinho de quem e em qual direção.
Mensagem principal
Este estudo mostra que nem todas as ferramentas para ler vizinhanças celulares são criadas iguais, e que pequenas escolhas algorítmicas podem moldar fortemente conclusões biológicas. Ao clarificar como os métodos existentes funcionam e ao introduzir o COZI junto com a razão condicional de células, os autores fornecem um roteiro para escolher e interpretar análises de vizinhança em dados espaciais de tecido. Para não especialistas, a ideia-chave é que entender quem mora ao lado de quem na “cidade” do tecido — e quem está invadindo o território de quem — pode revelar sinais precoces de doença, respostas à terapia e rotas para tratamento direcionado, desde que esses padrões sejam medidos com as ferramentas adequadas.
Citação: Schiller, C., Ibarra-Arellano, M.A., Bestak, K. et al. Comparison and optimization of cellular neighbor preference methods for quantitative tissue analysis. Nat Commun 17, 3514 (2026). https://doi.org/10.1038/s41467-026-71699-z
Palavras-chave: ômica espacial, vizinhanças celulares, microambiente tumoral, infiltração de células imunes, patologia computacional