Clear Sky Science · he
שיטה אוניברסלית חדשה ממוקדת דומיין לסיווג חלבונים
מדוע מיון חלבונים חשוב לבריאות
בתוך כל תא, אלפי מכונות חלבוניות זעירות שומרות על תפקוד החיים. בין החשובות שבהן נמצאות קינאזות חלבון, אנזימים שמכבים ומפעילים חלבונים אחרים ומהווים מטרות עיקריות של תרופות מודרניות, ובפרט טיפולים בסרטן. עם זאת, מדענים עדיין נאבקים למיין את כל הקינאזות למשפחות שמייצגות את פעילותן באופן מדויק. מאמר זה מציג שיטה חדשה לסיווג קינאזות — ובעיקרון גם חלבונים אחרים — על ידי התמקדות באזור הליבה המשותף שבאמת מבצע את העבודה, ובתכונות הפיזיקליות והכימיות הבסיסיות של אבני הבניין שלו. הדבר מבטיח מפות חדות יותר של משפחות חלבוניות ולבסוף רמזים טובים יותר לעיצוב תרופות.
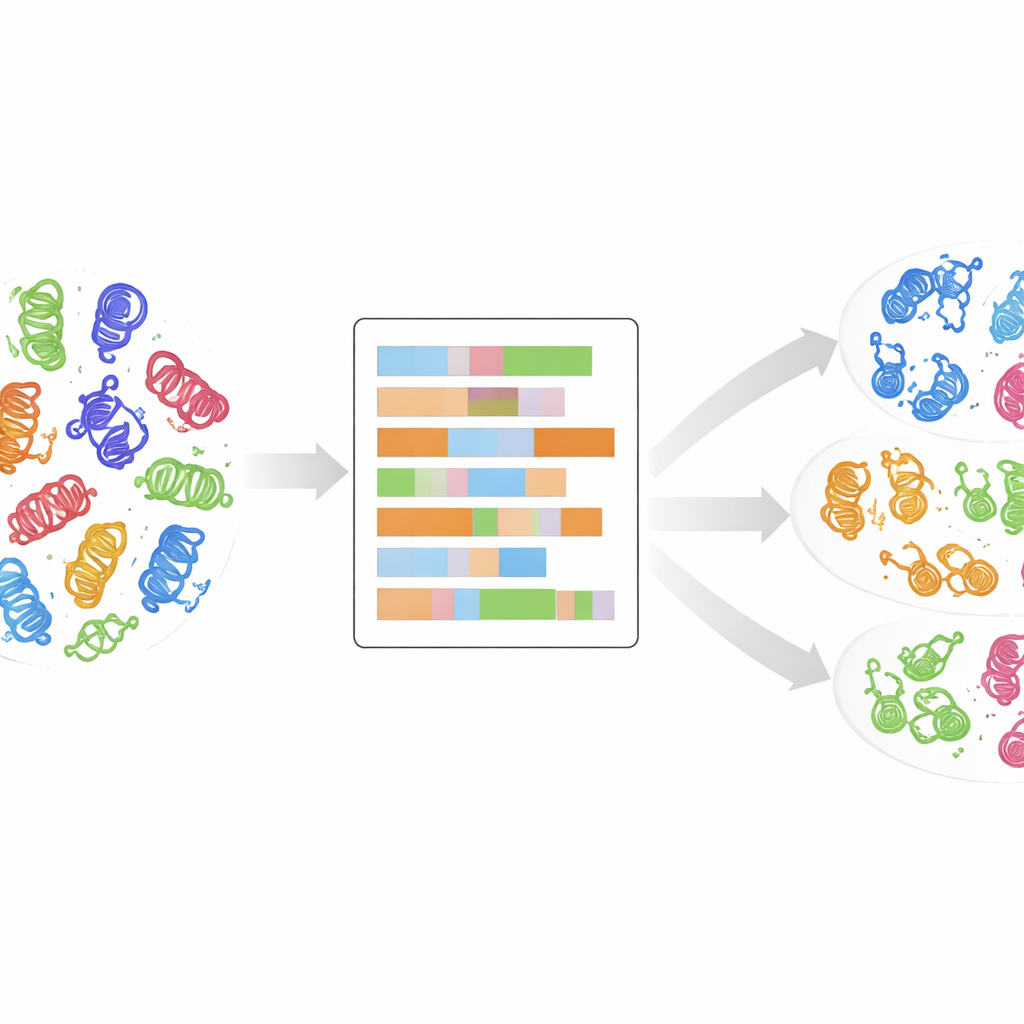
מעצי משפחה אל טביעת אצבע מפורטת יותר
מסורתית, הקינאזות קובצו למחלקות על בסיס השוואת רצפי הגנים או החלבונים ובניית "עצי משפחה" אבולוציוניים. גישה זו הצליחה היטב, וחשפה כ־500 קינאזות אנושיות החולקות מספר קבוצות עיקריות כגון AGC, CAMK, CMGC, STE, TK, TKL ואחרות. ועדיין, קינאזות שגילו לאחרונה לעיתים אינן משתלבות בצורה נקייה בקבוצות אלה: הרצפים שלהן נראים שונים, אף על פי שהן עשויות לפעול בדומה בתאים. השוואות סטנדרטיות גם מתייחסות מעט לתכונות הבסיסיות של כל חומצת אמינו — הגודל, המטען או האהדה למים שקובעות כיצד החלבון מתקפל ומתפקד. המחברים טוענים שעל מנת להבין באמת את משפחות הקינאזות, צריך להסתכל מעבר להתאמות דמויות-אלפבית ברצף ולבחון את טביעות האצבע הפיזיקו-כימיות הללו.
התמקדות בליבת הפעילות של הקינאזות
לשם כך השתמשו החוקרים בהצבה איכותית גבוהה של 497 דומיינים של קינאזות אנושיות, הליבות הקומפקטיות שמבצעות בפועל את התגובה הכימית של הוספת קבוצות פוספט. לכל מיקום במפת הדומיין המשותפת הזו החליפו את אות חומצת האמינו בעד כ־30 תיאורים מספריים שלכדו תכונות כמו מטען, הידרופוביות, קוטביות וגודל, בתוספת סימון לפתחים. התוצאה היא דיוקן מספרי מפורט של כל דומיין קינאז, שבו התנהגות דומה במרחב התלת-ממדי אמורה להתרגם לתבניות דומות במספרים האלה. לאחר מכן הפחיתו את המורכבות של דיוקנאות אלה באמצעות ניתוח רכיבים עיקריים, טכניקה סטנדרטית שמצמצמת מדידות רבות לכמה כיוונים עיקריים הלוכדים את ההבדלים הגדולים ביותר.
לתת לנתונים להתקבץ בעצמם
מבלי להורות למחשב איזו קינאז שייכת לאיזו מחלקה ידועה, הצוות השתמש בשיטת התקבצות לא-ממונחית בשם k-means על הנתונים המספריים המופחיתים. הם בדקו מספר אפשרויות של כמות אשכולות והשתמשו בציונים סטטיסטיים כדי לזהות את החלוקות המשמעותיות ביותר, ואז שילבו כמה פתרונות כאלה לסט סופי של 24 אשכולות, כל אחד עם ניקוד ביטחון המשקף עד כמה הוא יציב בין ריצות. מעניין שכשני שלישים עד כ־90% מהקינאזות הסתיימו באשכולות שעמדו בקנה אחד עם תוויות המחלקה המקוריות שלהן, מה שמרמז שהדיוקן הפיזיקו-כימי של הדומיין משחזר — ולעיתים מחדד — סיווגים קיימים. חלק מהאשכולות כללו תערובת של מחלקה עיקרית וקינאזות שסווגו קודם כ"אחרות", מצב שמרמז שחריגים אלה עשויים למעשה להשתייך למשפחה מוכרת.
גילוי מוקדי מבנה מרכזיים
מעבר לקיבוץ, השיטה חושפת אילו חלקים בדומיין הקינאז מובילים בפועל להבדלים אלה. על ידי שילוב הרכיבים העיקריים עם תכונות השרשראות ואז ביצוע בדיקות רנדומליזציה, המחברים זיהו מקומות ספציפיים שבהם תבניות התכונות מבחינות בחוזקה בין מחלקה אחת לאחרת. דוגמה בולטת היא אתר באזור לולאת ההפעלה של קינאזות CMGC שנושא כמעט תמיד שייר טעון חיובית, שונה מרוב שאר המחלקות. מודלים מבניים מראים שבקינאז CMGC מייצג, שייר זה מסייע לייצב אתרים מזורחנים סמוכים החיוניים להפעלת האנזים. מעניין שקינאז "לא מסווג" שנקרא CDC7 משתף סביבה דומה באתר זה, תומך בתחזית שהוא מתנהג כמו קינאז CMGC אף אם ההיסטוריה האבולוציונית שלו שונה.
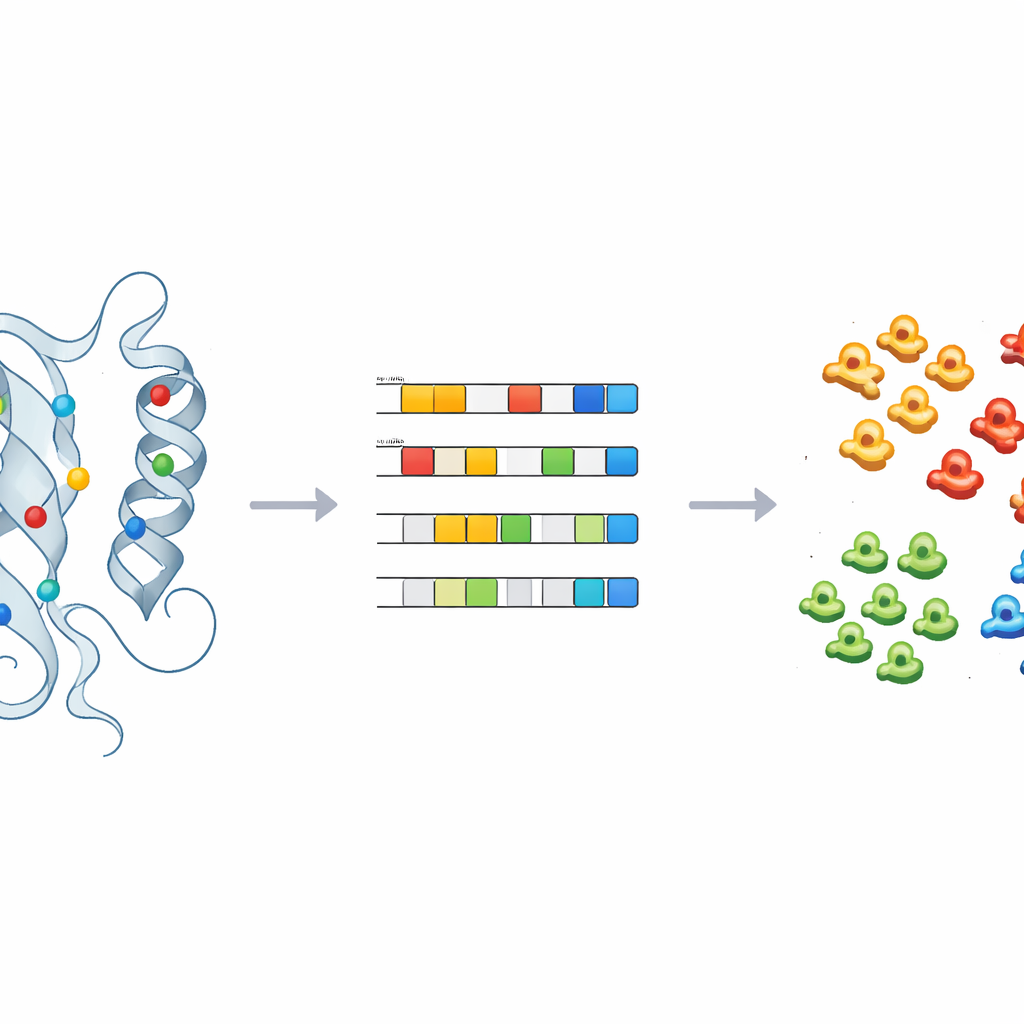
להדריך מכונות לתייג את הבלתי-ידוע
כדי להפוך תובנות אלה לניבויים מעשיים, האימנו החוקרים מודלים מפוקחים של למידת מכונה — כולל רגרסיה לוגיסטית, יער אקראי ומסווג פרובביליסטי — על הדיוקנאות הפיזיקו-כימיים של קינאזות עם תוויות ידועות. לאחר כיוונון זהיר ולבדיקות צולבות, המודלים יכלו למקם קינאזות למחלקות העיקריות בדיוק תוך שימוש רק בכמה רכיבים עיקריים. כשיישמו אותם על 66 קינאזות שנשארו בקבוצת "אחרות" הכוללת, המודלים הקצו בחזרה באופן עקבי כמה מהם, כגון CDC7 וחברים במשפחת ULK, למחלקות קינאז ספציפיות. בדיקות מבניות של שיבוצים אלה, במיוחד סביב המיקומים המרכזיים שהוזכרו קודם, תמכו בתחזיות המכונה והדגימו כיצד השיטה יכולה להנחות סיווג מחדש ומחקר ניסויי המשך.
מתכון כללי למיפוי משפחות חלבון
במונחים יומיומיים, עבודה זו מראה שניתן למיין חלבונים לא רק על ידי כתיבת רצפיהם, אלא על ידי זיקוק האופן שבו החלקים הליבתיים שלהם מתנהגים פיזיקלית וכימית. עבור קינאזות, גישה ממוקדת-דומיין ומבוססת-תכונות זו משחזרת משפחות מוכרות, מסייעת בתיוג מחדש של חריגים ומבליטה "מוקדי חום" מבניים שחשובים לפעילות ולבקרה. מאחר שהמתכון מסתמך רק על הצבה משותפת של דומיין ותיאורים כלליים של חומצות אמינו, המחברים מראים גם שניתן ליישם אותו לקבוצות חלבון אחרות, כגון GTPאזות קטנות, וייתכן שיוכל להתרחב לאימונוגלובולינים, קולטני G protein–coupled ואחרים. ככל שמפות כאלה יהפכו למעודנות יותר, הן עשויות להנחות עיצוב תרופות סלקטיביות יותר, לסייע בפרשנות מוטציות הגורמות למחלות, ולהציע אטלס ברור יותר, ממוקד-תפקוד, של יקום החלבונים.
ציטוט: Fadaei, S., Krebs, F.S. & Zoete, V. Novel universal domain-centric method for protein classification. Sci Rep 16, 11850 (2026). https://doi.org/10.1038/s41598-026-41142-w
מילות מפתח: קינאזות חלבון, סיווג חלבונים, למידת מכונה, דומיינים של חלבון, ביולוגיה מבוססת-מבנה