Clear Sky Science · fr
Diagnostic génétique de l’HCA liée à CYP21A2 : le séquençage longue lecture à échantillonnage adaptatif est une solution précise et évolutive
Pourquoi cela compte pour les familles et les médecins
De nombreux nouveau‑nés sont désormais dépistés à la naissance pour l’hyperplasie congénitale des surrénales (HCA), un trouble hormonal qui peut mettre la vie en danger s’il n’est pas détecté. Pourtant, confirmer le diagnostic au niveau de l’ADN est étonnamment difficile, car le gène clé se trouve dans une zone déroutante de notre génome, accompagnée d’un « gène leurre » presque identique. Cette étude montre qu’un nouveau type de lecture de l’ADN, appelé séquençage longue lecture à échantillonnage adaptatif, peut percer cette confusion, fournissant des réponses plus rapides et plus fiables pour les patients et leurs familles.
Un trouble hormonal aux tournures génétiques
L’hyperplasie congénitale des surrénales (HCA) affecte la production par les glandes surrénales d’hormones essentielles qui régulent l’équilibre du sel, les réponses au stress et les niveaux d’hormones sexuelles. Dans environ 95 % des cas, le problème remonte à des altérations d’un seul gène, CYP21A2, qui participe à la fabrication de l’enzyme 21‑hydroxylase. Si cette enzyme fait défaut ou est déficiente, l’organisme ne peut pas produire suffisamment de cortisol et d’aldostérone, et produit à la place un excès d’androgènes, entraînant des symptômes allant des crises d’élimination du sel chez les nouveau‑nés à une pilosité excessive et des problèmes de fertilité plus tard dans la vie. La plupart des patients portent des changements pathogènes différents sur chaque copie du gène, et la combinaison de ces altérations influence fortement la sévérité de la maladie.
Un gène dissimulé à côté de son sosie
Le vrai défi est que CYP21A2 se situe dans un quartier complexe du chromosome 6, à côté d’un « pseudogène » presque identique, CYP21A1P, qui n’est plus fonctionnel. Leur séquence d’ADN est d’environ 98 % identique, et la région est sujette à des réarrangements où des segments du gène actif et du pseudogène s’échangent, fusionnent ou sont supprimés. Les méthodes classiques reposent sur l’amplification de segments d’ADN par PCR puis leur lecture par séquençage Sanger, parfois complétée par une technique appelée MLPA pour compter les copies géniques. Ces méthodes sont lentes, laborieuses et peuvent peiner à détecter de grands réarrangements ou à déterminer si plusieurs altérations se trouvent sur le même chromosome ou sur des chromosomes opposés — information cruciale pour estimer le risque chez le patient et les apparentés.
Une nouvelle façon de lire la région délicate
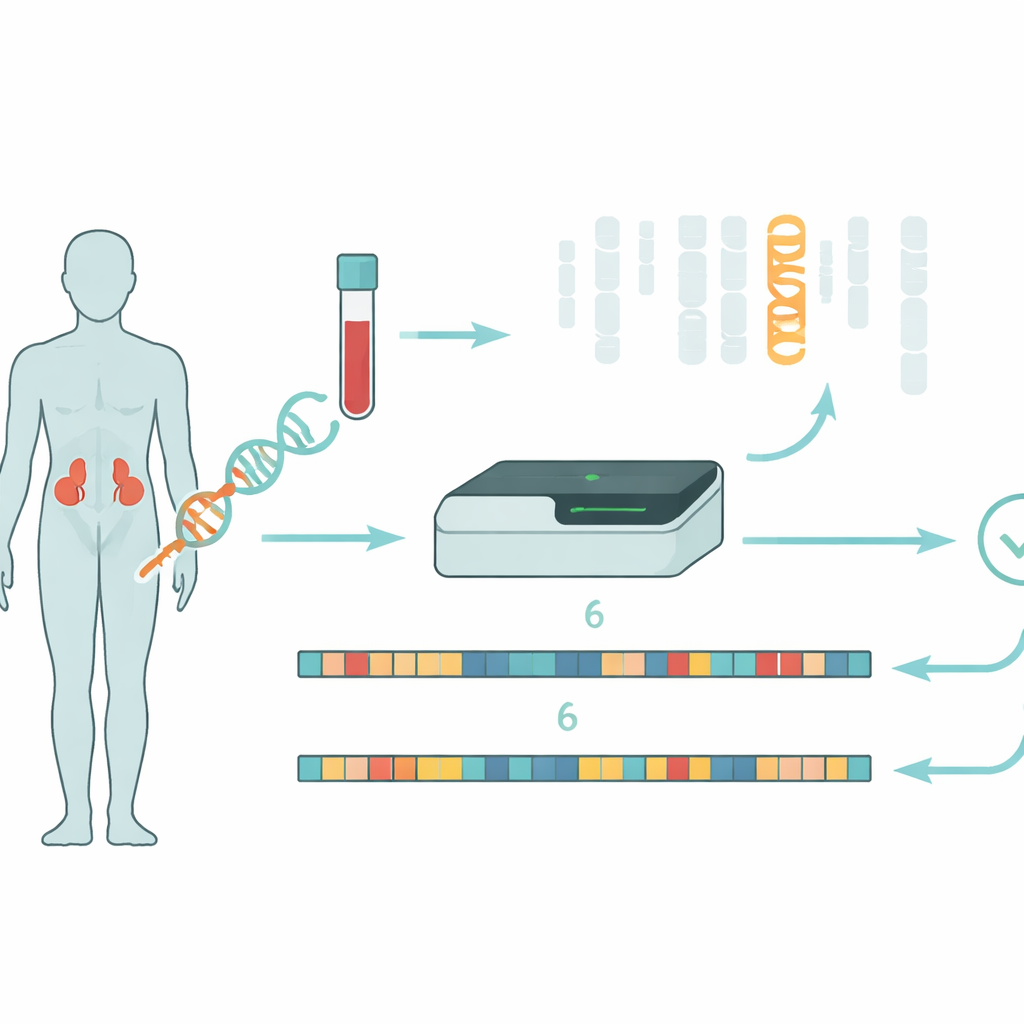
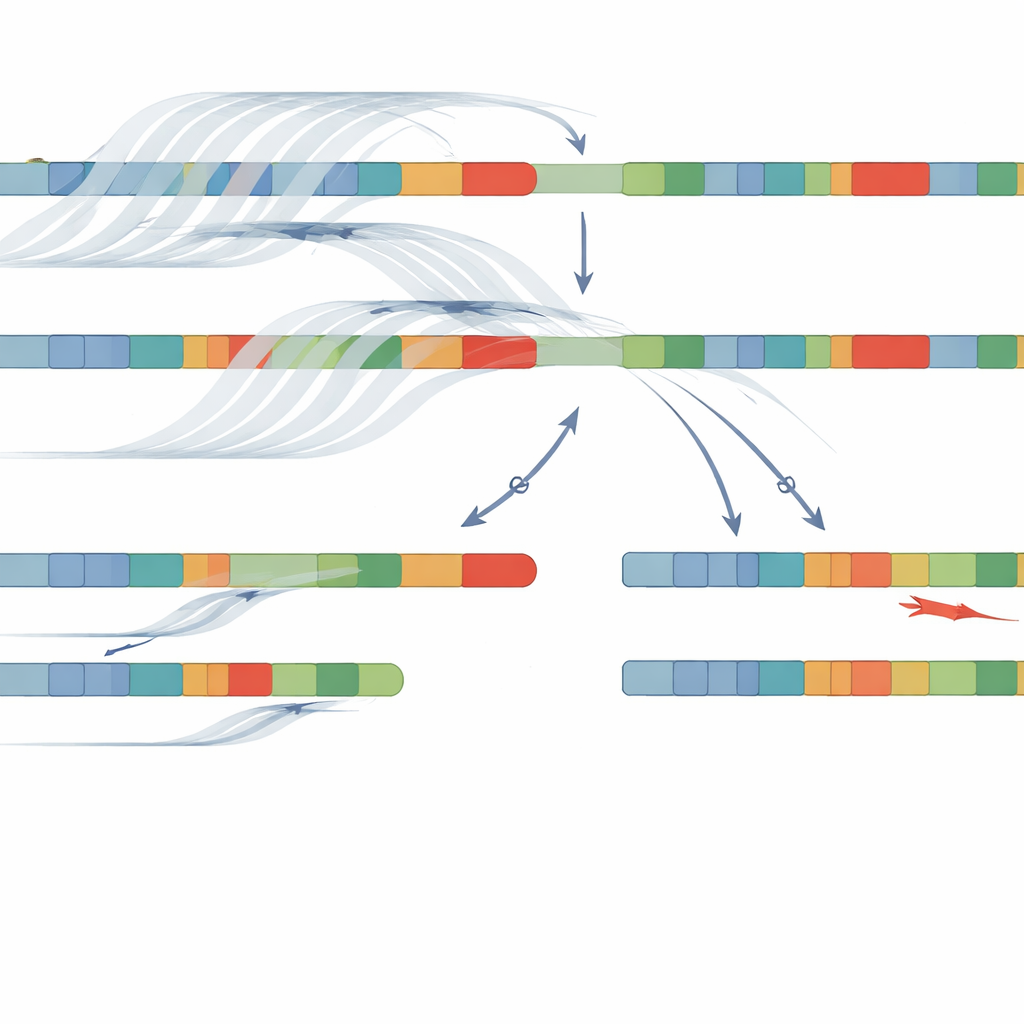
Les chercheurs ont exploré une stratégie différente utilisant le séquençage longue lecture sur la plateforme Oxford Nanopore. Plutôt que de fragmenter l’ADN en très petits morceaux, cette technologie lit des étendues beaucoup plus longues, ce qui aide à relier des éléments distants le long du chromosome. Ils ont utilisé l’« échantillonnage adaptatif », où le séquenceur est instruit en temps réel de se concentrer sur une région choisie — ici le chromosome 6 — augmentant la couverture sans étapes de laboratoire complexes. À partir de 34 patients ayant un diagnostic clinique d’HCA, l’ADN a été séquencé sans PCR, évitant des biais qui peuvent faire disparaître une version du gène. Pour gérer la très grande similarité entre CYP21A2 et son pseudogène, l’équipe a développé un outil logiciel personnalisé appelé NanoCAH, qui examine soigneusement l’alignement de chaque lecture longue, décide si elle provient réellement du gène fonctionnel ou du leurre, et reconstruit les deux versions régionales de chaque patient.
Des réponses plus nettes chez la plupart des patients
En utilisant cette combinaison de séquençage longue lecture à échantillonnage adaptatif et de NanoCAH, l’équipe a identifié des altérations pathogènes chez 32 des 34 patients, soit un taux de réussite de 94 %. Ils ont non seulement confirmé presque toutes les observations des méthodes antérieures, mais aussi révélé des détails importants qui avaient été manqués ou mal classés. Chez certains patients, des tests antérieurs avaient qualifié une altération d’« homozygote », comme si les deux chromosomes portaient la même erreur ; la nouvelle méthode a montré qu’un chromosome portait en réalité une délétion ou une fusion complexe entre le gène et le pseudogène. Chez d’autres, des fautes d’orthographe auparavant invisibles dans le gène ont été identifiées parce que la nouvelle approche lit l’intégralité de la région plutôt qu’un ensemble restreint de points chauds courants. Essentiellement, les lectures longues ont permis à l’équipe de « phaser » les variants — montrant quelles altérations sont associées sur le même chromosome — sans nécessiter l’ADN des parents.
Ce que cela signifie pour les tests futurs
L’étude conclut que le séquençage longue lecture à échantillonnage adaptatif, associé à un logiciel d’analyse spécialisé, peut fournir des diagnostics génétiques de l’HCA plus rapides, plus évolutifs et plus précis que les tests standard actuels. En donnant une image plus claire des réarrangements géniques complexes et en séparant de façon fiable le gène fonctionnel de son quasi‑jumeau, cette approche peut améliorer le diagnostic, guider les décisions thérapeutiques et soutenir des dépistages de porteurs et prénataux plus précis au sein des familles concernées. Comme de nombreux autres gènes impliqués dans des maladies se trouvent aussi dans des segments d’ADN répétitifs et embrouillés, la même stratégie pourrait aider à démêler des questions génétiques difficiles bien au‑delà de l’HCA.
Citation: Lildballe, D.L., Huno, M.R., Ridder, L.O.R. et al. Genetic diagnosis of CYP21A2-related CAH: adaptive sampling long-read sequencing is an accurate and scalable solution. Eur J Hum Genet 34, 535–542 (2026). https://doi.org/10.1038/s41431-026-02019-8
Mots-clés: hyperplasie congénitale des surrénales, CYP21A2, séquençage longue lecture, diagnostic génétique, échantillonnage adaptatif