Clear Sky Science · de
FAIMS mit niedriger Auflösung für erhöhte Peptidabdeckung bei geringen Probenmengen und Einzelzell-Proteomik
Mehr sehen mit weniger
Die moderne Biologie arbeitet häufig mit verschwindend kleinen Proben – manchmal mit dem Inhalt einer einzigen Zelle. Um zu verstehen, was in diesen winzigen Welten passiert, verlassen sich Forschende auf Instrumente, die Tausende unterschiedlicher Proteine gleichzeitig erkennen können. Diese Studie zeigt, dass man durch eine behutsame Änderung der Betriebsweise eines solchen Instruments, genannt FAIMS, deutlich mehr Proteinfragmente aus derselben kleinen Materialmenge sichtbar machen kann, ohne neue Geräte anzuschaffen oder Software umzuschreiben.
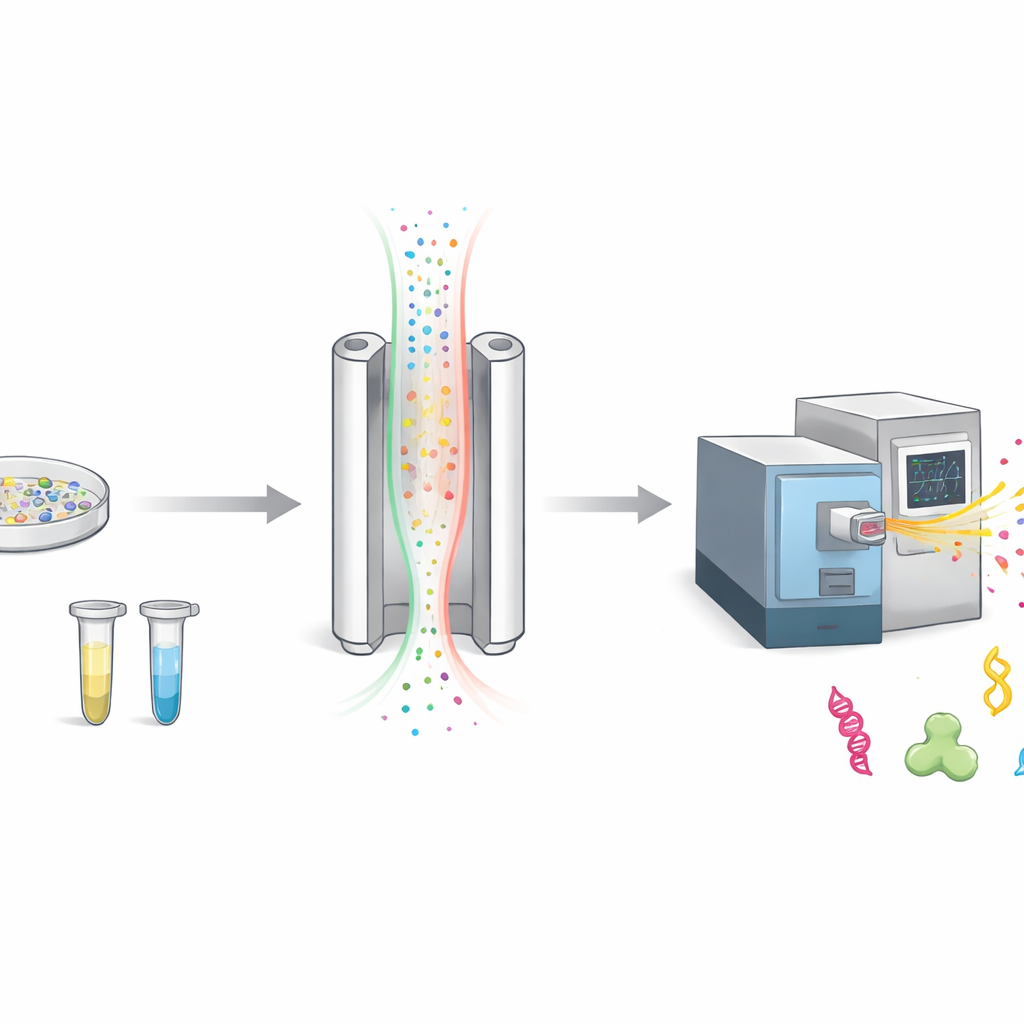
Wie wir geladene Moleküle in der Luft sortieren
Wenn Forschende Proteine untersuchen, zerlegen sie sie meist in kleinere Stücke, sogenannte Peptide, und wiegen diese dann mit einem Massenspektrometer. Vor dem Wiegen fügt FAIMS einen zusätzlichen Sortierschritt hinzu. Geladene Moleküle werden durch einen schmalen Spalt zwischen zwei Metallplatten geleitet, während ein elektrisches Feld schnell ein- und ausgeschaltet wird. Nur Moleküle, deren Bewegung zu einer eingestellten Bedingung passt, gelangen zum Detektor; der Rest wird als Hintergrund verworfen. Das macht die Messung sauberer, bedeutet aber auch, dass viele potenziell interessante Moleküle nie das Instrument erreichen.
Der Kompromiss zwischen Schärfe und Helligkeit
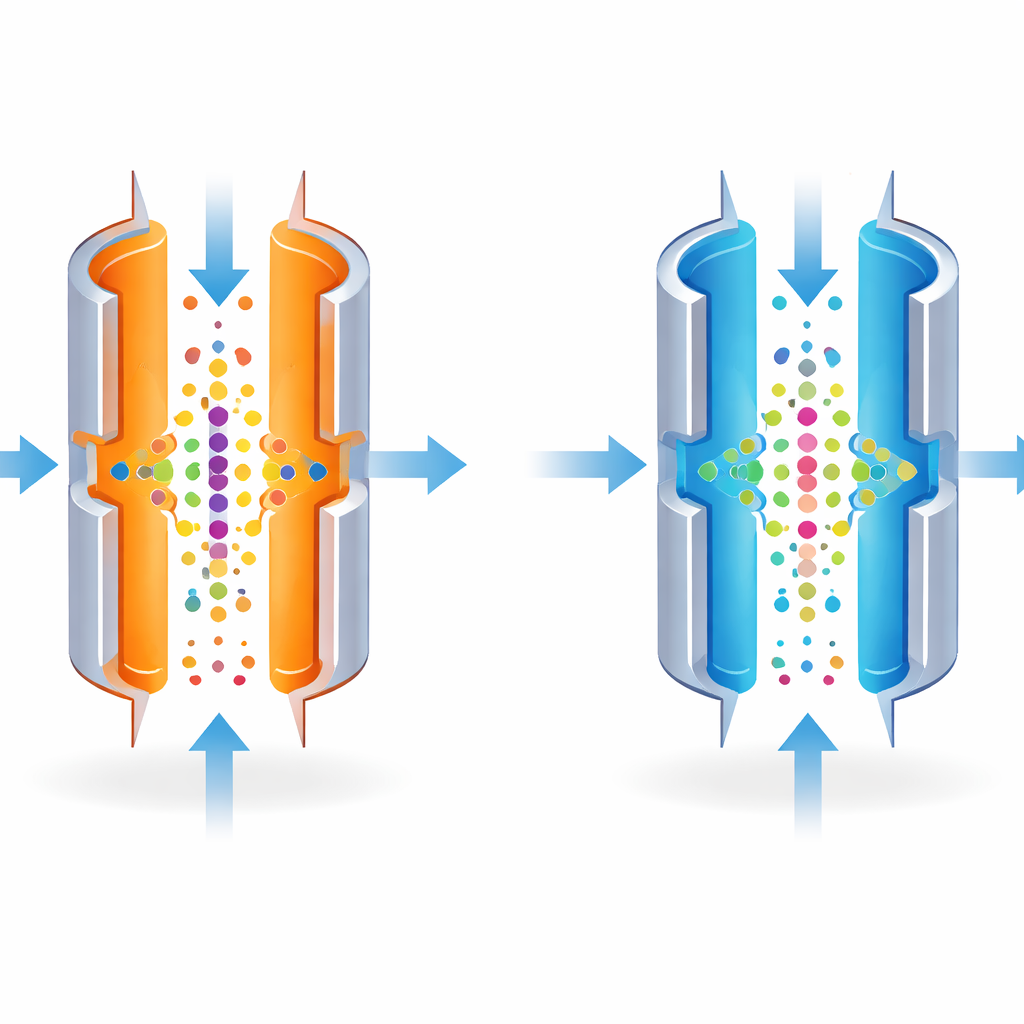
FAIMS lässt sich so einstellen, dass Moleküle sehr präzise getrennt werden, ähnlich wie ein Kameraobjektiv auf einen einzelnen Punkt fokussiert. Die schärfsten Einstellungen lassen allerdings nur einen engen Bereich von Molekülen durch und schwächen so das Gesamtsignal. Die Autorinnen und Autoren erkannten, dass die Temperatur der Metallplatten stark beeinflusst, wie eng dieser Bereich definiert ist. Indem sie die äußere Platte kühler als die innere machten, machten sie die Sortierung bewusst weniger strikt. Dadurch vergrößerte sich der Bereich der Moleküle, die bei einer bestimmten Einstellung passieren konnten, wodurch mehr Ionen in einem einzigen Lauf das Massenspektrometer erreichten.
Die Temperatur senken, um versteckte Peptide zu entdecken
Das Team testete die Idee zuerst mit Standardmischungen bekannter Moleküle und mit sehr geringen Mengen einer gut untersuchten Zelllinie (HeLa). Durch das Senken der Temperatur der äußeren Platte von 100 °C auf 80 °C erweiterte sich das Fenster der Moleküle, die FAIMS durchließen, und die Gesamtzahl der detektierten Ionen stieg. In der Praxis bedeutete dies, dass das Instrument 25–34 % mehr verschiedene Peptide und etwas mehr Proteine aus derselben winzigen Probe identifizierte. Diese Zugewinne waren bei den geringsten Probenmengen am größten, wo jedes zusätzlich detektierte Molekül am wichtigsten ist.
Bessere Einblicke in einzelne Zellen
Die Forschenden wandten die Methode anschließend auf echte Einzelzellproben einer Lungenkrebszelllinie namens H460 an. Mit der sanfteren FAIMS-Einstellung stieg erneut sowohl die Anzahl der Peptide als auch die der Proteine, die in jeder Zelle detektiert wurden. Die zusätzliche Empfindlichkeit verbesserte die „Fingerabdrücke“, die die Proteinzusammensetzung jeder Zelle beschreiben, und machte Unterschiede zwischen Zellen deutlicher. Kontrollbrunnen ohne Zellen lieferten ebenfalls Signale, diese spiegelten jedoch überwiegend Hintergrund und Handhabungsschritte wider. Die zentrale Beobachtung war, dass allein das Ändern der Plattentemperatur beeinflusste, wie viele aussagekräftige Proteine in jeder einzelnen Zelle sichtbar wurden.
Eine einfache Anpassung mit großer Wirkung
Insgesamt zeigt die Studie, dass das bewusste Herabsetzen der Auflösung von FAIMS – durch das Kühlen einer seiner Platten – die Anzahl der aus winzigen Proben, einschließlich Einzelzellen, detektierten Proteinfragmente deutlich erhöhen kann. Für Nichtfachleute lautet die Erkenntnis, dass das Lockern eines Filters manchmal mehr von dem sichtbar macht, was wichtig ist: Hier führt eine etwas unscharfere Trennung in FAIMS zu einem insgesamt helleren Bild der Proteinlandschaft einer Zelle. Da diese Änderung vorhandene Hardware und einfache Einstellungen nutzt, können viele Labore sie schnell übernehmen, um ihren Blick in die Biologie auf kleinstem Maßstab zu vertiefen.
Zitation: Hoch, D.G., Belford, M., Heil, L.R. et al. Low-resolution FAIMS for increased peptide coverage in low-load and single-cell proteomics. Sci Rep 16, 14454 (2026). https://doi.org/10.1038/s41598-026-45228-3
Schlüsselwörter: Einzelzell-Proteomik, FAIMS, Massenpektrometrie, Proteinanalyse, Ionenmobilität