Clear Sky Science · zh
Smoothie:从去噪空间转录组数据高效推断与整合空间共表达网络
以前所未有的细节观察细胞邻里关系
身体的每一块组织都是细胞繁忙的城市,细胞在特定位置精准地开启或关闭基因。新的“空间转录组学”技术如今可以读取组织切片上几乎每个点的基因活性,但原始数据通常非常嘈杂且不完整。本文介绍了 Smoothie,一种计算方法,它清理这些模糊测量并揭示在空间中协同作用的基因群,帮助科学家解码组织如何构建、如何运作以及在时间或疾病过程中如何变化。
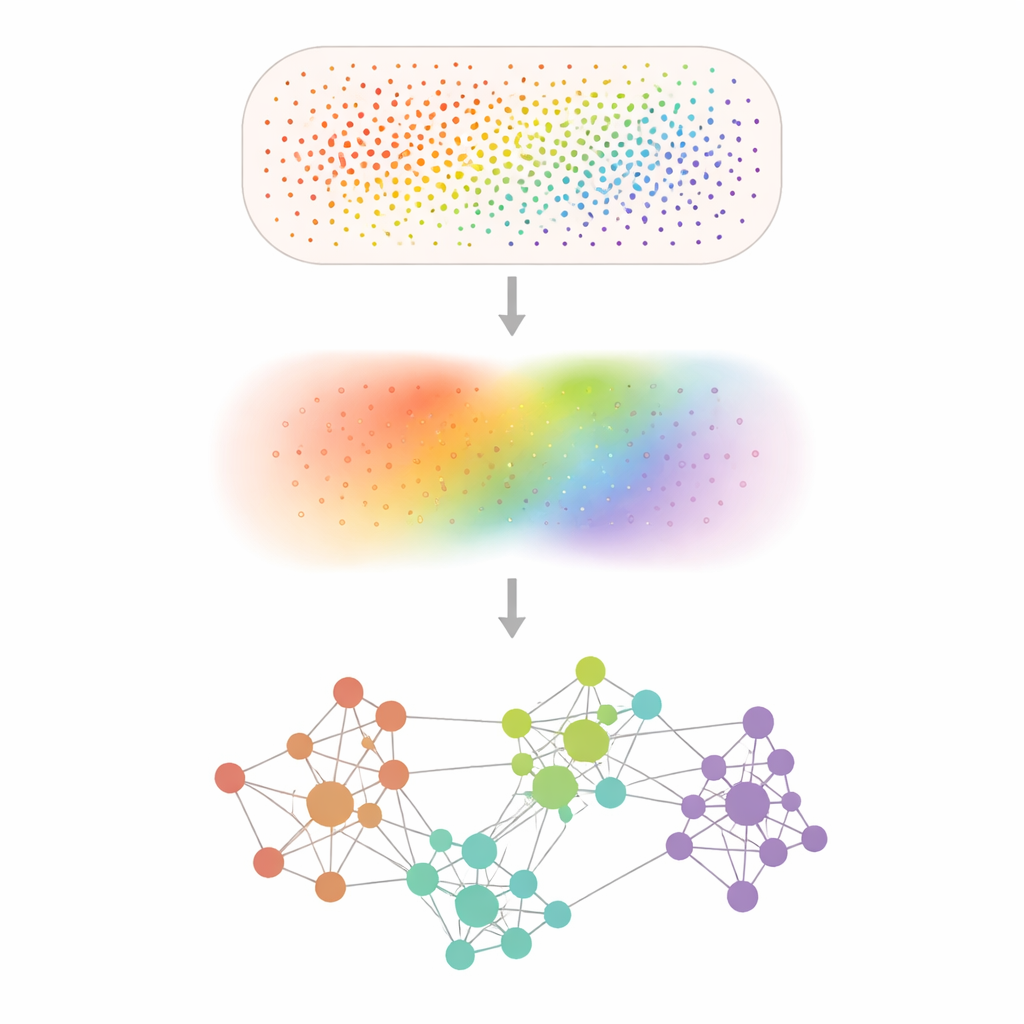
把嘈杂的点阵变为清晰的模式
空间转录组学实验在数万个到数亿个微小位置记录基因活性,但许多基因检测信号微弱,测量受到随机噪声点缀。Smoothie 通过温和地对数据进行数学“平滑”来应对这一问题,即将每个测量值与其邻域平均,就像对像素化照片应用柔焦滤镜。去噪之后,Smoothie 比较每一对基因,查看它们在组织中平滑后的模式是否同步升降。那些高度同步的基因对在网络中相互连接,网络内的聚类揭示了具有共同空间模式并很可能具有共同生物学功能的基因组。
解读大脑与胚胎的基因地图
作者首先在成人小鼠小脑的高分辨率基因活性图上测试了 Smoothie,小脑参与平衡与协调功能。Smoothie 发现了与已知细胞类型精确对应的不同基因群体,包括 Purkinje 神经元、颗粒细胞、少突胶质细胞和支持性细胞。通过与三种主流方法比较,团队显示 Smoothie 能发现更多的基因群、包含更多基因,并形成更紧密、更分明的簇,同时运行速度更快。关键在于,平滑步骤通过增强共享标记基因之间的相关性,使真实的生物学关系更容易被检测到。
发现隐藏的细胞类型与未知基因
接着,研究人员将 Smoothie 推向了高强度测试:一套来自胚胎中期小鼠、亚微米分辨率的大规模空间数据集。无需大量预处理,Smoothie 在约一小时内分析了超过1.75亿个空间点和2万多个基因。它揭示了数百个与器官、器官内亚区域以及肝脏、肾脏、大脑和皮肤中特化细胞类型对应的基因模块。由于能包含大量基因,Smoothie 还通过将诸多表征较差的基因归入含已知标记的模块,为这些基因分配了可能的功能。有趣的是,一些模块由在基因组上彼此相邻的基因组成,暗示局部 DNA 结构可能有助于塑造哪些基因在空间上共同被激活。
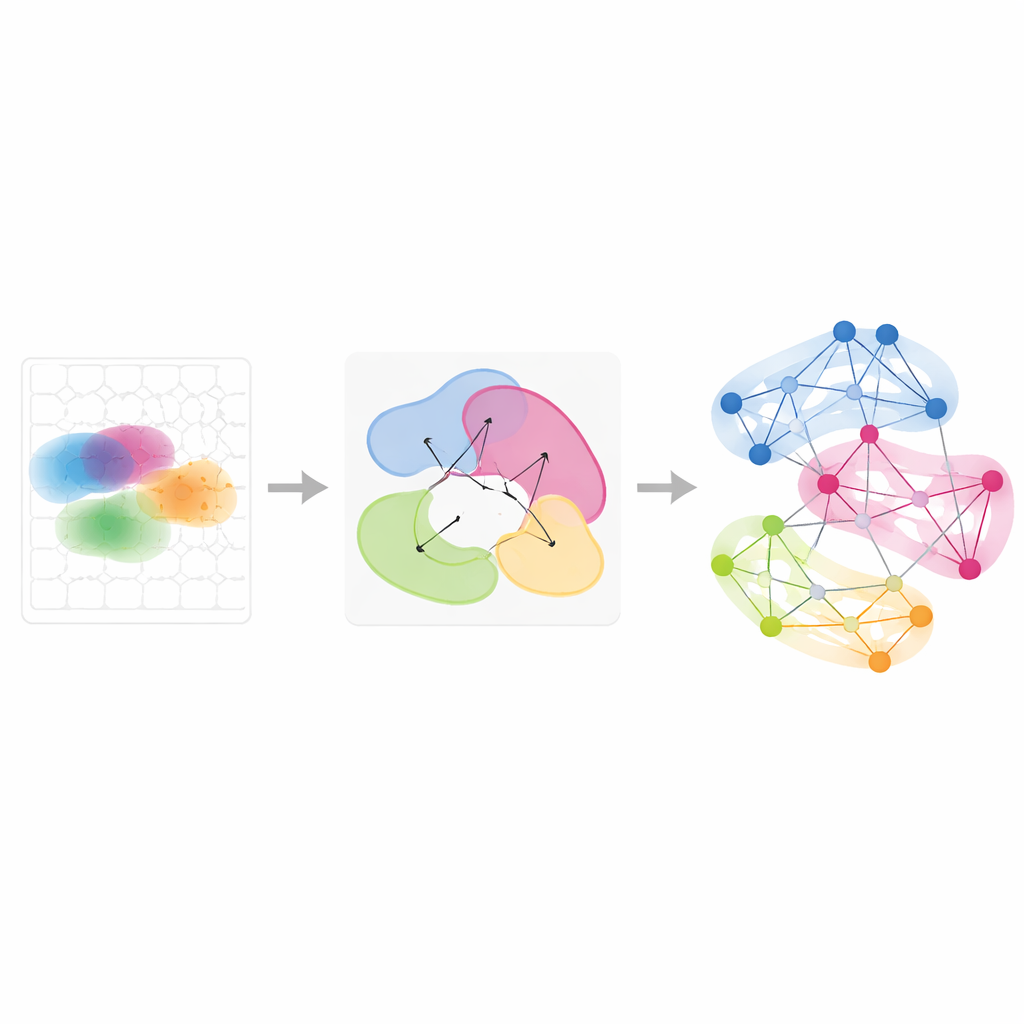
追踪基因程序随时间与条件的变化
超越单一组织,Smoothie 能整合多次空间实验以观察基因模式如何被共享或发生变化。作者将其应用于不同发育阶段的一系列小鼠胚胎,以及在激素诱导排卵过程中在八个时间点采样的卵巢。通过比较基因在不同样本中网络中伙伴的变化,Smoothie 将基因排序为稳定或动态。例如,这揭示了在发育过程中随红细胞迁移而从肝脏转移到血管的基因群,以及在促使排卵的卵巢支持细胞中按序开启的波动式基因程序。这些分析表明,与原始图像相比,基因网络提供了一种强有力的通用语言,用于对齐不匹配的组织与时间点。
为空间生物学提供一副新镜
从实用角度看,Smoothie 将庞大而嘈杂的空间基因图转化为清晰且可解释的网络,凸显基因在真实组织中在哪里以及如何协同工作。对非专家而言,核心信息是该方法大大简化了识别有意义模式、将未知基因关联到已知细胞类型以及追踪组织随时间或处理变化的过程。随着空间基因组学技术不断提高,像 Smoothie 这样的工具将有助于把数以百万计微小的分子测量转化为关于发育、健康与疾病的连贯故事。
引用: Holdener, C., De Vlaminck, I. Smoothie: efficient inference and integration of spatial co-expression networks from denoised spatial transcriptomics data. Commun Biol 9, 459 (2026). https://doi.org/10.1038/s42003-026-09898-z
关键词: 空间转录组学, 基因共表达网络, 组织结构, 发育生物学, 计算基因组学