Clear Sky Science · es
Smoothie: inferencia e integración eficientes de redes de coexpresión espacial a partir de datos de transcriptómica espacial desruidos
Ver los vecindarios celulares con nuevo detalle
Cada tejido del cuerpo es una ciudad bulliciosa de células, cada una activando y desactivando genes en lugares precisos. Las nuevas tecnologías de “transcriptómica espacial” pueden ahora leer qué genes están activos en casi cualquier punto de una lámina tisular, pero los datos sin procesar son extremadamente ruidosos e incompletos. Este artículo presenta Smoothie, un método computacional que limpia esas mediciones borrosas y revela grupos de genes que actúan juntos en el espacio, ayudando a los científicos a descifrar cómo se construyen los tejidos, cómo funcionan y cómo cambian con el tiempo o en la enfermedad.
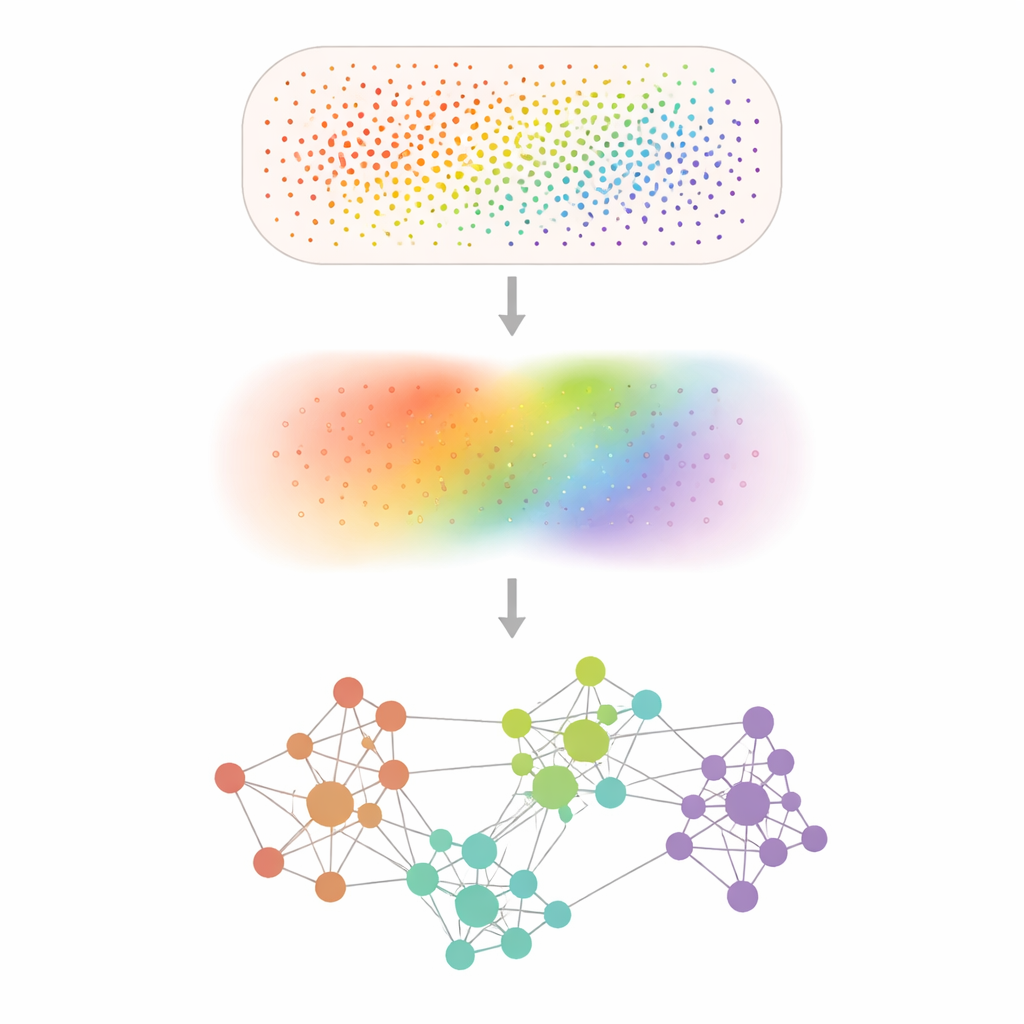
Convertir puntos ruidosos en patrones nítidos
Los experimentos de transcriptómica espacial registran la actividad génica en decenas de miles hasta cientos de millones de posiciones diminutas, pero muchos genes se detectan apenas y las mediciones están salpicadas por ruido aleatorio. Smoothie aborda esto suavizando los datos con un paso matemático de “lissage” que promedia cada medición con sus vecinas, de forma similar a aplicar un filtro de enfoque suave a una fotografía pixelada. Tras este desruido, Smoothie compara cada par de genes para ver dónde sus patrones suavizados suben y bajan juntos a lo largo del tejido. Los pares que están fuertemente sincronizados se conectan en una red, y los clústeres dentro de esa red revelan grupos de genes que comparten un patrón espacial común y, probablemente, una función biológica común.
Leer el mapa génico del cerebro y del embrión
Los autores probaron primero Smoothie en un mapa de alta resolución de la actividad génica en el cerebelo adulto de ratón, una región del cerebro implicada en el equilibrio y la coordinación. Smoothie descubrió grupos génicos distintos que coincidían claramente con tipos celulares conocidos, incluidos las neuronas de Purkinje, las células granulares, los oligodendrocitos y las células de soporte. Al comparar los resultados con tres métodos punteros, el equipo demostró que Smoothie encuentra más grupos génicos, incluye más genes en conjunto y forma clústeres más compactos y mejor separados, todo ello ejecutándose mucho más rápido. Crucialmente, el paso de suavizado hizo que las relaciones biológicas reales fuesen más fáciles de detectar al aumentar las correlaciones entre genes marcadores conocidos que comparten un tipo celular.
Descubrir tipos celulares ocultos y genes desconocidos
A continuación, los investigadores sometieron a Smoothie a una prueba exigente: un conjunto de datos espacial masivo de un embrión de ratón en gestación media medido a resolución submicrón. Sin recurrir a un preprocesamiento intensivo, Smoothie analizó más de 175 millones de puntos espaciales y más de 20 000 genes en aproximadamente una hora. Reveló cientos de módulos génicos que correspondían a órganos, subregiones dentro de órganos y tipos celulares especializados en el hígado, riñón, cerebro y piel. Debido a que se pudieron incluir tantos genes, Smoothie también asignó funciones probables a decenas de genes poco caracterizados al ubicarlos en módulos con marcadores conocidos. De forma intrigante, algunos módulos consistían en genes adyacentes en el genoma, lo que sugiere que la organización local del ADN contribuye a determinar qué genes se activan juntos en el espacio.
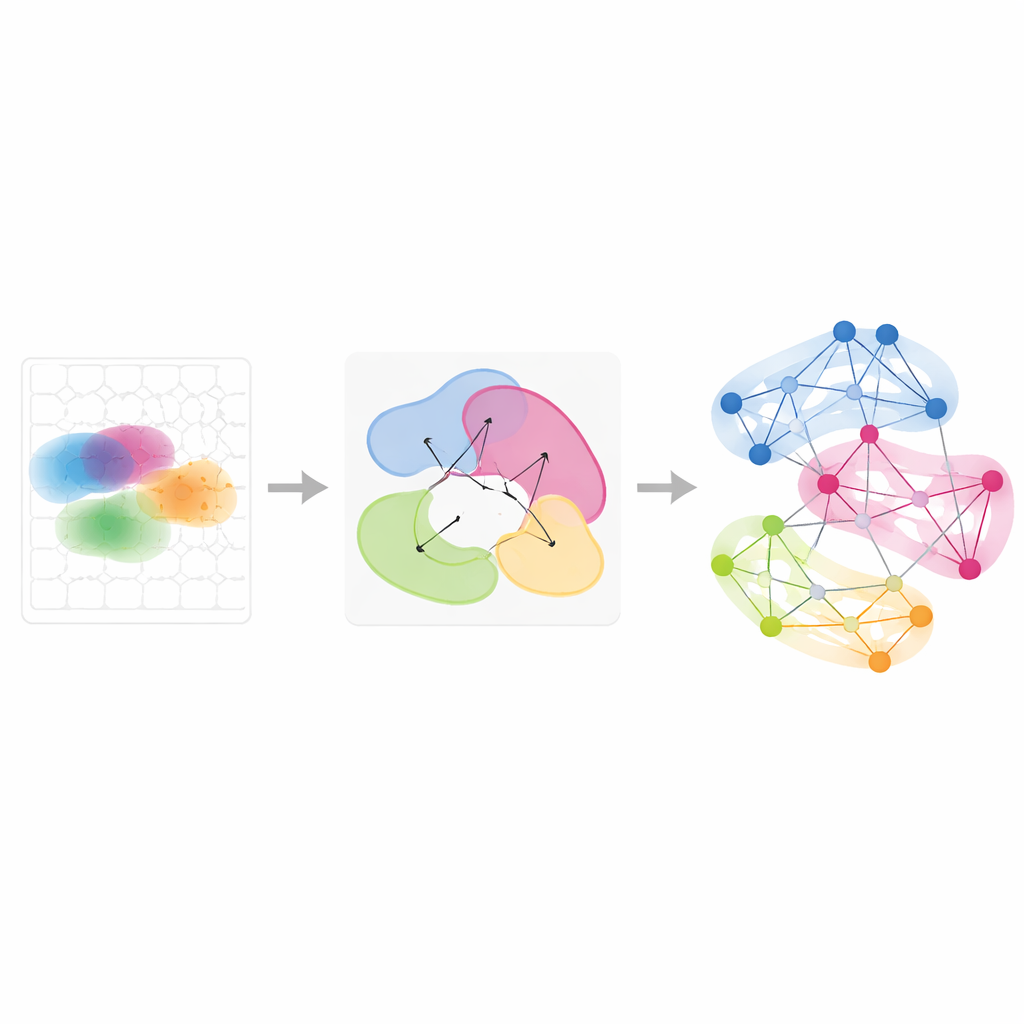
Seguir programas génicos a través del tiempo y las condiciones
Más allá de tejidos individuales, Smoothie puede integrar múltiples experimentos espaciales para ver cómo se comparten o cambian los patrones génicos. Los autores aplicaron esto a una serie de embriones de ratón de estadios de desarrollo ligeramente distintos y a ovarios muestreados en ocho puntos temporales durante la ovulación inducida por hormonas. Al comparar cómo cambian los socios de un gen en la red entre muestras, Smoothie clasifica a los genes como estables o dinámicos. Esto reveló, por ejemplo, grupos génicos que se desplazan del hígado a los vasos sanguíneos a medida que las células sanguíneas rojas migran durante el desarrollo, y programas génicos en forma de ondas en células de soporte ováricas que se activan en secuencia para impulsar la ovulación. Estos análisis muestran que las redes génicas, más que las imágenes crudas, proporcionan un lenguaje común potente para alinear tejidos y puntos temporales no coincidentes.
Una nueva lente para la biología espacial
En términos prácticos, Smoothie convierte vastos y ruidosos mapas espaciales de expresión génica en redes claras e interpretables que destacan dónde y cómo los genes actúan juntos en tejidos reales. Para no expertos, el mensaje clave es que este método facilita mucho identificar patrones significativos, conectar genes desconocidos con tipos celulares conocidos y seguir cómo los tejidos cambian con el tiempo o con tratamientos. A medida que las tecnologías de genómica espacial siguen afinándose, herramientas como Smoothie ayudarán a transformar millones de minúsculas mediciones moleculares en historias coherentes sobre el desarrollo, la salud y la enfermedad.
Cita: Holdener, C., De Vlaminck, I. Smoothie: efficient inference and integration of spatial co-expression networks from denoised spatial transcriptomics data. Commun Biol 9, 459 (2026). https://doi.org/10.1038/s42003-026-09898-z
Palabras clave: transcriptómica espacial, redes de coexpresión génica, arquitectura tisular, biología del desarrollo, genómica computacional