Clear Sky Science · nl
Smoothie: efficiënte inferentie en integratie van ruimtelijke co-expressienetwerken uit gedenoiseerde ruimtelijke transcriptomicsgegevens
Cellulaire buurten in nieuw detail zien
Elk weefsel in het lichaam is een bedrijvende stad van cellen, waarbij elk celtype genen op precieze plekken aan- en uitzet. Nieuwe "ruimtelijke transcriptomics"-technologieën kunnen nu aflezen welke genen actief zijn op bijna elk punt van een weefselsnit, maar de ruwe data zijn extreem lawaaierig en incompleet. Dit artikel introduceert Smoothie, een computationele methode die die vage metingen opschoont en genengroepen blootlegt die in de ruimte samen optreden, waarmee wetenschappers kunnen ontrafelen hoe weefsels worden opgebouwd, hoe ze functioneren en hoe ze veranderen in de tijd of bij ziekte.
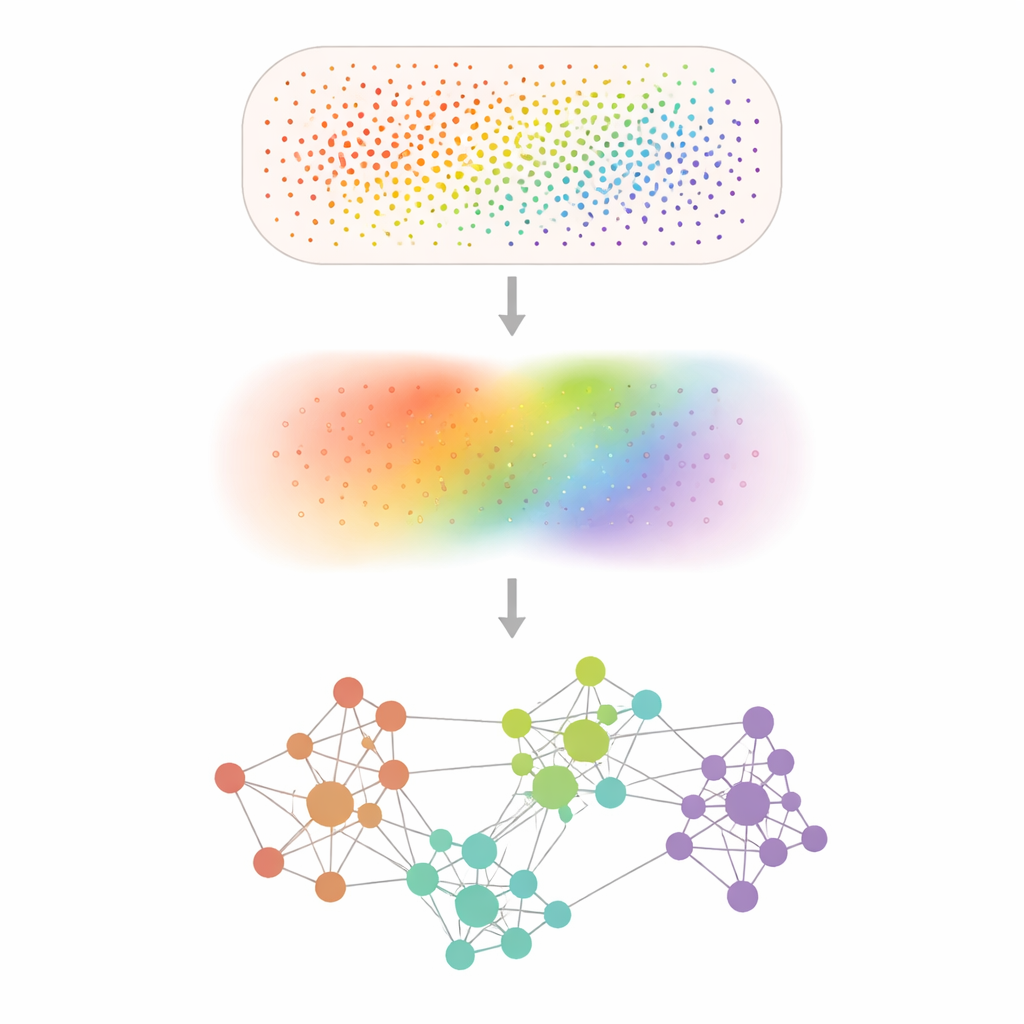
Van lawaaierige puntjes naar heldere patronen
Ruimtelijke transcriptomics-experimenten registreren genactiviteit op tienduizenden tot honderden miljoenen kleine posities, maar veel genen worden nauwelijks gedetecteerd en metingen zijn bezaaid met willekeurig ruis. Smoothie pakt dit aan door de data voorzichtig te vervagen met een wiskundige "smoothing"-stap die elke meting mediumt met zijn buren, vergelijkbaar met het toepassen van een zachte focusfilter op een gepixelde foto. Na deze denoising vergelijkt Smoothie elk genpaar om te zien waar hun gladgestreken patronen samen op- en neergaan door het weefsel. Paren die sterk synchroon lopen, worden verbonden in een netwerk, en clusters binnen dat netwerk onthullen genengroepen die een gemeenschappelijk ruimtelijk patroon en waarschijnlijk een gemeenschappelijke biologische functie delen.
De genkaart van hersenen en embryo lezen
De auteurs testten Smoothie eerst op een hoogresolutiemap van genactiviteit in de volwassen muiscerebellum, een hersendeel dat betrokken is bij balans en coördinatie. Smoothie ontdekte onderscheidende gengroepen die netjes overeenkwamen met bekende celtypen, waaronder Purkinje-neuronen, granulecellen, oligodendrocyten en ondersteunende cellen. Door de resultaten te vergelijken met drie toonaangevende methoden, toonde het team aan dat Smoothie meer gengroepen vindt, meer genen in totaal omvat en strakkere, beter gescheiden clusters vormt, en dat alles veel sneller werkt. Cruciaal was dat de smoothing-stap echte biologische relaties beter zichtbaar maakte door de correlaties te versterken tussen bekende markergenen die hetzelfde celtype delen.
Verborgen celtypen en onbekende genen ontdekken
Vervolgens stelden de onderzoekers Smoothie op de proef met een veeleisende dataset: een enorme ruimtelijke dataset van een muisembryo halverwege de draagtijd, gemeten op submicron-resolutie. Zonder te vervallen in zware preprocessing analyseerde Smoothie meer dan 175 miljoen ruimtelijke punten en meer dan 20.000 genen in ongeveer een uur. Het onthulde honderden genmodules die overeenkwamen met organen, subregio's binnen organen en gespecialiseerde celtypen in lever, nier, hersenen en huid. Omdat zoveel genen konden worden opgenomen, koppelde Smoothie ook waarschijnlijke functies aan tientallen slecht gekarakteriseerde genen door ze in modules met bekende markers te plaatsen. Intrigerend genoeg bestonden sommige modules uit genen die naast elkaar op het genoom liggen, wat suggereert dat lokale DNA-organisatie beïnvloedt welke genen samen in de ruimte actief zijn.
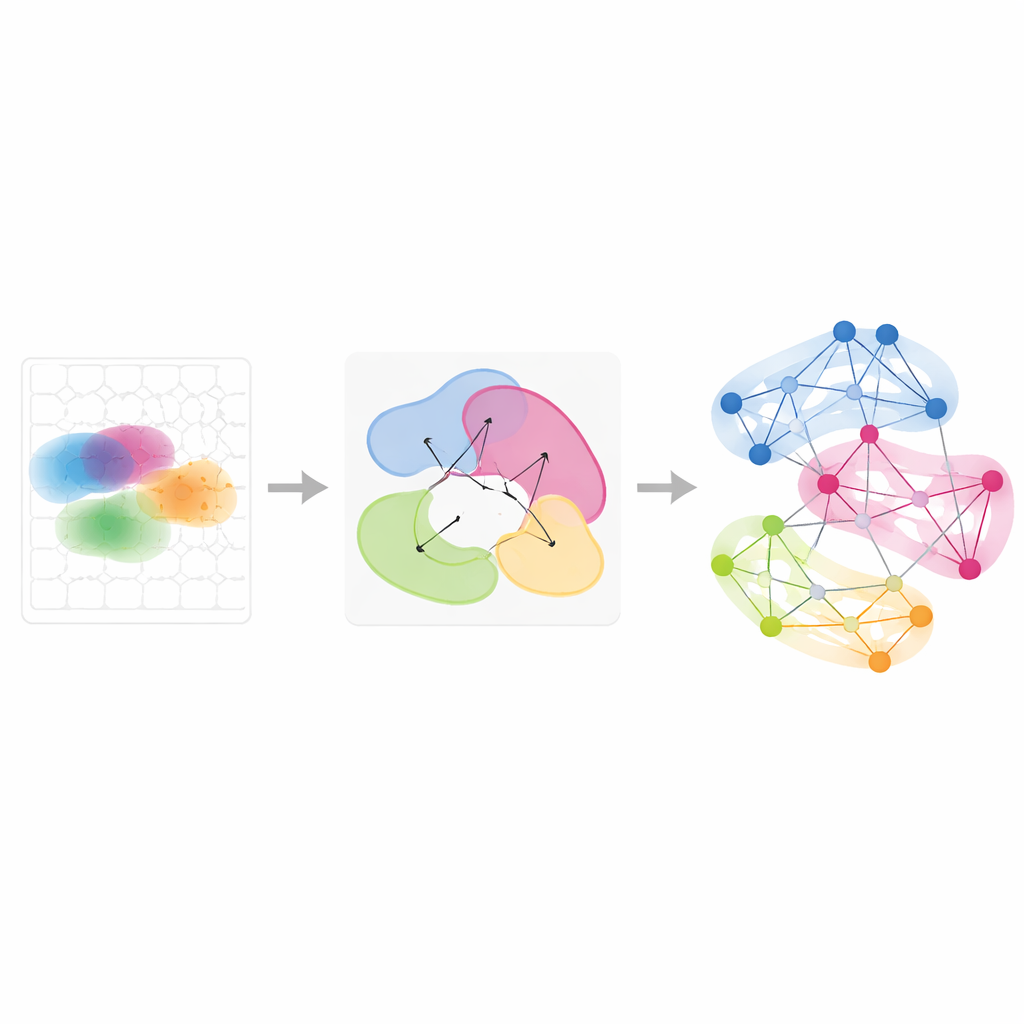
Genprogramma's volgen over tijd en condities
Buiten individuele weefsels kan Smoothie meerdere ruimtelijke experimenten integreren om te zien hoe genpatronen gedeeld worden of veranderen. De auteurs pasten dit toe op een reeks muisembryo's uit licht verschillende ontwikkelingsstadia en op eierstokken bemonsterd op acht tijdstippen tijdens hormoongeïnduceerde ovulatie. Door te vergelijken hoe de partners van een gen in het netwerk tussen monsters verschuiven, rangschikt Smoothie genen als stabiel of dynamisch. Dit onthulde bijvoorbeeld gengroepen die migreren van de lever naar bloedvaten terwijl rode bloedcellen zich tijdens de ontwikkeling verplaatsen, en golfachtige genprogramma's in ondersteunende cellen van de eierstok die sequentieel aanzetten om ovulatie te stimuleren. Deze analyses laten zien dat gen-netwerken, in plaats van ruwe beelden, een krachtig gemeenschappelijk vocabulaire bieden om niet-overeenkomende weefsels en tijdpunten op elkaar af te stemmen.
Een nieuwe lens voor ruimtelijke biologie
In praktische termen verandert Smoothie enorme, lawaaierige ruimtelijke genkaarten in heldere, interpreteerbare netwerken die benadrukken waar en hoe genen samenwerken in echte weefsels. Voor niet-experts is de kernboodschap dat deze methode het veel eenvoudiger maakt om betekenisvolle patronen te herkennen, onbekende genen te koppelen aan bekende celtypen en te volgen hoe weefsels veranderen over tijd of behandeling. Naarmate ruimtelijke genomica-technologieën blijven verscherpen, zullen tools als Smoothie helpen miljoenen kleine moleculaire metingen te transformeren tot coherente verhalen over ontwikkeling, gezondheid en ziekte.
Bronvermelding: Holdener, C., De Vlaminck, I. Smoothie: efficient inference and integration of spatial co-expression networks from denoised spatial transcriptomics data. Commun Biol 9, 459 (2026). https://doi.org/10.1038/s42003-026-09898-z
Trefwoorden: ruimtelijke transcriptomics, gen co-expressienetwerken, weefselarchitectuur, ontwikkelingsbiologie, computationale genomica