Clear Sky Science · pt
Smoothie: inferência e integração eficientes de redes de co‑expressão espacial a partir de dados de transcriptômica espacial desruídos
Vendo os Vizinhos Celulares com Novo Nível de Detalhe
Cada tecido do corpo é uma cidade movimentada de células, cada uma ligando e desligando genes em locais precisos. Novas tecnologias de “transcriptômica espacial” agora conseguem ler quais genes estão ativos em quase todos os pontos de uma lâmina de tecido, mas os dados brutos são extremamente ruidosos e incompletos. Este artigo apresenta o Smoothie, um método computacional que limpa essas medições borradas e revela grupos de genes que atuam juntos no espaço, ajudando cientistas a decodificar como tecidos são construídos, como funcionam e como mudam ao longo do tempo ou em doença.
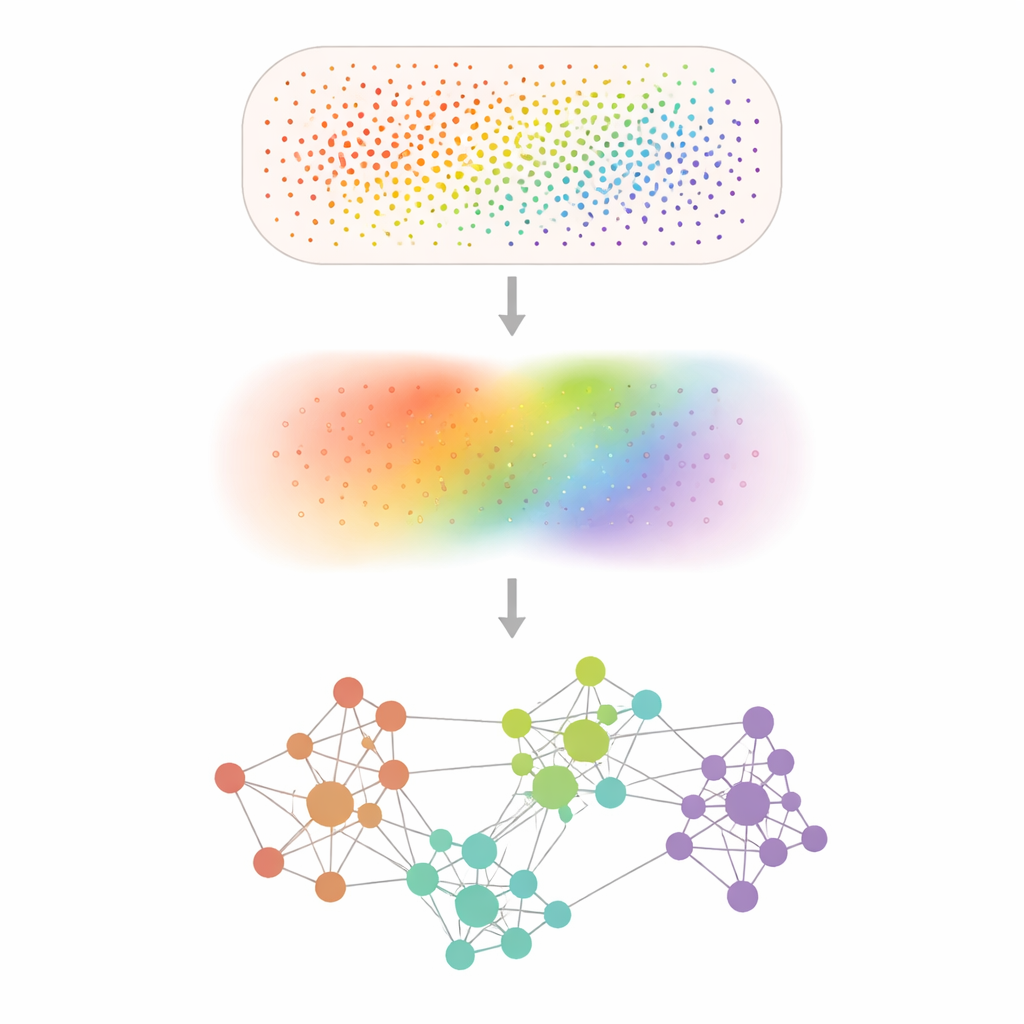
Transformando Pontos Ruidosos em Padrões Nítidos
Experimentos de transcriptômica espacial registram atividade gênica em dezenas de milhares a centenas de milhões de posições minúsculas, mas muitos genes são mal detectados e as medições são salpicadas por ruído aleatório. O Smoothie resolve isso ao suavizar os dados com um passo matemático que faz uma média de cada medição com seus vizinhos, semelhante a aplicar um filtro de foco suave em uma fotografia pixelada. Após essa redução de ruído, o Smoothie compara cada par de genes para ver onde seus padrões suavizados sobem e descem juntos pelo tecido. Pares fortemente sincronizados são conectados em uma rede, e os clusters nessa rede revelam grupos de genes que compartilham um padrão espacial comum e, provavelmente, um papel biológico comum.
Lendo o Mapa Gênico do Cérebro e do Embrião
Os autores primeiro testaram o Smoothie em um mapa de alta resolução da atividade gênica no cerebelo de camundongo adulto, uma parte do cérebro envolvida em equilíbrio e coordenação. O Smoothie identificou grupos gênicos distintos que corresponderam de forma precisa a tipos celulares conhecidos, incluindo neurônios de Purkinje, células granulares, oligodendrócitos e células de suporte. Ao comparar os resultados com três métodos de ponta, a equipe mostrou que o Smoothie encontra mais grupos gênicos, inclui mais genes no total e forma clusters mais compactos e melhor separados, tudo isso rodando muito mais rápido. Crucialmente, a etapa de suavização facilitou a detecção de relações biológicas reais ao aumentar as correlações entre genes marcadores conhecidos que compartilham um tipo celular.
Descobrindo Tipos Celulares Ocultos e Genes Desconhecidos
Em seguida, os pesquisadores submeteram o Smoothie a um teste exigente: um conjunto espacial massivo de dados de um embrião de camundongo em gestação média medido em resolução sub‑micrométrica. Sem recorrer a pré‑processamentos pesados, o Smoothie analisou mais de 175 milhões de pontos espaciais e mais de 20.000 genes em cerca de uma hora. Revelou centenas de módulos gênicos que correspondiam a órgãos, sub‑regiões dentro de órgãos e tipos celulares especializados no fígado, rim, cérebro e pele. Como tantos genes puderam ser incluídos, o Smoothie também atribuiu funções prováveis a dezenas de genes pouco caracterizados ao colocá‑los em módulos com marcadores conhecidos. De forma intrigante, alguns módulos consistiam de genes localizados lado a lado ao longo do genoma, sugerindo que a organização local do DNA ajuda a moldar quais genes são ativados conjuntamente no espaço.
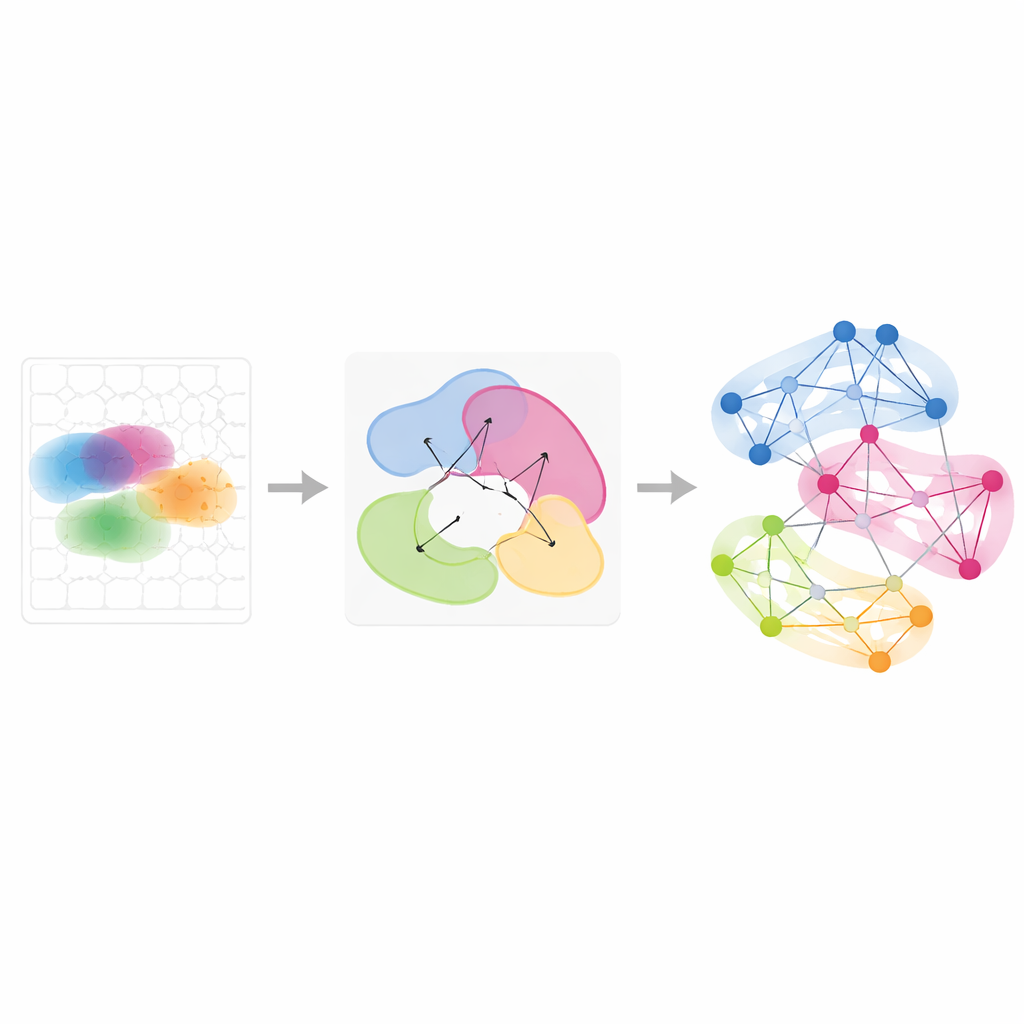
Acompanhando Programas Gênicos ao Longo do Tempo e Condições
Além de tecidos isolados, o Smoothie pode integrar múltiplos experimentos espaciais para ver como padrões gênicos são compartilhados ou mudam. Os autores aplicaram isso a uma série de embriões de camundongo em estágios de desenvolvimento ligeiramente diferentes e a ovários amostrados em oito pontos durante a ovulação induzida por hormônios. Ao comparar como os parceiros de um gene na rede mudam entre amostras, o Smoothie classifica genes como estáveis ou dinâmicos. Isso revelou, por exemplo, grupos gênicos que se deslocam do fígado para vasos sanguíneos à medida que glóbulos vermelhos migram durante o desenvolvimento, e programas gênicos em ondas em células de suporte ovarianas que se ativam em sequência para impulsionar a ovulação. Essas análises mostram que redes gênicas, mais do que imagens brutas, fornecem uma linguagem comum poderosa para alinhar tecidos e pontos temporais incompatíveis.
Uma Nova Lente para a Biologia Espacial
Em termos práticos, o Smoothie transforma vastos e ruidosos mapas espaciais de genes em redes claras e interpretáveis que destacam onde e como genes atuam juntos em tecidos reais. Para não especialistas, a mensagem chave é que esse método facilita muito identificar padrões significativos, conectar genes desconhecidos a tipos celulares conhecidos e acompanhar como tecidos mudam ao longo do tempo ou de tratamentos. À medida que as tecnologias de genômica espacial continuam a se aprimorar, ferramentas como o Smoothie ajudarão a transformar milhões de pequenas medições moleculares em histórias coerentes sobre desenvolvimento, saúde e doença.
Citação: Holdener, C., De Vlaminck, I. Smoothie: efficient inference and integration of spatial co-expression networks from denoised spatial transcriptomics data. Commun Biol 9, 459 (2026). https://doi.org/10.1038/s42003-026-09898-z
Palavras-chave: transcriptômica espacial, redes de co‑expressão gênica, arquitetura tecidual, biologia do desenvolvimento, genômica computacional