Clear Sky Science · pl
Smoothie: wydajne wnioskowanie i integrowanie przestrzennych sieci współekspresji na oczyszczonych danych transkryptomicznych
Widzieć sąsiedztwa komórkowe w nowym szczególe
Każda tkanka w ciele to tętniące życiem miasto komórek, z których każda włącza i wyłącza geny w precyzyjnych miejscach. Nowe technologie „transkryptomiki przestrzennej” potrafią teraz odczytać, które geny są aktywne niemal w każdym punkcie plastra tkanki, ale surowe dane są bardzo zaszumione i niekompletne. W artykule przedstawiono Smoothie — metodę obliczeniową, która oczyszcza te rozmyte pomiary i ujawnia grupy genów współdziałających przestrzennie, pomagając naukowcom odszyfrować, jak budowane są tkanki, jak funkcjonują i jak zmieniają się w czasie lub w chorobie.
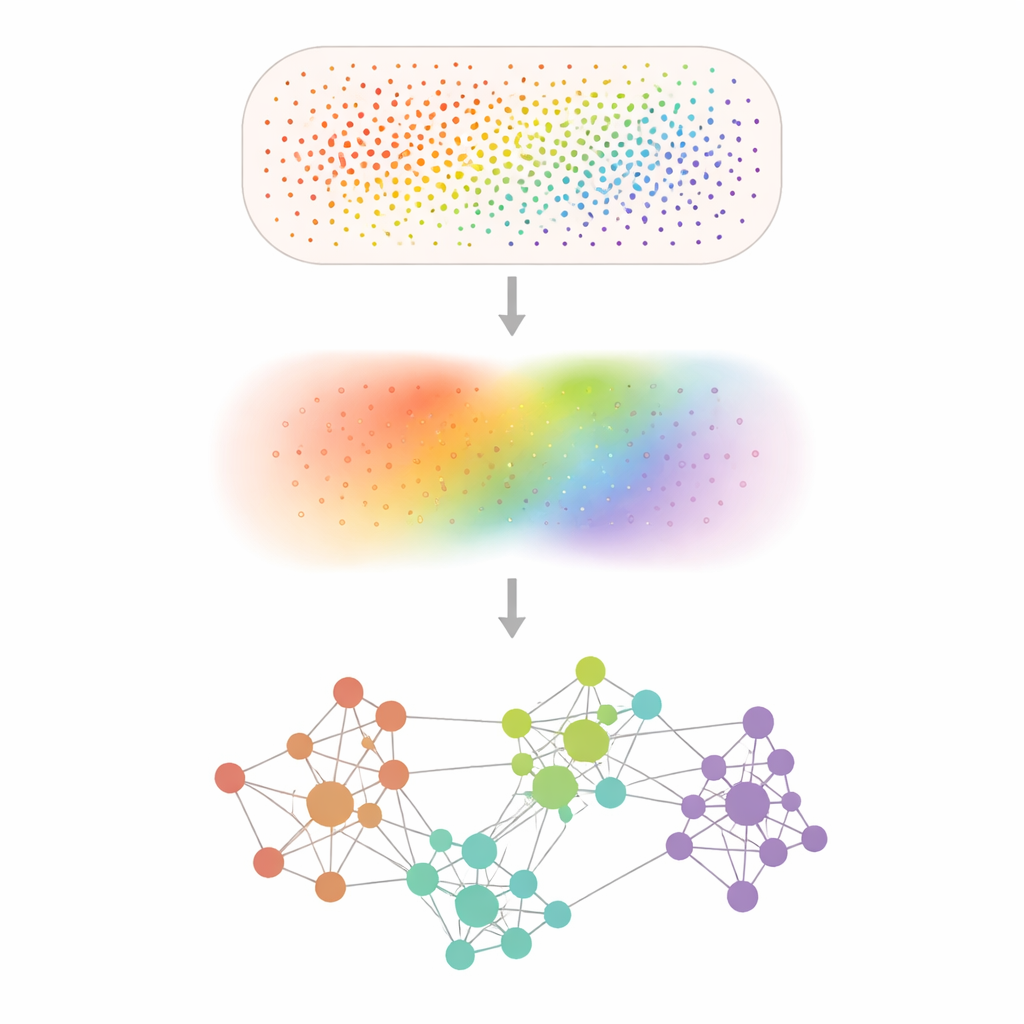
Przekształcanie zaszumionych punktów w czytelne wzory
Eksperymenty transkryptomiki przestrzennej rejestrują aktywność genów w dziesiątkach tysięcy do setek milionów drobnych pozycji, lecz wiele genów jest wykrywanych słabo, a pomiary zakłócone są przez losowy szum. Smoothie rozwiązuje ten problem poprzez delikatne wygładzenie danych za pomocą matematycznego kroku „smoothing”, który uśrednia każdy pomiar z jego sąsiadami — podobnie jak zastosowanie miękkiego filtra ostrości do pikselowanej fotografii. Po tym odszumieniu Smoothie porównuje każdą parę genów, by sprawdzić, gdzie ich wygładzone wzory rosną i maleją razem w tkance. Pary silnie zsynchronizowane są łączone w sieć, a klastry w tej sieci ujawniają grupy genów o wspólnym wzorze przestrzennym i prawdopodobnie wspólnej roli biologicznej.
Odczytywanie mapy genów mózgu i zarodka
Autorzy najpierw przetestowali Smoothie na mapie wysokiej rozdzielczości aktywności genów w dorosłym móżdżku myszy — części mózgu zaangażowanej w równowagę i koordynację. Smoothie odkrył odrębne grupy genów, które precyzyjnie odpowiadały znanym typom komórek, w tym komórkom Purkinjego, komórkom ziarnistym, oligodendrocytom i komórkom podporowym. Porównując wyniki z trzema wiodącymi metodami, zespół wykazał, że Smoothie znajduje więcej grup genów, obejmuje więcej genów łącznie i tworzy ciaśniejsze, lepiej rozdzielone klastry, a przy tym działa znacznie szybciej. Kluczowe znaczenie miało to, że etap wygładzania ułatwił wykrycie rzeczywistych zależności biologicznych poprzez wzmocnienie korelacji między znanymi markerami genowymi należącymi do tych samych typów komórek.
Odkrywanie ukrytych typów komórek i nieznanych genów
Następnie badacze wystawili Smoothie na trudny test: ogromny zestaw danych przestrzennych z zarodka myszy w połowie ciąży, zmierzony w rozdzielczości submikronowej. Bez uciekania się do silnego wstępnego przetwarzania, Smoothie przeanalizował ponad 175 milionów punktów przestrzennych i więcej niż 20 000 genów w około godzinę. Odkrył setki modułów genowych odpowiadających narządom, podregionom w obrębie narządów oraz wyspecjalizowanym typom komórek w wątrobie, nerkach, mózgu i skórze. Dzięki temu, że można było uwzględnić tak wiele genów, Smoothie przypisał prawdopodobne funkcje do dziesiątek słabo scharakteryzowanych genów, umieszczając je w modułach z znanymi markerami. Co ciekawe, niektóre moduły składały się z genów położonych obok siebie wzdłuż genomu, co sugeruje, że lokalna organizacja DNA pomaga kształtować, które geny są aktywne razem w przestrzeni.
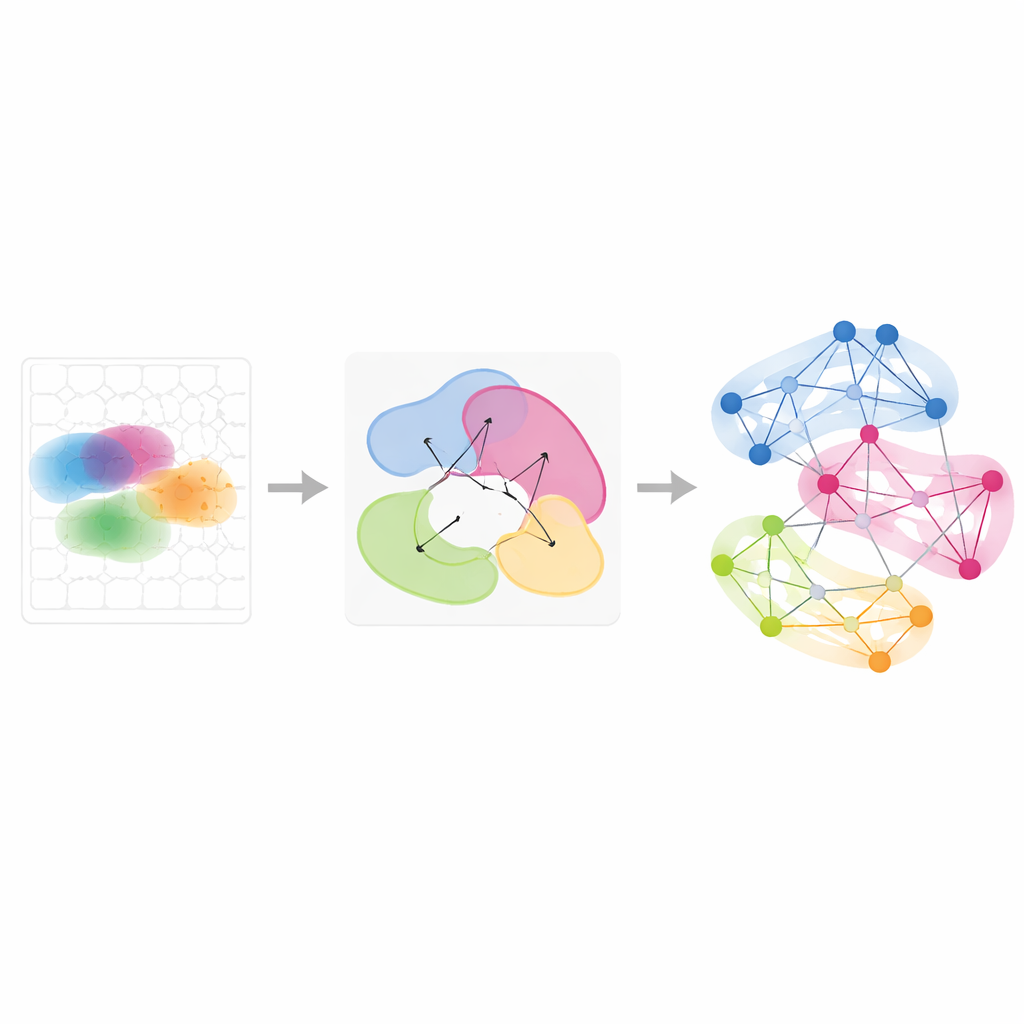
Śledzenie programów genowych w czasie i warunkach
Ponad pojedynczymi tkankami, Smoothie potrafi integrować wiele eksperymentów przestrzennych, by zobaczyć, jak wzory genowe są współdzielone lub się zmieniają. Autorzy zastosowali to do serii zarodków myszy z nieco różnych etapów rozwoju oraz do jajników pobranych w ośmiu punktach czasowych podczas owulacji indukowanej hormonami. Porównując, jak partnerzy genów w sieci zmieniają się między próbkami, Smoothie rankinguje geny jako stabilne lub dynamiczne. Wykazało to, na przykład, grupy genów przemieszczające się z wątroby do naczyń krwionośnych, gdy erytrocyty migrują podczas rozwoju, oraz falowe programy genowe w komórkach podporowych jajnika, które włączają się kolejno, aby napędzać owulację. Te analizy pokazują, że sieci genowe, a nie surowe obrazy, dostarczają potężnego wspólnego języka do wyrównywania niepasujących tkanek i punktów czasowych.
Nowa soczewka dla biologii przestrzennej
W praktycznym ujęciu Smoothie przekształca rozległe, zaszumione mapy genów przestrzennych w czytelne, interpretowalne sieci, które uwypuklają gdzie i jak geny współdziałają w rzeczywistych tkankach. Dla osób niebędących ekspertami kluczowy wniosek jest taki, że metoda ta znacznie ułatwia dostrzeganie istotnych wzorców, łączenie nieznanych genów z rozpoznanymi typami komórek oraz śledzenie, jak tkanki zmieniają się w czasie lub pod wpływem leczenia. W miarę jak technologie genomiki przestrzennej będą się dalej wyostrzać, narzędzia takie jak Smoothie pomogą przekształcić miliony drobnych pomiarów molekularnych w spójne opowieści o rozwoju, zdrowiu i chorobie.
Cytowanie: Holdener, C., De Vlaminck, I. Smoothie: efficient inference and integration of spatial co-expression networks from denoised spatial transcriptomics data. Commun Biol 9, 459 (2026). https://doi.org/10.1038/s42003-026-09898-z
Słowa kluczowe: transkryptomika przestrzenna, genowe sieci współekspresji, architektura tkanki, biologia rozwoju, genomika obliczeniowa