Clear Sky Science · it
Smoothie: inferenza e integrazione efficiente di reti di co‑espressione spaziale da dati di transcriptomica spaziale denoised
Osservare i quartieri cellulari con nuovi dettagli
Ogni tessuto del corpo è una città vivace di cellule, ognuna delle quali accende e spegne geni in posizioni precise. Le nuove tecnologie di “transcriptomica spaziale” possono ora leggere quali geni sono attivi in quasi ogni punto di un taglio di tessuto, ma i dati grezzi sono estremamente rumorosi e incompleti. Questo articolo presenta Smoothie, un metodo computazionale che ripulisce quelle misure sfocate e rivela gruppi di geni che agiscono insieme nello spazio, aiutando i ricercatori a decodificare come i tessuti sono costruiti, come funzionano e come cambiano nel tempo o durante le malattie.
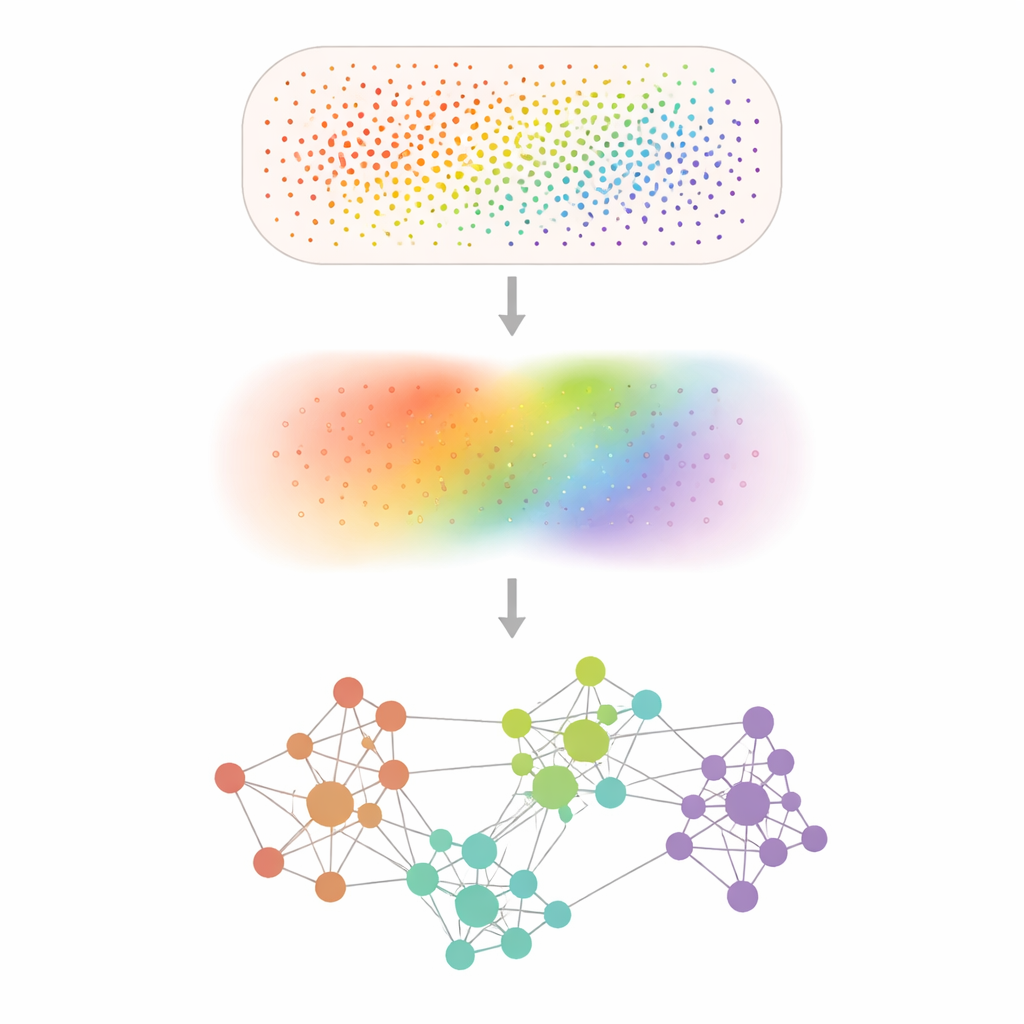
Trasformare punti rumorosi in schemi nitidi
Gli esperimenti di transcriptomica spaziale registrano l’attività genica in decine di migliaia fino a centinaia di milioni di posizioni minute, ma molti geni sono rilevati solo marginalmente e le misure sono puntellate da rumore casuale. Smoothie affronta questo problema sfocando delicatamente i dati con una fase matematica di “smoothing” che media ogni misura con i suoi vicini, un po’ come applicare un filtro soft‑focus a una fotografia pixelata. Dopo questo denoising, Smoothie confronta ogni coppia di geni per vedere dove i loro pattern levigati aumentano e diminuiscono insieme attraverso il tessuto. Le coppie fortemente sincronizzate sono connesse in una rete, e i cluster all’interno di questa rete rivelano gruppi di geni che condividono uno schema spaziale comune e probabilmente un ruolo biologico condiviso.
Leggere la mappa genica del cervello e dell’embrione
Gli autori hanno prima testato Smoothie su una mappa ad alta risoluzione dell’attività genica nel cervelletto adulto del topo, una parte del cervello coinvolta nell’equilibrio e nella coordinazione. Smoothie ha scoperto gruppi genici distinti che corrispondevano chiaramente a tipi cellulari noti, incluse le cellule di Purkinje, le cellule granulari, gli oligodendrociti e le cellule di supporto. Confrontando i risultati con tre metodi di punta, il gruppo ha mostrato che Smoothie trova più gruppi genici, include un maggior numero di geni complessivamente e forma cluster più compatti e meglio separati, il tutto con tempi di esecuzione molto più rapidi. Crucialmente, la fase di smoothing ha reso più facili da rilevare relazioni biologiche reali aumentandone le correlazioni tra geni marker noti che condividono un tipo cellulare.
Scoprire tipi cellulari nascosti e geni non annotati
Successivamente i ricercatori hanno messo Smoothie a una prova impegnativa: un enorme dataset spaziale da un embrione di topo a metà gestazione misurato a risoluzione sub‑micron. Senza ricorrere a preprocessamenti pesanti, Smoothie ha analizzato oltre 175 milioni di punti spaziali e più di 20.000 geni in circa un’ora. Ha rivelato centinaia di moduli genici corrispondenti a organi, sotto‑regioni all’interno degli organi e tipi cellulari specializzati nel fegato, nel rene, nel cervello e nella pelle. Poiché è stato possibile includere un gran numero di geni, Smoothie ha anche assegnato probabili funzioni a dozzine di geni scarsamente caratterizzati collocandoli in moduli con marker noti. In modo intrigante, alcuni moduli erano composti da geni adiacenti sul genoma, suggerendo che l’organizzazione locale del DNA contribuisca a determinare quali geni siano attivi insieme nello spazio.
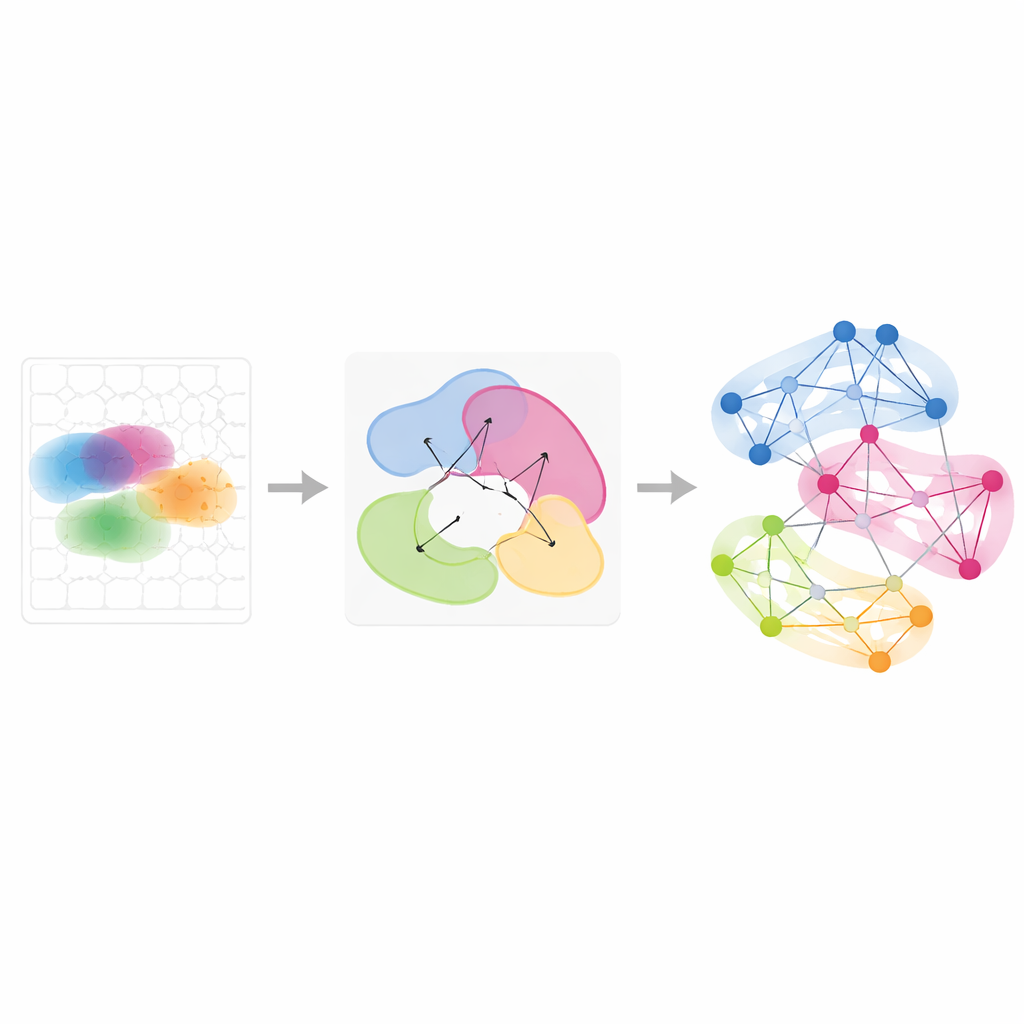
Seguire i programmi genici nel tempo e tra condizioni
Oltre ai singoli tessuti, Smoothie può integrare più esperimenti spaziali per vedere come i pattern genici vengano condivisi o modificati. Gli autori hanno applicato questo approccio a una serie di embrioni di topo di stadi di sviluppo leggermente diversi e a ovaie campionate in otto punti temporali durante l’ovulazione indotta da ormoni. Confrontando come i partner di un gene nella rete cambiano tra i campioni, Smoothie classifica i geni come stabili o dinamici. Questo ha rivelato, per esempio, gruppi genici che si spostano dal fegato ai vasi sanguigni mentre i globuli rossi migrano durante lo sviluppo, e programmi genici ondulatori nelle cellule di supporto ovariche che si accendono in sequenza per guidare l’ovulazione. Queste analisi mostrano che le reti geniche, più che le immagini grezze, forniscono un linguaggio comune potente per allineare tessuti e punti temporali non corrispondenti.
Una nuova lente per la biologia spaziale
In termini pratici, Smoothie trasforma vaste e rumorose mappe spaziali geniche in reti chiare e interpretabili che evidenziano dove e come i geni lavorano insieme nei tessuti reali. Per i non esperti, il messaggio chiave è che questo metodo rende molto più semplice individuare pattern significativi, collegare geni sconosciuti a tipi cellulari noti e tracciare come i tessuti cambiano nel tempo o a seguito di trattamenti. Man mano che le tecnologie di genomica spaziale diventano sempre più precise, strumenti come Smoothie aiuteranno a trasformare milioni di piccole misurazioni molecolari in narrazioni coerenti sullo sviluppo, la salute e la malattia.
Citazione: Holdener, C., De Vlaminck, I. Smoothie: efficient inference and integration of spatial co-expression networks from denoised spatial transcriptomics data. Commun Biol 9, 459 (2026). https://doi.org/10.1038/s42003-026-09898-z
Parole chiave: transcriptomica spaziale, reti di co‑espressione genica, architettura dei tessuti, biologia dello sviluppo, genomica computazionale