Clear Sky Science · sv
Maskin- och djupinlärning avslöjar sekvensbestämningar som kodar för bivalenta histonmodifieringar
Hur DNAs skiljetecken formar en cells framtid
Varje cell i din kropp bär i stort sett samma DNA, ändå beter sig nervceller och muskelceller helt olika. En orsak är att kemiska etiketter på DNA-packande proteiner kan slå på eller av gener utan att ändra den genetiska koden. I denna studie ställs en förvånansvärt enkel fråga med stora följder: finns det dolda mönster i DNAs sekvens som talar om för cellen var den ska placera en speciell typ av "blandad" etikett som håller viktiga gener i ett tillstånd mellan tystnad och aktivitet?
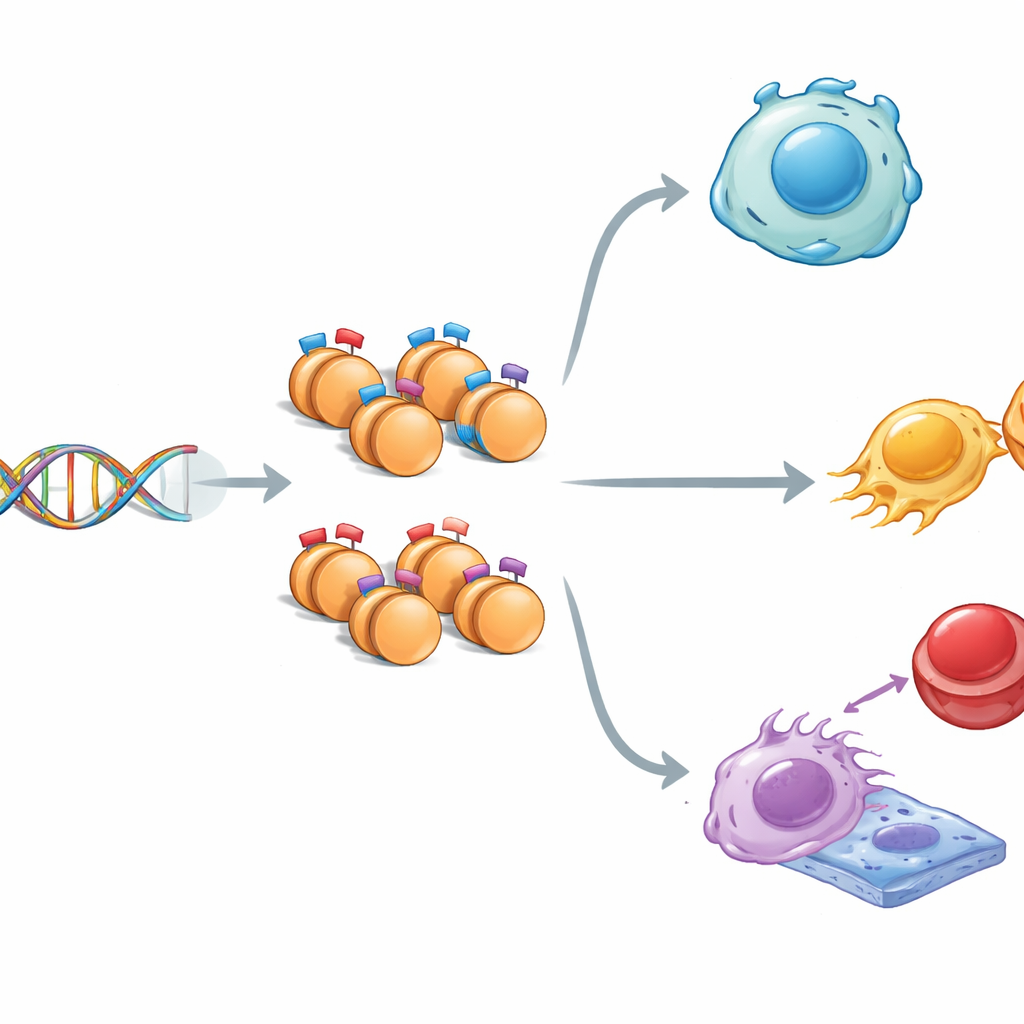
En berättelse om två motsatta etiketter
Inne i kärnan är DNA lindat runt proteinspolar som kallas histoner. Dessa histoner kan bära signaler som antingen uppmuntrar genaktivitet ("kör") eller hämmar den ("stopp"). Ibland sitter båda typerna av signaler tillsammans på samma ställe och skapar det forskare kallar ett "bivalent" tillstånd—gener hålls i ett berett men avvaktande läge. Med hjälp av musens embryonala stamceller, som kan bli nästan vilken vävnad som helst, kartlade forskarna tre viktiga histonmarkörer över genomet. De fann att regioner med blandade markörer skiljde sig från regioner med enstaka markörer: de var något smalare, rikare på DNA-bokstäverna G och C, och mer starkt bevarade genom evolutionen, vilket antyder att dessa beredda DNA-avsnitt är särskilt viktiga och noggrant skyddade.
Beredda brytare för utveckling och sjukdom
När teamet kopplade dessa markerade regioner till närliggande gener framträdde ett mönster. Gener märkta med blandade histonsignaler tenderade att vara måttligt aktiva och var starkt involverade i tidig utveckling och i beslutet för stamceller att förbli flexibla eller specialisera sig. Vägledningar som Hippo, MAPK, Wnt och TGF-beta—centrala kommunikationskretsar för tillväxt och vävnadsbildning—var väl representerade. Vissa bivalenta gener har också kopplats till cancer, vilket antyder att samma beredda kontrollsystem som styr normal utveckling kan kapras vid sjukdom. Sammantaget verkar de blandade markeringarna fungera som fint ställda dimrar, som ger gener en diskret grundaktivitet samtidigt som de håller dem redo att öka eller stängas av när signaler kommer.
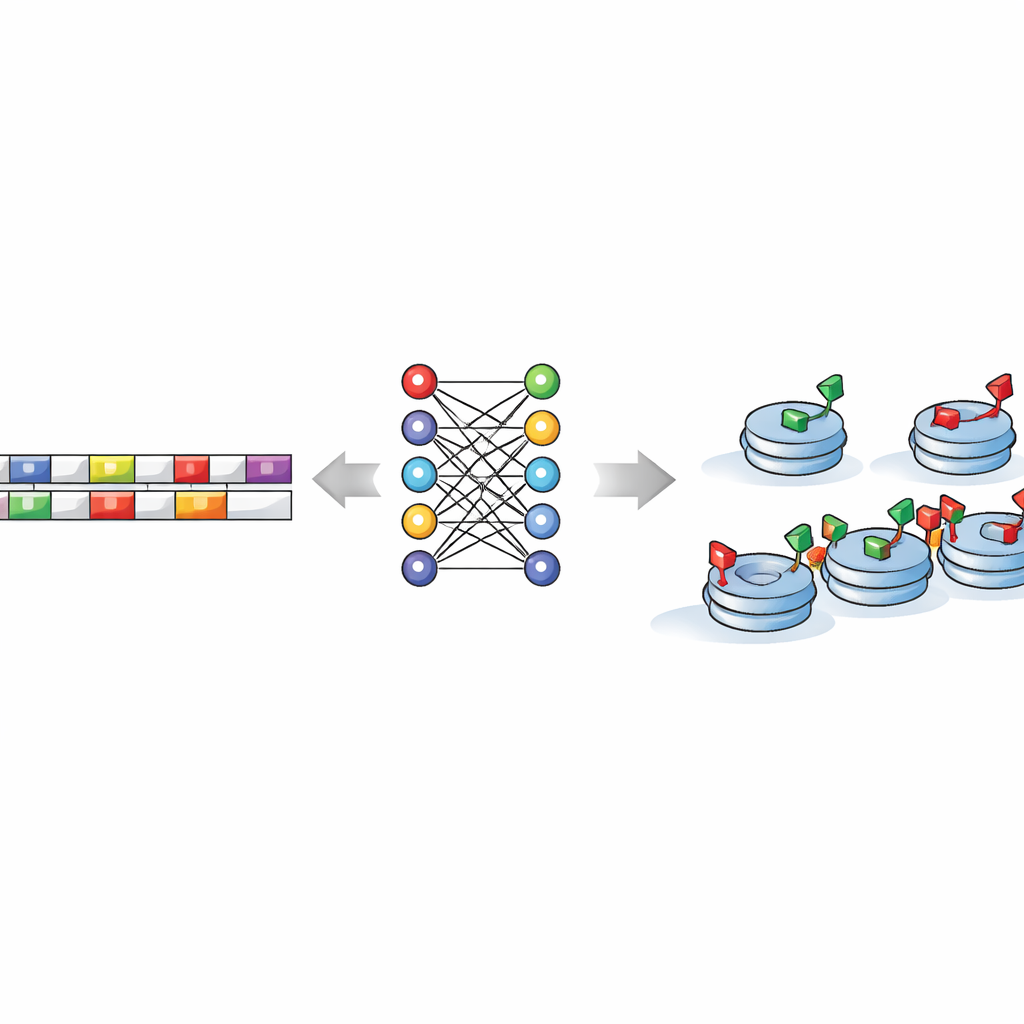
Att lära maskiner läsa dolda DNA-mönster
Kärnan i studien är frågan om DNA-sekvensen i sig kodar instruktioner för var dessa beredda tillstånd bör bildas. För att testa detta matade forskarna in korta DNA-avsnitt—uppdelade i alla möjliga små "ord" av några bokstäver—i en uppsättning maskin- och djupinlärningsmodeller. Dessa algoritmer lärde sig att skilja regioner med blandade markörer från dem med endast aktiverande eller endast repressiva markörer, ofta med hög noggrannhet. Avgörande var att när DNA-bokstäverna slumpades om misslyckades modellerna, vilket visar att det verkliga genomet bär autentiska prediktiva signaler snarare än slumpmässigt brus. Det innebär att en dator, utan experimentella mätningar, utifrån själva DNA-texten kan gissa var cellen sannolikt kommer att placera dessa blandade histonmarkörer.
Sekvensmotif som molekylära vägskyltar
Genom att granska modellerna upptäckte författarna ett fåtal korta DNA-motif—återkommande bokstavsmönster—som var särskilt informativa. Vissa, som sekvenser som liknar TCTGAA och TCACAG, matchade kända bindningsställen för centrala stamcellsregulatorer som OCT4, SOX2, ESRRB och en faktor kallad TCFCP2l1. Andra tenderade att klustra nära kanterna av bivalenta regioner, vilket antyder att vissa motif kan hjälpa till att sätta gränserna för dessa beredda kromatinzoner. Olika kombinationer och placeringar av motif särskilde en typ av blandad markering från en annan, vilket antyder att varje klass av bivalens följer sin egen "grammatik" av sekvensregler samtidigt som många av samma reglerande proteiner delas.
Vad detta betyder för stamceller och vidare
Enkelt uttryckt visar studien att DNA inte bara är en lista över gener; det bär också inbäddade instruktioner om hur tätt dessa gener ska paketeras och hur redo de är att reagera. I embryonala stamceller hjälper specifika korta DNA-mönster till att rekrytera proteinfaktorer och forma regioner där motsatta histonmarkörer samexisterar, vilket håller utvecklingsgener balanserade på en knivsegg mellan på och av. Genom att använda maskin- och djupinlärning för att läsa denna dolda kod ger författarna både ett praktiskt verktyg för att förutsäga epigenetiska tillstånd från sekvens och en klarare bild av hur celler programmerar flexibilitet i sina genom under tidigt liv—och hur den programmeringen kan gå fel vid sjukdom.
Citering: Zhao, X., Wu, J., Che, Y. et al. Machine and Deep Learning Reveal Sequence Determinants Encoding Bivalent Histone Modifications. Commun Biol 9, 491 (2026). https://doi.org/10.1038/s42003-026-09962-8
Nyckelord: bivalent kromatin, histonmodifieringar, embryonala stamceller, DNA-sekvensmotif, maskininlärning inom genomik