Clear Sky Science · sv
Genomsekvensmontering av 5S rDNA-lokuserna ger insikt i haplotypspecificitet och evolution hos större andmat Spirodela polyrhiza
Varför små flytande växter spelar roll
Större andmat är en liten vattenväxt som sprider sig snabbt över dammar och kanaler, men i dess celler ligger ett förvånansvärt förenklat genom. Denna studie dyker ned i en av de mest gåtfulla delarna av det genomet: de DNA‑sträckor som bygger upp maskineriet för proteinsyntes, cellens ribosomer. Genom att fullständigt avkoda dessa svårlästa regioner i andmat visar författarna hur nödvändiga gener är organiserade och finjusterade, vilket ger ledtrådar till hur växtgenom utvecklas och hur celler kontrollerar ett av sina mest grundläggande livsuppehållande system.
Byggstenar i cellens proteinfabriker
Ribosomerna, de molekylära maskiner som sätter ihop proteiner, är uppbyggda av både proteiner och specialiserade RNA‑molekyler. Några av dessa RNA kodas av det så kallade 5S ribosomala DNA (5S rDNA), som normalt förekommer i hundratals eller tusentals upprepade kopior i växtgenom. Eftersom dessa upprepningar är långa och nästan identiska är de ökända för att vara svåra att montera med standardsekvensering. I större andmat (Spirodela polyrhiza) visade tidigare arbete dock att antalet 5S‑kopior är ovanligt lågt, vilket gör denna växt till en idealisk modell för att slutligen kartlägga en hel 5S rDNA‑region från början till slut och se hur kopiorna är ordnade på kromosomerna.
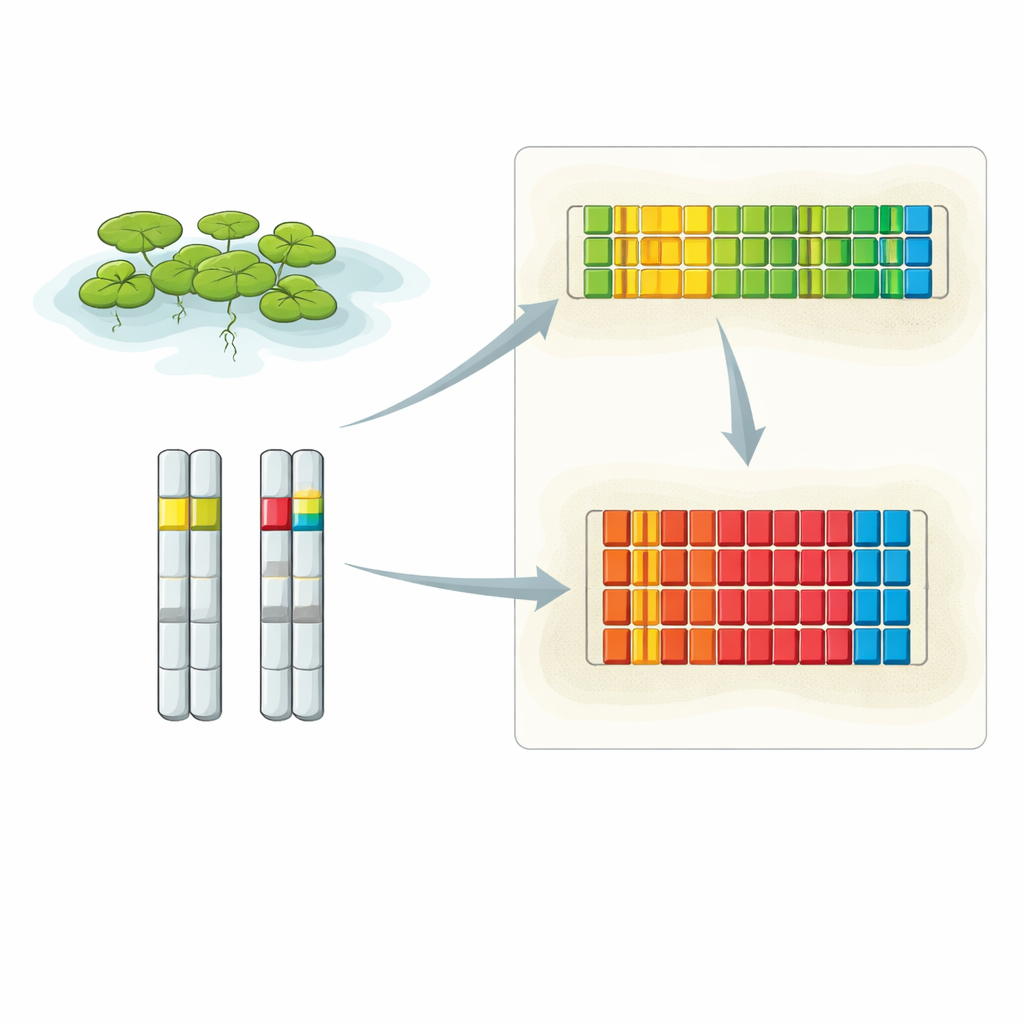
Zooma in på två centrala DNA‑områden
Forskarna kombinerade flera avancerade tekniker för att avslöja hela utformningen av andmatens 5S rDNA. De använde extra långa DNA‑läsningar från Oxford Nanopore‑sekvensering, konventionell högprecisionssekvensering av klonade fragment och högupplöst fluorescens in situ‑hybridisering (FISH), som lyser upp specifika DNA‑sträckor i intakta cellkärnor. Deras analyser visade att 5S rDNA är koncentrerat till två huvudplatser, vardera på en annan kromosom. Ett locus ligger på kromosom 6 och innehåller en serie korta upprepningsenheter, medan det andra ligger på kromosom 13 och är byggt av längre repetitiva enheter. FISH‑bilder visade att signalstyrkan från dessa lokuser skiljer sig mellan kromosomparens kopior i varje cell, vilket antyder att en homolog kan bära märkbart fler 5S‑upprepningar än den andra.
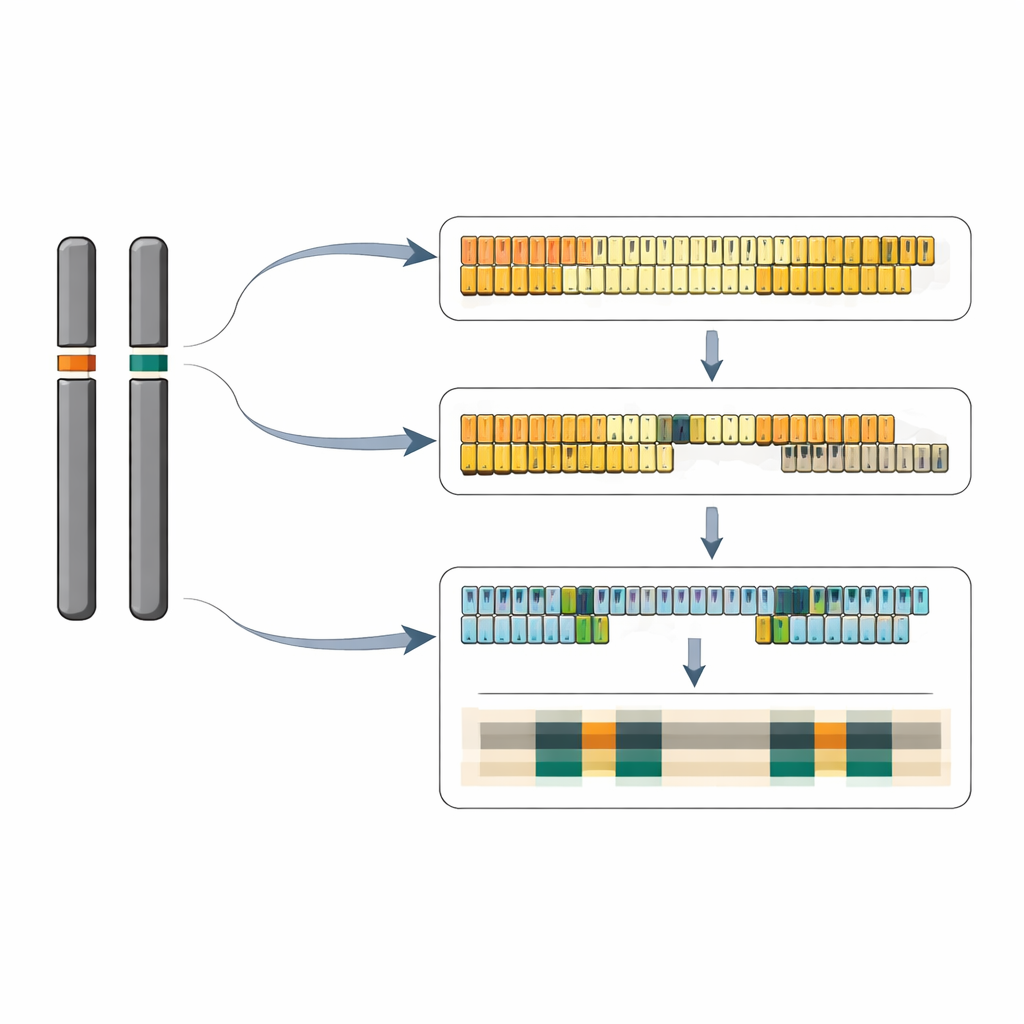
Ojämlika upprepningar och speglade kluster
Genom att noggrant sy ihop långa sekvenseringsläsningar monterade teamet nästan kompletta DNA‑sekvenser för båda lokuserna. På en version av kromosom 6 rekonstruerade de ett kontinuerligt stycke med 40 5S‑upprepningsenheter; partnerkromosomen bär mer än 65 enheter av samma korta typ. På kromosom 13 spårade de ett mer komplext landskap: ett stort kluster av minst 64 långa upprepningar och ett mindre kluster med två upprepningar placerade i motsatt orientering, separerade av över 12 000 baspar av ordinärt kromosomalt DNA. Inom det långrepetitiva lokuset bär vissa enheter en liten insättning på 13 baser i spacern mellan generna, och dessa något olika enheter tenderar att gruppera sig i underkluster. Sammantaget står de två lokuserna tillsammans för ungefär 320–390 5S‑genkopior per diploid genom, i linje med oberoende uppskattningar av kopioantalet.
DNA‑kemi och reglerspakar
När författarna undersökte den kemiska sammansättningen av dessa regioner framträdde ett slående mönster. Själva 5S‑upprepningsarrayerna är ovanligt rika på baserna G och C, medan de omgivande kromosomsegmenten runt dem är starkt förmånligt för A och T. Dessa AT‑rika randzoner liknar DNA‑element som är associerade med replikationsorigin och öppet, aktivt kromatin i andra organismer, och liknande motiv förekommer spridda över alla 20 andmatskromosomer. På den finare skalan av individuella upprepningsenheter identifierade teamet små men konsekventa skillnader i korta kontrollsekvenser uppströms och nedströms om 5S‑genen, inklusive variationer i TATA‑lika motiv och sträckor av GA‑upprepningar. Dessa är i andra arter kända för att interagera med generella transkriptionsfaktorer och GAGA‑bindande proteiner, vilket tyder på att varje locus kan vara finjusterat på olika sätt även om den 5S‑RNA de producerar är identisk.
Vad detta betyder för växtgenom
Sammantaget levererar arbetet den första kompletta, nukleotidnivåvyn av ett växtligt 5S rDNA‑system och visar hur upprepningsantal, sekvensvarianter och den omgivande kromosomala kontexten samverkar i ett kompakt genom. Större andmat tycks ha gjort sig av med många överflödiga ribosomgenkopior jämfört med andra blomväxter, samtidigt som den upprätthåller två distinkta, sannolikt aktiva 5S‑lokuser med noggrant organiserade kluster av genvarianter. Författarna föreslår att båda lokuserna kan bidra till 5S‑RNA‑produktionen beroende på förhållanden, och att subtila skillnader i närliggande DNA och spacersekvenser hjälper till att reglera när och hur starkt varje kluster används. Bortom andmat erbjuder studien en modell för hur man avkodar liknande repetitiva regioner i andra arter och fördjupar vår förståelse av hur viktiga genfamiljer formas under evolutionen.
Citering: Stepanenko, A., Schubert, V., Chen, G. et al. Genome sequence assembly of the 5S rDNA loci informs haplotype specificity and evolution in the greater duckweed Spirodela polyrhiza. Commun Biol 9, 516 (2026). https://doi.org/10.1038/s42003-026-09598-8
Nyckelord: ribosomalt DNA, andmatsgenom, växtgenetik, repetitivt DNA, genomevolution