Clear Sky Science · pt
Montagem da sequência do genoma dos loci 5S rDNA esclarece especificidade de haplótipos e evolução na lentilha-d’água maior Spirodela polyrhiza
Por que plantas flutuantes minúsculas são importantes
A lentilha-d’água maior é uma planta aquática pequena que se espalha rapidamente por lagoas e canais, mas dentro de suas células repousa um genoma surpreendentemente enxuto. Este estudo investiga uma das regiões mais enigmáticas desse genoma: os trechos de DNA que codificam a maquinaria central para fabricar proteínas, os ribossomos da célula. Ao decodificar completamente essas regiões de difícil leitura na lentilha-d’água, os autores mostram como genes essenciais são organizados e afinados, oferecendo pistas sobre como genomas de plantas evoluem e como as células controlam um dos seus sistemas de suporte à vida mais básicos.
Blocos de construção das fábricas de proteína da célula
Os ribossomos, as máquinas moleculares que montam proteínas, são formados por proteínas e por moléculas de RNA especiais. Alguns desses RNAs são codificados pelo chamado DNA ribossômico 5S (5S rDNA), que normalmente aparece em centenas ou milhares de cópias repetidas nos genomas de plantas. Porque essas repetições são longas e quase idênticas, elas são notoriamente difíceis de montar com o sequenciamento de DNA padrão. Na lentilha-d’água maior (Spirodela polyrhiza), entretanto, trabalhos anteriores mostraram que o número de cópias 5S é incomumente baixo, tornando essa planta um modelo ideal para finalmente mapear uma região completa de 5S rDNA de ponta a ponta e ver como suas cópias estão dispostas nos cromossomos.
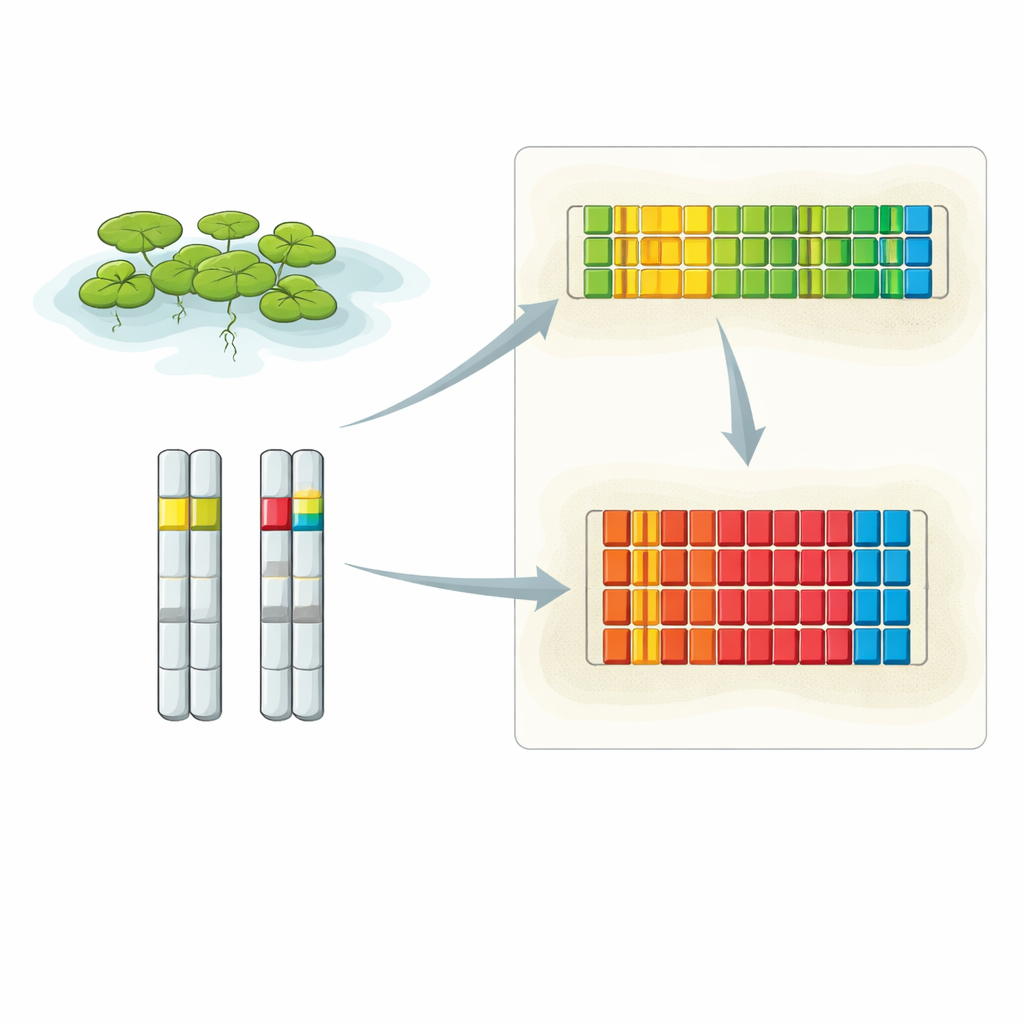
Ampliando o foco em dois bairros de DNA chave
Os pesquisadores combinaram várias técnicas avançadas para descobrir o layout completo do 5S rDNA na lentilha-d’água. Eles usaram leituras de DNA extra-longas do sequenciamento Oxford Nanopore, sequenciamento convencional de alta precisão de fragmentos clonados e hibridização fluorescente in situ (FISH) de alta resolução, que ilumina trechos específicos de DNA dentro de núcleos intactos. As análises revelaram que o 5S rDNA está concentrado em dois locais principais, cada um em um cromossomo diferente. Um locus fica no cromossomo 6 e contém uma série de unidades repetidas curtas, enquanto o outro está no cromossomo 13 e é composto por unidades de repetição mais longas. Imagens de FISH mostraram que a intensidade do sinal desses loci difere entre o par de cópias do cromossomo em cada célula, sugerindo que um homólogo pode carregar visivelmente mais repetições 5S do que o outro.
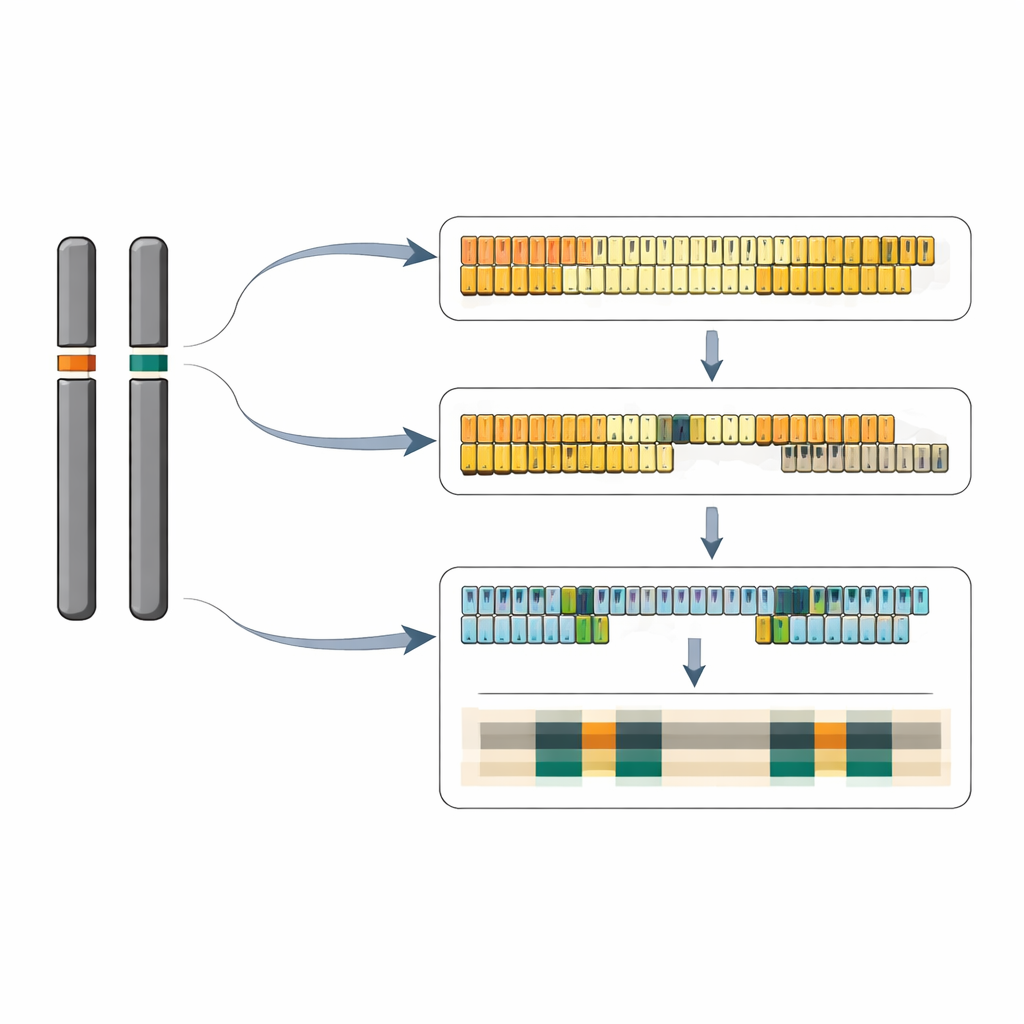
Repetições desiguais e aglomerados espelhados
Ao costurar cuidadosamente leituras longas de sequenciamento, a equipe montou sequências de DNA quase completas para ambos os loci. Em uma versão do cromossomo 6, eles reconstruíram um trecho contínuo de 40 unidades repetidas 5S; o cromossomo parceiro carrega mais de 65 unidades do mesmo tipo curto. No cromossomo 13, traçaram um panorama mais complexo: um grande aglomerado de pelo menos 64 repetições longas e um aglomerado menor de duas repetições posicionadas na orientação oposta, separados por mais de 12.000 pares de bases de DNA cromossômico comum. Dentro do locus de repetições longas, algumas unidades carregam uma pequena inserção de 13 bases na região espaçadora entre genes, e essas unidades ligeiramente diferentes tendem a se agrupar em subaglomerados. No total, os dois loci juntos correspondem a aproximadamente 320–390 cópias do gene 5S por genoma diplóide, consistente com estimativas independentes do número de cópias.
Química do DNA e interruptores de controle
Quando os autores examinaram a composição química dessas regiões, surgiu um padrão marcante. As matrizes de repetições 5S são incomumente ricas nas bases de DNA G e C, enquanto os segmentos cromossômicos flanqueadores ao redor delas são fortemente enriquecidos em A e T. Essas zonas limitantes ricas em AT assemelham-se a elementos de DNA associados a origens de replicação e a cromatina aberta e ativa em outros organismos, e motivos semelhantes aparecem espalhados por todos os 20 cromossomos da lentilha-d’água. Em uma escala mais fina, nas unidades repetidas individuais, a equipe identificou pequenas mas consistentes diferenças em sequências de controle curtas a montante e a jusante do gene 5S, incluindo variações em motivos semelhantes a TATA e trechos de repetições GA. Sabe-se em outras espécies que esses elementos interagem com fatores gerais de transcrição e proteínas que se ligam a GAGA, o que sugere que cada locus pode ser regulado de forma distinta mesmo que o RNA 5S produzido seja idêntico.
O que isso significa para genomas de plantas
Em conjunto, o trabalho fornece a primeira visão completa, ao nível de nucleotídeo, de um sistema 5S rDNA em planta, revelando como número de repetições, variantes de sequência e contexto cromossômico circundante se combinam em um genoma compacto. A lentilha-d’água maior parece ter eliminado muitas cópias ribossômicas supérfluas em comparação com outras plantas com flores, mas mantém dois loci 5S distintos e provavelmente ativos, com aglomerados de variantes de genes organizados de forma precisa. Os autores propõem que ambos os loci podem contribuir para a produção de RNA 5S, dependendo das condições, e que diferenças sutis no DNA vizinho e nas sequências espaçadoras ajudam a regular quando e com que intensidade cada aglomerado é usado. Além da lentilha-d’água, o estudo oferece um roteiro para decodificar regiões repetitivas semelhantes em outras espécies e aprofunda nossa compreensão de como famílias de genes essenciais são moldadas pela evolução.
Citação: Stepanenko, A., Schubert, V., Chen, G. et al. Genome sequence assembly of the 5S rDNA loci informs haplotype specificity and evolution in the greater duckweed Spirodela polyrhiza. Commun Biol 9, 516 (2026). https://doi.org/10.1038/s42003-026-09598-8
Palavras-chave: DNA ribossômico, genoma de lentilha-d’água, genética de plantas, DNA repetitivo, evolução do genoma