Clear Sky Science · pl
Składanie sekwencji genomu loci 5S rDNA informuje o specyficzności haplotypów i ewolucji w większej rzęsitce Spirodela polyrhiza
Dlaczego małe rośliny pływające mają znaczenie
Większa rzęsitka to niewielka roślina wodna, która szybko rozprzestrzenia się po stawach i kanałach, lecz wewnątrz jej komórek kryje się zaskakująco zredukowany genom. To badanie zagłębia się w jedną z najbardziej tajemniczych części tego genomu: odcinki DNA tworzące podstawowe mechanizmy budowy białek, czyli rybosomy komórkowe. Dzięki pełnemu odczytaniu tych trudnych do złożenia regionów w rzęsitce autorzy pokazują, jak zorganizowane i precyzyjnie regulowane są te niezbędne geny, dostarczając wskazówek dotyczących ewolucji genomów roślin oraz kontroli jednego z podstawowych systemów podtrzymywania życia komórki.
Elementy budulcowe fabryk białek komórki
Rybosomy, molekularne maszyny składające białka, zbudowane są zarówno z białek, jak i ze specjalnych cząsteczek RNA. Część z tych RNA kodowana jest przez tzw. 5S rybosomalne DNA (5S rDNA), które u roślin zwykle występuje w setkach lub tysiącach powtarzających się kopii. Ponieważ powtórzenia te są długie i niemal identyczne, są niezwykle trudne do zmontowania przy użyciu standardowego sekwencjonowania DNA. W większej rzęsitce (Spirodela polyrhiza), wcześniejsze badania wykazały jednak, że liczba kopii 5S jest wyjątkowo niska, co czyni tę roślinę doskonałym modelem do mapowania całego regionu 5S rDNA od jednego końca do drugiego i zbadania, jak kopie rozmieszczone są na chromosomach.
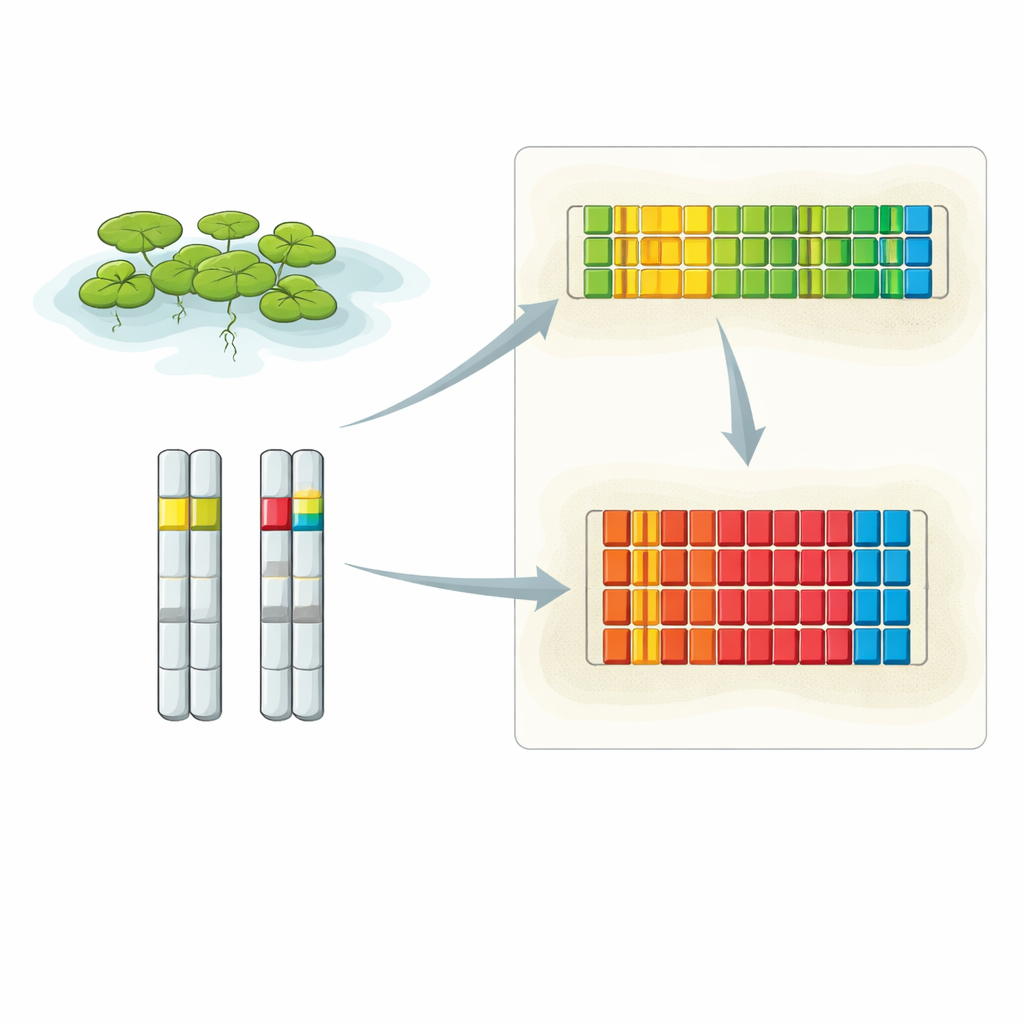
Zbliżenie na dwa kluczowe sąsiedztwa DNA
Naukowcy połączyli kilka zaawansowanych technik, aby odsłonić pełny układ 5S rDNA rzęsitki. Wykorzystali bardzo długie odczyty DNA z sekwencjonowania Oxford Nanopore, konwencjonalne, wysokodokładne sekwencjonowanie sklonowanych fragmentów oraz wysokorozdzielczą fluorescencyjną hybrydyzację in situ (FISH), która uwidacznia konkretne odcinki DNA wewnątrz nieuszkodzonych jąder. Ich analizy ujawniły, że 5S rDNA skoncentrowane jest w dwóch głównych lokalizacjach, każda na innym chromosomie. Jedno locus znajduje się na chromosomie 6 i zawiera serię krótkich jednostek powtórzeniowych, podczas gdy drugie leży na chromosomie 13 i zbudowane jest z dłuższych jednostek powtórzeniowych. Obrazy FISH pokazały, że siła sygnału z tych locusów różni się między parą kopii chromosomów w każdej komórce, co sugeruje, że jeden homolog może mieć zauważalnie więcej powtórzeń 5S niż drugi.
Nierówne powtórzenia i lustrzane klastry
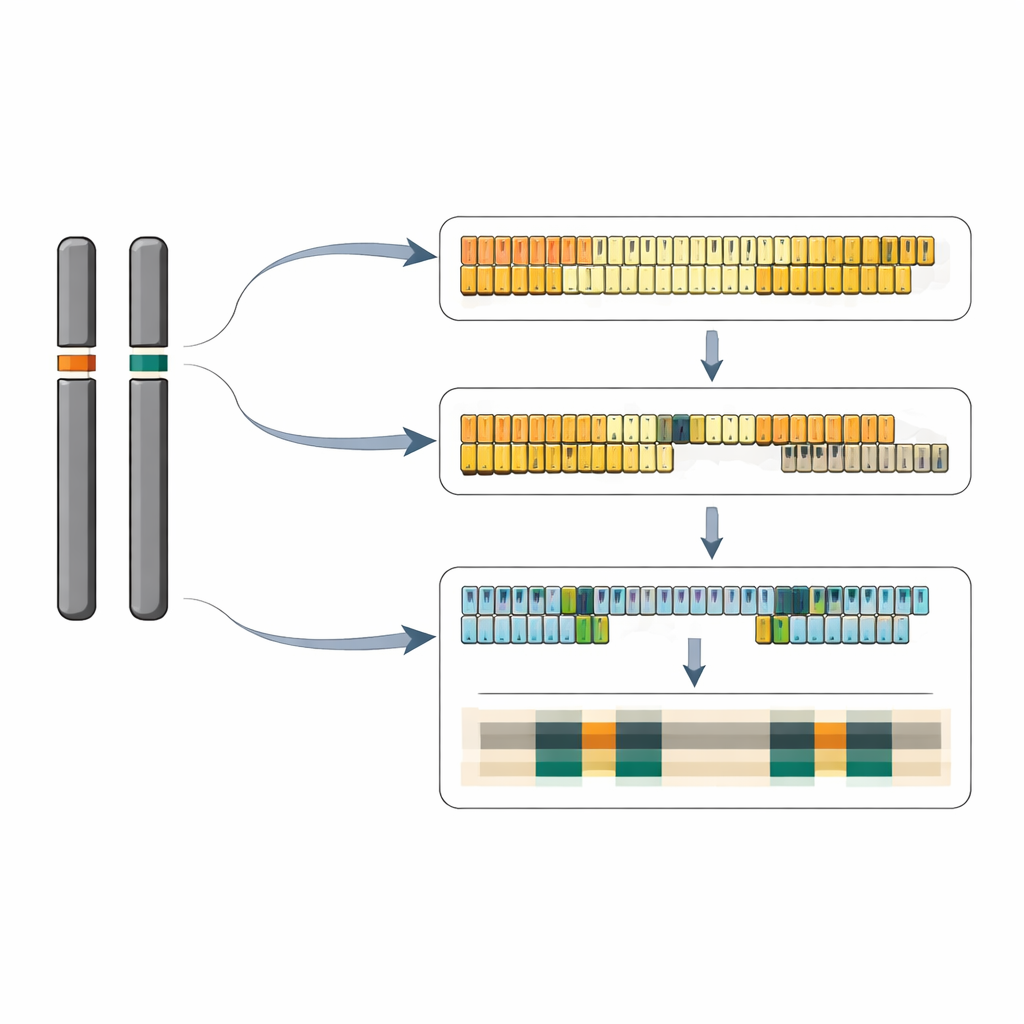
Poprzez staranne składanie długich odczytów sekwencyjnych zespół zmontował niemal kompletne sekwencje DNA obu locusów. W jednej wersji chromosomu 6 odtworzyli ciągłą serię 40 jednostek powtórzeniowych 5S; partner chromosomu nosi ponad 65 jednostek tego samego krótkiego typu. Na chromosomie 13 odtworzyli bardziej złożony obraz: główny klaster co najmniej 64 długich powtórzeń oraz mniejszy klaster dwóch powtórzeń ustawionych w odwrotnej orientacji, oddzielony ponad 12 000 parami zasad zwykłego DNA chromosomowego. W obrębie locus z długimi powtórzeniami niektóre jednostki zawierają małą, 13‑zasadową insercję w regionie spacerowym między genami, a te nieco różne jednostki mają tendencję do grupowania się w podklastry. Łącznie oba lokusy odpowiadają za około 320–390 kopii genu 5S na genom diploidalny, co zgadza się z niezależnymi oszacowaniami liczby kopii.
Chemia DNA i przełączniki kontroli
Po zbadaniu składu chemicznego tych regionów wyłonił się uderzający wzorzec. Same szeregi powtórzeń 5S są wyjątkowo bogate w zasady G i C, podczas gdy otaczające je segmenty chromosomowe są silnie wzbogacone w A i T. Te bogate w AT strefy graniczne przypominają elementy DNA związane z początkiem replikacji i otwartą, aktywną chromatyną w innych organizmach, a podobne motywy pojawiają się rozrzucone na wszystkich 20 chromosomach rzęsitki. W skali pojedynczych jednostek powtórzeniowych zespół zidentyfikował małe, lecz konsekwentne różnice w krótkich sekwencjach kontrolnych powyżej i poniżej genu 5S, w tym warianty w motywach podobnych do TATA oraz odcinki z powtórzeniami GA. W innych gatunkach takie sekwencje znane są z oddziaływań z czynnikami transkrypcyjnymi i białkami wiążącymi GAGA, co sugeruje, że każdy locus może być regulowany inaczej, mimo że produkowany przez nie RNA 5S jest identyczny.
Co to oznacza dla genomów roślin
Podsumowując, praca dostarcza pierwszego kompletnego, na poziomie nukleotydowym obrazu roślinnego systemu 5S rDNA, ukazując, jak liczba powtórzeń, warianty sekwencji i kontekst chromosomowy współgrają w kompaktowym genomie. Większa rzęsitka zdaje się pozbyć wielu nadmiarowych kopii genów rybosomalnych w porównaniu z innymi roślinami kwiatowymi, a mimo to zachowuje dwa odrębne, prawdopodobnie aktywne lokusy 5S z uporządkowanymi klastrami wariantów genowych. Autorzy proponują, że oba lokusy mogą przyczyniać się do produkcji RNA 5S w zależności od warunków, a subtelne różnice w sąsiednim DNA i sekwencjach spacerowych pomagają regulować, kiedy i jak silnie każdy klaster jest wykorzystywany. Poza rzęsitką badanie stanowi plan postępowania dla odszyfrowania podobnych powtarzalnych regionów u innych gatunków i pogłębia nasze zrozumienie, jak kluczowe rodziny genów kształtują się w toku ewolucji.
Cytowanie: Stepanenko, A., Schubert, V., Chen, G. et al. Genome sequence assembly of the 5S rDNA loci informs haplotype specificity and evolution in the greater duckweed Spirodela polyrhiza. Commun Biol 9, 516 (2026). https://doi.org/10.1038/s42003-026-09598-8
Słowa kluczowe: DNA rybosomalne, genom rzęsitki, genetyka roślin, DNA powtarzalne, ewolucja genomu