Clear Sky Science · it
Assemblaggio della sequenza del genoma dei loci 5S rDNA informa sulla specificità degli aplotipi e sull’evoluzione nella lenticchia d’acqua maggiore Spirodela polyrhiza
Perché le piccole piante galleggianti contano
La lenticchia d’acqua maggiore è una piccola pianta acquatica che si diffonde rapidamente in stagni e canali, ma all’interno delle sue cellule nasconde un genoma sorprendentemente essenziale e compatto. Questo studio si concentra su una delle parti più enigmatiche di quel genoma: gli intervalli di DNA che codificano la macchina fondamentale per assemblare le proteine, i ribosomi della cellula. Decodificando completamente queste regioni difficili da leggere nella lenticchia d’acqua, gli autori mostrano come sono organizzati e raffinati geni essenziali, offrendo indicazioni su come evolvono i genomi delle piante e su come le cellule regolano uno dei loro sistemi di supporto vitale più basilari.
Mattoni delle officine proteiche della cellula
I ribosomi, le macchine molecolari che assemblano le proteine, sono composti sia da proteine sia da particolari molecole di RNA. Alcuni di questi RNA sono codificati dal cosiddetto DNA ribosomale 5S (5S rDNA), che nelle piante si presenta normalmente in centinaia o migliaia di copie ripetute. Poiché queste ripetizioni sono lunghe e quasi identiche, risultano notoriamente difficili da assemblare con i metodi standard di sequenziamento. Nella lenticchia d’acqua maggiore (Spirodela polyrhiza), però, lavori precedenti hanno mostrato che il numero di copie 5S è insolitamente basso, rendendo questa pianta un modello ideale per mappare finalmente un intero locus 5S rDNA da un capo all’altro e osservare come le sue copie siano disposte sui cromosomi.
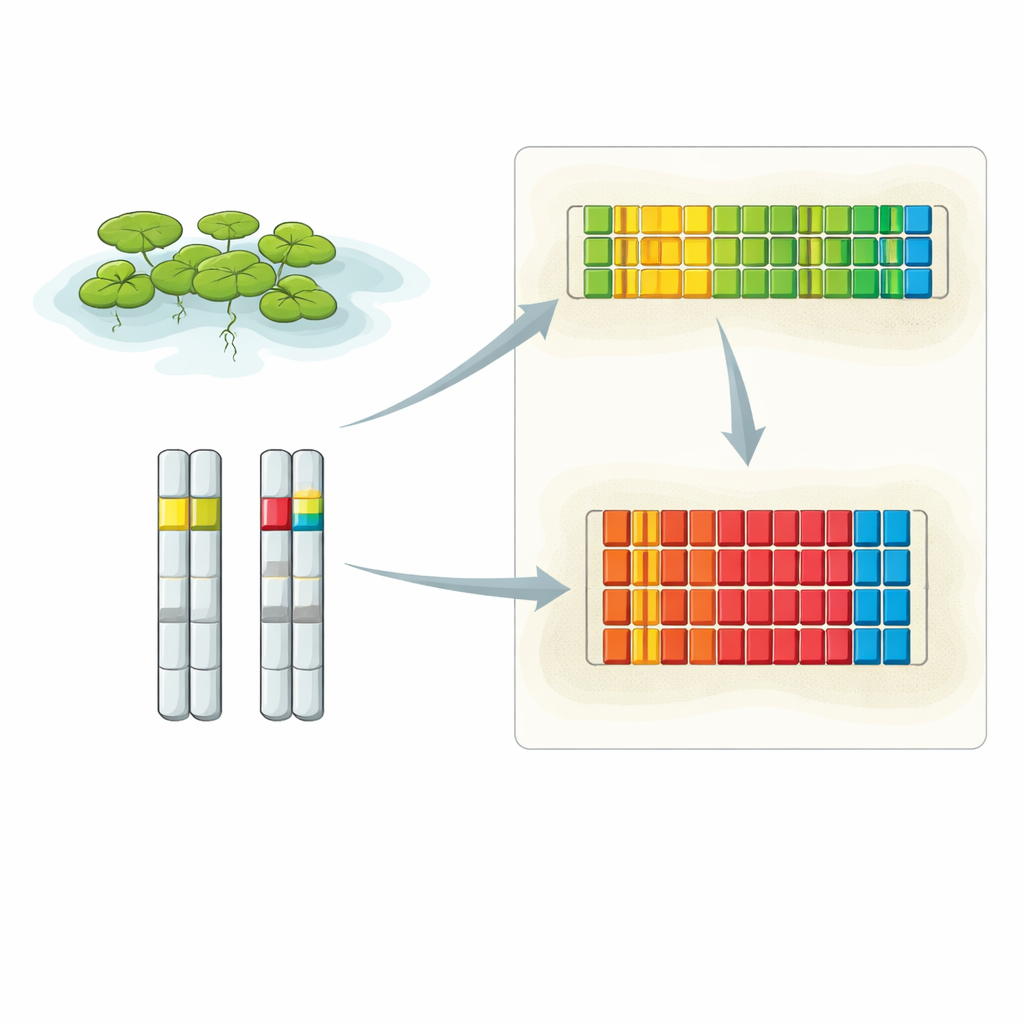
Ingrandire due quartieri chiave del DNA
I ricercatori hanno combinato diverse tecniche avanzate per svelare la disposizione completa del 5S rDNA nella lenticchia d’acqua. Hanno utilizzato letture di DNA extra-lunghe dal sequenziamento Oxford Nanopore, sequenziamento convenzionale ad alta accuratezza di frammenti clonati e ibridazione fluorescente in situ (FISH) ad alta risoluzione, che illumina tratti specifici di DNA all’interno di nuclei intatti. Le analisi hanno rilevato che il 5S rDNA è concentrato in due posizioni principali, ciascuna su un cromosoma diverso. Un locus si trova sul cromosoma 6 e contiene una serie di unità ripetute corte, mentre l’altro risiede sul cromosoma 13 ed è costituito da unità di ripetizione più lunghe. Le immagini FISH hanno mostrato che l’intensità del segnale proveniente da questi loci differisce tra la coppia di cromosomi in ogni cellula, suggerendo che un omologo può portare significativamente più ripetizioni 5S dell’altro.
Ripetizioni diseguali e cluster speculari
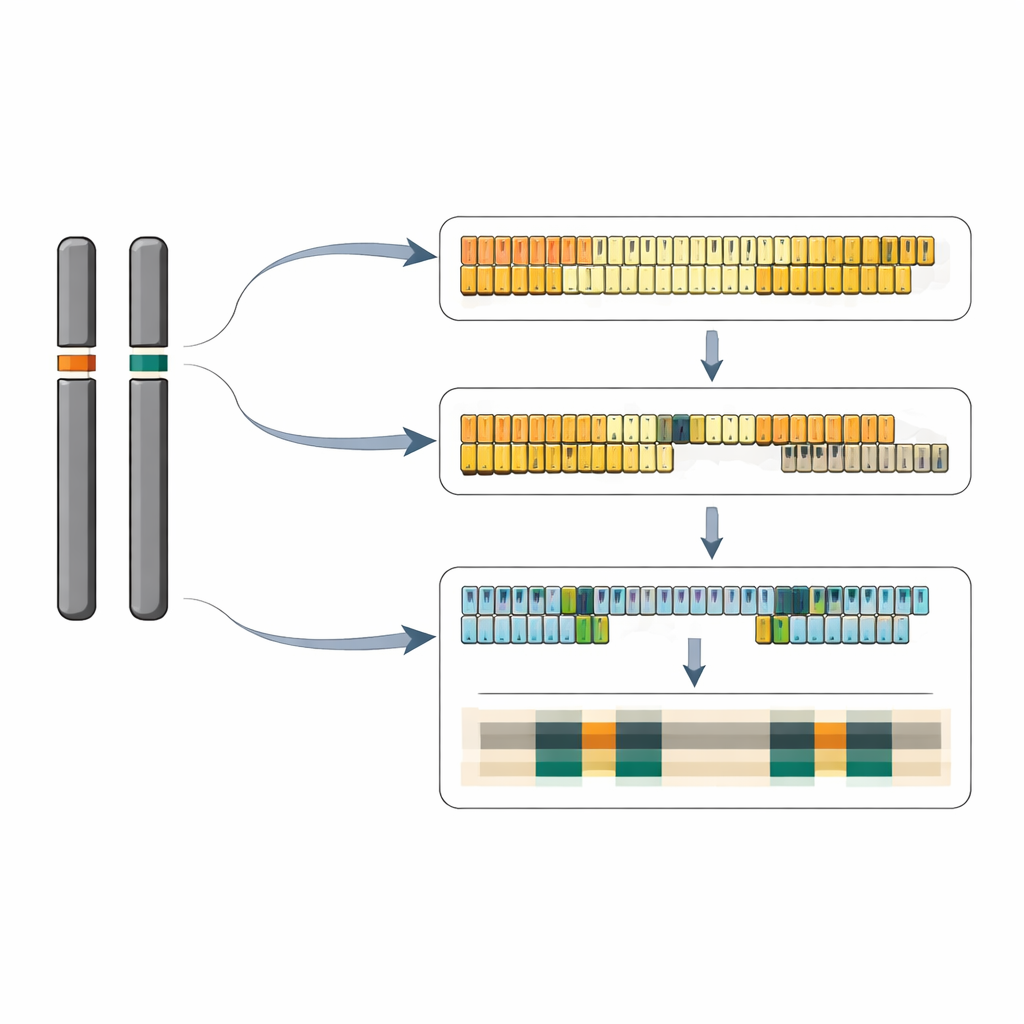
Assemblando con cura letture di sequenziamento lunghe, il team ha ricostruito sequenze di DNA quasi complete per entrambi i loci. In una copia del cromosoma 6 hanno ricostruito un tratto continuo di 40 unità ripetute 5S; il cromosoma partner porta più di 65 unità dello stesso tipo corto. Sul cromosoma 13 hanno tracciato un quadro più complesso: un cluster principale di almeno 64 ripetizioni lunghe e un cluster minore di due ripetizioni posizionate in orientamento opposto, separate da oltre 12.000 paia di basi di DNA cromosomico ordinario. All’interno del locus a ripetizione lunga, alcune unità presentano una piccola inserzione di 13 basi nella regione spacer tra i geni, e queste unità leggermente diverse tendono a raggrupparsi in sotto-cluster. Complessivamente, i due loci insieme rappresentano circa 320–390 copie del gene 5S per genoma diploide, in accordo con stime indipendenti del numero di copie.
Chimica del DNA e interruttori di controllo
Quando gli autori hanno esaminato la composizione chimica di queste regioni, è emerso un motivo sorprendente. Gli array di ripetizioni 5S sono essi stessi insolitamente ricchi delle basi G e C, mentre i segmenti cromosomici flanking intorno a essi sono fortemente arricchiti in A e T. Queste zone bordanti ricche di AT somigliano a elementi di DNA associati a origini di replicazione e a cromatina aperta e attiva in altri organismi, e motivi simili compaiono sparsi su tutti i 20 cromosomi della lenticchia d’acqua. A scala più fine delle singole unità ripetute, il gruppo ha identificato piccole ma coerenti differenze in brevi sequenze di controllo a monte e a valle del gene 5S, incluse variazioni in motivi simili a TATA e tratti di ripetizioni GA. In altre specie questi elementi interagiscono con fattori generali della trascrizione e proteine leganti GAGA, suggerendo che ogni locus possa essere regolato in modo diverso anche se l’RNA 5S che producono è identico.
Cosa significa per i genomi delle piante
Nel complesso, il lavoro fornisce la prima vista completa a livello di nucleotidi di un sistema 5S rDNA in una pianta, rivelando come numero di ripetizioni, varianti di sequenza e contesto cromosomico circostante si combinino in un genoma compatto. La lenticchia d’acqua maggiore sembra aver perso molte copie di geni ribosomiali rispetto ad altre piante da fiore, ma mantiene due loci 5S distinti e probabilmente attivi con cluster di varianti geniche ordinati. Gli autori propongono che entrambi i loci possano contribuire alla produzione di RNA 5S a seconda delle condizioni, e che differenze sottili nel DNA vicino e nelle sequenze spacer aiutino a regolare quando e con quale intensità ciascun cluster viene utilizzato. Oltre la lenticchia d’acqua, lo studio offre un modello per decodificare regioni ripetitive simili in altre specie e approfondisce la nostra comprensione di come famiglie geniche essenziali vengano modellate dall’evoluzione.
Citazione: Stepanenko, A., Schubert, V., Chen, G. et al. Genome sequence assembly of the 5S rDNA loci informs haplotype specificity and evolution in the greater duckweed Spirodela polyrhiza. Commun Biol 9, 516 (2026). https://doi.org/10.1038/s42003-026-09598-8
Parole chiave: DNA ribosomale, genoma della lenticchia d’acqua, genetica delle piante, DNA ripetitivo, evoluzione del genoma