Clear Sky Science · fr
Assemblage de la séquence du génome des loci 5S rDNA éclaire la spécificité d’haplotype et l’évolution chez la grande lentille d’eau Spirodela polyrhiza
Pourquoi ces petites plantes flottantes comptent
La grande lentille d’eau est une petite plante aquatique qui se propage rapidement dans les étangs et les canaux, mais à l’intérieur de ses cellules se cache un génome étonnamment épuré. Cette étude explore l’un des segments les plus mystérieux de ce génome : les portions d’ADN qui codent la machinerie centrale de fabrication des protéines, les ribosomes cellulaires. En décodant complètement ces régions difficiles à lire chez la lentille d’eau, les auteurs montrent comment des gènes essentiels sont organisés et ajustés, fournissant des indices sur l’évolution des génomes végétaux et sur la façon dont les cellules contrôlent l’un de leurs systèmes de soutien vital les plus fondamentaux.
Les éléments constitutifs des usines à protéines cellulaires
Les ribosomes, machines moléculaires qui assemblent les protéines, sont constitués à la fois de protéines et d’ARN spécialisés. Certains de ces ARN sont encodés par ce qu’on appelle l’ADN ribosomal 5S (5S rDNA), qui apparaît normalement par centaines ou milliers de copies répétées dans les génomes des plantes. Parce que ces répétitions sont longues et quasi identiques, elles sont notoirement difficiles à assembler avec les méthodes classiques de séquençage. Dans la grande lentille d’eau (Spirodela polyrhiza), toutefois, des travaux antérieurs ont montré que le nombre de copies 5S est anormalement faible, faisant de cette plante un modèle idéal pour cartographier enfin une région complète de 5S rDNA d’un bout à l’autre et observer comment ses copies sont disposées sur les chromosomes.
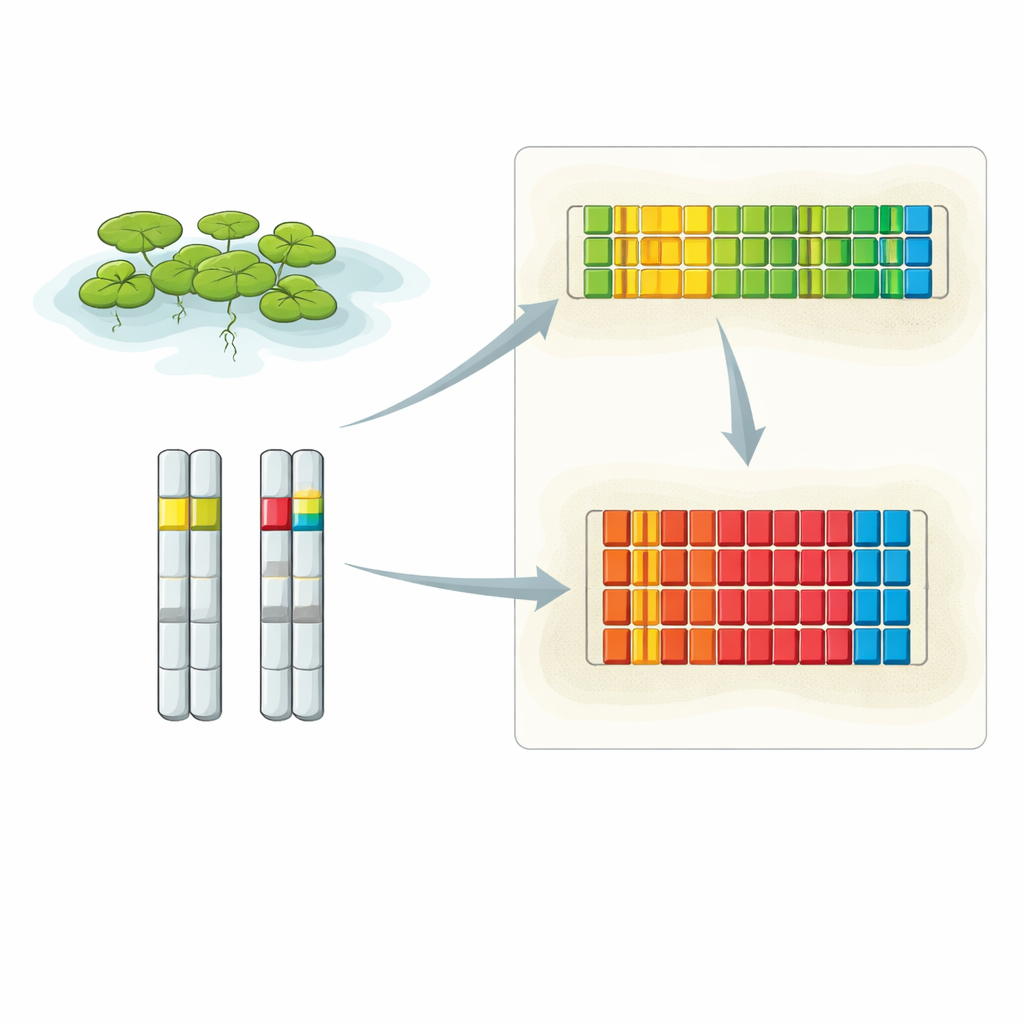
Zoom sur deux quartiers d’ADN clés
Les chercheurs ont combiné plusieurs techniques avancées pour découvrir l’agencement complet du 5S rDNA de la lentille d’eau. Ils ont utilisé des lectures d’ADN extra-longues issues du séquençage Oxford Nanopore, un séquençage conventionnel haute précision de fragments clonés, et l’hybridation in situ fluorescente (FISH) à haute résolution, qui met en lumière des segments d’ADN spécifiques à l’intérieur de noyaux intacts. Leurs analyses ont révélé que le 5S rDNA se concentre en deux emplacements principaux, chacun sur un chromosome différent. Un locus se situe sur le chromosome 6 et contient une série d’unités répétées courtes, tandis que l’autre se trouve sur le chromosome 13 et est constitué d’unités répétées plus longues. Les images FISH ont montré que l’intensité du signal provenant de ces loci diffère entre la paire de chromosomes présents dans chaque cellule, suggérant qu’un des homologues peut porter sensiblement plus de répétitions 5S que l’autre.
Répétitions inégales et amas en miroir
En reconstituant soigneusement des lectures longues, l’équipe a assemblé des séquences d’ADN presque complètes pour les deux loci. Sur une version du chromosome 6, ils ont reconstruit un segment continu de 40 unités répétées 5S ; le chromosome partenaire porte plus de 65 unités du même type court. Sur le chromosome 13, ils ont retracé un paysage plus complexe : un amas principal d’au moins 64 répétitions longues et un petit amas de deux répétitions positionnées en orientation opposée, séparés par plus de 12 000 paires de bases d’ADN chromosomique ordinaire. À l’intérieur du locus à répétitions longues, certaines unités portent une petite insertion de 13 bases dans la région intergénique, et ces unités légèrement différentes ont tendance à se regrouper en sous-amas. Dans l’ensemble, les deux loci représentent environ 320–390 copies du gène 5S par génome diploïde, en accord avec des estimations indépendantes du nombre de copies.
Chimie de l’ADN et interrupteurs de contrôle
Lorsque les auteurs ont examiné la composition chimique de ces régions, un motif frappant est apparu. Les séries de répétitions 5S elles-mêmes sont exceptionnellement riches en bases G et C, tandis que les segments chromosomiques adjacents sont fortement enrichis en A et T. Ces zones bordantes riches en AT ressemblent à des éléments d’ADN associés aux origines de réplication et à une chromatine ouverte et active chez d’autres organismes, et des motifs similaires apparaissent dispersés sur les 20 chromosomes de la lentille d’eau. À une échelle plus fine, au niveau des unités répétées individuelles, l’équipe a identifié de petites mais constantes différences dans de courtes séquences de contrôle en amont et en aval du gène 5S, incluant des variations dans des motifs TATA-like et des tronçons de répétitions GA. Ces éléments sont connus dans d’autres espèces pour interagir avec des facteurs généraux de transcription et des protéines liant GAGA, ce qui suggère que chaque locus peut être régulé différemment même si l’ARN 5S qu’ils produisent est identique.
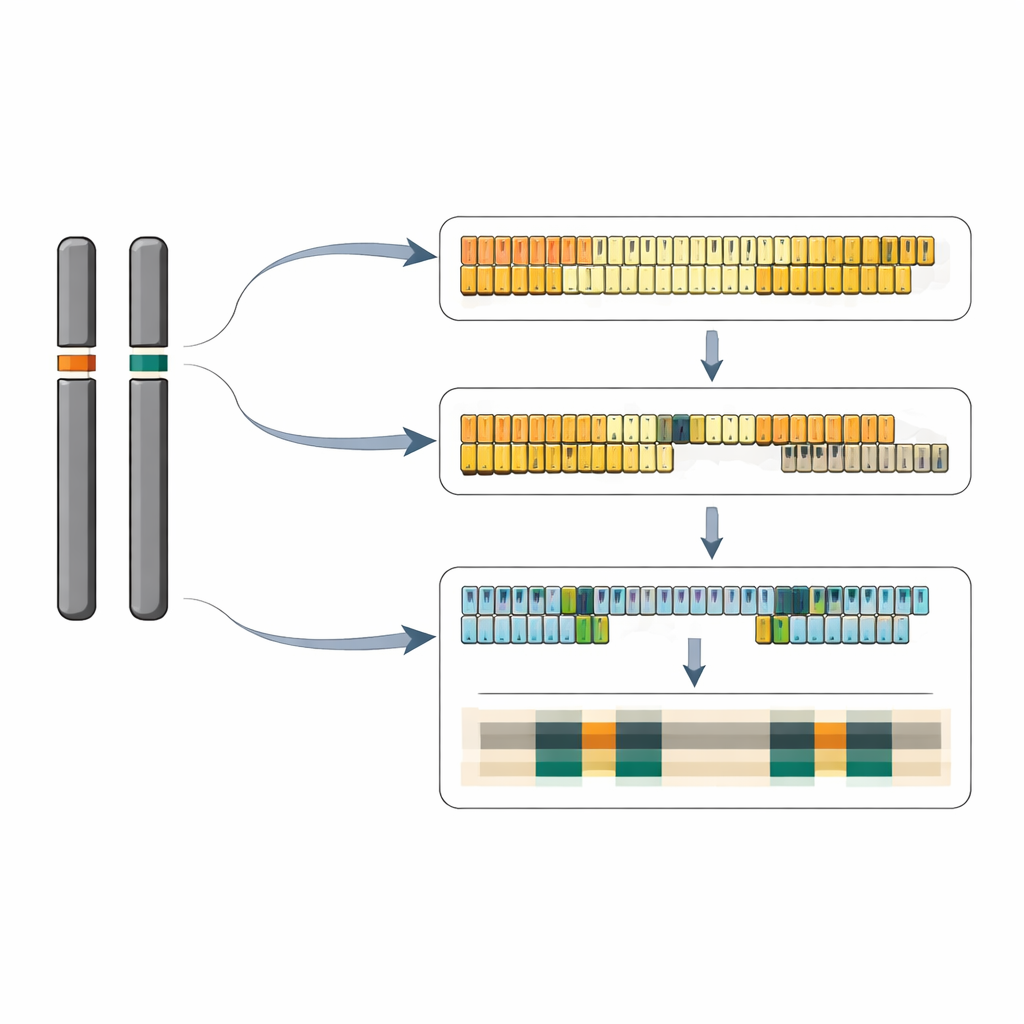
Ce que cela signifie pour les génomes végétaux
Pris ensemble, ces travaux fournissent la première vue complète au niveau des nucléotides d’un système 5S rDNA végétal, révélant comment le nombre de répétitions, les variantes de séquence et le contexte chromosomique environnant se combinent dans un génome compact. La grande lentille d’eau semble avoir perdu de nombreuses copies redondantes de gènes ribosomaux par rapport à d’autres plantes à fleurs, tout en conservant deux loci 5S distincts et vraisemblablement actifs avec des amas de variantes de gènes soigneusement organisés. Les auteurs proposent que les deux loci puissent contribuer à la production d’ARN 5S selon les conditions, et que des différences subtiles dans l’ADN voisin et les séquences intergéniques aident à réguler quand et avec quelle intensité chaque amas est utilisé. Au-delà de la lentille d’eau, l’étude offre une feuille de route pour décoder des régions répétitives similaires chez d’autres espèces et approfondit notre compréhension de la façon dont les familles de gènes essentiels sont façonnées au cours de l’évolution.
Citation: Stepanenko, A., Schubert, V., Chen, G. et al. Genome sequence assembly of the 5S rDNA loci informs haplotype specificity and evolution in the greater duckweed Spirodela polyrhiza. Commun Biol 9, 516 (2026). https://doi.org/10.1038/s42003-026-09598-8
Mots-clés: ADN ribosomal, génome de la lentille d’eau, génétique végétale, ADN répétitif, évolution du génome