Clear Sky Science · es
El ensamblaje de la secuencia del genoma de los loci 5S rDNA aclara la especificidad de haplotipo y la evolución en la lenteja de agua mayor Spirodela polyrhiza
Por qué importan las plantas flotantes diminutas
La lenteja de agua mayor es una planta acuática pequeña que se propaga rápidamente por estanques y canales, pero en el interior de sus células alberga un genoma sorprendentemente depurado. Este estudio se adentra en una de las partes más enigmáticas de ese genoma: los tramos de ADN que generan la maquinaria central para fabricar proteínas, los ribosomas de la célula. Al decodificar por completo estas regiones difíciles de leer en la lenteja de agua, los autores muestran cómo están organizados y afinados los genes esenciales, ofreciendo pistas sobre cómo evolucionan los genomas vegetales y cómo las células controlan uno de sus sistemas básicos de soporte vital.
Bloques constructores de las fábricas de proteínas celulares
Los ribosomas, las máquinas moleculares que ensamblan proteínas, se componen de proteínas y de ARN especiales. Parte de estos ARNs están codificados por el llamado ADN ribosómico 5S (5S rDNA), que normalmente aparece en cientos o miles de copias repetidas en los genomas de plantas. Debido a que estas repeticiones son largas y casi idénticas, son notoriamente difíciles de ensamblar con métodos estándar de secuenciación. En la lenteja de agua mayor (Spirodela polyrhiza), sin embargo, trabajos previos mostraron que el número de copias 5S es inusualmente bajo, lo que convierte a esta planta en un modelo ideal para cartografiar por fin una región completa de 5S rDNA de extremo a extremo y ver cómo se disponen sus copias en los cromosomas.
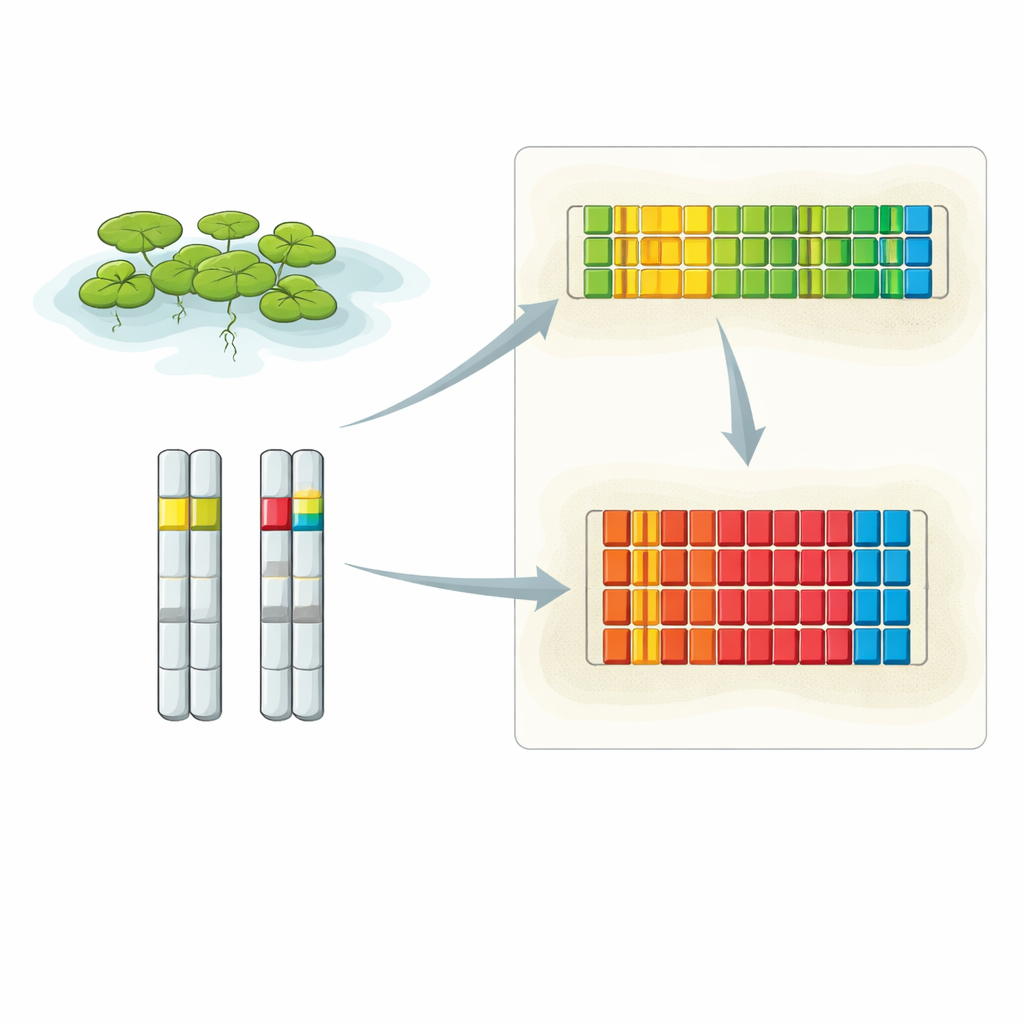
Acercándose a dos barrios clave del ADN
Los investigadores combinaron varias técnicas avanzadas para descubrir la disposición completa del 5S rDNA en la lenteja de agua. Usaron lecturas de ADN extra‑largas de la secuenciación Oxford Nanopore, secuenciación convencional de alta precisión de fragmentos clonados y hibridación fluorescente in situ (FISH) de alta resolución, que ilumina tramos específicos de ADN dentro de núcleos intactos. Sus análisis revelaron que el 5S rDNA está concentrado en dos ubicaciones principales, cada una en un cromosoma diferente. Un locus se sitúa en el cromosoma 6 y contiene una serie de unidades repetidas cortas, mientras que el otro está en el cromosoma 13 y está formado por unidades repetidas más largas. Las imágenes de FISH mostraron que la intensidad de la señal de estos loci difiere entre el par de copias cromosómicas en cada célula, lo que sugiere que un homologado puede portar considerablemente más repeticiones 5S que el otro.
Repeticiones desiguales y cúmulos espejo
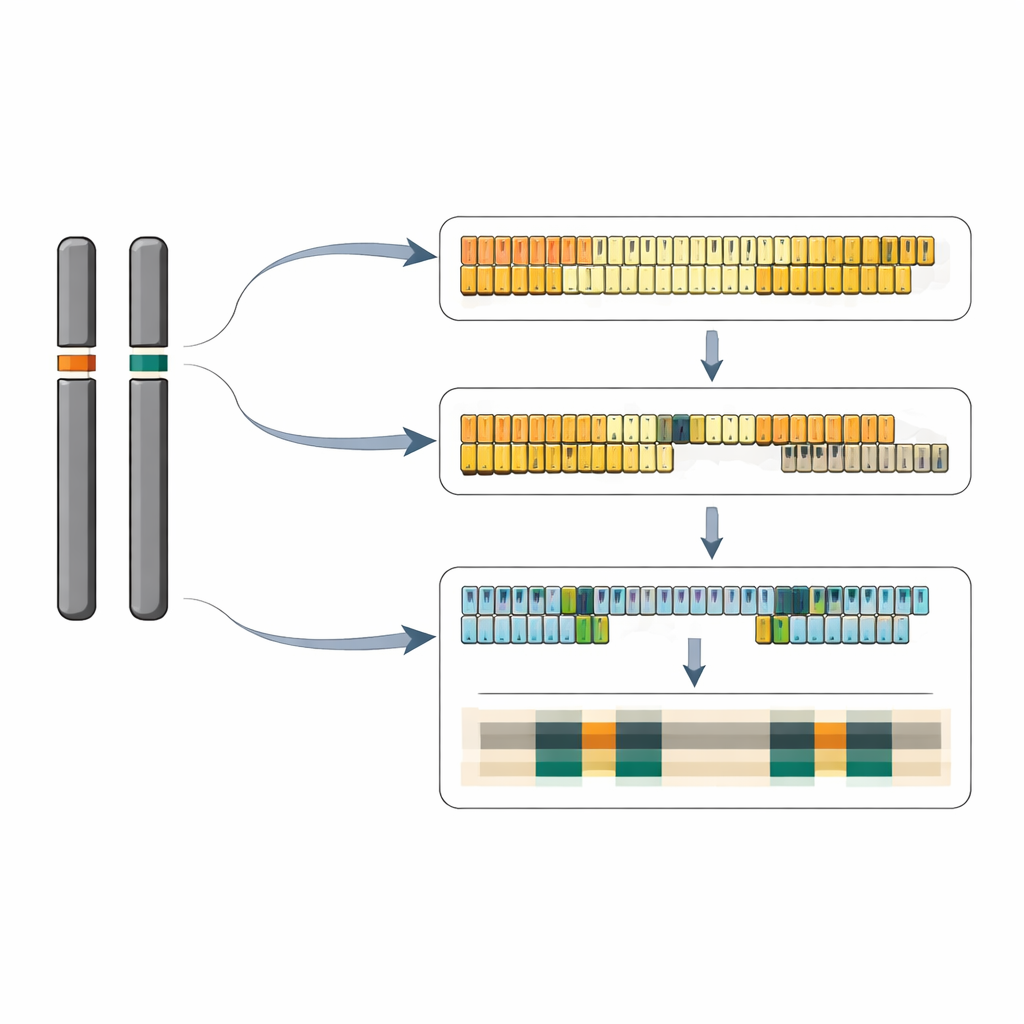
Al ensamblar cuidadosamente las lecturas largas de secuenciación, el equipo reconstruyó secuencias de ADN casi completas para ambos loci. En una versión del cromosoma 6 reconstruyeron un tramo continuo de 40 unidades repetidas 5S; el cromosoma compañero lleva más de 65 unidades del mismo tipo corto. En el cromosoma 13 trazaron un panorama más complejo: un cúmulo principal de al menos 64 repeticiones largas y un cúmulo más pequeño de dos repeticiones posicionadas en la orientación opuesta, separadas por más de 12.000 pares de bases de ADN cromosómico ordinario. Dentro del locus de repeticiones largas, algunas unidades contienen una pequeña inserción de 13 bases en la región espaciadora entre genes, y estas unidades ligeramente diferentes tienden a agruparse en subcúmulos. En conjunto, los dos loci representan aproximadamente entre 320 y 390 copias del gen 5S por genoma diploide, coherente con estimaciones independientes del número de copias.
Química del ADN y interruptores de control
Al examinar la composición química de estas regiones emergió un patrón llamativo. Los arreglos de repeticiones 5S en sí son inusualmente ricos en las bases G y C, mientras que los segmentos cromosómicos adyacentes están fuertemente enriquecidos en A y T. Estas zonas limitantes ricas en AT se parecen a elementos de ADN asociados con orígenes de replicación y con cromatina abierta y activa en otros organismos, y motivos similares aparecen dispersos por los 20 cromosomas de la lenteja de agua. A escala más fina, en las unidades repetidas individuales, el equipo identificó pequeñas pero consistentes diferencias en secuencias de control cortas corriente arriba y corriente abajo del gen 5S, incluyendo variaciones en motivos similares a TATA y tramos de repeticiones GA. Se sabe en otras especies que estas secuencias interactúan con factores generales de transcripción y proteínas que se unen a GAGA, lo que sugiere que cada locus puede estar regulado de forma distinta aunque el ARN 5S que producen sea idéntico.
Qué implica esto para los genomas vegetales
En conjunto, el trabajo proporciona la primera vista completa a nivel de nucleótido de un sistema 5S rDNA en plantas, revelando cómo el número de repeticiones, las variantes de secuencia y el contexto cromosómico circundante se combinan en un genoma compacto. La lenteja de agua mayor parece haber perdido muchas copias sobrantes de genes ribosómicos en comparación con otras plantas con flor, sin embargo mantiene dos loci 5S distintos y probablemente activos con cúmulos organizados de variantes génicas. Los autores proponen que ambos loci pueden contribuir a la producción de ARN 5S según las condiciones, y que diferencias sutiles en el ADN vecino y en las secuencias espaciadoras ayudan a regular cuándo y con qué intensidad se utiliza cada cúmulo. Más allá de la lenteja de agua, el estudio ofrece un plano para decodificar regiones repetitivas similares en otras especies y profundiza nuestra comprensión de cómo las familias de genes esenciales se moldean a lo largo de la evolución.
Cita: Stepanenko, A., Schubert, V., Chen, G. et al. Genome sequence assembly of the 5S rDNA loci informs haplotype specificity and evolution in the greater duckweed Spirodela polyrhiza. Commun Biol 9, 516 (2026). https://doi.org/10.1038/s42003-026-09598-8
Palabras clave: ADN ribosómico, genoma de lenteja de agua, genética vegetal, ADN repetitivo, evolución del genoma