Clear Sky Science · nl
Genoomassembleer van de 5S rDNA-loci belicht haplotype-specificiteit en evolutie in het grotere eendekruid Spirodela polyrhiza
Waarom piepkleine drijvende planten ertoe doen
Het grotere eendekruid is een klein waterplantje dat zich snel over vijvers en grachten verspreidt, maar in zijn cellen schuilt een verrassend gestroomlijnd genoom. Deze studie duikt in een van de meest mysterieuze delen van dat genoom: de DNA-streken die de kernmachinerie voor het bouwen van eiwitten coderen, de ribosomen van de cel. Door deze moeilijk leesbare regio’s in eendekruid volledig te decoderen, laten de auteurs zien hoe essentiële genen zijn georganiseerd en bijgesteld, en bieden zij aanwijzingen voor hoe plantengenomen evolueren en hoe cellen een van hun meest fundamentele levensondersteunende systemen regelen.
Bouwelementen van de eiwitfabrieken van de cel
Ribosomen, de moleculaire machines die eiwitten assembleren, bestaan uit zowel eiwitten als speciale RNA-moleculen. Sommige van deze RNA’s worden gecodeerd door het zogenaamde 5S ribosomaal DNA (5S rDNA), dat bij planten doorgaans in honderden of duizenden herhaalde kopieën voorkomt. Omdat deze herhalingen lang en bijna identiek zijn, zijn ze berucht moeilijk samen te stellen met standaard DNA-sequencing. Bij het grotere eendekruid (Spirodela polyrhiza) toonde eerder werk echter aan dat het aantal 5S-kopieën uitzonderlijk laag is, waardoor deze plant een ideaal model is om uiteindelijk een volledige 5S rDNA-regio van begin tot eind in kaart te brengen en te zien hoe de kopieën op de chromosomen zijn gerangschikt.
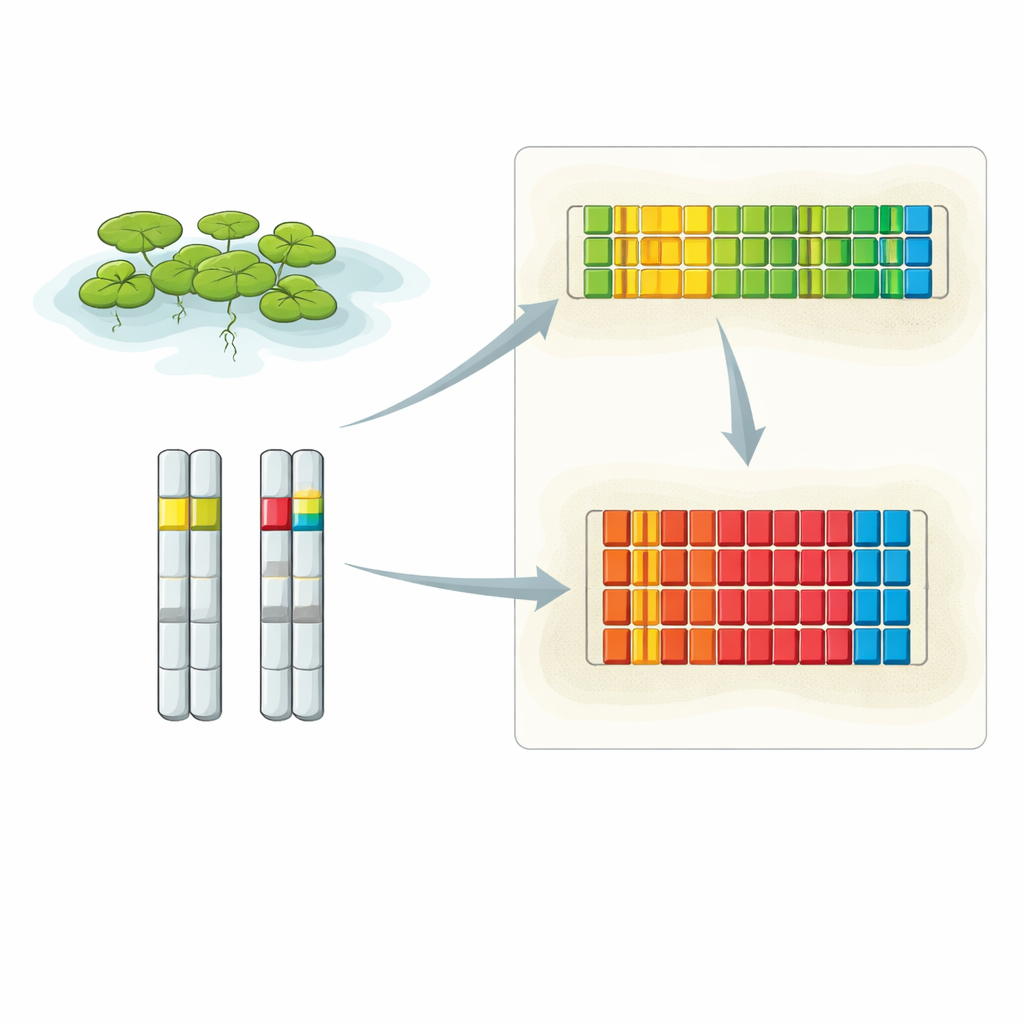
Naar twee belangrijke DNA-buurten zoomen
De onderzoekers combineerden meerdere geavanceerde technieken om de volledige indeling van het eendekruid 5S rDNA te onthullen. Ze gebruikten extra-lange DNA-reads van Oxford Nanopore-sequencing, conventionele hoogaccurate sequencing van gekloonde fragmenten en hoogresolutie fluorescentie in situ hybridisatie (FISH), die specifieke DNA-streken in intacte kernen oplicht. Hun analyses toonden aan dat 5S rDNA geconcentreerd is op twee hoofdlocaties, elk op een ander chromosoom. Eén locus bevindt zich op chromosoom 6 en bevat een reeks korte herhalende eenheden, terwijl de andere op chromosoom 13 ligt en is opgebouwd uit langere herhaaleenheden. FISH-beelden lieten zien dat de signaalsterkte van deze loci verschilt tussen de twee chromosoomkopieën in elke cel, wat erop wijst dat de ene homolog duidelijk meer 5S-herhalingen kan dragen dan de andere.
Ongelijke herhalingen en spiegelende clusters
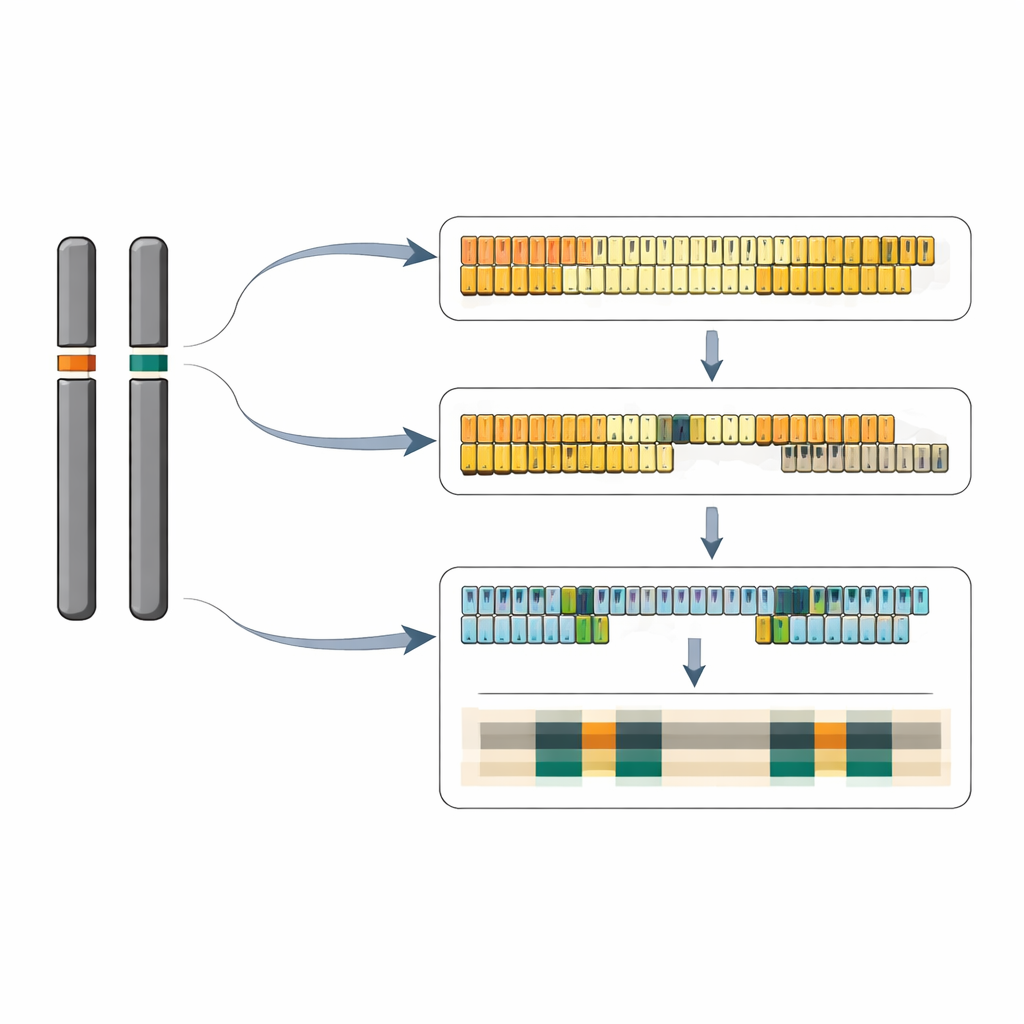
Door lange sequencing-reads zorgvuldig aaneen te rijgen, stelde het team bijna volledige DNA-sequenties voor beide loci samen. Op één versie van chromosoom 6 reconstrueerden zij een aaneengesloten strook van 40 5S-herhaaleenheden; het partnerchromosoom draagt meer dan 65 eenheden van hetzelfde korte type. Op chromosoom 13 beschreven ze een complexer landschap: een grote cluster van minstens 64 lange herhalingen en een kleinere cluster van twee herhalingen in de omgekeerde oriëntatie, gescheiden door meer dan 12.000 basenparen gewone chromosoom-DNA. Binnen de locus met lange herhalingen dragen sommige eenheden een kleine invoeging van 13 basen in de spacer-regio tussen genen, en deze licht afwijkende eenheden groeperen vaak in subclusters. In totaal vertegenwoordigen de twee loci samen ongeveer 320–390 5S-gencopies per diploïd genoom, in overeenstemming met onafhankelijke schattingen van het kopieaantal.
DNA-chemie en schakelaarachtige controles
Bij onderzoek naar de chemische samenstelling van deze regio’s kwam een opvallend patroon naar voren. De 5S-herhalingsarrays zelf zijn ongewoon rijk aan de DNA-basissen G en C, terwijl de flankerende chromosoomsegmenten daaromheen sterk verrijkt zijn in A en T. Deze AT-rijke grenszones lijken op DNA-elementen die geassocieerd worden met replicatie‑origines en open, actieve chromatine in andere organismen, en vergelijkbare motieven verschijnen verspreid over alle 20 eendekruidchromosomen. Op fijner schaalniveau van individuele herhaaleenheden identificeerde het team kleine maar consistente verschillen in korte controlesignalen stroomop- en stroomafwaarts van het 5S-gen, waaronder variaties in TATA‑achtige motieven en reeksen van GA-herhalingen. Deze zijn in andere soorten bekend om interacties aan te gaan met algemene transcriptiefactoren en GAGA-bindende eiwitten, wat suggereert dat elke locus mogelijk verschillend is afgesteld, hoewel het 5S‑RNA dat ze produceren identiek is.
Wat dit betekent voor plantengenomen
Gezamenlijk biedt het werk het eerste complete, nucleotide‑niveaubeeld van een plantaardig 5S rDNA-systeem, en onthult hoe herhalingsaantal, sequentievarianten en de omliggende chromosoomcontext samenkomen in een compact genoom. Het grotere eendekruid lijkt veel overbodige ribosomale gencopies te hebben afgestoten vergeleken met andere bloemplanten, maar behoudt toch twee onderscheiden, waarschijnlijk actieve 5S-loci met zorgvuldig georganiseerde clusters van genvarianten. De auteurs stellen dat beide loci kunnen bijdragen aan de productie van 5S‑RNA, afhankelijk van omstandigheden, en dat subtiele verschillen in naburig DNA en spacer-sequenties helpen reguleren wanneer en hoe sterk elke cluster wordt gebruikt. Buiten eendekruid biedt de studie een blauwdruk voor het ontcijferen van vergelijkbare herhaalde regio’s in andere soorten en verdiept zij ons begrip van hoe essentiële genfamilies door evolutie worden gevormd.
Bronvermelding: Stepanenko, A., Schubert, V., Chen, G. et al. Genome sequence assembly of the 5S rDNA loci informs haplotype specificity and evolution in the greater duckweed Spirodela polyrhiza. Commun Biol 9, 516 (2026). https://doi.org/10.1038/s42003-026-09598-8
Trefwoorden: ribosomaal DNA, eendekruidgenoom, plantengenetica, herhalend DNA, genoomevolutie