Clear Sky Science · sv
Multiuppgiftsinlärningsbaserad tidig prediktionsmodell för antibiotikaresistens med data från flera institutioner
Varför detta är viktigt för vård i vardagen
Antibiotikaresistens förvandlar tyst tidigare lätt behandlade infektioner till livshotande sjukdomar. Läkare måste ofta välja antibiotika innan laboratorietester visar vilka läkemedel som fungerar, en fördröjning som kan ta flera dagar. Denna studie undersöker hur datorbaserade modeller som tränats på journaldata kan ge läkare tidiga indikationer på vilka antibiotika som sannolikt kommer att misslyckas, vilket kan skydda patienter och bromsa spridningen av resistenta bakterier.
Antibiotika under press
Modern medicin är i hög grad beroende av antibiotika för allt från rutinoperationer till cancerbehandling. Men bakterier utvecklas snabbt, och nya antibiotika kommer fram långsammare än de gamla förlorar sin effekt. I Sydkorea, där denna studie genomfördes, bedöms upp till en tredjedel av antibiotikaförskrivningarna på sjukhus vara olämpliga. Odlingstester som visar om en mikrob är resistent tar vanligtvis tre till fem dagar, vilket tvingar läkare att behandla i blindo. Forskarna strävade efter att förutsäga resistens mot nio stora antibiotikagrupper med endast information som finns tillgänglig tidigt under en patients sjukhusvistelse.
Att omvandla sjukhusdata till tidiga varningssignaler
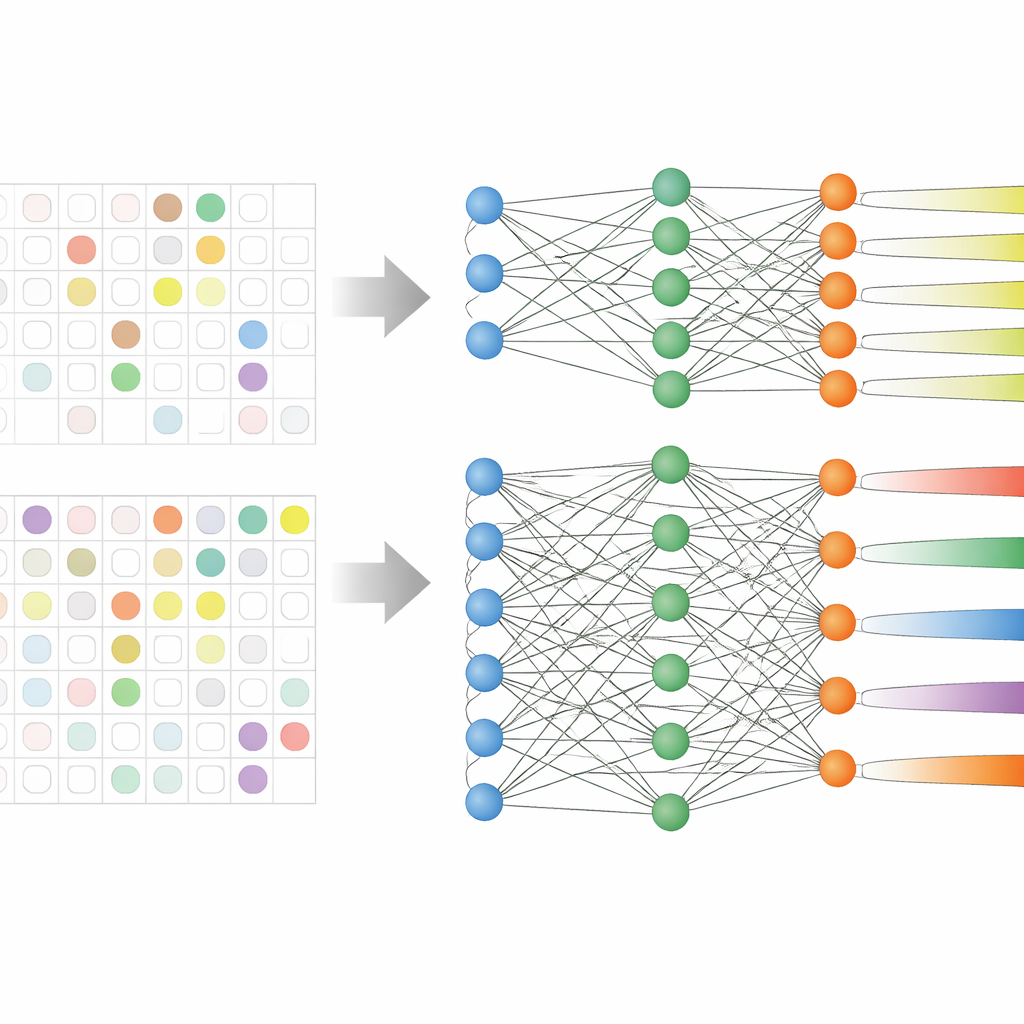
Teamet analyserade elektroniska patientjournaler från 59 551 vuxna patienter vid tre stora koreanska sjukhus under mer än ett decennium. Dessa journaler innehöll ålder, vitala parametrar, vårdtid, tidigare antibiotikaanvändning och, avgörande, tidigare odlingsresultat som visade vilka antibiotika som redan hade misslyckats. Istället för att träna nio separata modeller—en för varje antibiotikagrupp—använde de en strategi som kallas multiuppgiftsinlärning, vilket gör det möjligt för en enda modell att lära sig flera relaterade prediktionsuppgifter samtidigt. Två varianter testades: en med en gemensam kärna som förgrenar sig till separata utgångar för varje antibiotikagrupp (hard sharing), och en där uppgifterna är mer löst kopplade (soft sharing).
Att lösa problemet med ofullständiga labbresultat
Riktiga sjukhusdata är röriga: inte alla patienter testas mot varje antibiotikum. Tidigare studier slängde ofta bort dessa delvis etiketterade fall, vilket krympte datamängderna och bortsåg från mönster som sträcker sig över olika läkemedel. Här skrev forskarna om modellens inlärningsregel så att den helt enkelt hoppar över saknade labbresultat när den beräknar träningsfelet. Det gjorde att de kunde behålla nästan alla patienter i analysen, även när vissa antibiotikaresultat saknades. Särskilt den hårda delade modellen gynnades av denna uppsättning, eftersom den kunde lära sig gemensamma signaler för resistens samtidigt som den finjusterade sina prediktioner för varje läkemedelsgrupp.
Hur bra presterade modellerna?
När de testades på data från sjukhus de inte sett tidigare presterade multiuppgiftsmodellerna generellt bättre än mer traditionella metoder som logistisk regression och standard boosting-algoritmer. I genomsnitt visade hard-sharing-modellen den bästa balansen mellan noggrannhet och stabilitet över de nio antibiotikaklasserna, och den var särskilt stark för läkemedelsgrupper med den knappaste datamängden, såsom aminoglykosider. En separat analys som förklarar vilka egenskaper som driver prediktionerna visade att en patients tidigare resistens mot ett antibiotikum var den enskilt viktigaste faktorn, följt av resistens eller användning av relaterade läkemedel, samt ålder och vårdtid. Subgruppsanalyser visade att hard sharing fungerade bäst när tidigare odlingsresultat för ett visst antibiotikum fanns tillgängliga, medan soft sharing var bättre när sådan historik saknades.
Vad detta betyder för patienter och kliniker
Studien tyder på att ett smart utnyttjande av sjukhusjournaler kan ge tidiga, relativt pålitliga prognoser om antibiotikaresistens över flera stora läkemedelsfamiljer. Även blygsamma förbättringar i prediktionsnoggrannhet, applicerade på stora patientgrupper, kan hjälpa läkare att tidigare välja smalare, mer riktade antibiotika och tryggare trappa ned från breda läkemedel. Det kan i sin tur minska komplikationer, förkorta vårdtider och bromsa den bredare utvecklingen av resistens. Författarna påpekar att deras modell fortfarande behöver testas och förfinas i verkliga kliniska miljöer, särskilt när tidigare odlingsdata saknas, men menar att multiuppgiftsinlärning erbjuder ett lovande sätt att bättre utnyttja ofullständiga medicinska data och stödja mer varsam antibiotikaanvändning.
Citering: Kim, Y., Jeong, I., Park, JH. et al. Multi task learning based early prediction model for antibiotic resistance using multi institutional cohort data. Sci Rep 16, 11891 (2026). https://doi.org/10.1038/s41598-026-41185-z
Nyckelord: antibiotikaresistens, kliniskt beslutsstöd, elektroniska patientjournaler, maskininlärning, multiuppgiftsinlärning