Clear Sky Science · sv
MSF-VMDNet för flerkategori-segmentering av hela histologiska skivepitelskivor med ett multifrekvent dubbel‑encoder‑nätverk
Varför kartläggning av hudcancer är viktig
När läkare ställer diagnos på hudcancer studerar de ofta ultradetajlade mikroskopbilder av färgade vävnadssnitt. Dessa bilder visar inte bara tumören utan också många typer av normal hudstruktur som är tätt sammanflätade. Att manuellt rita exakta gränser runt varje region är tidskrävande och kan variera mellan specialister. Denna studie presenterar en ny datorbaserad metod utformad för att automatiskt separera dessa sammanflätade vävnader med mycket hög noggrannhet, vilket potentiellt sparar tid och gör diagnostiken mer konsekvent.
Från enkla fläckar till invecklad vävnad
Hudcancer är en av de vanligaste cancerformerna globalt, delvis drivet av ökad exponering för ultraviolett ljus. Modern diagnostik börjar oftast med dermatoskopi, en förstorad hudbild, och fortsätter ofta med en biopsi: en liten hudbit tas bort, färgas och undersöks i mikroskop. I dessa helslidesbilder slingrar sig tumörer genom lager som överhuden, djupare bindväv, hårsäckar, svettkörtlar och fett. Många av dessa områden liknar varandra i färg och textur, och deras gränser kan vara otydliga, vilket gör det svårt även för experter att tydligt avgränsa tumör från frisk vävnad.
Ett nytt sätt att tolka komplexa bilder
De flesta tidigare datorverktyg behandlade problemet som att färglägga en bild med bara två kritor: ”lesion” och ”inte lesion”. Det kan fungera för enklare ytfoton, men brister när en hel skiva måste delas in i många vävnadstyper samtidigt. Författarna fokuserar på en utmanande dataset med icke‑melanom hudcancer där varje bild måste delas upp i upp till tio olika vävnadsklasser. Målet är att bygga ett system som kan förstå vävnadens övergripande struktur samtidigt som det fångar små detaljer vid gränserna — något traditionella neurala nätverk ofta har svårt att balansera.
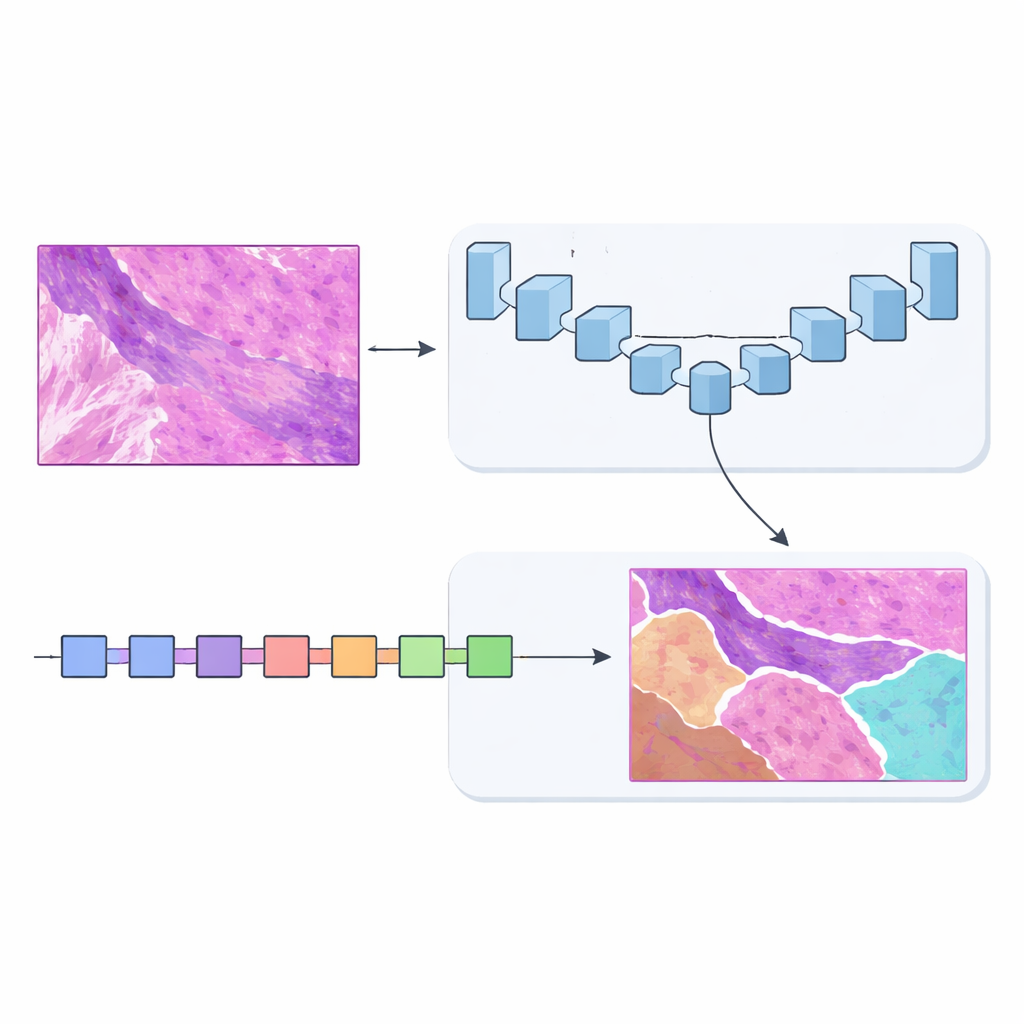
Två hjärnor är bättre än en
För att lösa detta konstruerade teamet MSF‑VMDNet, ett dubbel‑encoder‑nätverk som kan ses som två kompletterande ”hjärnor” som granskar samma helskiva parallellt. En gren bygger på U‑Net, en populär modell inom medicinsk bildbehandling som är skicklig på att fånga finlokala detaljer. Författarna förstärker den med en spektral modul som konverterar bilden till en uppsättning frekvenser — vissa beskriver långsamma, mjuka förändringar, andra fångar skarpa kanter och texturer — för att sedan kombinera dem igen och stärka klassgränserna. Samtidigt skannar en andra gren, byggd på en nyare metod kallad Vision Mamba, bilden på ett mer strömlinjeformat sätt och modellerar effektivt long‑range‑relationer så att avlägsna men relaterade regioner kan informera varandra.
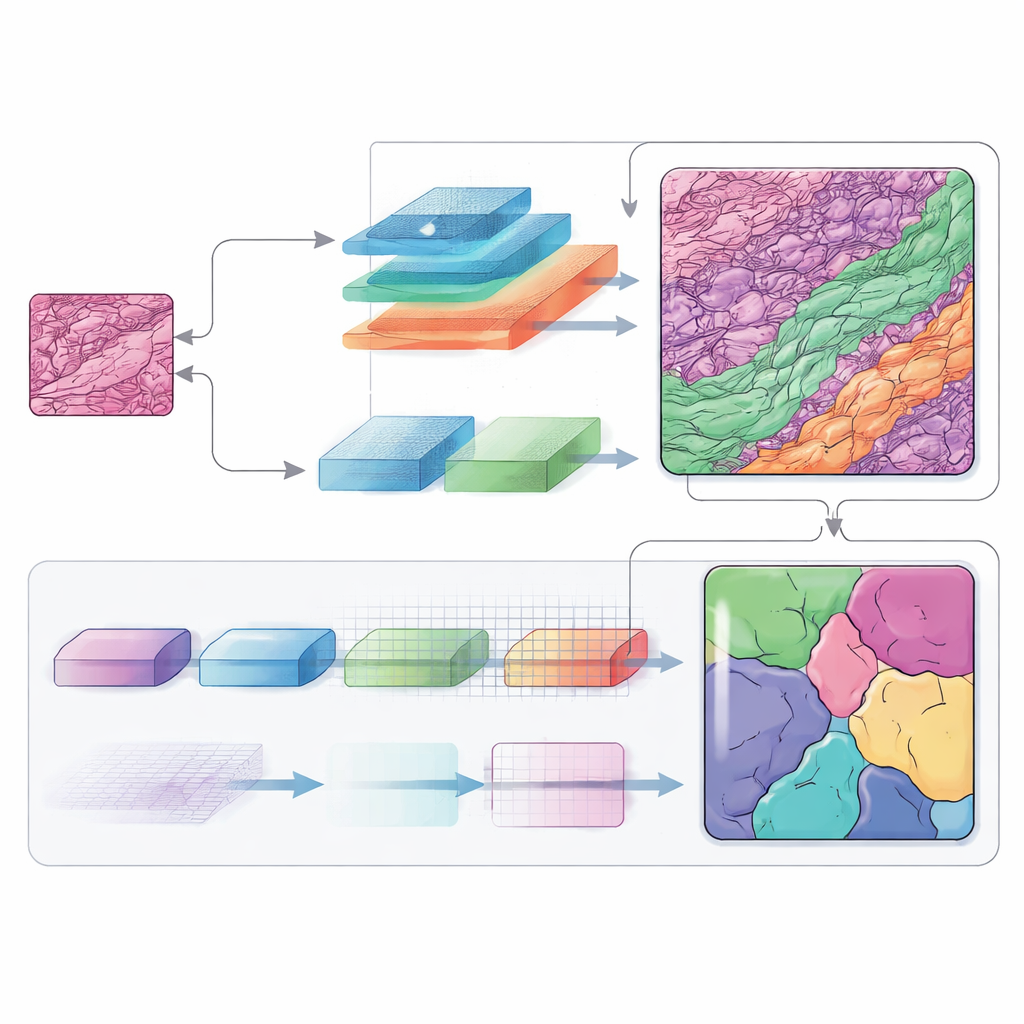
Lyssna på många frekvenser samtidigt
Frekvensinformation spelar en central roll i denna arkitektur. Genom att växla mellan vanlig bildrepresentation och en frekvensbaserad vy kan nätverket behandla breda former och små strukturer annorlunda. Lågfrekventa komponenter hjälper det att förstå tumörens övergripande layout och de omgivande hudlagren, medan högfrekventa komponenter skärper kanterna där en vävnadstyp slutar och en annan börjar. Noggrant utformade moduler slår ihop dessa vyer tillbaka till en spatial karta, och en extra avkodningsblock (kallat SCConv) filtrerar bort redundanta signaler samtidigt som verkligt informativa mönster förstärks. Resultatet blir en renare, mer säker karta över varje vävnadsregion.
Hur bra fungerar det i praktiken?
Forskarlaget testade MSF‑VMDNet på datasetet för icke‑melanom hudcancer och jämförde det med en rad ledande segmenteringsmodeller, inklusive klassisk U‑Net, transformer‑baserade metoder och andra Vision Mamba‑hybrider. Deras system producerade tydligare tumörkonturer och färre fel i svåra områden där tumör, hårsäckar och inflammerad vävnad flätas samman. På standardmått för överlappning överträffade det alla konkurrenter och nådde omkring 95 procent överensstämmelse med expert‑ritade masker. För att kontrollera om metoden generaliserar bortom ett laboratorium och en cancertyp utvärderade teamet den också på tre ytterligare samlingar: dermatoskopiska foton av hudlesioner, mikroskopbilder av olika typer av cellkärnor och CT‑skanningar av bukorgan. I samtliga fall förblev metoden högt exakt och presterade statistiskt bättre än starka baslinjer.
Vad detta betyder för patienter och läkare
Enkelt uttryckt är MSF‑VMDNet en automatiserad kartmakare för medicinska bilder som kan separera tumörer från det täta landskapet av normal vävnad med ovanlig precision. Även om den inte ersätter patologens bedömning kan den ge en snabb, detaljerad utgångspunkt, minska det manuella arbete som krävs och bidra till att subtila tumörområden inte förbises. Eftersom samma angreppssätt fungerar väl på mycket olika typer av medicinska bilder kan det bli ett mångsidigt verktyg för många diagnostiska uppgifter. Med fortsatt utveckling och integration av klinisk information kan system som detta stödja mer tillförlitlig gradindelning av hudcancer och i förlängningen bättre underbyggda behandlingsval.
Citering: Zhang, J., Pu, Q., Tian, J. et al. MSF-VMDNet for multi class segmentation of skin cancer whole slide images using a multi frequency dual encoder network. Sci Rep 16, 11722 (2026). https://doi.org/10.1038/s41598-026-40044-1
Nyckelord: hudcanceravbildning, medicinsk bildsegmentering, djupinlärning i patologi, histopatologisk analys, AI-diagnostik