Clear Sky Science · fr
MSF-VMDNet pour la segmentation multiclasses d’images entières de cancer de la peau à l’aide d’un réseau double encodeur multi-fréquence
Pourquoi il est important de cartographier le cancer de la peau
Lorsque les médecins diagnostiquent un cancer de la peau, ils examinent souvent des images microscopiques ultra-détaillées de coupes de tissu colorées. Ces images montrent non seulement la tumeur, mais aussi de nombreuses structures cutanées normales étroitement entremêlées. Tracer manuellement des limites précises autour de chaque zone est lent et peut varier d’un spécialiste à l’autre. Cette étude présente une nouvelle méthode informatique conçue pour séparer automatiquement ces tissus entremêlés avec une très grande précision, ce qui pourrait permettre de gagner du temps et d’homogénéiser les diagnostics.
Des taches simples aux tissus emmêlés
Le cancer de la peau fait partie des cancers les plus fréquents dans le monde, en partie à cause de l’exposition accrue aux ultraviolets. Le diagnostic moderne débute généralement par la dermoscopie, une photographie de peau agrandie, et se poursuit souvent par une biopsie : un petit morceau de peau est prélevé, coloré et examiné au microscope. Dans ces images de lames entières, les tumeurs serpentent à travers des couches telles que l’épiderme, le tissu conjonctif profond, les follicules pileux, les glandes sudoripares et le tissu adipeux. Beaucoup de ces régions se ressemblent par la couleur et la texture, et leurs frontières peuvent être floues, rendant difficile, même pour les experts, la distinction nette entre tumeur et tissu sain.
Une nouvelle façon d’interpréter des images complexes
La plupart des outils informatiques antérieurs traitaient le problème comme si l’on coloriait une image avec seulement deux crayons : « lésion » et « non lésion ». Cela peut fonctionner pour des photos de surface plus simples, mais échoue quand une lame doit être divisée en de nombreux types de tissus à la fois. Les auteurs se concentrent sur un jeu de données difficile de cancers cutanés non mélanocytaires dans lequel chaque image doit être segmentée en jusqu’à dix classes tissulaires distinctes. Leur objectif est de construire un système capable de comprendre la configuration globale du tissu tout en capturant aussi les détails infimes le long des frontières — un équilibre souvent difficile à atteindre pour les réseaux neuronaux traditionnels.
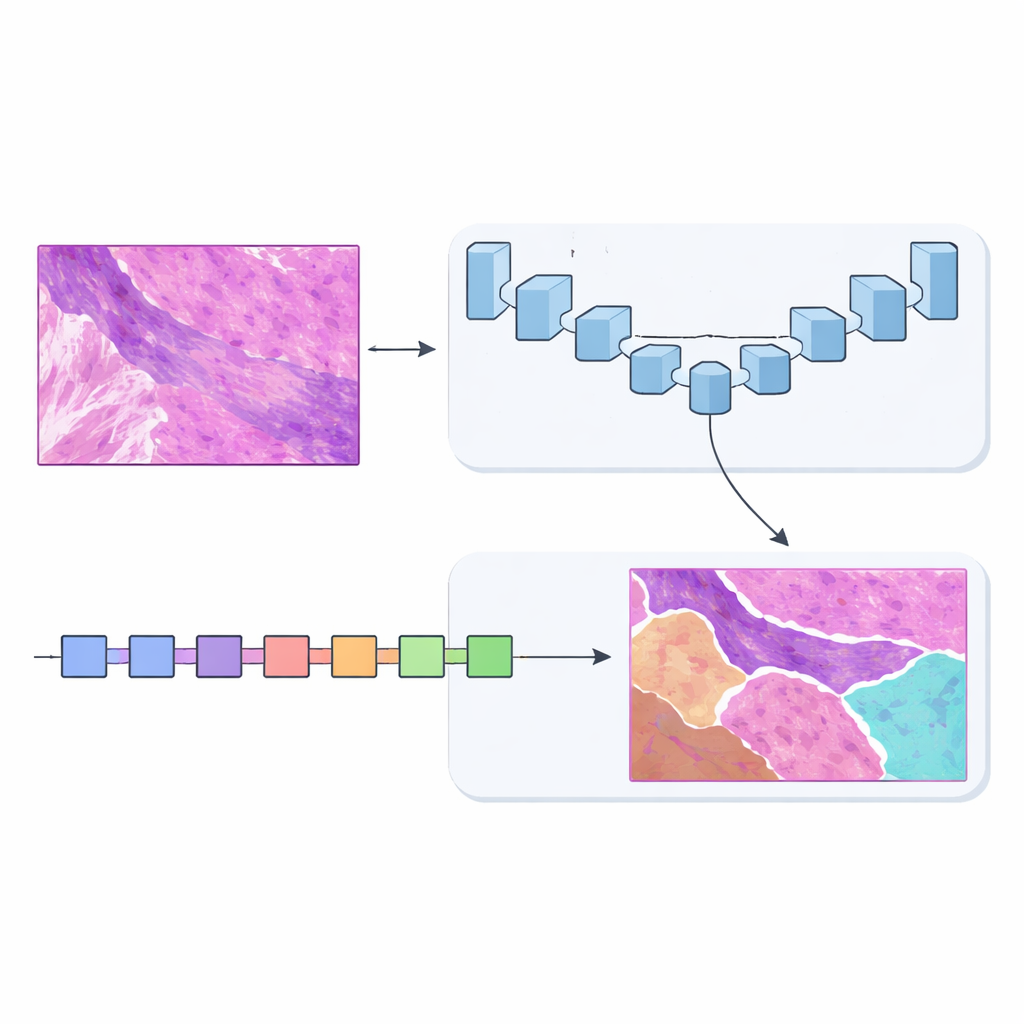
Deux cerveaux valent mieux qu’un
Pour résoudre ce problème, l’équipe a conçu MSF-VMDNet, un réseau à double encodeur qui peut être vu comme deux « cerveaux » complémentaires examinant la même lame en parallèle. Une branche est basée sur U‑Net, un modèle d’imagerie médicale populaire qui excelle à capter les détails locaux fins. Les auteurs l’enrichissent d’un module spectral qui convertit l’image en un ensemble de fréquences — certaines décrivant des variations lentes et lisses, d’autres captant des arêtes et des textures nettes — puis les recombine pour renforcer les frontières de classe. Parallèlement, une seconde branche, fondée sur une approche plus récente appelée Vision Mamba, parcourt la lame de manière plus fluide, modélisant efficacement les relations à longue portée pour que des régions éloignées mais liées puissent s’informer mutuellement.
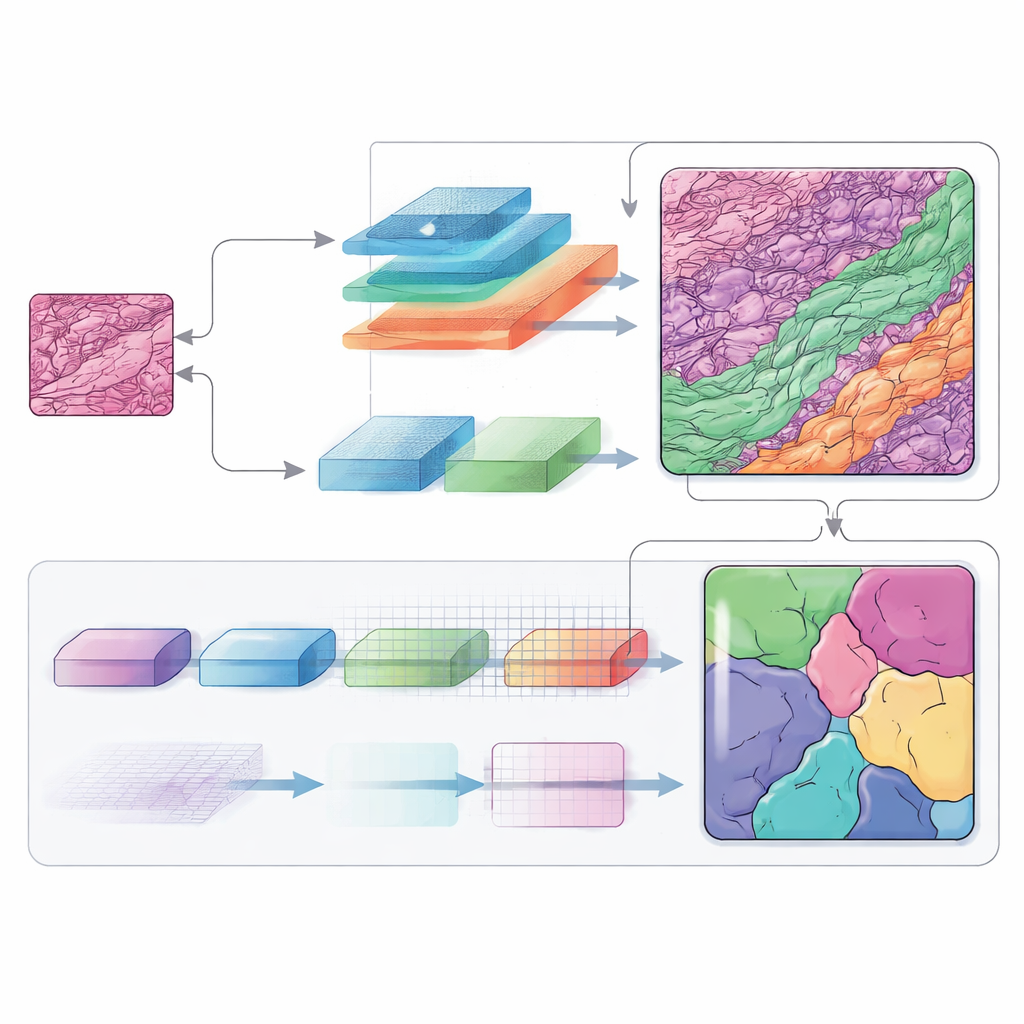
Écouter de nombreuses fréquences à la fois
L’information fréquentielle joue un rôle central dans cette architecture. En passant de l’espace image ordinaire à une vue basée sur les fréquences, le réseau peut traiter différemment les formes larges et les structures fines. Les composantes basse fréquence l’aident à comprendre l’agencement général de la tumeur et des couches cutanées environnantes, tandis que les composantes haute fréquence affûtent les bords où un type de tissu se termine et un autre commence. Des modules conçus avec soin fusionnent ces vues en une carte spatiale, et un bloc de décodage supplémentaire (appelé SCConv) filtre les signaux redondants tout en renforçant les motifs réellement informatifs. Le résultat est une carte de chaque région tissulaire plus nette et plus sûre.
Quelle est son efficacité en pratique ?
Les chercheurs ont testé MSF‑VMDNet sur le jeu de données de cancers cutanés non mélanocytaires et l’ont comparé à un large éventail de modèles de segmentation de pointe, y compris le classique U‑Net, des méthodes basées sur les Transformers et d’autres hybrides Vision Mamba. Leur système a produit des contours tumoraux plus clairs et moins d’erreurs dans les zones délicates où tumeur, follicules pileux et tissus inflammés s’entremêlent. Sur des mesures d’overlap standard, il a surpassé tous les concurrents, atteignant environ 95 % d’accord avec les masques tracés par des experts. Pour vérifier la capacité de généralisation au-delà d’un seul laboratoire et d’un seul type de cancer, l’équipe l’a également évalué sur trois autres collections : des photos dermoscopiques de lésions cutanées, des images microscopiques de différents types de noyaux cellulaires et des scans CT d’organes abdominaux. Dans tous les cas, la méthode est restée très précise et a dépassé statistiquement des bases de référence solides.
Ce que cela signifie pour les patients et les médecins
En termes simples, MSF‑VMDNet est un cartographe automatisé pour les images médicales capable de séparer les tumeurs du paysage dense des tissus normaux avec une précision inhabituelle. Bien qu’il ne remplace pas le jugement des pathologistes, il peut fournir un point de départ rapide et détaillé, réduire le travail manuel requis et aider à garantir que des régions tumorales subtiles ne soient pas négligées. Étant donné que la même approche fonctionne bien sur des types d’images médicales très différents, elle pourrait devenir un outil polyvalent pour de nombreuses tâches diagnostiques. Avec des développements supplémentaires et l’intégration d’informations cliniques, des systèmes de ce type pourraient soutenir une gradation plus fiable des cancers cutanés et, ultimement, des décisions thérapeutiques mieux informées.
Citation: Zhang, J., Pu, Q., Tian, J. et al. MSF-VMDNet for multi class segmentation of skin cancer whole slide images using a multi frequency dual encoder network. Sci Rep 16, 11722 (2026). https://doi.org/10.1038/s41598-026-40044-1
Mots-clés: imagerie du cancer de la peau, segmentation d’images médicales, apprentissage profond en pathologie, analyse histopathologique, diagnostic par IA