Clear Sky Science · pt
MSF-VMDNet para segmentação multiclasses de imagens de lâminas inteiras de câncer de pele usando uma rede de duplo codificador multifaixa
Por que mapear o câncer de pele é importante
Quando médicos diagnosticam câncer de pele, eles costumam analisar imagens microscópicas ultra-detalhadas de fatias de tecido coradas. Essas imagens mostram não apenas o tumor, mas também muitos tipos de estruturas cutâneas normais entrelaçadas. Traçar contornos precisos de cada região manualmente é lento e pode variar entre especialistas. Este estudo apresenta um novo método computacional projetado para separar automaticamente esses tecidos confusos com alta precisão, potencialmente economizando tempo e tornando os diagnósticos mais consistentes.
De manchas simples a tecidos entrelaçados
O câncer de pele está entre os tipos mais comuns no mundo, impulsionado em parte pelo aumento da exposição à radiação ultravioleta. O diagnóstico moderno geralmente começa com dermatoscopia, um tipo de fotografia ampliada da pele, e frequentemente segue com uma biópsia: um pequeno fragmento de pele é removido, corado e examinado ao microscópio. Nessas imagens de lâmina inteira, os tumores serpenteiam por camadas como a epiderme, tecido conjuntivo mais profundo, folículos pilosos, glândulas sudoríparas e gordura. Muitas dessas regiões têm aparência semelhante em cor e textura, e seus limites podem ser difusos, tornando difícil até para especialistas separar claramente tumor de tecido saudável.
Uma nova forma de ler imagens complexas
A maioria das ferramentas anteriores tratava o problema como colorir uma imagem com apenas dois lápis de cor: “lesão” e “não lesão”. Isso pode funcionar para fotos de superfície mais simples, mas falha quando uma lâmina precisa ser dividida em muitos tipos de tecido ao mesmo tempo. Os autores focam em um conjunto de dados desafiador de cânceres de pele não melanomas em que cada imagem deve ser segmentada em até dez classes de tecido distintas. O objetivo é construir um sistema capaz de entender a disposição global do tecido ao mesmo tempo em que captura detalhes minúsculos nas bordas — algo que redes neurais tradicionais frequentemente têm dificuldade em equilibrar.
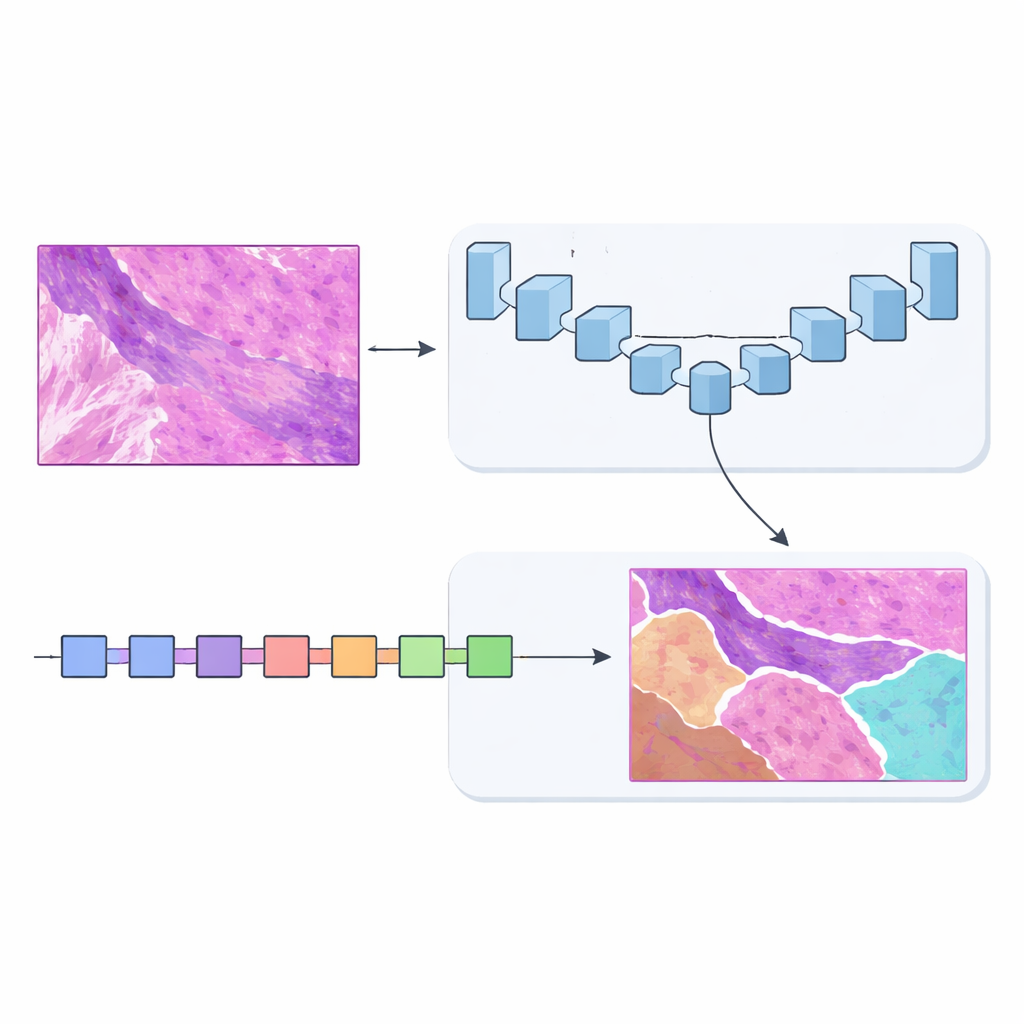
Dois cérebros valem mais que um
Para resolver isso, a equipe projetou a MSF-VMDNet, uma rede de duplo codificador que pode ser vista como dois “cérebros” complementares examinando a mesma lâmina em paralelo. Um ramo é baseado no U-Net, um modelo popular em imagem médica que se destaca em capturar detalhes locais finos. Os autores o aprimoram com um módulo espectral que converte a imagem em um conjunto de frequências — algumas descrevem mudanças lentas e suaves, outras capturam arestas e texturas agudas — e então as recombina para reforçar as fronteiras entre classes. Ao mesmo tempo, um segundo ramo, construído sobre uma abordagem mais recente chamada Vision Mamba, analisa a lâmina de forma mais enxuta, modelando eficientemente relações de longo alcance para que regiões distantes, mas relacionadas, possam informar umas às outras.
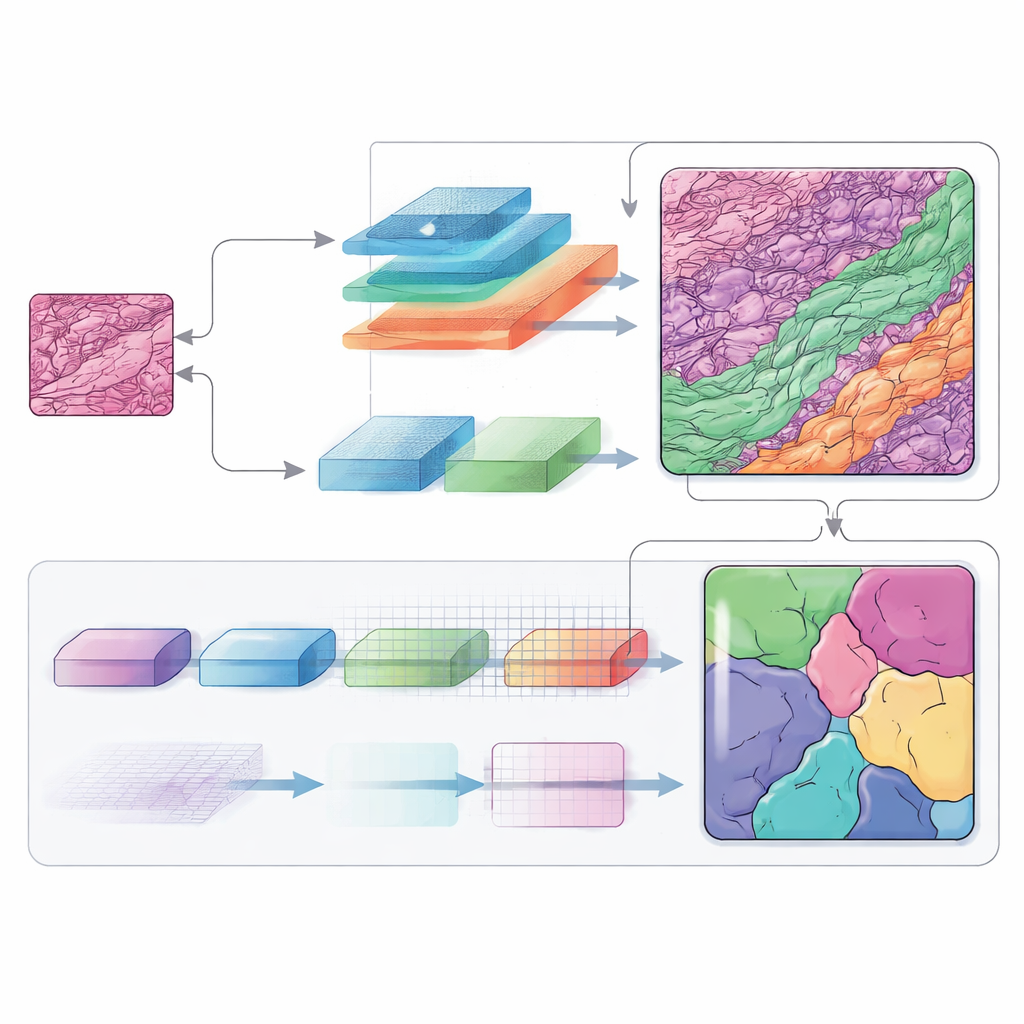
Ouvindo muitas frequências ao mesmo tempo
A informação de frequência desempenha um papel central nessa arquitetura. Ao alternar entre o espaço de imagem ordinário e uma visão baseada em frequências, a rede consegue tratar formas amplas e estruturas minúsculas de maneira distinta. Componentes de baixa frequência ajudam a entender a disposição geral do tumor e das camadas cutâneas circundantes, enquanto componentes de alta frequência afinam as bordas onde um tipo de tecido termina e outro começa. Módulos cuidadosamente projetados mesclam essas visões de volta em um mapa espacial, e um bloco adicional de decodificação (chamado SCConv) filtra sinais redundantes enquanto reforça padrões realmente informativos. O resultado é um mapa de cada região tecidual mais limpo e com maior confiança.
Qual é o desempenho na prática?
Os pesquisadores testaram a MSF-VMDNet no conjunto de dados de câncer de pele não melanoma e a compararam com uma ampla gama de modelos de segmentação de ponta, incluindo o clássico U-Net, métodos baseados em Transformers e outros híbridos Vision Mamba. O sistema produziu contornos de tumor mais nítidos e menos erros em áreas difíceis onde tumor, folículos pilosos e tecido inflamado se entrelaçam. Em medidas padrão de sobreposição, superou todos os concorrentes, atingindo cerca de 95% de concordância com máscaras desenhadas por especialistas. Para verificar se o método generaliza além de um laboratório e um tipo de câncer, a equipe também o avaliou em três coleções adicionais: fotos dermatoscópicas de lesões cutâneas, imagens microscópicas de diferentes tipos de núcleos celulares e tomografias computadorizadas de órgãos abdominais. Em todos os casos, o método permaneceu altamente preciso e estatisticamente superior a baselines fortes.
O que isso significa para pacientes e médicos
Em termos simples, a MSF-VMDNet é um gerador automático de mapas para imagens médicas que pode separar tumores da paisagem congestionada de tecidos normais com precisão incomum. Embora não substitua o julgamento dos patologistas, pode oferecer um ponto de partida rápido e detalhado, reduzindo o esforço manual necessário e ajudando a garantir que regiões tumorais sutis não sejam negligenciadas. Como a mesma abordagem funciona bem em tipos muito diferentes de imagens médicas, ela pode se tornar uma ferramenta versátil para muitas tarefas diagnósticas. Com desenvolvimento adicional e integração de informações clínicas, sistemas como este podem apoiar uma classificação de câncer de pele mais confiável e, em última instância, escolhas de tratamento mais bem informadas.
Citação: Zhang, J., Pu, Q., Tian, J. et al. MSF-VMDNet for multi class segmentation of skin cancer whole slide images using a multi frequency dual encoder network. Sci Rep 16, 11722 (2026). https://doi.org/10.1038/s41598-026-40044-1
Palavras-chave: imagens de câncer de pele, segmentação de imagem médica, aprendizado profundo em patologia, análise histopatológica, diagnóstico por IA