Clear Sky Science · sv
Förbättrad förutsägelse av läkemedel–sjukdomsassociationer genom multimodal dataintegration och meta‑paths‑styrd global‑lokal funktionsfusion
Varför det är viktigt att hitta nya användningsområden för befintliga läkemedel
Att utveckla ett helt nytt läkemedel från grunden är långsamt, riskfyllt och extremt kostsamt. Ändå finns det i dagens apotek många läkemedel som kanske också skulle kunna behandla andra sjukdomar, om vi bara kunde upptäcka dessa ytterligare användningar. Denna studie presenterar MedPathEx, en datorbaserad metod som silar igenom stora samlingar biomedicinska data för att förutsäga vilka befintliga läkemedel som sannolikt kan verka mot vilka sjukdomar, vilket potentiellt kan påskynda sökandet efter nya behandlingar och göra bättre användning av läkemedel vi redan har.
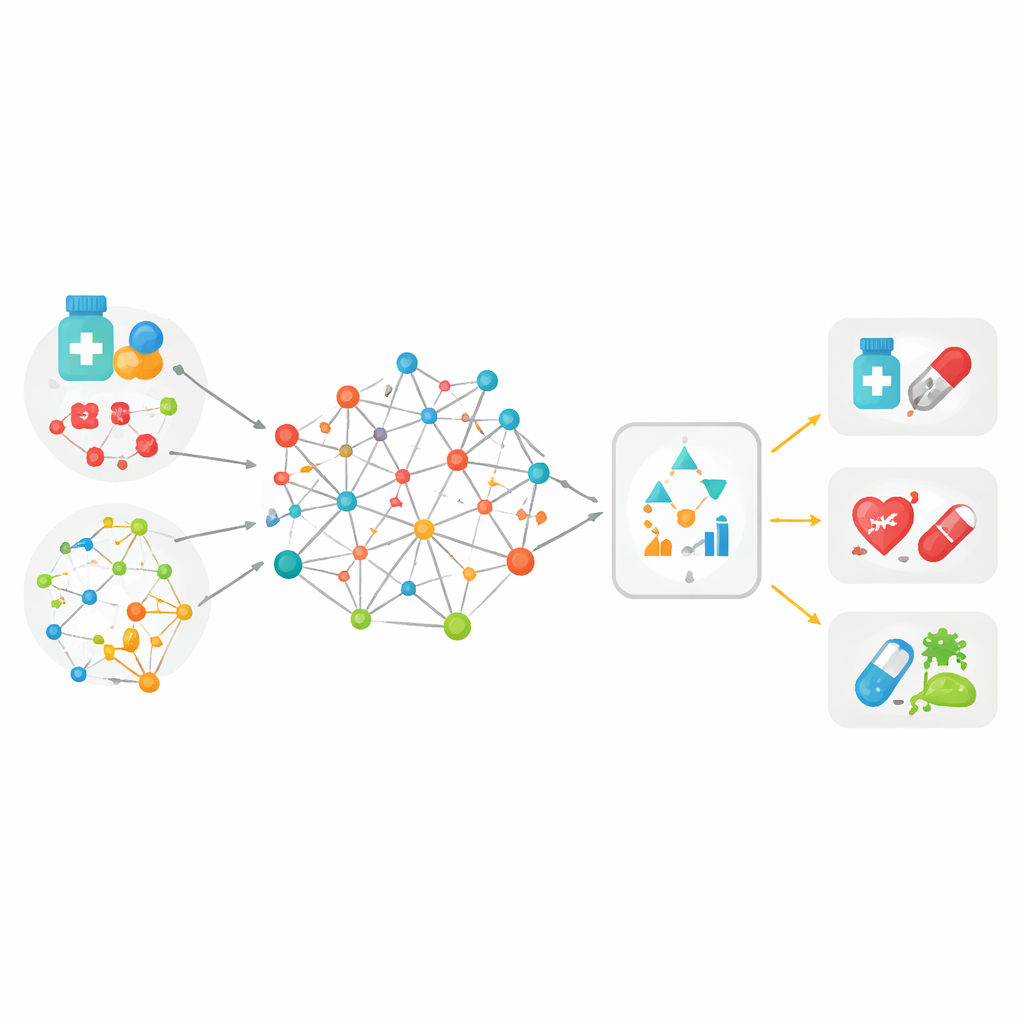
Att föra många ledtrådar samman i en stor karta
De flesta tidigare verktyg för att matcha läkemedel med sjukdomar förlitade sig på bara en typ av information—till exempel hur lika två läkemedelsmolekyler ser ut, eller hur nära två sjukdomar är i patientjournaler. MedPathEx bygger på idén att ingen enskild ledtråd är tillräcklig. Författarna konstruerar en stor ”karta” som länkar tre typer av aktörer: läkemedel, sjukdomar och gener. Ovanpå dessa länkar lägger de flera slags ledtrådar: hur läkemedelsmolekyler är uppbyggda, hur de klassificeras i terapi, vilka biverkningar de orsakar, hur sjukdomar framträder hos patienter och i medicinskt språk, samt vad som är känt om genfunktion. Genom att väva in all denna multimodala information i ett heterogent nätverk beskrivs varje läkemedel, sjukdom och gen på ett rikare och mer realistiskt sätt än tidigare.
Att se både grannskapet och hela staden
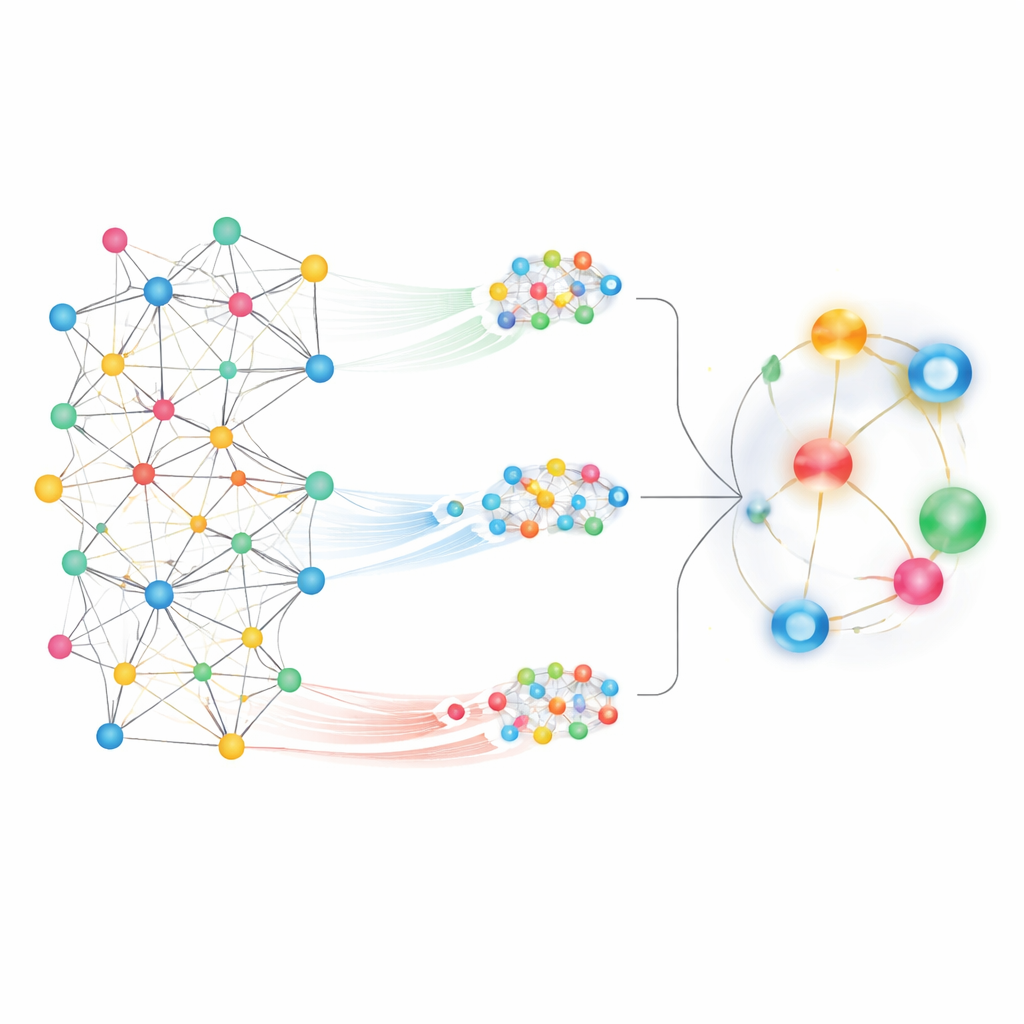
När man betraktar en så stor karta är en utmaning att avgöra vilka mönster som är betydelsefulla. MedPathEx angriper detta genom att kombinera två kompletterande vyer av nätverket. För det första zoomar metoden in på lokala grannskap och följer korta, meningsfulla stigar—till exempel läkemedel → gen → sjukdom—för att fånga hur specifika gener kan koppla ett läkemedel till en sjukdom. Dessa mönstrade vandringar, kallade meta‑paths, framhäver finmaskiga relationer. För det andra zoomar metoden ut för att beakta den globala bilden, vilket tillåter varje nod att ”uppmärksamma” många andra över hela kartan. Denna globala uppmärksamhetsvy fångar bredare trender och långdistanskopplingar som skulle missas om man bara följde lokala stigar.
Att blanda olika vyer till en enda signal
För att omvandla dessa nätverksvyer till förutsägelser använder MedPathEx moderna neurala nätverkstekniker för att konvertera den komplexa kartan till kompakta numeriska fingeravtryck för varje läkemedel, sjukdom och gen. En del av modellen lär sig från likhetsgrafer byggda inom varje typ (läkemedel–läkemedel, sjukdom–sjukdom, gen–gen). En annan del fokuserar på de lokala meta‑path‑grannskapen, medan en tredje fångar den globala strukturen i hela nätverket. Modellen lär sig sedan hur mycket vikt som ska ges till varje informationskälla och fusionerar dem till en enda, sammansatt representation för varje nod. När systemet jämför de sammansatta fingeravtrycken för ett givet läkemedel och en sjukdom ger det en poäng som speglar hur sannolikt det är att paret är verkligt kopplat i den verkliga världen.
Testa prestanda och undersöka vad som betyder mest
Forskarna testade MedPathEx med hjälp av offentliga databaser som katalogiserar hundratusentals kända länkar mellan tusentals läkemedel, sjukdomar och gener. I rigorös femfaldig korsvalidering presterade MedPathEx bättre än en rad konkurrerande metoder, inklusive klassiska maskininlärningsmetoder och flera avancerade grafbaserade modeller. Mått på noggrannhet såsom AUC, genomsnittlig precision och F1‑poäng var alla högre, vilket visar att metoden mer tillförlitligt skiljer sanna läkemedel–sjukdomspar från falska. När komponenter togs bort en efter en sjönk prestandan, särskilt när antingen den lokala meta‑path‑vyn eller den globala uppmärksamhetsvyn togs bort, vilket understryker att båda perspektiven är väsentliga. Analysen visade också att den lokala meta‑path‑informationen bidrar mest, medan globala och likhetsbaserade funktioner ger viktiga förfiningar.
Exempel från verkligheten: hjärtsjukdom och högt blodtryck
Utöver siffror kontrollerade författarna om MedPathEx:s högt rankade förslag för två vanliga tillstånd—kranskärlssjukdom och hypertoni—stämde överens med vad som är känt i medicinsk litteratur. För varje sjukdom föreslog systemet flera läkemedel, varav några redan används kliniskt för relaterade hjärtproblem, vilket ger trovärdighet åt metodiken. Andra är mindre uppenbara kandidater som ändå visar biologiska kopplingar, till exempel genom att påverka inflammation, blodkärlsfunktion eller plackuppbyggnad i kärlen. Nätverksdiagram över läkemedel, gener och sjukdomar illustrerar hur dessa läkemedel kan påverka sjukdomsrelaterade vägar, och pekar på plausibla mekanismer som kan utforskas i laboratorie‑ eller kliniska studier.
Vad detta innebär för framtidens läkemedel
Enkelt uttryckt visar MedPathEx att genom att kombinera många källor av biomedicinska data och betrakta både lokala och globala mönster i hur läkemedel, gener och sjukdomar hänger ihop kan datorer göra ett bättre jobb med att gissa vilka mediciner som kan hjälpa vilka sjukdomar. Även om detta verktyg inte ersätter kliniska prövningar eller verklig testning kan det begränsa det stora sökutrymmet och lyfta fram lovande läkemedelskandidater—särskilt för komplexa sjukdomar som hjärtsjukdom och högt blodtryck. När mer detaljerad biologisk data blir tillgänglig och sådana modeller valideras vidare kan tillvägagångssätt som MedPathEx bli kraftfulla partners i arbetet med att återanvända befintliga läkemedel och utforma mer effektiva behandlingsstrategier.
Citering: Wu, S., Wang, W., Jiao, H. et al. Enhanced drug disease association prediction through multimodal data integration and meta path guided global local feature fusion. Sci Rep 16, 11038 (2026). https://doi.org/10.1038/s41598-026-36223-9
Nyckelord: läkemedelsomplacering, läkemedel–sjukdomsassociationer, heterogena nätverk, grafneuralnätverk, beräkningsbaserad läkemedelsupptäckt