Clear Sky Science · pt
Predição aprimorada de associações droga-doença por meio da integração multimodal de dados e fusão global-local de características guiada por meta-caminhos
Por que encontrar novos usos para medicamentos antigos importa
Desenvolver um medicamento novo do zero é lento, arriscado e extremamente caro. Ainda assim, escondidos nas farmácias atuais existem muitos fármacos que também poderiam ajudar a tratar outras doenças, se conseguirmos descobrir esses usos adicionais. Este estudo apresenta o MedPathEx, uma abordagem computacional que vasculha grandes conjuntos de dados biomédicos para prever quais medicamentos existentes são provavelmente eficazes para quais doenças, potencialmente acelerando a busca por novos tratamentos e aproveitando melhor remédios que já temos.
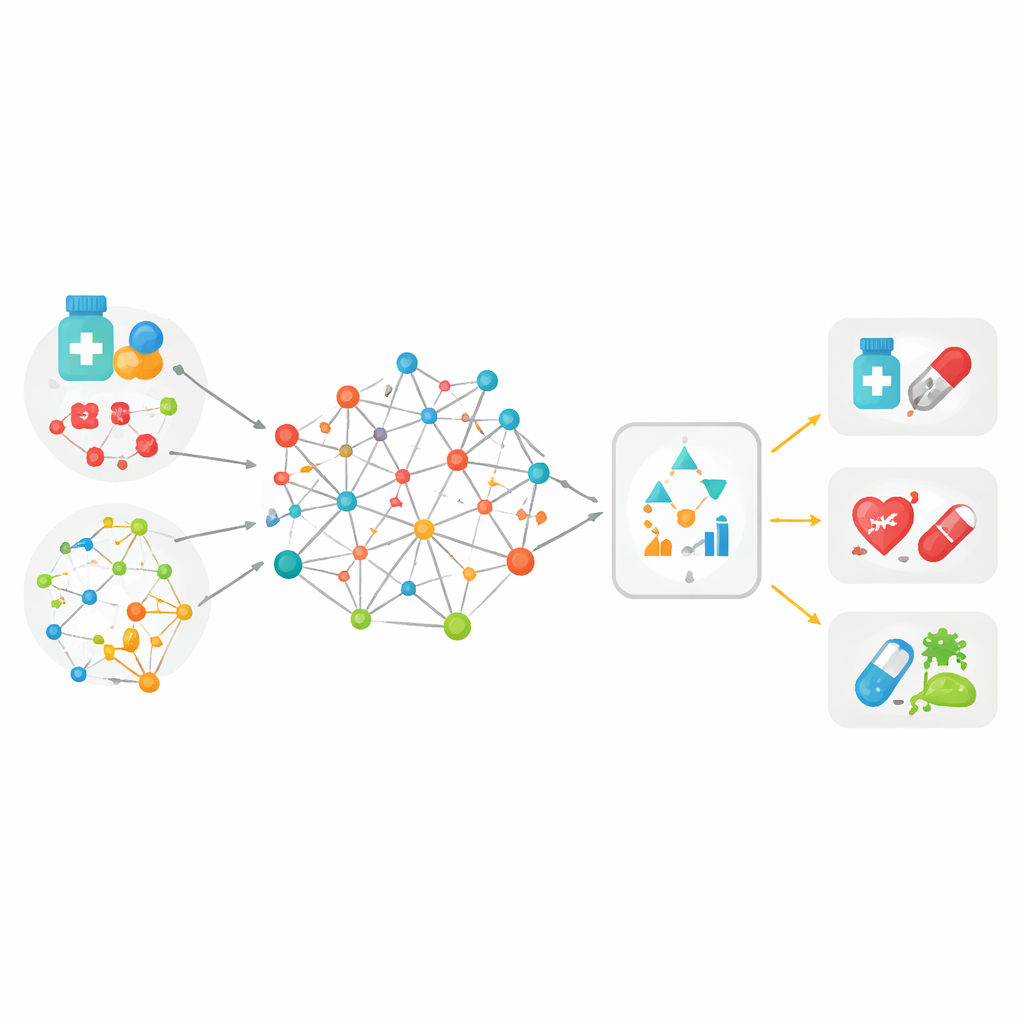
Reunindo muitas pistas em um grande mapa
A maioria das ferramentas anteriores para casar medicamentos a doenças baseava-se em apenas um tipo de informação — por exemplo, quão semelhantes são duas moléculas de fármaco, ou quão próximas duas doenças aparecem em registros médicos. O MedPathEx parte da ideia de que nenhuma pista isolada é suficiente. Os autores constroem um grande “mapa” que conecta três tipos de elementos: medicamentos, doenças e genes. Sobre essas ligações, eles sobrepõem múltiplos tipos de pistas: como as moléculas dos fármacos são construídas, como são classificadas terapeuticamente, quais efeitos colaterais causam, como as doenças se manifestam em pacientes e na linguagem médica, e o que se sabe sobre a função gênica. Ao entrelaçar todas essas informações multimodais em uma rede heterogênea, cada medicamento, doença e gene é descrito de forma mais rica e realista do que antes.
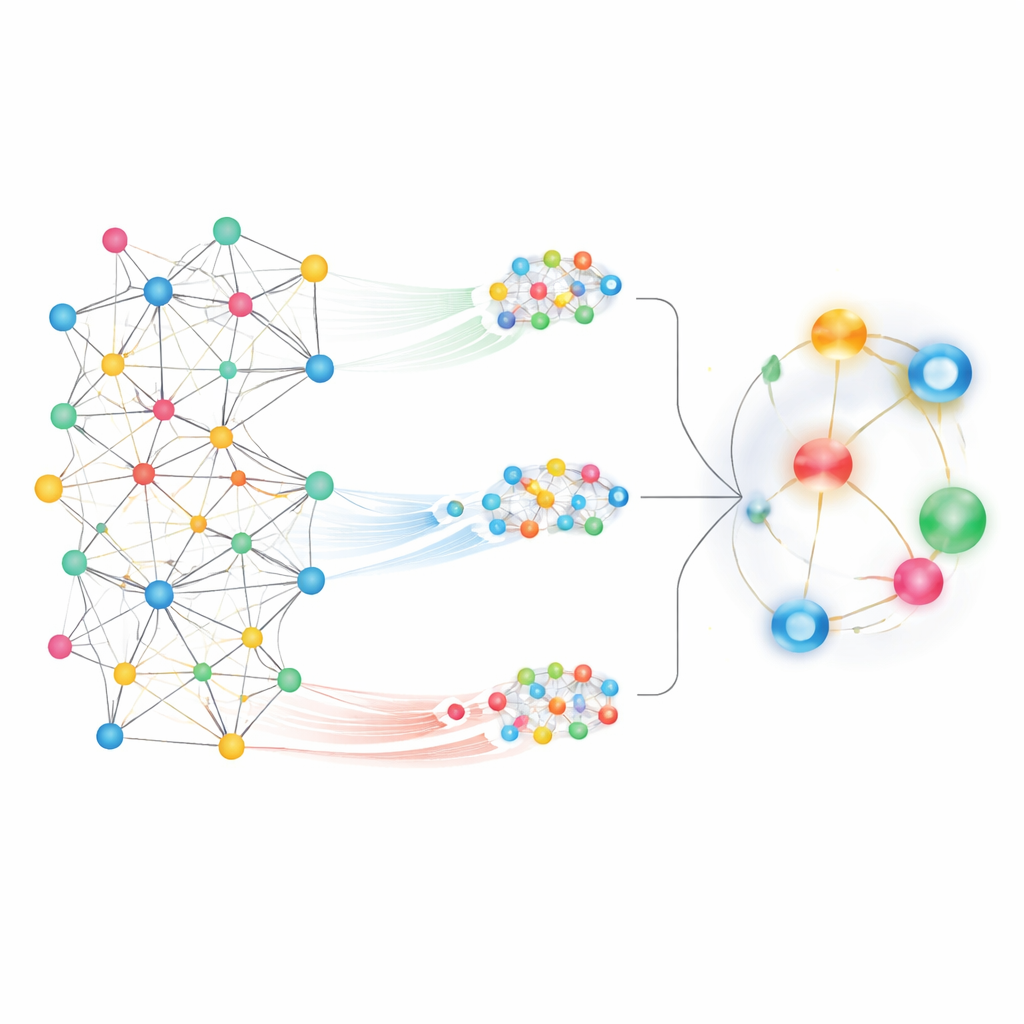
Vendo tanto o bairro quanto a cidade inteira
Ao olhar para um mapa tão grande, um desafio é decidir quais padrões importam. O MedPathEx enfrenta isso combinando duas visões complementares da rede. Primeiro, ele amplia as vizinhanças locais, traçando caminhos curtos e significativos — por exemplo, medicamento → gene → doença — para capturar como genes específicos podem conectar um fármaco a uma enfermidade. Esses percursos padronizados, chamados meta-caminhos, destacam relações de granularidade fina. Em segundo lugar, o método afasta o zoom para considerar o quadro global, permitindo que cada nó “preste atenção” a muitos outros através de todo o mapa. Essa visão de atenção global capta tendências mais amplas e conexões de longo alcance que seriam perdidas ao seguir apenas caminhos locais.
Mesclando diferentes visões em um único sinal
Para transformar essas visões de rede em predições, o MedPathEx usa técnicas modernas de redes neurais para converter o mapa complexo em impressões numéricas compactas para cada medicamento, doença e gene. Uma parte do modelo aprende a partir de grafos de similaridade construídos dentro de cada tipo (medicamento–medicamento, doença–doença, gene–gene). Outra parte foca nas vizinhanças locais de meta-caminhos, enquanto uma terceira captura a estrutura global de toda a rede. O modelo então aprende quanto peso dar a cada uma dessas fontes e as funde em uma representação combinada única para cada nó. Quando o sistema compara as impressões combinadas de um determinado medicamento e doença, ele gera uma pontuação que reflete a probabilidade de que o par esteja realmente conectado no mundo real.
Testando performance e investigando o que importa
Os pesquisadores testaram o MedPathEx usando bases de dados públicas que catalogam centenas de milhares de ligações conhecidas entre milhares de medicamentos, doenças e genes. Em uma validação cruzada rigorosa em cinco dobras, o MedPathEx superou várias abordagens concorrentes, incluindo métodos clássicos de aprendizado de máquina e vários modelos avançados baseados em grafos. Medidas de acurácia, como AUC, precisão média e pontuação F1, foram todas maiores, mostrando que o método separa com mais confiabilidade pares droga–doença verdadeiros dos falsos. Quando componentes foram removidos um a um, o desempenho caiu, especialmente quando a visão local por meta-caminhos ou a visão de atenção global foi retirada, ressaltando que ambas as perspectivas são essenciais. A análise também mostrou que a informação local de meta-caminhos contribui mais, com recursos globais e de similaridade fornecendo refinamentos importantes.
Exemplos do mundo real em doenças cardíacas e hipertensão
Além dos números, os autores verificaram se as sugestões de topo do MedPathEx para duas condições comuns — doença arterial coronariana e hipertensão — correspondiam ao que é conhecido na literatura médica. Para cada doença, o sistema propôs vários medicamentos, alguns dos quais já são usados clinicamente para problemas cardíacos relacionados, conferindo credibilidade à abordagem. Outros são candidatos menos óbvios que, ainda assim, possuem ligações biológicas, como influenciar inflamação, a função dos vasos sanguíneos ou o acúmulo de placas nas artérias. Diagramas de rede de medicamentos, genes e doenças ilustram como esses fármacos podem influenciar vias relacionadas à doença, apontando mecanismos plausíveis que poderiam ser explorados em estudos laboratoriais ou clínicos.
O que isso significa para medicamentos futuros
Em termos simples, o MedPathEx mostra que ao combinar muitas fontes de dados biomédicos e observar tanto padrões locais quanto globais em como medicamentos, genes e doenças se conectam, os computadores podem fazer um trabalho melhor em estimar quais remédios podem ajudar quais enfermidades. Embora essa ferramenta não substitua ensaios clínicos ou testes no mundo real, ela pode reduzir o vasto espaço de busca e destacar candidatos promissores — especialmente para doenças complexas como as cardíacas e a hipertensão. À medida que dados biológicos mais detalhados se tornem disponíveis e que tais modelos sejam mais validados, abordagens como o MedPathEx podem se tornar parceiros poderosos na busca por reutilização de medicamentos existentes e no desenvolvimento de estratégias de tratamento mais eficientes.
Citação: Wu, S., Wang, W., Jiao, H. et al. Enhanced drug disease association prediction through multimodal data integration and meta path guided global local feature fusion. Sci Rep 16, 11038 (2026). https://doi.org/10.1038/s41598-026-36223-9
Palavras-chave: reutilização de medicamentos, associações droga–doença, redes heterogêneas, redes neurais gráficas, descoberta computacional de fármacos