Clear Sky Science · it
Miglioramento della predizione delle associazioni farmaco-malattia tramite integrazione multimodale dei dati e fusione globale-locale delle feature guidata da meta-path
Perché trovare nuovi usi per farmaci esistenti è importante
Sviluppare un nuovo medicinale da zero è lento, rischioso e estremamente costoso. Eppure nelle farmacie di oggi sono nascosti molti farmaci che potrebbero aiutare a trattare altre malattie, se solo riuscissimo a scoprirne questi usi aggiuntivi. Questo studio presenta MedPathEx, un approccio basato su computer che setaccia vaste raccolte di dati biomedici per prevedere quali farmaci esistenti sono probabilmente efficaci per quali malattie, accelerando potenzialmente la ricerca di nuovi trattamenti e sfruttando meglio i medicinali già disponibili.
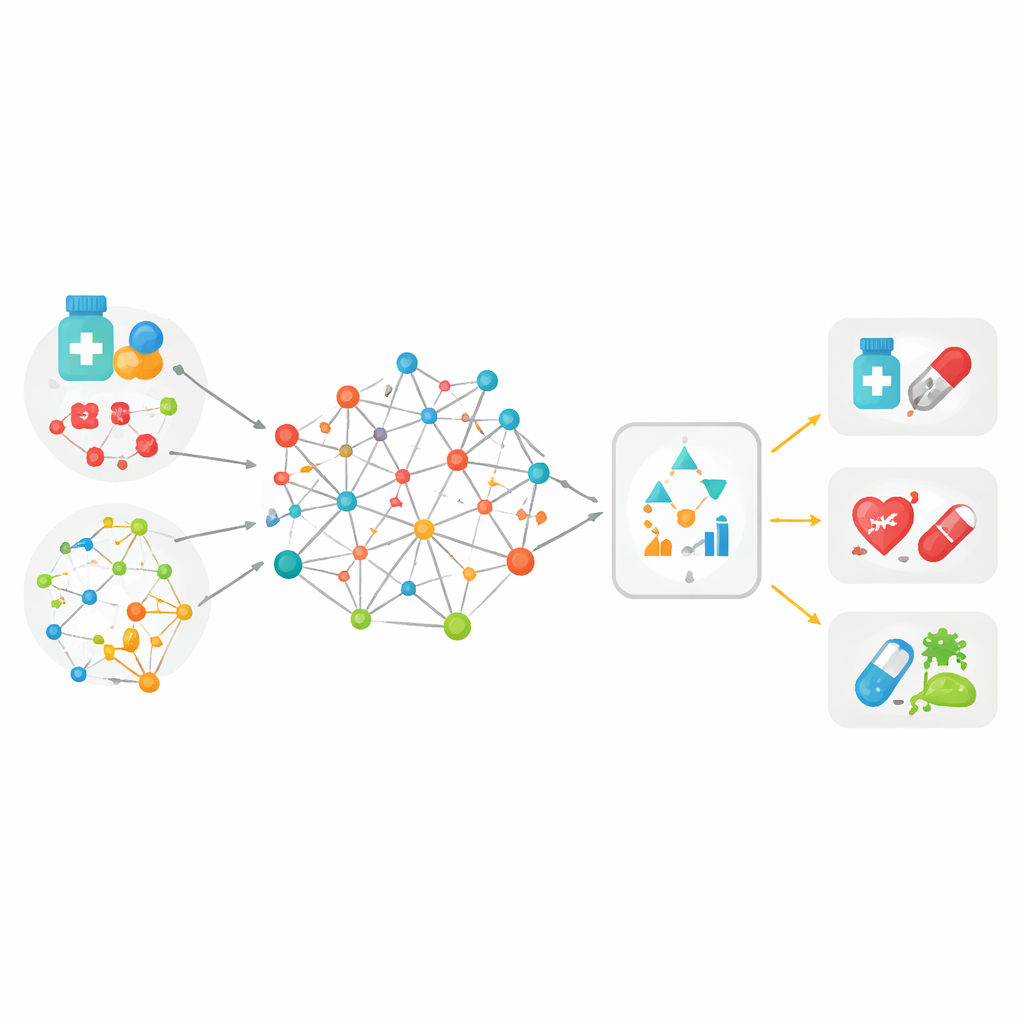
Unire molti indizi in un’unica grande mappa
La maggior parte degli strumenti precedenti per accoppiare farmaci e malattie si basava su un solo tipo di informazione—for esempio, quanto due molecole di farmaci sono simili nella struttura, o quanto due malattie sono correlate nelle cartelle cliniche. MedPathEx parte dall’idea che nessun singolo indizio sia sufficiente. Gli autori costruiscono una grande “mappa” che collega tre tipi di attori: farmaci, malattie e geni. Su questi collegamenti sovrappongono molteplici tipi di indizi: la struttura delle molecole dei farmaci, la loro classificazione terapeutica, gli effetti collaterali che causano, come le malattie si manifestano nei pazienti e nella terminologia medica, e ciò che è noto sulla funzione dei geni. Tessendo tutte queste informazioni multimodali in un’unica rete eterogenea, ogni farmaco, malattia e gene viene descritto in modo più ricco e realistico rispetto al passato.
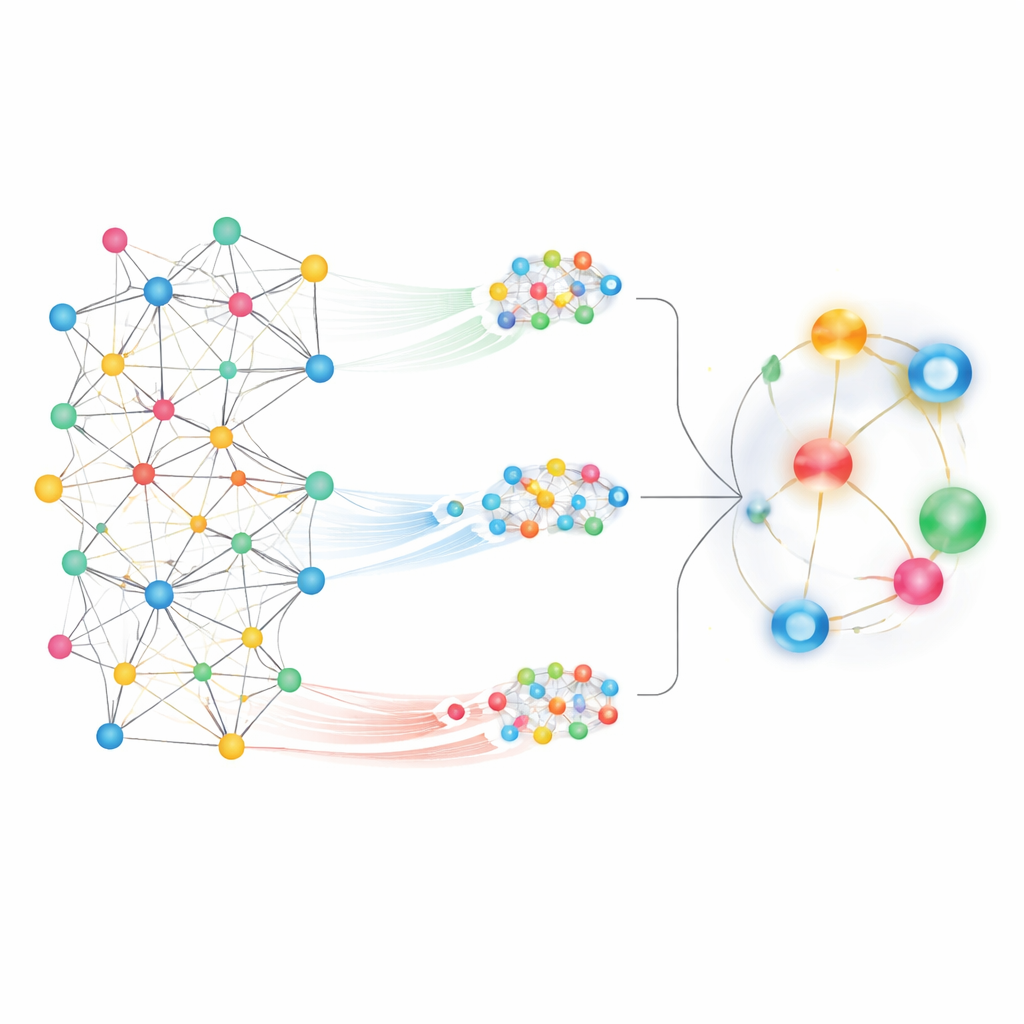
Vedere sia il vicinato che l’intera città
Davanti a una mappa così ampia, una sfida è decidere quali pattern siano rilevanti. MedPathEx affronta questo problema combinando due viste complementari della rete. Primo, si concentra sui vicinati locali, tracciando percorsi brevi e significativi—per esempio, farmaco → gene → malattia—per catturare come geni specifici possano collegare un farmaco a una patologia. Queste passeggiate strutturate, chiamate meta-path, mettono in evidenza relazioni a grana fine. Secondo, il metodo amplia lo sguardo per considerare il quadro globale, permettendo a ciascun nodo di “prestare attenzione” a molti altri nell’intera mappa. Questa vista con attenzione globale coglie tendenze più ampie e connessioni a lungo raggio che verrebbero perse seguendo solo i percorsi locali.
Fondere diverse viste in un unico segnale
Per trasformare queste viste della rete in predizioni, MedPathEx utilizza tecniche moderne di reti neurali per convertire la mappa complessa in impronte numeriche compatte per ogni farmaco, malattia e gene. Una parte del modello apprende da grafi di similarità costruiti all’interno di ciascun tipo (farmaco–farmaco, malattia–malattia, gene–gene). Un’altra parte si concentra sui vicinati locali definiti dalle meta-path, mentre una terza cattura la struttura globale dell’intera rete. Il modello impara quindi quanto peso assegnare a ciascuna di queste fonti e le fonde in una rappresentazione combinata per ogni nodo. Quando il sistema confronta le impronte combinate di un dato farmaco e di una malattia, restituisce un punteggio che riflette la probabilità che la coppia sia realmente connessa nel mondo reale.
Testare le prestazioni e sondare ciò che conta
I ricercatori hanno messo alla prova MedPathEx utilizzando database pubblici che catalogano centinaia di migliaia di collegamenti noti tra migliaia di farmaci, malattie e geni. In una rigorosa validazione incrociata a cinque fold, MedPathEx ha superato vari approcci concorrenti, inclusi metodi classici di machine learning e diversi modelli avanzati basati sui grafi. Metriche di accuratezza come AUC, precisione media e F1 score sono risultate tutte più elevate, mostrando che il metodo separa in modo più affidabile le vere coppie farmaco–malattia da quelle false. Quando i componenti sono stati rimossi uno a uno, le prestazioni sono diminuite, soprattutto quando è stata tolta la vista locale basata sulle meta-path o la vista con attenzione globale, sottolineando che entrambe le prospettive sono essenziali. L’analisi ha anche mostrato che l’informazione locale delle meta-path contribuisce maggiormente, con caratteristiche globali e di similarità che forniscono importanti rifiniture.
Esempi reali in cardiopatia e ipertensione
Oltre ai numeri, gli autori hanno verificato se le proposte meglio classificate da MedPathEx per due condizioni comuni—la malattia coronarica e l’ipertensione—corrispondevano a quanto noto in letteratura medica. Per ciascuna malattia, il sistema ha proposto diversi farmaci, alcuni già impiegati clinicamente per problemi cardiaci correlati, conferendo credibilità all’approccio. Altri sono candidati meno ovvi che tuttavia hanno legami biologici, come effetti sull’infiammazione, sulla funzione dei vasi sanguigni o sull’accumulo di placche nelle arterie. Diagrammi di rete di farmaci, geni e malattie illustrano come questi medicinali potrebbero influenzare percorsi legati alla patologia, indicando meccanismi plausibili da esplorare in studi di laboratorio o clinici.
Cosa significa per i futuri farmaci
In termini semplici, MedPathEx mostra che combinando molte fonti di dati biomedici e osservando sia schemi locali sia globali nelle connessioni tra farmaci, geni e malattie, i computer possono fare un lavoro migliore nel prevedere quali medicinali potrebbero aiutare quali patologie. Pur non sostituendo gli studi clinici o i test nel mondo reale, questo strumento può restringere l’enorme spazio di ricerca e mettere in evidenza candidati promettenti—specialmente per malattie complesse come le cardiopatie e l’ipertensione. Con l’aumentare della disponibilità di dati biologici più dettagliati e la validazione ulteriore di tali modelli, approcci come MedPathEx potrebbero diventare partner potenti nella ricerca di riutilizzo dei farmaci e nella progettazione di strategie terapeutiche più efficienti.
Citazione: Wu, S., Wang, W., Jiao, H. et al. Enhanced drug disease association prediction through multimodal data integration and meta path guided global local feature fusion. Sci Rep 16, 11038 (2026). https://doi.org/10.1038/s41598-026-36223-9
Parole chiave: riutilizzo dei farmaci, associazioni farmaco–malattia, reti eterogenee, reti neurali su grafi, scoperta computazionale di farmaci