Clear Sky Science · nl
Verbeterde voorspelling van medicijn-ziekte-associaties door multimodale gegevensintegratie en meta-pad-gestuurde globale-lokale feature-fusie
Waarom het vinden van nieuwe toepassingen voor bestaande geneesmiddelen ertoe doet
Een nieuw geneesmiddel helemaal vanaf nul ontwikkelen is traag, risicovol en buitengewoon duur. Toch bevinden zich in de huidige apotheken veel middelen die mogelijk ook andere ziekten kunnen behandelen, als we die extra toepassingen maar kunnen ontdekken. Deze studie introduceert MedPathEx, een computergebaseerde methode die grote verzamelingen biomedische gegevens doorzoekt om te voorspellen welke bestaande geneesmiddelen waarschijnlijk werken voor welke ziekten. Dat kan de zoektocht naar nieuwe behandelingen versnellen en beter gebruikmaken van medicijnen die we al hebben.
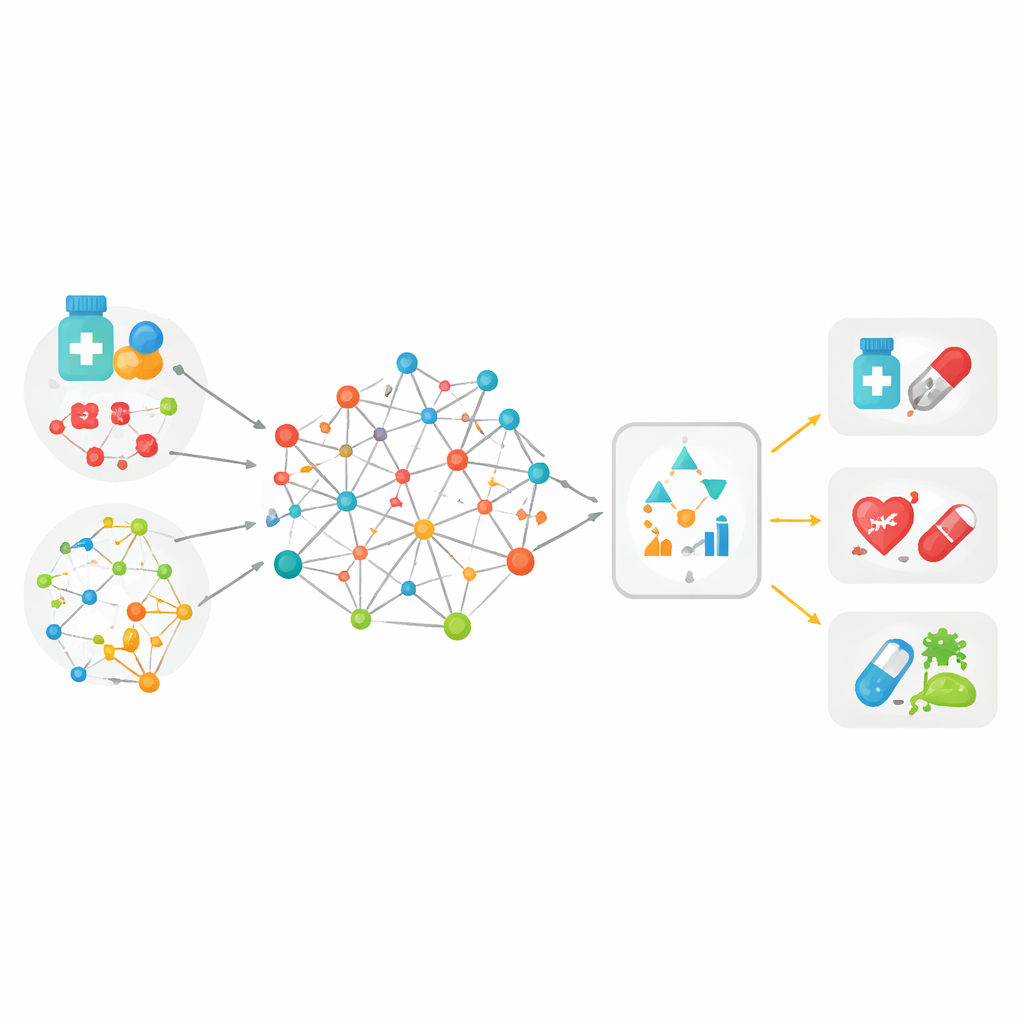
Verschillende aanwijzingen samenbrengen in één grote kaart
De meeste eerdere hulpmiddelen om geneesmiddelen aan ziekten te koppelen waren gebaseerd op slechts één soort informatie — bijvoorbeeld hoe gelijk twee medicijnmoleculen eruitzien, of hoe nauw twee ziekten met elkaar samenhangen in medische dossiers. MedPathEx vertrekt van het idee dat geen enkele aanwijzing op zichzelf voldoende is. De auteurs bouwen een grote “kaart” die drie soorten actoren verbindt: geneesmiddelen, ziekten en genen. Bovenop deze verbindingen leggen ze meerdere soorten aanwijzingen: de moleculaire opbouw van geneesmiddelen, hun classificatie binnen therapeutische categorieën, welke bijwerkingen ze veroorzaken, hoe ziekten bij patiënten en in medische terminologie voorkomen, en wat bekend is over genfunctie. Door al deze multimodale informatie te weven in één heterogeen netwerk, wordt elk geneesmiddel, elke ziekte en elk gen rijker en realistischer beschreven dan voorheen.
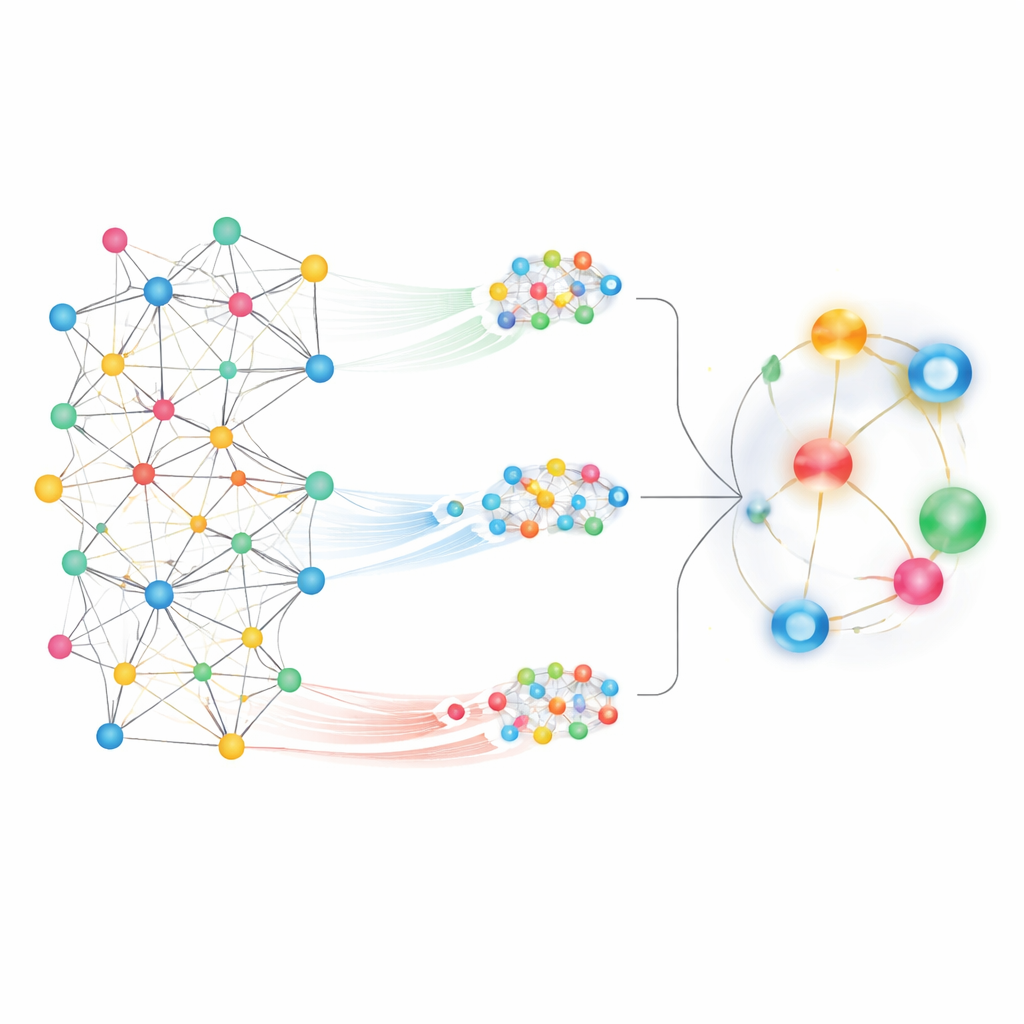
Zowel de buurt als de hele stad zien
Bij het bekijken van zo’n enorme kaart is één uitdaging bepalen welke patronen ertoe doen. MedPathEx pakt dit aan door twee complementaire gezichtspunten op het netwerk te combineren. Ten eerste zoomt het in op lokale buurten en volgt het korte, betekenisvolle paden — bijvoorbeeld geneesmiddel → gen → ziekte — om vast te leggen hoe specifieke genen een medicijn met een aandoening kunnen verbinden. Deze patroonmatige wandelingen, meta-paden genoemd, benadrukken fijnmazige relaties. Ten tweede zoomt de methode uit om het globale beeld te beschouwen, waardoor elke knoop “aandacht” kan geven aan vele andere knopen verspreid over de hele kaart. Deze globale aandachtsperspectief legt bredere trends en langeafstandverbindingen bloot die gemist zouden worden wanneer men alleen lokale paden volgt.
Verschillende gezichtspunten samensmelten tot één signaal
Om deze netwerkvisies om te zetten in voorspellingen gebruikt MedPathEx moderne neurale-netwerktechnieken om de complexe kaart te converteren naar compacte numerieke vingerafdrukken voor elk geneesmiddel, elke ziekte en elk gen. Een deel van het model leert van gelijkenheidsgraafjes binnen elk type (geneesmiddel–geneesmiddel, ziekte–ziekte, gen–gen). Een ander deel richt zich op de lokale meta-pad-buurten, terwijl een derde deel de globale structuur van het gehele netwerk vastlegt. Het model leert vervolgens hoeveel gewicht aan elk van deze bronnen moet worden toegekend en fuseert ze tot één gecombineerde representatie per knoop. Wanneer het systeem de gecombineerde vingerafdrukken van een bepaald geneesmiddel en een ziekte vergelijkt, geeft het een score die weerspiegelt hoe waarschijnlijk het is dat het paar in de echte wereld daadwerkelijk verbonden is.
Prestaties testen en nagaan wat telt
De onderzoekers hebben MedPathEx getest met openbare databases die honderduizenden bekende koppelingen tussen duizenden geneesmiddelen, ziekten en genen registreren. In een rigoureuze vijfvoudige cross-validatie overtrof MedPathEx diverse concurrerende benaderingen, waaronder klassieke machine-learningmethoden en meerdere geavanceerde grafiekgebaseerde modellen. Maatstaven voor nauwkeurigheid zoals AUC, gemiddelde precisie en F1-score waren allemaal hoger, wat aantoont dat de methode betrouwbaarder echte geneesmiddel–ziekte-paren van valse onderscheidt. Wanneer componenten één voor één werden verwijderd, daalde de prestatie, vooral wanneer ofwel het lokale meta-pad-perspectief of het globale aandachtsperspectief werd weggenomen, wat onderstreept dat beide perspectieven essentieel zijn. De analyse toonde ook aan dat de lokale meta-pad-informatie het meest bijdraagt, terwijl globale en gelijkenheidskenmerken belangrijke verfijningen leveren.
Praktijkvoorbeelden bij hartziekten en hoge bloeddruk
Buiten de cijfers controleerden de auteurs of MedPathEx’s hoogst gerangschikte voorstellen voor twee veelvoorkomende aandoeningen — coronaire hartziekte en hypertensie — overeenkwamen met wat bekend is uit de medische literatuur. Voor elke ziekte stelde het systeem meerdere geneesmiddelen voor, waarvan sommige al klinisch worden gebruikt voor verwante hartaandoeningen, wat de aanpak geloofwaardigheid geeft. Andere zijn minder voor de hand liggende kandidaten die desalniettemin biologische connecties hebben, zoals effecten op ontsteking, de functie van bloedvaten of de ophoping van plaque in de slagaders. Netwerkdiagrammen van geneesmiddelen, genen en ziekten illustreren hoe deze middelen ziektegerelateerde paden zouden kunnen beïnvloeden, en wijzen op plausibele mechanismen die in laboratorium- of klinische studies verder onderzocht kunnen worden.
Wat dit betekent voor toekomstige geneesmiddelen
Simpel gezegd laat MedPathEx zien dat door vele bronnen van biomedische data te combineren en zowel lokale als globale patronen in de verbindingen tussen geneesmiddelen, genen en ziekten te bekijken, computers beter kunnen inschatten welke medicijnen welke aandoeningen mogelijk helpen. Hoewel dit hulpmiddel geen klinische proeven of testen in de echte wereld vervangt, kan het de enorme zoekruimte verkleinen en veelbelovende kandidaat-geneesmiddelen aan het licht brengen — vooral voor complexe ziekten zoals hartziekten en hypertensie. Naarmate meer gedetailleerde biologische gegevens beschikbaar komen en dergelijke modellen verder worden gevalideerd, zouden benaderingen als MedPathEx krachtige partners kunnen worden in het streven naar het herbestemmen van bestaande geneesmiddelen en het ontwerpen van efficiëntere behandelingsstrategieën.
Bronvermelding: Wu, S., Wang, W., Jiao, H. et al. Enhanced drug disease association prediction through multimodal data integration and meta path guided global local feature fusion. Sci Rep 16, 11038 (2026). https://doi.org/10.1038/s41598-026-36223-9
Trefwoorden: hergebruik van geneesmiddelen, medicijn–ziekte-associaties, heterogene netwerken, grafiek-neurale netwerken, computationele medicijnontdekking