Clear Sky Science · pl
Ulepszone przewidywanie związków lek–choroba dzięki integracji danych multimodalnych i globalno‑lokalnej fuzji cech kierowanej ścieżkami meta
Dlaczego warto szukać nowych zastosowań dla starych leków
Opracowanie nowego leku od podstaw jest powolne, obarczone ryzykiem i niezwykle kosztowne. Tymczasem w aptekach i zbiorach leków znajdują się preparaty, które mogłyby pomóc w leczeniu innych chorób — gdyby tylko udało się odkryć te dodatkowe zastosowania. W tym badaniu przedstawiono MedPathEx, podejście komputerowe przesiewające duże zbiory danych biomedycznych w celu przewidywania, które istniejące leki mogą działać na konkretne choroby, co może przyspieszyć poszukiwanie nowych terapii i lepiej wykorzystać dostępne leki.
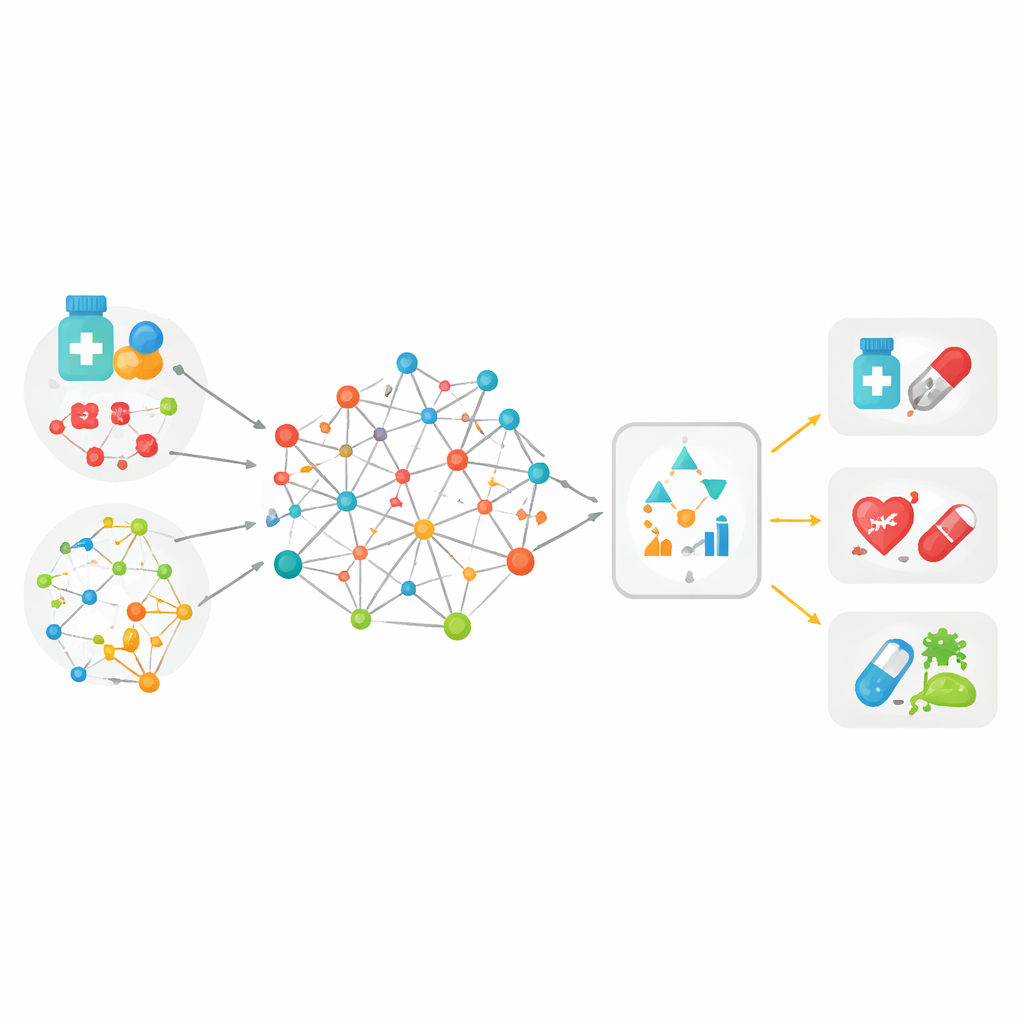
Łączenie wielu wskazówek w jedną dużą mapę
Większość wcześniejszych narzędzi dopasowujących leki do chorób opierała się na jednym rodzaju informacji — na przykład na podobieństwie dwóch cząsteczek leku lub na tym, jak blisko powiązane są dwie choroby w dokumentacji medycznej. MedPathEx zaczyna od założenia, że pojedyncza wskazówka nie wystarczy. Autorzy budują dużą „mapę” łączącą trzy typy elementów: leki, choroby i geny. Na tej sieci nakładają wiele rodzajów sygnałów: strukturę cząsteczek leków, klasyfikację terapeutyczną, działania niepożądane, sposób występowania chorób u pacjentów i w języku medycznym oraz znane informacje o funkcjach genów. Poprzez splecenie tych multimodalnych danych w heterogeniczną sieć, każdy lek, choroba i gen zostaje opisany w sposób bogatszy i bardziej realistyczny niż wcześniej.
Widzieć zarówno sąsiedztwo, jak i całe miasto
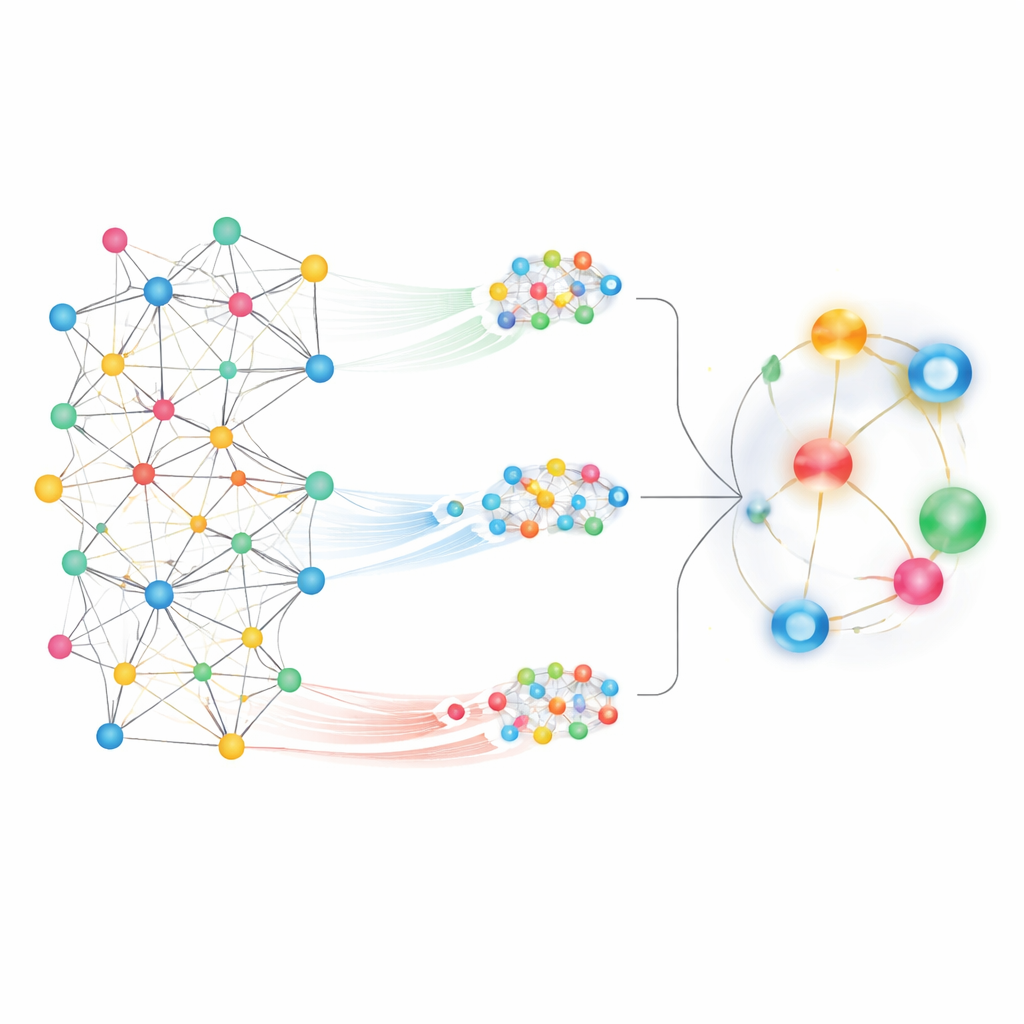
Patrząc na tak rozległą mapę, jednym z wyzwań jest ustalenie, które wzorce są istotne. MedPathEx rozwiązuje to, łącząc dwa komplementarne sposoby patrzenia na sieć. Najpierw przybliża lokalne sąsiedztwa, śledząc krótkie, znaczące ścieżki — na przykład lek → gen → choroba — aby uchwycić, jak konkretne geny mogą łączyć lek z chorobą. Takie zaplanowane przejścia, zwane meta‑ścieżkami, uwypuklają drobne relacje. Po drugie, metoda oddala się, aby uwzględnić obraz globalny, pozwalając każdemu węzłowi „zwracać uwagę” na wiele innych w całej mapie. Globalny widok uwagi wychwytuje szersze trendy i dalekosiężne powiązania, które zostałyby pominięte przy skupieniu wyłącznie na lokalnych ścieżkach.
Mieszanie różnych perspektyw w jeden sygnał
Aby przekształcić te widoki sieci w przewidywania, MedPathEx wykorzystuje nowoczesne techniki sieci neuronowych do konwersji złożonej mapy w zwarte numeryczne odciski dla każdego leku, choroby i genu. Jedna część modelu uczy się z grafów podobieństwa zbudowanych wewnątrz każdego typu (lek–lek, choroba–choroba, gen–gen). Inna część koncentruje się na lokalnych środowiskach meta‑ścieżek, a trzecia przechwytuje globalną strukturę całej sieci. Model następnie uczy się, jaką wagę przypisać każdemu z tych źródeł i scala je w pojedynczą, połączoną reprezentację dla każdego węzła. Gdy system porównuje skonsolidowane odciski danego leku i choroby, zwraca wynik odzwierciedlający prawdopodobieństwo, że para jest rzeczywiście powiązana w świecie rzeczywistym.
Testowanie wydajności i badanie, co ma znaczenie
Naukowcy przetestowali MedPathEx, wykorzystując publiczne bazy danych katalogujące setki tysięcy znanych powiązań między tysiącami leków, chorób i genów. W rygorystycznej pięciokrotnej walidacji krzyżowej MedPathEx przewyższył szereg konkurencyjnych podejść, w tym klasyczne metody uczenia maszynowego i kilka zaawansowanych modeli grafowych. Miary dokładności, takie jak AUC, średnia precyzja i F1, były wyższe, co pokazuje, że metoda bardziej niezawodnie odróżnia prawdziwe pary lek–choroba od fałszywych. Po usuwaniu komponentów pojedynczo wydajność spadała, szczególnie gdy zabrano albo lokalny widok meta‑ścieżek, albo globalny widok uwagi, podkreślając, że obie perspektywy są niezbędne. Analiza wykazała również, że informacje z lokalnych meta‑ścieżek wnoszą największy wkład, natomiast cechy globalne i podobieństwa dostarczają ważnych uzupełnień.
Przykłady z praktyki: choroby serca i nadciśnienie
Poza wynikami liczbowymi autorzy sprawdzili, czy najwyżej oceniane sugestie MedPathEx dla dwóch powszechnych schorzeń — choroby wieńcowej i nadciśnienia — zgadzają się z istniejącą literaturą medyczną. Dla każdej choroby system zaproponował kilka leków, z których niektóre są już stosowane klinicznie w pokrewnych problemach sercowych, co zwiększa wiarygodność podejścia. Inne propozycje są mniej oczywiste, lecz mimo to mają biologiczne powiązania, na przykład wpływ na zapalenie, funkcję naczyń krwionośnych czy odkładanie się blaszek w tętnicach. Diagramy sieci leków, genów i chorób ilustrują, jak te leki mogłyby oddziaływać na szlaki związane z chorobą, wskazując na prawdopodobne mechanizmy, które można badać w laboratorium lub w badaniach klinicznych.
Co to oznacza dla przyszłych leków
Mówiąc prosto, MedPathEx pokazuje, że łącząc wiele źródeł danych biomedycznych i analizując zarówno lokalne, jak i globalne wzorce połączeń między lekami, genami i chorobami, komputery potrafią lepiej przewidywać, które leki mogą pomóc przy konkretnych schorzeniach. Narzędzie to nie zastąpi badań klinicznych ani testów w warunkach rzeczywistych, ale może zawęzić ogromną przestrzeń poszukiwań i wskazać obiecujące kandydatury leków — szczególnie w przypadku złożonych chorób, takich jak choroby serca i nadciśnienie. W miarę pojawiania się bardziej szczegółowych danych biologicznych i dalszej weryfikacji takich modeli, podejścia podobne do MedPathEx mogą stać się wartościowymi partnerami w dążeniu do ponownego zastosowania istniejących leków i projektowania wydajniejszych strategii leczenia.
Cytowanie: Wu, S., Wang, W., Jiao, H. et al. Enhanced drug disease association prediction through multimodal data integration and meta path guided global local feature fusion. Sci Rep 16, 11038 (2026). https://doi.org/10.1038/s41598-026-36223-9
Słowa kluczowe: ponowne zastosowanie leków, powiązania lek–choroba, heterogeniczne sieci, grafowe sieci neuronowe, komputerowe odkrywanie leków