Clear Sky Science · es
Mejora en la predicción de asociaciones fármaco‑enfermedad mediante la integración multimodal de datos y la fusión global‑local de características guiada por meta‑rutas
Por qué importa encontrar nuevos usos para fármacos ya existentes
Desarrollar un medicamento nuevo desde cero es lento, arriesgado y extremadamente caro. Sin embargo, en las farmacias actuales hay muchos fármacos que podrían ayudar a tratar otras enfermedades si se descubrieran esos usos adicionales. Este estudio presenta MedPathEx, un enfoque informático que rastrea grandes colecciones de datos biomédicos para predecir qué fármacos existentes podrían ser efectivos para qué enfermedades, acelerando potencialmente la búsqueda de nuevos tratamientos y aprovechando mejor los medicamentos que ya tenemos.
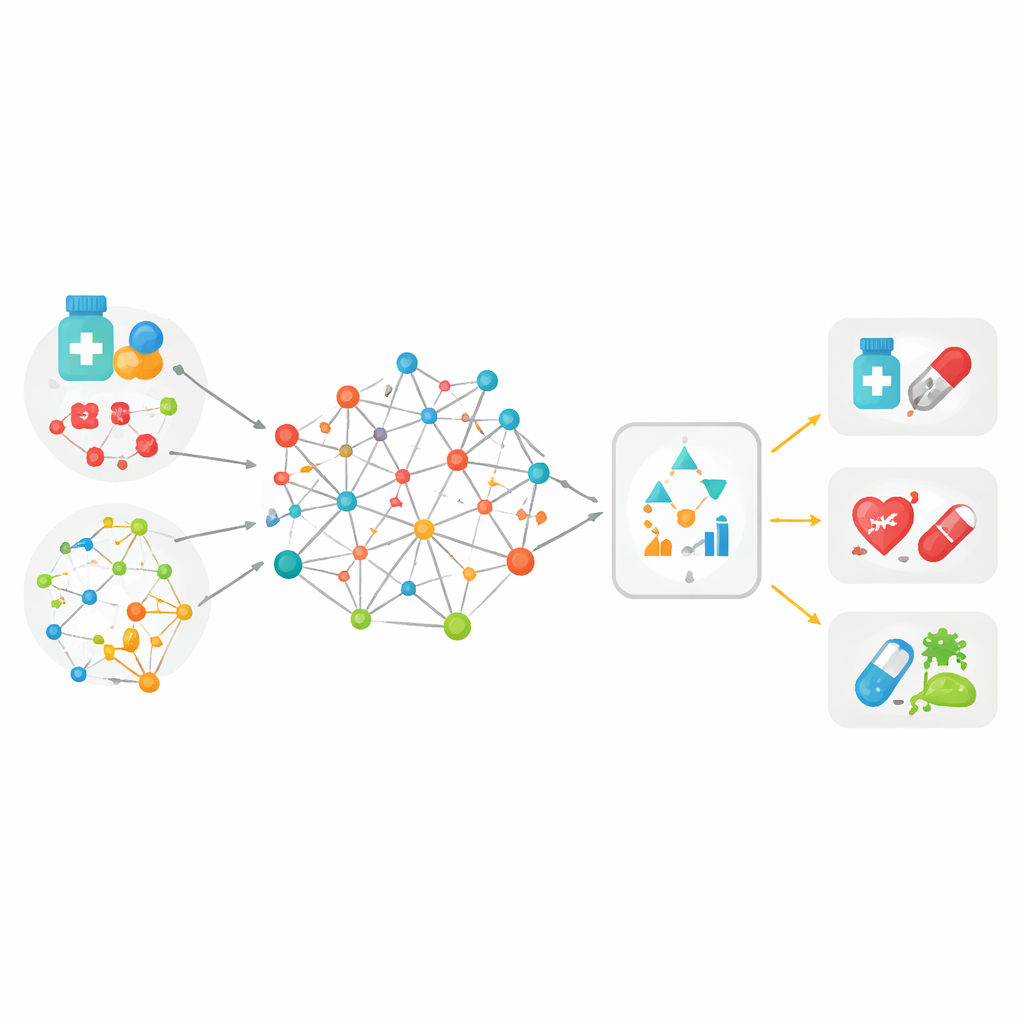
Reunir muchas pistas en un gran mapa
La mayoría de las herramientas previas para emparejar fármacos con enfermedades se basaban en un solo tipo de información —por ejemplo, cómo se parecen dos moléculas de fármaco o cuán relacionadas están dos enfermedades en los registros médicos. MedPathEx parte de la idea de que ninguna pista aislada es suficiente. Los autores construyen un gran “mapa” que conecta tres tipos de actores: fármacos, enfermedades y genes. Sobre estas conexiones superponen múltiples tipos de pistas: la estructura de las moléculas de los fármacos, su clasificación terapéutica, los efectos secundarios que causan, cómo se presentan las enfermedades en pacientes y en el lenguaje médico, y lo que se sabe sobre la función génica. Al entretejer toda esta información multimodal en una red heterogénea, cada fármaco, enfermedad y gen queda descrito de manera más rica y realista que antes.
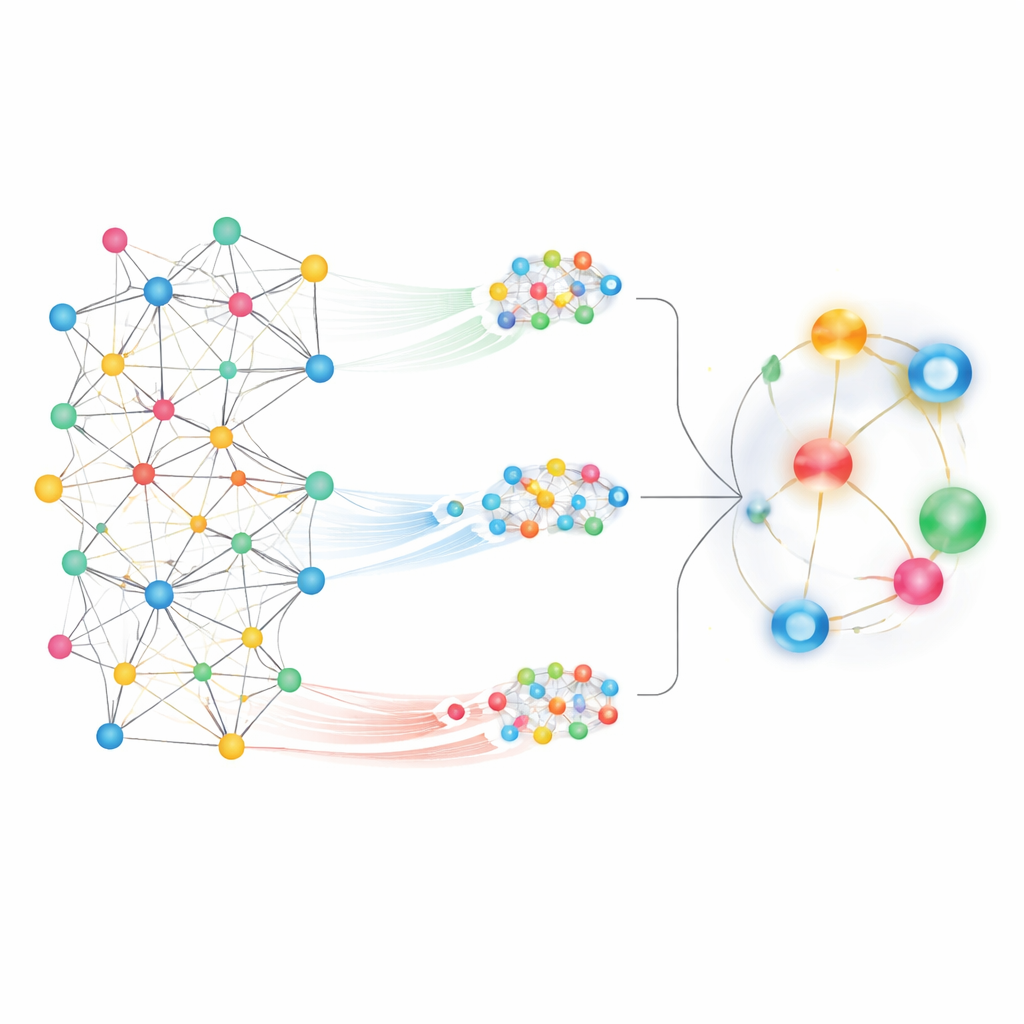
Ver tanto el vecindario como la ciudad entera
Al observar un mapa tan grande, un desafío es decidir qué patrones son relevantes. MedPathEx aborda esto combinando dos vistas complementarias de la red. Primero, se aproxima a los vecindarios locales, trazando rutas cortas y significativas —por ejemplo, fármaco → gen → enfermedad— para captar cómo genes concretos podrían conectar un medicamento con una dolencia. Estos recorridos con patrón, llamados meta‑rutas, realzan relaciones de detalle fino. Segundo, el método se aleja para considerar la imagen global, permitiendo que cada nodo “preste atención” a muchos otros a lo largo de todo el mapa. Esta vista de atención global capta tendencias amplias y conexiones a larga distancia que se perderían si solo se siguieran rutas locales.
Fusionar distintas perspectivas en una única señal
Para convertir estas vistas de la red en predicciones, MedPathEx utiliza técnicas modernas de redes neuronales para transformar el mapa complejo en huellas numéricas compactas para cada fármaco, enfermedad y gen. Una parte del modelo aprende a partir de grafos de similitud dentro de cada tipo (fármaco‑fármaco, enfermedad‑enfermedad, gen‑gen). Otra parte se centra en los vecindarios locales de meta‑rutas, mientras que una tercera captura la estructura global de toda la red. El modelo aprende entonces cuánto peso dar a cada una de estas fuentes y las fusiona en una representación combinada para cada nodo. Cuando el sistema compara las huellas combinadas de un fármaco y una enfermedad, emite una puntuación que refleja la probabilidad de que el par esté realmente conectado en el mundo real.
Probar el rendimiento y explorar qué importa
Los investigadores evaluaron MedPathEx usando bases de datos públicas que catalogan cientos de miles de enlaces conocidos entre miles de fármacos, enfermedades y genes. En una rigurosa validación cruzada de cinco pliegues, MedPathEx superó a una variedad de enfoques competidores, incluidos métodos clásicos de aprendizaje automático y varios modelos avanzados basados en grafos. Medidas de precisión como el AUC, la precisión media y la puntuación F1 fueron todas superiores, mostrando que el método separa de manera más fiable los pares fármaco‑enfermedad verdaderos de los falsos. Cuando se eliminaron componentes uno por uno, el rendimiento cayó, especialmente al suprimir la vista local de meta‑rutas o la vista de atención global, lo que subraya que ambas perspectivas son esenciales. El análisis también mostró que la información local de meta‑rutas contribuye más, mientras que las características globales y de similitud proporcionan importantes refinamientos.
Ejemplos reales en enfermedad coronaria e hipertensión
Más allá de los números, los autores verificaron si las sugerencias mejor clasificadas por MedPathEx para dos condiciones comunes —enfermedad de las arterias coronarias e hipertensión— coincidían con lo conocido en la literatura médica. Para cada enfermedad, el sistema propuso varios fármacos, algunos ya utilizados clínicamente para problemas cardíacos relacionados, lo que da credibilidad al enfoque. Otros son candidatos menos obvios que, no obstante, tienen vínculos biológicos, como afectar la inflamación, la función vascular o la acumulación de placa en las arterias. Diagramas de la red de fármacos, genes y enfermedades ilustran cómo estos medicamentos podrían influir en vías relacionadas con la enfermedad, señalando mecanismos plausibles que podrían explorarse en estudios de laboratorio o clínicos.
Qué significa esto para los medicamentos del futuro
En términos sencillos, MedPathEx demuestra que al combinar muchas fuentes de datos biomédicos y observar tanto patrones locales como globales en cómo se conectan fármacos, genes y enfermedades, los ordenadores pueden hacer un mejor trabajo al inferir qué medicamentos podrían ayudar contra qué dolencias. Aunque esta herramienta no sustituye a los ensayos clínicos ni a las pruebas en el mundo real, puede reducir el vasto espacio de búsqueda y resaltar candidatos farmacológicos prometedores —especialmente para enfermedades complejas como la cardiopatía y la hipertensión. A medida que se disponga de datos biológicos más detallados y estos modelos se validen más, enfoques como MedPathEx podrían convertirse en socios potentes en la tarea de reposicionar fármacos existentes y diseñar estrategias de tratamiento más eficientes.
Cita: Wu, S., Wang, W., Jiao, H. et al. Enhanced drug disease association prediction through multimodal data integration and meta path guided global local feature fusion. Sci Rep 16, 11038 (2026). https://doi.org/10.1038/s41598-026-36223-9
Palabras clave: reposicionamiento de fármacos, asociaciones fármaco‑enfermedad, redes heterogéneas, redes neuronales de grafos, descubrimiento computacional de fármacos