Clear Sky Science · de
Verbesserte Vorhersage von Arzneimittel‑Krankheits‑Assoziationen durch multimodale Datenintegration und meta‑Pfad‑gesteuerte globale‑lokale Merkmalsfusion
Warum es wichtig ist, neue Anwendungen für bestehende Medikamente zu finden
Ein neues Medikament von Grund auf zu entwickeln ist langsam, risikoreich und extrem teuer. In den Apotheken von heute verbergen sich jedoch viele Wirkstoffe, die möglicherweise auch andere Krankheiten behandeln könnten, wenn man ihre zusätzlichen Einsatzmöglichkeiten nur entdecken würde. Diese Studie stellt MedPathEx vor, einen computerbasierten Ansatz, der große Sammlungen biomedizinischer Daten durchsucht, um vorherzusagen, welche bekannten Medikamente für welche Erkrankungen wirksam sein könnten. Das kann die Suche nach neuen Therapien beschleunigen und vorhandene Arzneimittel besser nutzbar machen.
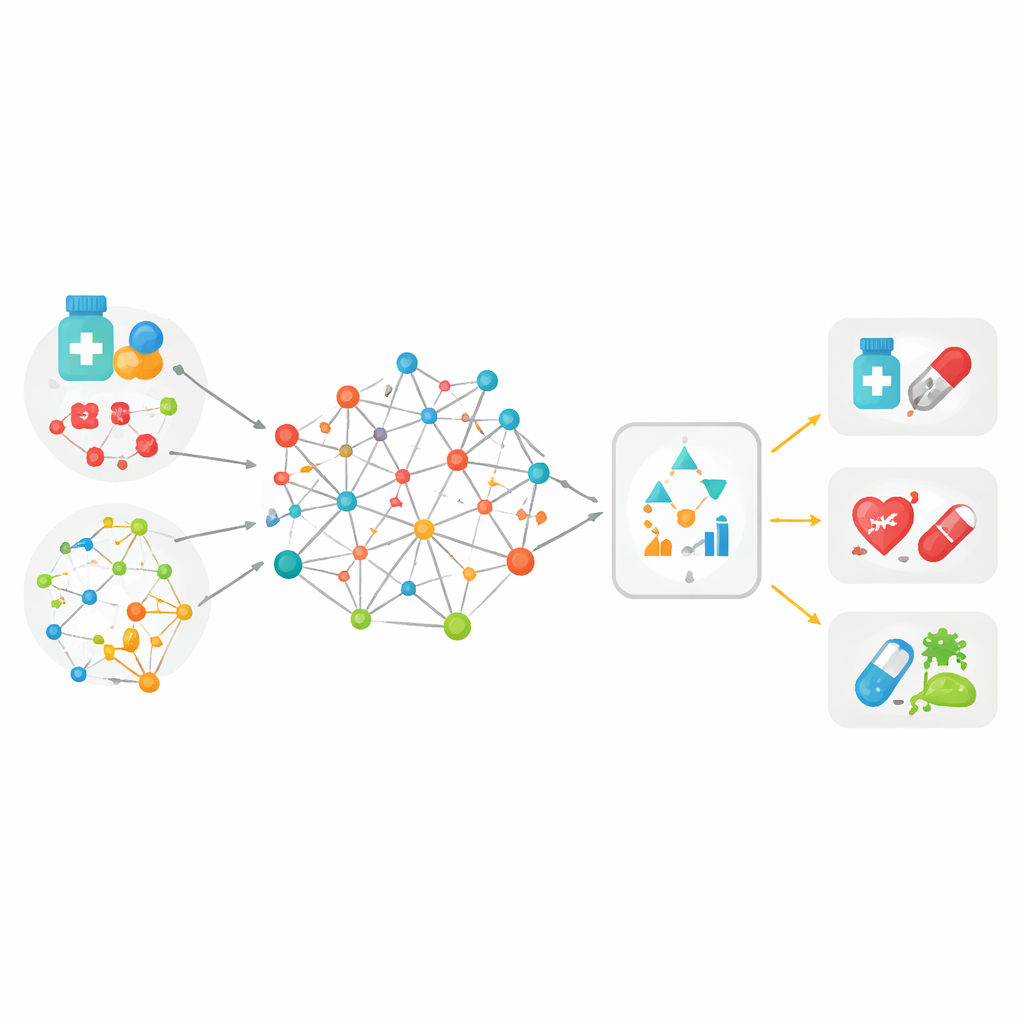
Viele Hinweise in einer großen Karte zusammenführen
Die meisten bisherigen Werkzeuge zur Zuordnung von Arzneimitteln zu Krankheiten stützten sich nur auf einen Informationstyp – zum Beispiel darauf, wie ähnlich sich zwei Wirkstoffmoleküle sind, oder wie eng zwei Erkrankungen in Patientenakten miteinander verknüpft sind. MedPathEx geht von der Idee aus, dass kein einzelner Hinweis ausreicht. Die Autor:innen erstellen eine große „Karte“, die drei Akteursgruppen verbindet: Arzneimittel, Krankheiten und Gene. Auf diese Verbindungen legen sie mehrere Informationsschichten: die molekulare Struktur von Wirkstoffen, ihre therapeutische Klassifizierung, verursachte Nebenwirkungen, wie Krankheiten bei Patient:innen und in medizinischer Sprache auftreten sowie bekannte Informationen zur Genfunktion. Indem all diese multimodalen Daten in ein heterogenes Netzwerk verwoben werden, werden jedes Medikament, jede Krankheit und jedes Gen reichhaltiger und realistischer beschrieben als zuvor.
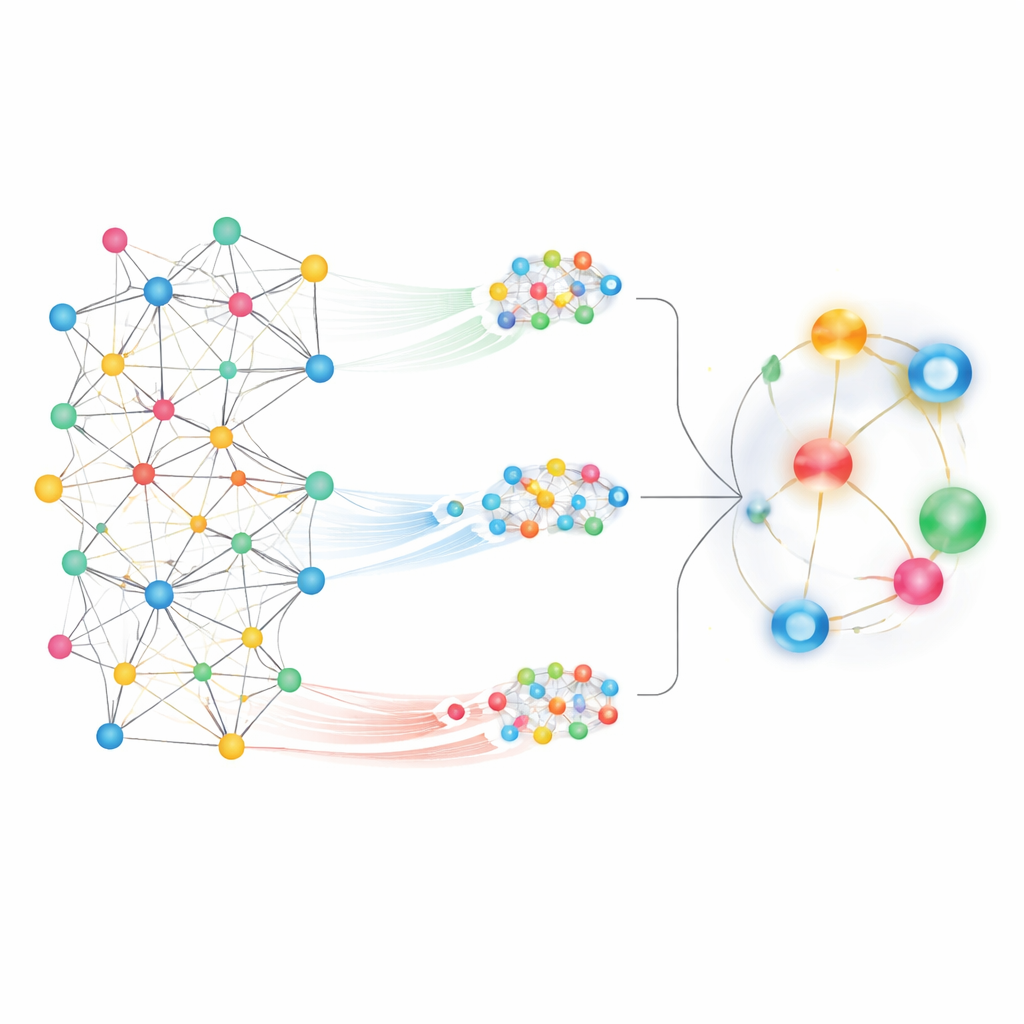
Sowohl die Nachbarschaft als auch die ganze Stadt sehen
Bei einer so großen Karte besteht eine Herausforderung darin, zu entscheiden, welche Muster wichtig sind. MedPathEx begegnet dem, indem es zwei komplementäre Sichtweisen des Netzwerks kombiniert. Zuerst zoomt es in lokale Nachbarschaften und verfolgt kurze, aussagekräftige Pfade – zum Beispiel Arzneimittel → Gen → Krankheit –, um zu erfassen, wie bestimmte Gene ein Medikament mit einer Erkrankung verbinden könnten. Diese strukturierten Spaziergänge, sogenannte Meta‑Pfade, heben feinkörnige Beziehungen hervor. Zweitens zoomt die Methode heraus, um das globale Bild zu betrachten, wobei jeder Knoten „Aufmerksamkeit“ auf viele andere über die gesamte Karte hinweg richten kann. Diese globale Attention‑Sicht nimmt breitere Trends und fernere Verbindungen wahr, die beim Ausschließlich‑folgenden lokaler Pfade verloren gingen.
Verschiedene Sichten zu einem einzigen Signal verschmelzen
Um diese Netzwerkansichten in Vorhersagen zu überführen, verwendet MedPathEx moderne neuronale Netze, die die komplexe Karte in kompakte numerische Fingerabdrücke für jedes Arzneimittel, jede Krankheit und jedes Gen umwandeln. Ein Teil des Modells lernt aus Ähnlichkeitsgraphen, die innerhalb jeder Klasse aufgebaut sind (Arzneimittel–Arzneimittel, Krankheit–Krankheit, Gen–Gen). Ein anderer Teil konzentriert sich auf die lokalen Meta‑Pfad‑Nachbarschaften, während ein dritter die globale Struktur des gesamten Netzwerks erfasst. Das Modell lernt dann, wie viel Gewicht jeder dieser Quellen beigemessen werden soll, und fusioniert sie zu einer einzigen kombinierten Repräsentation für jeden Knoten. Wenn das System die kombinierten Fingerabdrücke eines bestimmten Arzneimittels und einer Erkrankung vergleicht, liefert es einen Score, der widerspiegelt, wie wahrscheinlich es ist, dass das Paar in der realen Welt tatsächlich verbunden ist.
Leistung testen und relevante Faktoren untersuchen
Die Forschenden haben MedPathEx anhand öffentlicher Datenbanken getestet, die Hunderttausende bekannter Verbindungen zwischen Tausenden von Arzneimitteln, Krankheiten und Genen katalogisieren. In einer strengen fünf‑fachen Kreuzvalidierung übertraf MedPathEx eine Reihe konkurrierender Ansätze, darunter klassische Machine‑Learning‑Verfahren und mehrere fortgeschrittene graphbasierte Modelle. Genauigkeitsmaße wie AUC, durchschnittliche Präzision und F1‑Score lagen durchweg höher, was zeigt, dass die Methode wahre Arzneimittel–Krankheits‑Paare zuverlässiger von falschen trennt. Beim Entfernen einzelner Komponenten sank die Leistung, besonders wenn entweder die lokale Meta‑Pfad‑Sicht oder die globale Attention‑Sicht entfiel, was unterstreicht, dass beide Perspektiven wesentlich sind. Die Analyse zeigte außerdem, dass die lokalen Meta‑Pfad‑Informationen den größten Beitrag leisten, während globale und Ähnlichkeitsmerkmale wichtige Verfeinerungen liefern.
Konkrete Beispiele bei Herzkrankheiten und Bluthochdruck
Über Zahlen hinaus prüften die Autor:innen, ob MedPathEx’ bestplatzierte Vorschläge für zwei häufige Erkrankungen – koronare Herzkrankheit und Hypertonie – mit dem übereinstimmen, was aus der medizinischen Literatur bekannt ist. Für jede Krankheit schlug das System mehrere Arzneimittel vor, von denen einige bereits klinisch für verwandte Herzprobleme eingesetzt werden, was der Methode Glaubwürdigkeit verleiht. Andere sind weniger offensichtliche Kandidaten, die dennoch biologische Verknüpfungen aufweisen, etwa durch Einfluss auf Entzündungen, Gefäßfunktion oder Plaquebildung in Arterien. Netzwerkdiagramme von Arzneimitteln, Genen und Krankheiten veranschaulichen, wie diese Medikamente krankheitsrelevante Pfade beeinflussen könnten und weisen auf plausible Mechanismen hin, die in Labor- oder klinischen Studien untersucht werden könnten.
Was das für künftige Arzneimittel bedeutet
Kurz gesagt zeigt MedPathEx, dass Computer durch das Kombinieren vieler biomedizinischer Datenquellen und das Betrachten sowohl lokaler als auch globaler Muster in den Verbindungen zwischen Arzneimitteln, Genen und Krankheiten besser vorhersagen können, welche Medikamente gegen welche Leiden helfen könnten. Dieses Werkzeug ersetzt zwar nicht klinische Studien oder Tests in der realen Welt, kann aber den riesigen Suchraum einengen und vielversprechende Wirkstoffkandidaten hervorheben – insbesondere bei komplexen Erkrankungen wie Herzkrankheiten und Bluthochdruck. Mit immer detaillierteren biologischen Daten und weiterer Validierung solcher Modelle könnten Ansätze wie MedPathEx zu wertvollen Partnern bei der Umwidmung bestehender Medikamente und der Entwicklung effizienterer Behandlungsstrategien werden.
Zitation: Wu, S., Wang, W., Jiao, H. et al. Enhanced drug disease association prediction through multimodal data integration and meta path guided global local feature fusion. Sci Rep 16, 11038 (2026). https://doi.org/10.1038/s41598-026-36223-9
Schlüsselwörter: Wirkstoff‑Umwidmung, Arzneimittel–Krankheits‑Assoziationen, heterogene Netzwerke, Graph‑Neuronale Netze, computergestützte Wirkstoffentdeckung