Clear Sky Science · sv
Tillväxtdynamik för 3 909 Escherichia coli enkelgen‑utslag i rik och minimal odlingsmiljö
Varför det är viktigt att följa bakterietillväxt
Bakterier finns överallt, från våra tarmar till industriella fermenterare, och deras framgång beror på hur snabbt och hur väl de växer. Även för den välkända laborationsarbetshästen Escherichia coli saknas dock fortfarande detaljerade, standardiserade register över hur tusentals olika genetiska varianter växer över tid. Denna artikel presenterar en stor, noggrant organiserad datamängd som fångar hur nära fyratusen E. coli‑stammar, vardera saknande en enskild gen, växer i näringsrik respektive näringsfattig miljö. Resursen är avsedd som en delad grund som vem som helst kan analysera för att ställa nya frågor om gener, miljöer och bakteriellt beteende.
Många mutanta stammar, två mycket olika dieter
Arbetet utgår från Keio‑kollektionen, ett viktigt bibliotek av E. coli‑stammar där nästan varje icke‑väsentlig gen noggrant har tagits bort. Från denna samling undersökte författarna 3 909 olika mutanter. Var och en odlades parallellt i två typer av flytande odlingsmedia: en näringsrik buljong och ett minimalt medium som endast innehöll basala salter, vitaminer och en enda sockerart. Dessa kontrasterande dieter efterliknar en festmåltid kontra en enkel överlevnadsration, vilket gör det möjligt för forskarna att se hur frånvaron av gener spelar roll när resurser är rikliga jämfört med när de är knappa. 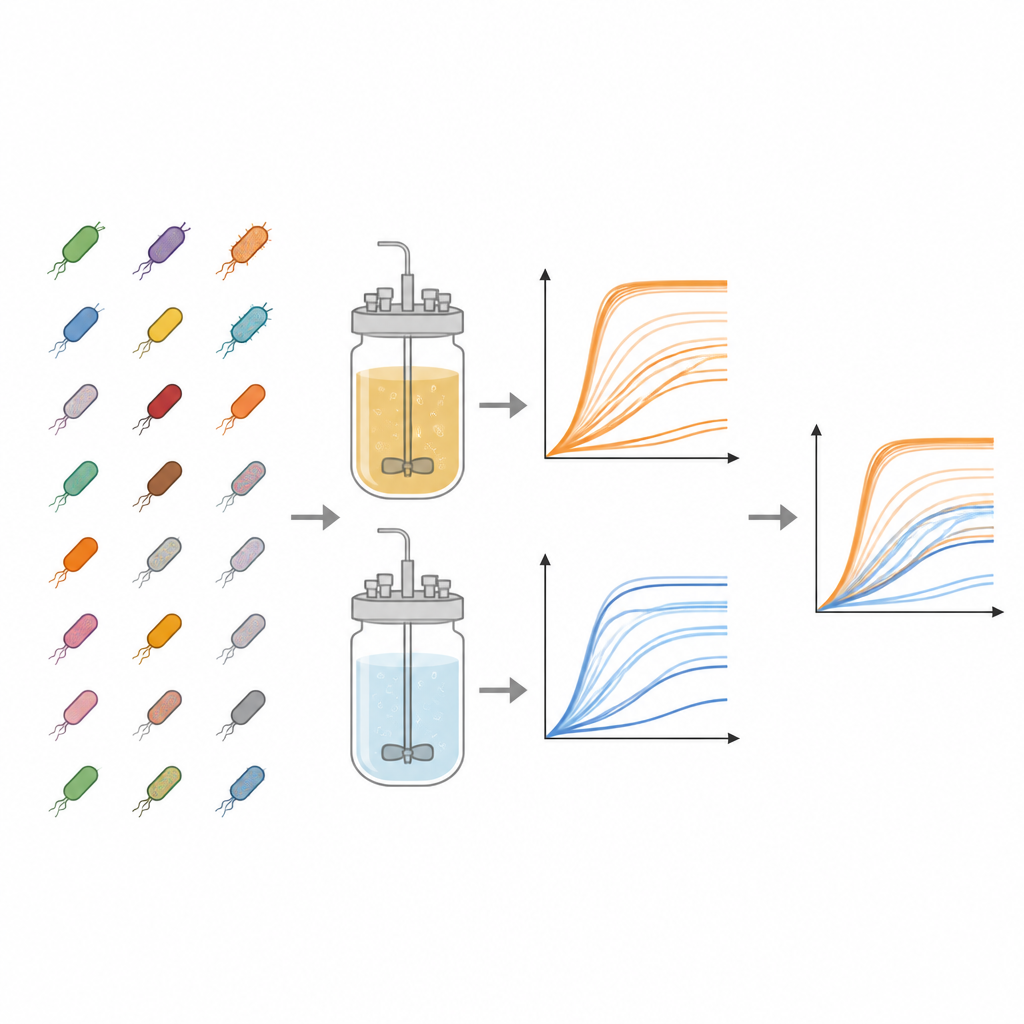
Höggenomströmning för övervakning av tillväxt över tid
För att följa hur varje stam multiplicerade sig använde teamet standardplattor av plast med 96 små brunnar, där varje brunn fylldes med medium och en liten mängd frysta bakterier. Plattorna inkuberades vid kroppslik temperatur med skakning, medan en apparat mätte grumligheten i varje brunn var femtonde minut i upp till två dygn. Grumligheten, avläst som optisk densitet vid 600 nanometer, ökar när cellerna förökar sig och ger en tillväxtkurva som visar lagfas, snabb tillväxt och slutlig mättnad. För varje kombination av stam och medium körde forskarna tre oberoende replikat, vilket genererade totalt 23 454 individuella tillväxtkurvor. De subtraherade en platt‑specifik bakgrundssignal för att rensa data och lagrade alla tidpunkter i tillgängliga kalkylbladsfiler.
Från råa kurvor till enkla beskriva mått
Eftersom tillväxtkurvor är informationsrika men komplexa beräknade författarna också två allmänt använda sammanfattande mått för varje kurva. Det ena är bärförmågan (carrying capacity), det ungefärliga maximala grumlighetsvärdet som uppnås och som speglar hur tät kulturen blir. Det andra är maximal tillväxthastighet, den brantaste delen av kurvan, som visar hur snabbt populationen expanderar under sin snabbaste fas. Dessa värden extraherades av ett Python‑program direkt från de osmidda mätningarna med korta fönster av på varandra följande tidpunkter, och forskarna flaggade fall där ofullständiga kurvor eller brusiga data kunde ge förskjutna resultat. Generellt var både maximal populationsstorlek och snabbaste tillväxthastighet högre i den näringsrika buljongen än i det minimala mediet, vilket överensstämmer med näringsmässiga förväntningar. 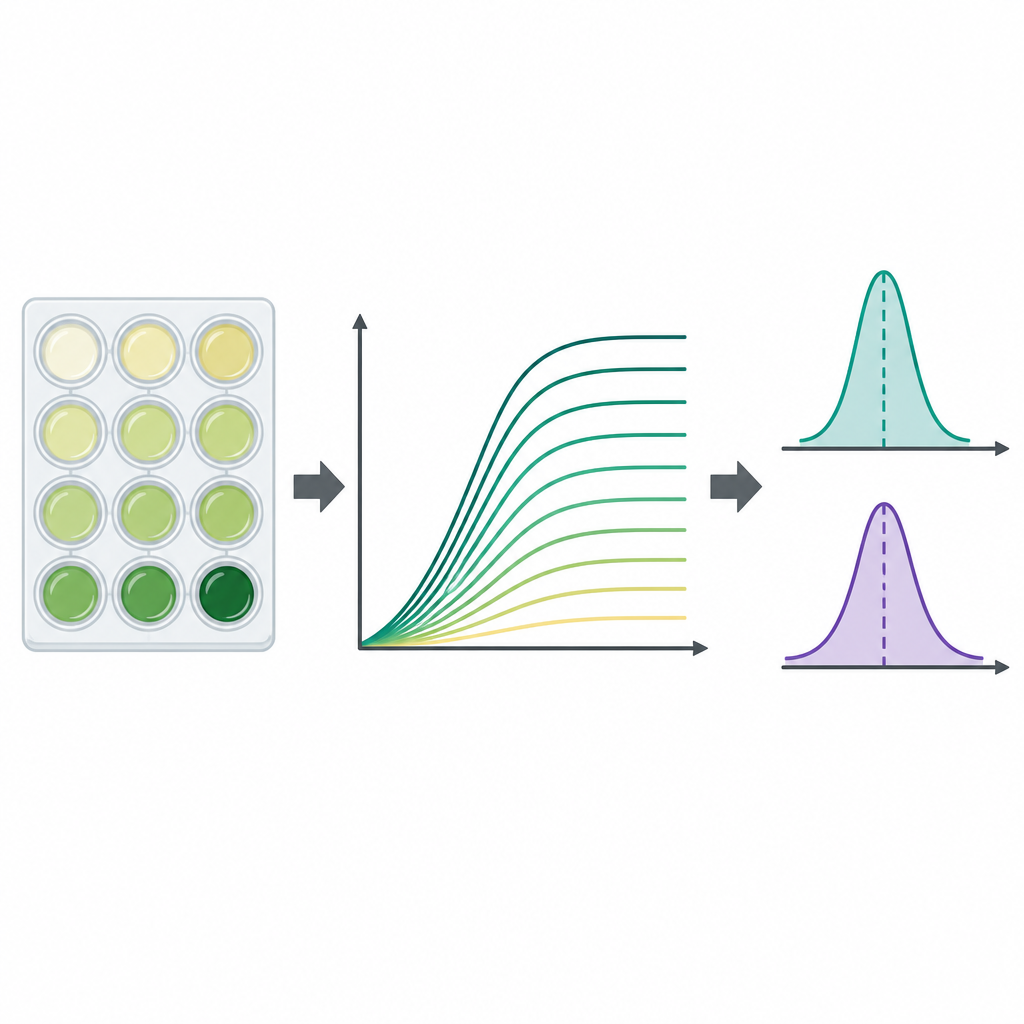
Kvalitetskontroller och sätt att återanvända data
Höggenomströmningsexperiment kan vara känsliga för subtila fel, så författarna kvantifierade noggrant hur reproducerbara deras mätningar var. För varje stam och medium jämförde de de tre replikaten och beräknade hur mycket bärförmåga och tillväxthastighet varierade. De inkluderade också markörer för potentiella avvikare och för kurvor där viktiga faser kan ha missats på grund av den fasta inspelningsfönstret. All denna information levereras tillsammans med huvuddatafilerna, vilket gör det möjligt för framtida användare att välja de delmängder som bäst motsvarar deras egna kvalitetskrav. Datamängden är formaterad för att vara maskinläsbar och kompletteras av genamn, identifierare och breda funktionella kategorier för varje raderad gen.
Vad denna resurs innebär för framtida studier
I stället för att föreslå ett enda biologiskt påstående levererar denna artikel en gemensam, väl dokumenterad karta över hur tusentals E. coli‑mutanter växer i två kontrasterande miljöer. Genom att göra varje tidpunkt och reproducerbarhetsflagga offentligt tillgängliga inbjuder författarna andra att reanalysera kurvorna, testa nya matematiska metoder och koppla tillväxtbeteende till genfunktion, metabola nätverk eller andra nivåer av cellulära data. För icke‑specialister är huvudbudskapet att bakterietillväxt formas av både deras gener och deras omgivning, och att en gemensam datamängd som denna gör det mycket enklare för många grupper att studera och jämföra dessa influenser på ett konsekvent sätt.
Citering: Lao, Z., Ying, BW. Growth dynamics of 3,909 Escherichia coli single-gene knockouts in rich and minimal media. Sci Data 13, 717 (2026). https://doi.org/10.1038/s41597-026-07075-9
Nyckelord: bakterietillväxt, Escherichia coli, genutslag, tillväxtkurvor, mikrobiell fenotypning