Clear Sky Science · es
Dinámica de crecimiento de 3.909 deleciones de un solo gen de Escherichia coli en medios ricos y mínimos
Por qué importa seguir el crecimiento bacteriano
Las bacterias están en todas partes, desde nuestros intestinos hasta biorreactores industriales, y su éxito depende de la rapidez y la eficacia con que crecen. Aun para el conocido organismo modelo de laboratorio Escherichia coli, los científicos carecen de registros detallados y estandarizados sobre cómo crecen con el tiempo miles de variantes genéticas distintas. Este artículo presenta un gran conjunto de datos cuidadosamente organizado que captura cómo cerca de cuatro mil cepas de E. coli, cada una con la pérdida de un solo gen, crecen en condiciones de alimento rico y pobre. El recurso está pensado como una base compartida que cualquiera puede explorar para formular nuevas preguntas sobre genes, ambientes y comportamiento bacteriano.
Muchas cepas mutantes, dos dietas muy distintas
El trabajo se centra en la colección Keio, una biblioteca histórica de cepas de E. coli en la que casi todos los genes no esenciales han sido eliminados con precisión. A partir de esta colección, los autores examinaron 3.909 mutantes distintos. Cada uno se cultivó en paralelo en dos tipos de medio líquido: un caldo nutritivo rico y un medio mínimo que contiene solo sales básicas, vitaminas y un único azúcar. Estas dietas contrastantes imitan un festín frente a una ración de supervivencia sencilla, lo que permite a los investigadores ver cuánto importan los genes faltantes cuando los recursos son abundantes frente a cuando escasean. 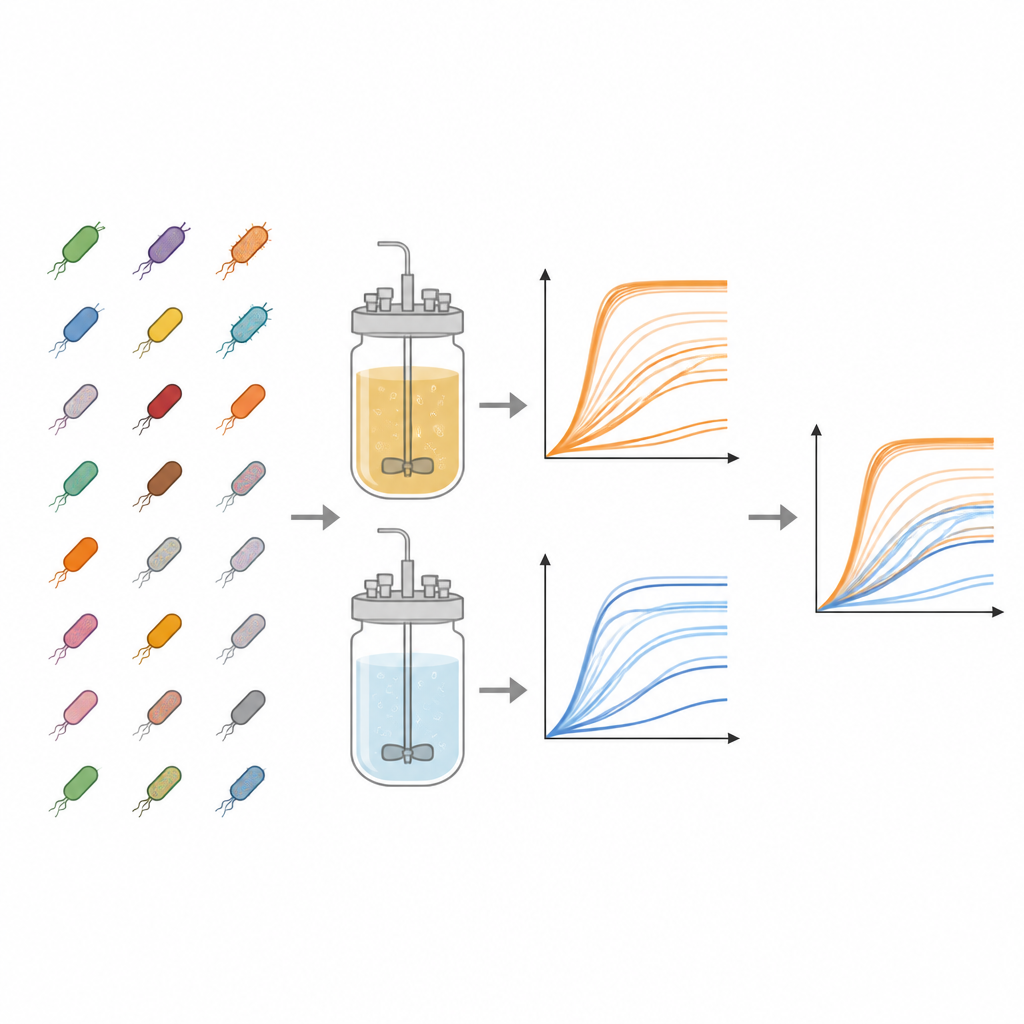
Monitorización de alto rendimiento del crecimiento a lo largo del tiempo
Para seguir cómo se multiplicaba cada cepa, el equipo usó placas plásticas estándar de 96 pocillos, llenando cada pocillo con medio y una pequeña cantidad de bacterias congeladas. Las placas se incubaron a temperatura similar a la corporal con agitación, mientras una máquina medía la turbidez de cada pocillo cada 15 minutos durante hasta dos días. La turbidez, leída como densidad óptica a 600 nanómetros, aumenta a medida que las células se multiplican, generando una curva de crecimiento que muestra la latencia, el crecimiento rápido y la eventual saturación. Para cada combinación de cepa y medio, los investigadores realizaron tres experimentos independientes, generando 23.454 curvas de crecimiento individuales en total. Restaron una señal de fondo específica de la placa para limpiar los datos y almacenaron todos los puntos temporales en archivos de hojas de cálculo accesibles.
De las curvas crudas a descriptores simples
Como las curvas de crecimiento son ricas pero complejas, los autores también calcularon dos cifras resumen muy usadas para cada curva. Una es la capacidad de carga, la turbidez máxima aproximada alcanzada, que refleja qué tan denso se vuelve el cultivo. La otra es la tasa máxima de crecimiento, la parte más empinada de la curva, que indica qué tan rápido se expande la población durante su fase más veloz. Estos valores fueron extraídos por un programa en Python directamente de las mediciones sin suavizar usando ventanas cortas de puntos temporales consecutivos, y los investigadores marcaron los casos en que curvas incompletas o datos ruidosos pudieran sesgar el resultado. En general, tanto el tamaño máximo de la población como la tasa de crecimiento más rápida fueron mayores en el caldo rico que en el medio mínimo, como cabría esperar desde el punto de vista nutricional. 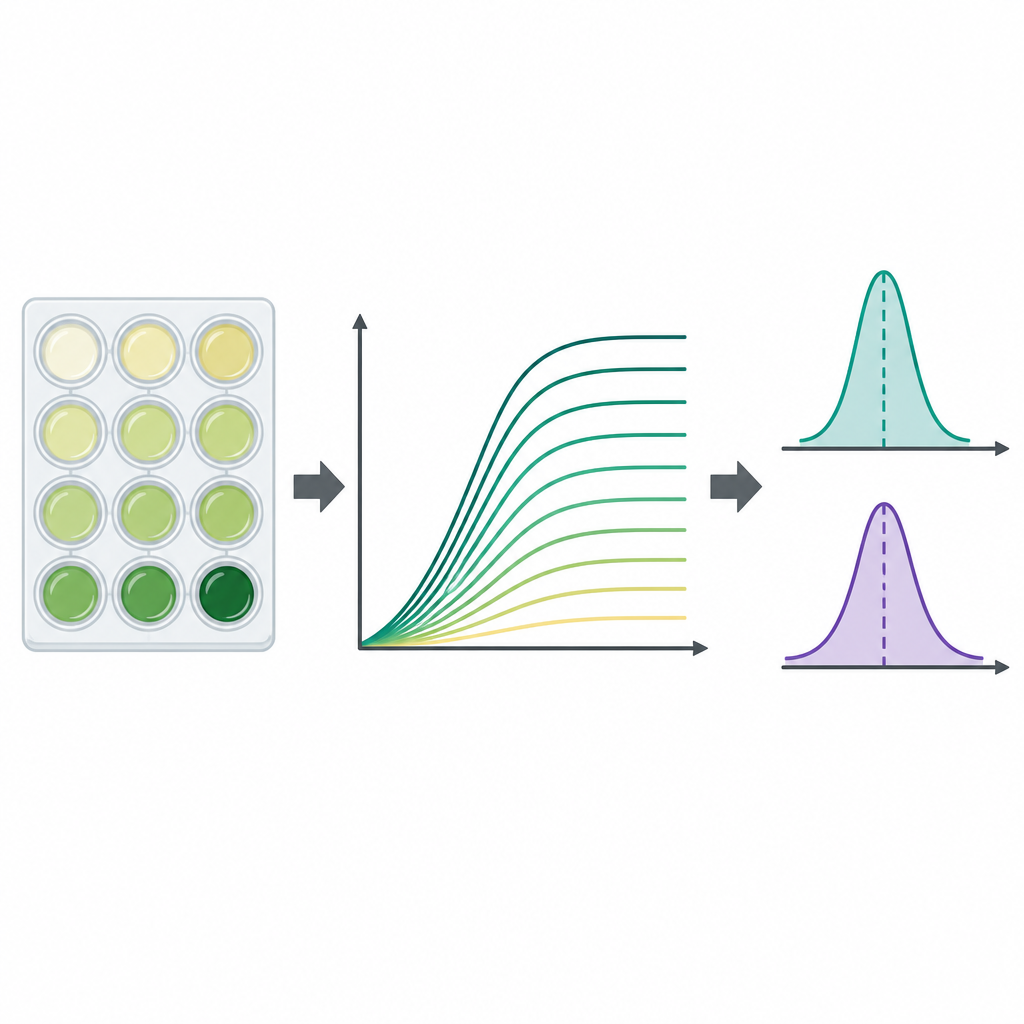
Controles de calidad y formas de reutilizar los datos
Los experimentos de alto rendimiento pueden ser propensos a errores sutiles, por lo que los autores cuantificaron cuidadosamente cuán repetibles eran sus mediciones. Para cada cepa y medio compararon las tres réplicas y calcularon cuánto variaban la capacidad de carga y la tasa de crecimiento. También incluyeron marcadores para posibles valores atípicos y para curvas en las que fases importantes podrían haberse perdido debido a la ventana de registro fija. Toda esta información se agrupa con los archivos de datos principales, lo que permite a futuros usuarios elegir los subconjuntos que mejor se ajusten a sus propios criterios de calidad. El conjunto de datos está formateado para ser legible por máquinas y va acompañado de nombres de genes, identificadores y categorías funcionales amplias para cada gen eliminado.
Qué significa este recurso para estudios futuros
En lugar de presentar una única afirmación biológica, este artículo ofrece un mapa compartido y bien documentado de cómo crecen miles de mutantes de E. coli en dos entornos contrastantes. Al hacer públicos todos los puntos temporales y las banderas de fiabilidad, los autores invitan a otros a reanalizar las curvas, probar nuevos métodos matemáticos y conectar el comportamiento de crecimiento con la función génica, redes metabólicas u otras capas de datos celulares. Para los no especialistas, el mensaje clave es que el crecimiento bacteriano está moldeado conjuntamente por sus genes y su entorno, y que disponer de un conjunto de datos común como este facilita enormemente que muchos grupos estudien y comparen esas influencias de manera consistente.
Cita: Lao, Z., Ying, BW. Growth dynamics of 3,909 Escherichia coli single-gene knockouts in rich and minimal media. Sci Data 13, 717 (2026). https://doi.org/10.1038/s41597-026-07075-9
Palabras clave: crecimiento bacteriano, Escherichia coli, deleciones génicas, curvas de crecimiento, fenotipado microbiano