Clear Sky Science · nl
Groeidynamiek van 3.909 Escherichia coli eencellige gen‑knockouts in rijke en minimale media
Waarom het volgen van bacteriële groei ertoe doet
Bacteriën zijn overal, van onze darmen tot industriële fermenters, en hun succes hangt af van hoe snel en hoe goed ze groeien. Zelfs voor de bekende laboratoriummodel E. coli ontbreken wetenschappers echter nog steeds gedetailleerde, gestandaardiseerde registraties van hoe duizenden verschillende genetische varianten zich in de tijd ontwikkelen. Dit artikel introduceert een grote, zorgvuldig geordende dataset die vastlegt hoe bijna vierenveertighonderd E. coli‑stammen, elk met precies één verwijderd gen, groeien in rijke en arme voedingsomstandigheden. De bron is bedoeld als gedeelde basis die iedereen kan gebruiken om nieuwe vragen te stellen over genen, omgeving en bacterieel gedrag.
Veel mutanten, twee heel verschillende diëten
Het werk draait om de Keio‑collectie, een baanbrekende bibliotheek van E. coli‑stammen waarin bijna elk niet‑essentieel gen precies is verwijderd. Uit deze collectie onderzochten de auteurs 3.909 verschillende mutanten. Elke stam werd parallel gekweekt in twee soorten vloeibaar medium: een voedingsrijk bouillon en een minimaal medium dat alleen basiszouten, vitamines en één suiker bevat. Deze contrasterende diëten bootsen een feestmaal versus een eenvoudige overlevingsrantsoen na, waardoor onderzoekers kunnen zien wanneer ontbrekende genen belangrijk worden: bij overvloed aan hulpbronnen vergeleken met schaarste. 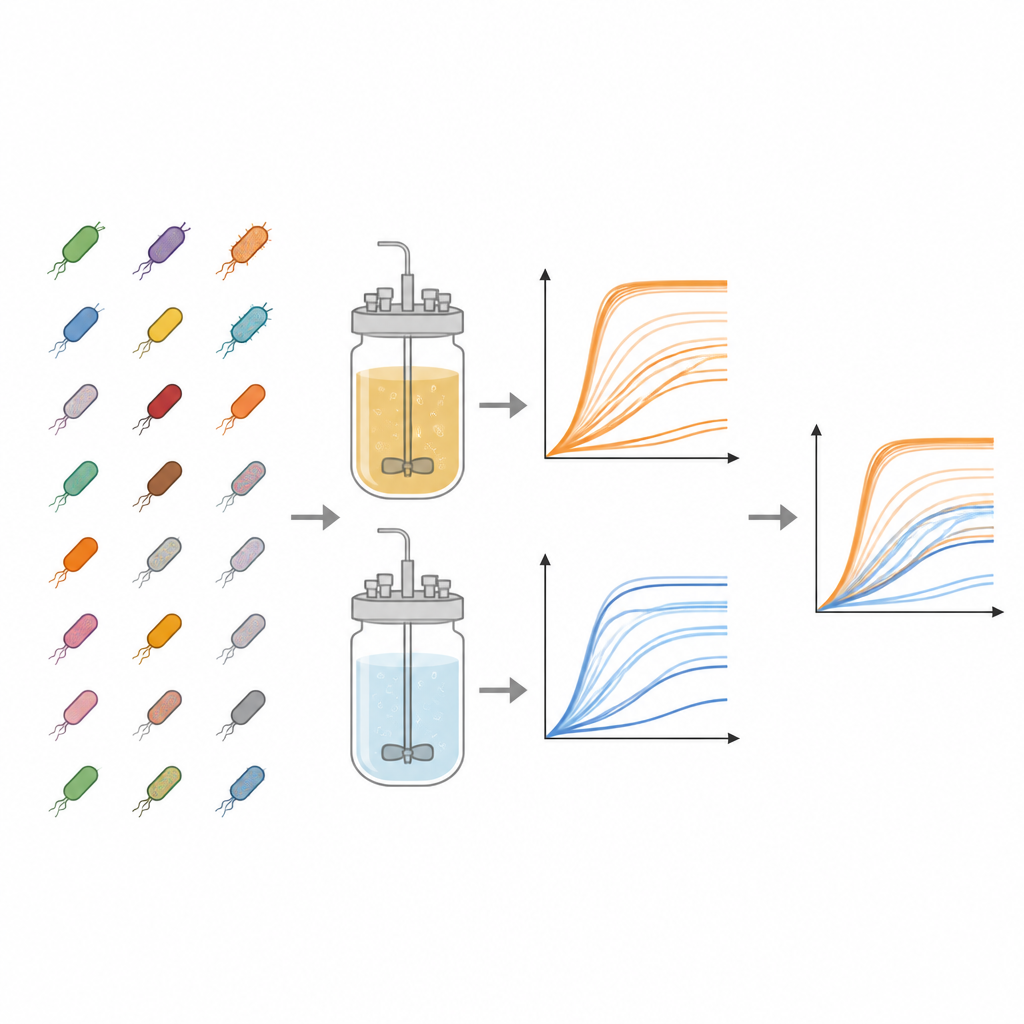
Hoge doorvoer bij het volgen van groei in de tijd
Om te volgen hoe elke stam zich vermeerderde, gebruikte het team standaard plastic platen met 96 kleine putjes, waarbij elk putje werd gevuld met medium en een kleine hoeveelheid ingevroren bacteriën. Platen werden op lichaamstemperatuur geïncubeerd met schudden, terwijl een apparaat elke 15 minuten gedurende maximaal twee dagen de troebeling van elk putje mat. Troebeling, gemeten als optische dichtheid bij 600 nanometer, neemt toe naarmate cellen zich vermenigvuldigen en levert een groeicurve op die vertraging, snelle groei en uiteindelijke verzadiging toont. Voor elke combinatie van stam en medium voerden de onderzoekers drie onafhankelijke experimenten uit, waarmee ze in totaal 23.454 individuele groeicurven genereerden. Ze trokken een plaat‑specifieke achtergrondsignaal af om de gegevens op te schonen en bewaarden alle tijdpunten in toegankelijke spreadsheetbestanden.
Van ruwe curven naar eenvoudige beschrijvers
Aangezien groeicurven rijk maar complex zijn, berekenden de auteurs ook twee veelgebruikte samenvattende grootheden voor elke curve. De ene is de draagcapaciteit, de geschatte maximale troebeling die wordt bereikt en die aangeeft hoe dicht de cultuur wordt. De andere is de maximale groeisnelheid, het steilste deel van de curve, dat aangeeft hoe snel de populatie zich tijdens de snelste fase uitbreidt. Deze waarden werden door een Python‑programma rechtstreeks uit de onbewerkte metingen gehaald met korte vensters van opeenvolgende tijdpunten, en de onderzoekers markeerden gevallen waarin onvolledige curven of lawaaierige data het resultaat zouden kunnen vertekenen. In het algemeen waren zowel de maximale populatieomvang als de snelste groeisnelheid hoger in de rijke bouillon dan in het minimale medium, zoals je vanuit nutritioneel perspectief zou verwachten. 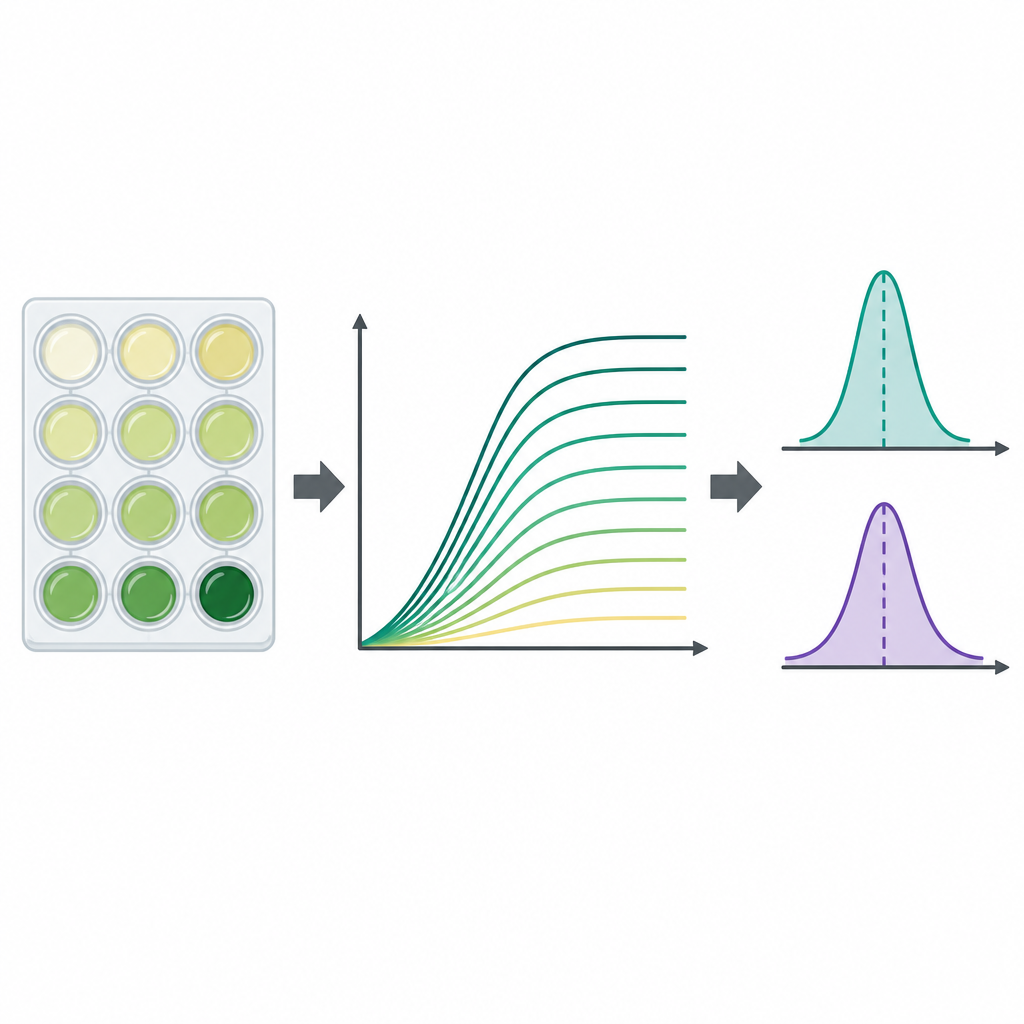
Kwaliteitscontroles en manieren om de data opnieuw te gebruiken
Hoge‑doorvoerexperimenten kunnen gevoelig zijn voor subtiele fouten, dus de auteurs kwantificeerden zorgvuldig hoe reproduceerbaar hun metingen waren. Voor elke stam en elk medium vergeleken ze de drie replicaten en berekenden ze hoeveel de draagcapaciteit en groeisnelheid varieerden. Ze toevoegden ook markeringen voor potentiële uitbijters en voor curven waarbij belangrijke fasen mogelijk zijn gemist door het vaste registratievenster. Al deze informatie wordt gebundeld met de hoofdgegevensbestanden, zodat toekomstige gebruikers de deelverzamelingen kunnen kiezen die het beste bij hun eigen kwaliteitsnormen passen. De dataset is geformatteerd om machinaal leesbaar te zijn en wordt aangevuld met genamen, identifiers en brede functionele categorieën voor elk verwijderde gen.
Wat deze bron betekent voor toekomstig onderzoek
In plaats van één enkele biologische claim te presenteren, levert dit artikel een gedeelde, goed gedocumenteerde kaart van hoe duizenden E. coli‑mutanten groeien in twee contrasterende omgevingen. Door elk tijdpunt en elke betrouwbaarheidsmarker openbaar beschikbaar te maken, nodigen de auteurs anderen uit om de curven opnieuw te analyseren, nieuwe wiskundige methoden te testen en groeigedrag te koppelen aan genfunctie, metabolische netwerken of andere lagen van cellulair bewijs. Voor niet‑specialisten is de kernboodschap dat de groei van bacteriën gezamenlijk wordt gevormd door hun genen en hun omgeving, en dat het beschikken over een gemeenschappelijke dataset als deze het voor veel groepen veel eenvoudiger maakt om die invloeden op een consistente manier te bestuderen en te vergelijken.
Bronvermelding: Lao, Z., Ying, BW. Growth dynamics of 3,909 Escherichia coli single-gene knockouts in rich and minimal media. Sci Data 13, 717 (2026). https://doi.org/10.1038/s41597-026-07075-9
Trefwoorden: bacteriële groei, Escherichia coli, gen knockouts, groeicurven, microbieel phenotyperen