Clear Sky Science · pl
Dynamiczne tempo wzrostu 3 909 pojedynczych delecji genów Escherichia coli w bogatym i minimalnym podłożu
Dlaczego śledzenie wzrostu bakterii ma znaczenie
Bakterie występują wszędzie — od naszych jelit po fermentory przemysłowe — a ich sukces zależy od tego, jak szybko i efektywnie się namnażają. Nawet dla znanej szczepu laboratoryjnego Escherichia coli wciąż brakuje szczegółowych, ustandaryzowanych zapisów pokazujących, jak tysiące różnych wariantów genetycznych rośnie w czasie. Artykuł przedstawia duży, starannie uporządkowany zestaw danych, który rejestruje, jak niemal cztery tysiące szczepów E. coli, z każdą pojedynczą utratą genu, rozwija się w warunkach bogatych i ubogich w składniki odżywcze. Zasób ma służyć jako wspólna podstawa, którą każdy może wykorzystać do zadawania nowych pytań o geny, środowisko i zachowanie bakterii.
Wiele szczepów mutantów, dwie wyraźnie różne diety
Badanie skupia się na kolekcji Keio — przełomowej bibliotece szczepów E. coli, w których niemal każdy gen nieistotny dla przeżycia został precyzyjnie usunięty. Z tej kolekcji autorzy przebadali 3 909 różnych mutantów. Każdy szczep hodowano równolegle w dwóch rodzajach płynnego podłoża: w pożywce bogatej w składniki oraz w minimalnym medium zawierającym jedynie podstawowe sole, witaminy i pojedynczy cukier. Te przeciwstawne „diery” naśladują uczty versus skromną rację przetrwania, pozwalając badaczom zobaczyć, jak brakujące geny wpływają przy bogatych zasobach w porównaniu z ich niedoborem. 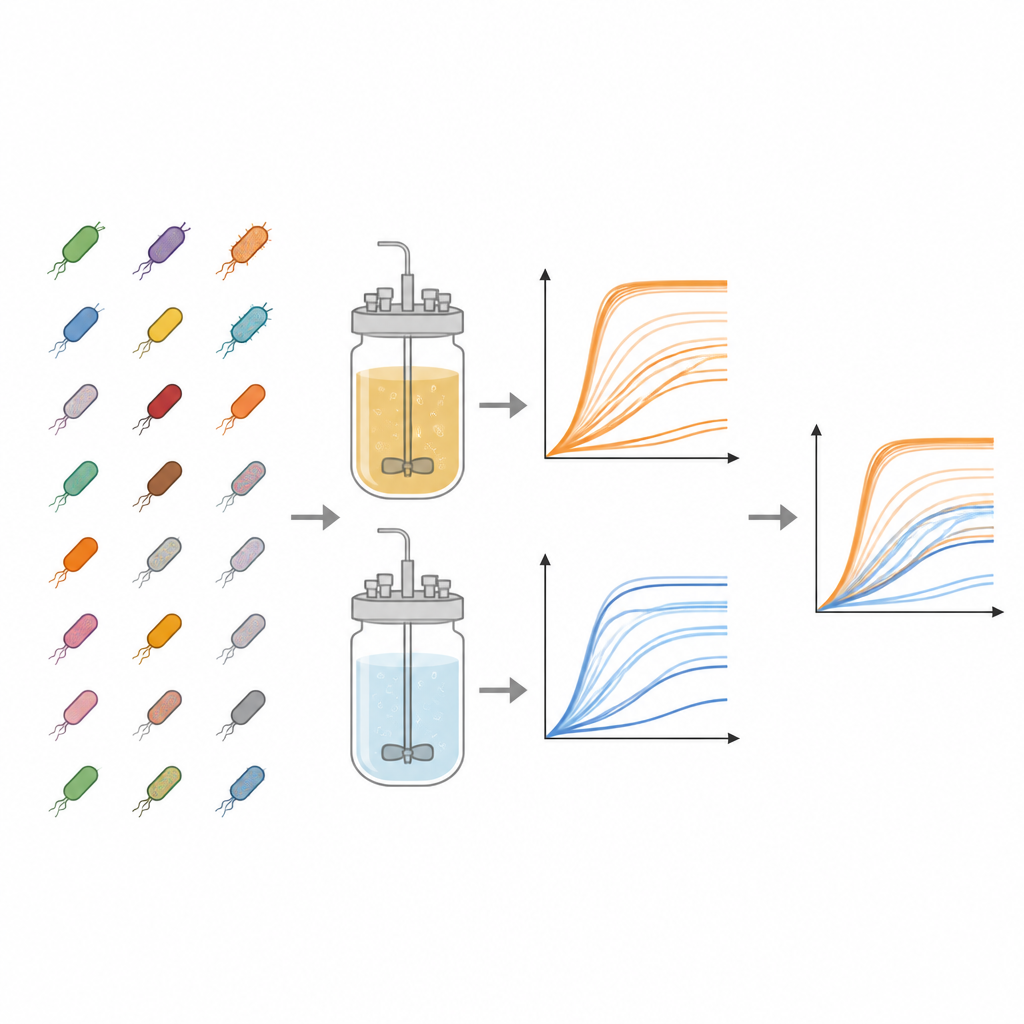
Wysokowydajne monitorowanie wzrostu w czasie
Aby śledzić namnażanie każdego szczepu, zespół użył standardowych plastikowych płytek z 96 małymi dołkami, napełniając każdy dołek podłożem i niewielką ilością rozmrożonych bakterii. Płytki inkubowano w temperaturze przypominającej temperaturę ciała z mieszaniem, podczas gdy urządzenie mierzyło mętność każdego dołka co 15 minut przez okres do dwóch dni. Mętność, mierzona jako gęstość optyczna przy 600 nanometrach, rośnie wraz z namnażaniem się komórek, tworząc krzywą wzrostu pokazującą fazę utajenia, szybki wzrost i ostateczne nasycenie. Dla każdej kombinacji szczep–podłoże badacze przeprowadzili trzy niezależne eksperymenty, generując łącznie 23 454 indywidualnych krzywych wzrostu. Odjęli sygnał tła specyficzny dla płytki, aby oczyścić dane, i zapisali wszystkie punkty czasowe w dostępnych plikach arkuszy kalkulacyjnych.
Z surowych krzywych do prostych deskryptorów
Ponieważ krzywe wzrostu są bogate, lecz skomplikowane, autorzy obliczyli także dwa powszechnie używane podsumowujące parametry dla każdej krzywej. Jednym z nich jest nośność (carrying capacity), czyli przybliżona maksymalna mętność osiągnięta przez hodowlę, odzwierciedlająca, jak gęsta staje się kultura. Drugim jest maksymalna szybkość wzrostu, czyli najstromszy fragment krzywej, mówiący, jak szybko populacja rośnie w najszybszej fazie. Wartości te wyodrębniono za pomocą programu w Pythonie bez wcześniejszego wygładzania pomiarów, stosując krótkie okna kolejnych punktów czasowych, a badacze oznaczyli przypadki, gdzie niekompletne krzywe lub zaszumione dane mogły zniekształcić wynik. Ogólnie rzecz biorąc, zarówno maksymalny rozmiar populacji, jak i najszybsza szybkość wzrostu były wyższe w bogatej pożywce niż w medium minimalnym — co z punktu widzenia żywieniowego jest spodziewane. 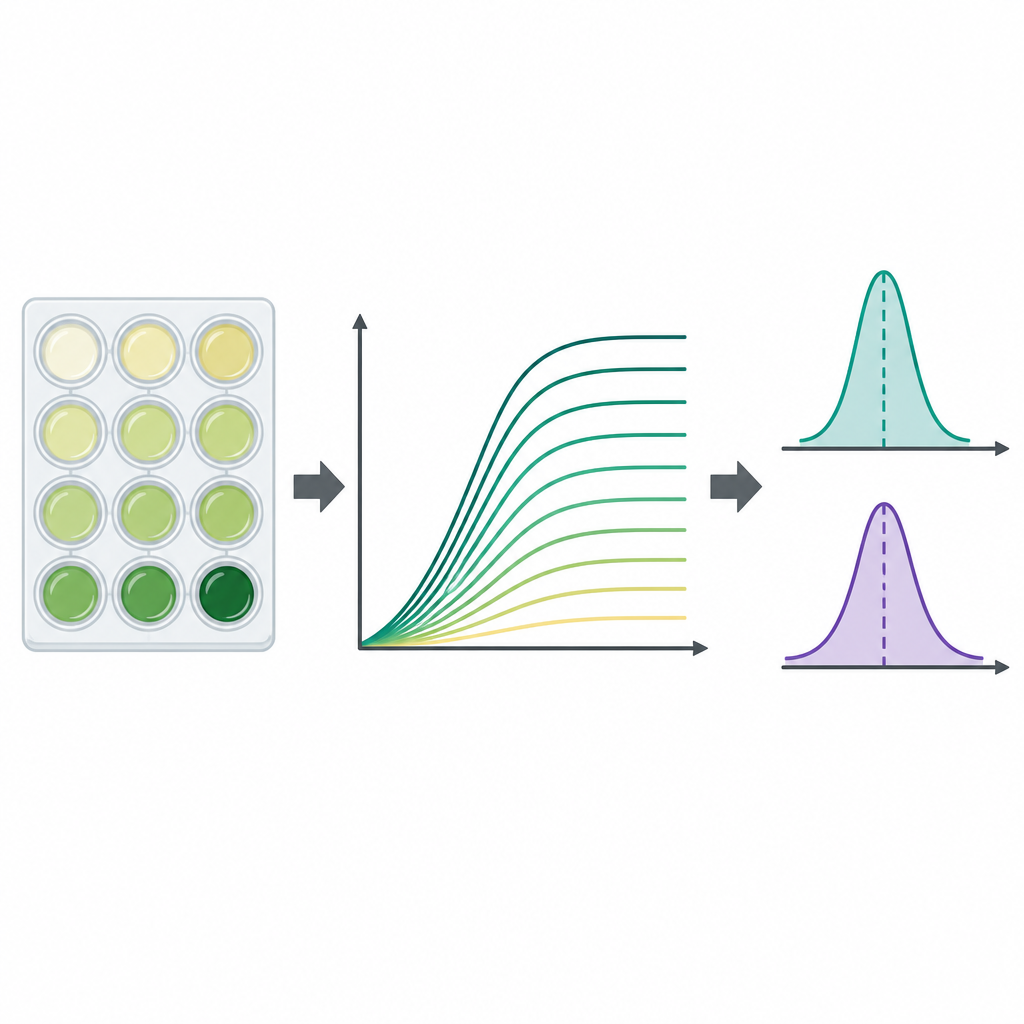
Kontrole jakości i sposoby ponownego wykorzystania danych
Eksperymenty wysokoprzepustowe są podatne na subtelne błędy, dlatego autorzy starannie ocenili powtarzalność swoich pomiarów. Dla każdego szczepu i podłoża porównali trzy replikaty i obliczyli, jak bardzo zmieniały się nośność oraz tempo wzrostu. Dołączyli także znaczniki potencjalnych wartości odstających oraz krzywych, w których ważne fazy mogły zostać pominięte z powodu stałego okna rejestracji. Wszystkie te informacje są dołączone do głównych plików danych, umożliwiając przyszłym użytkownikom wybór podzbiorów zgodnych z ich kryteriami jakości. Zestaw danych został sformatowany tak, by był czytelny dla maszyn, i opatrzony nazwami genów, identyfikatorami oraz szerokimi kategoriami funkcjonalnymi dla każdego usuniętego genu.
Co ten zasób oznacza dla przyszłych badań
Zamiast wysuwać jedną konkretną tezę biologiczną, artykuł dostarcza wspólną, dobrze udokumentowaną mapę tego, jak tysiące mutantów E. coli rośnie w dwóch kontrastujących środowiskach. Udostępniając każdy punkt czasowy i flagi wiarygodności publicznie, autorzy zachęcają innych do ponownej analizy krzywych, testowania nowych metod matematycznych oraz łączenia zachowań wzrostowych z funkcją genów, sieciami metabolicznymi lub innymi warstwami danych komórkowych. Dla osób niebędących specjalistami kluczowe przesłanie jest takie, że wzrost bakterii kształtują wspólnie ich geny i otoczenie, a posiadanie wspólnego zestawu danych ułatwia wielu grupom badanie i porównywanie tych wpływów w spójny sposób.
Cytowanie: Lao, Z., Ying, BW. Growth dynamics of 3,909 Escherichia coli single-gene knockouts in rich and minimal media. Sci Data 13, 717 (2026). https://doi.org/10.1038/s41597-026-07075-9
Słowa kluczowe: wzrost bakterii, Escherichia coli, deleje genów, krzywe wzrostu, fenotypowanie drobnoustrojów