Clear Sky Science · fr
Dynamiques de croissance de 3 909 mutants monogéniques d’Escherichia coli en milieux riches et minimaux
Pourquoi suivre la croissance bactérienne est important
Les bactéries sont omniprésentes, de nos intestins aux fermenteurs industriels, et leur réussite dépend de la rapidité et de l’efficacité de leur croissance. Pourtant, même pour le bien connu Escherichia coli utilisé en laboratoire, il manque encore des enregistrements détaillés et standardisés montrant comment des milliers de variantes génétiques croissent au fil du temps. Cet article présente un jeu de données vaste et soigneusement organisé qui capture la croissance de près de quatre mille souches d’E. coli, chacune privée d’un seul gène, en conditions alimentaires riches et pauvres. La ressource est conçue comme une base partagée que n’importe qui peut exploiter pour poser de nouvelles questions sur les gènes, les environnements et le comportement bactérien.
De nombreuses souches mutantes, deux régimes très différents
Le travail s’appuie sur la collection Keio, une bibliothèque emblématique de souches d’E. coli dans laquelle presque chaque gène non essentiel a été supprimé de manière précise. À partir de cette collection, les auteurs ont examiné 3 909 mutants différents. Chacun a été cultivé en parallèle dans deux types de milieux liquides : un bouillon riche en nutriments et un milieu minimal contenant seulement des sels de base, des vitamines et un seul sucre. Ces régimes contrastés reproduisent, d’une part, l’abondance et, d’autre part, une ration de survie simple, permettant aux chercheurs d’évaluer l’impact des gènes manquants lorsque les ressources sont abondantes comparé à lorsqu’elles sont limitées. 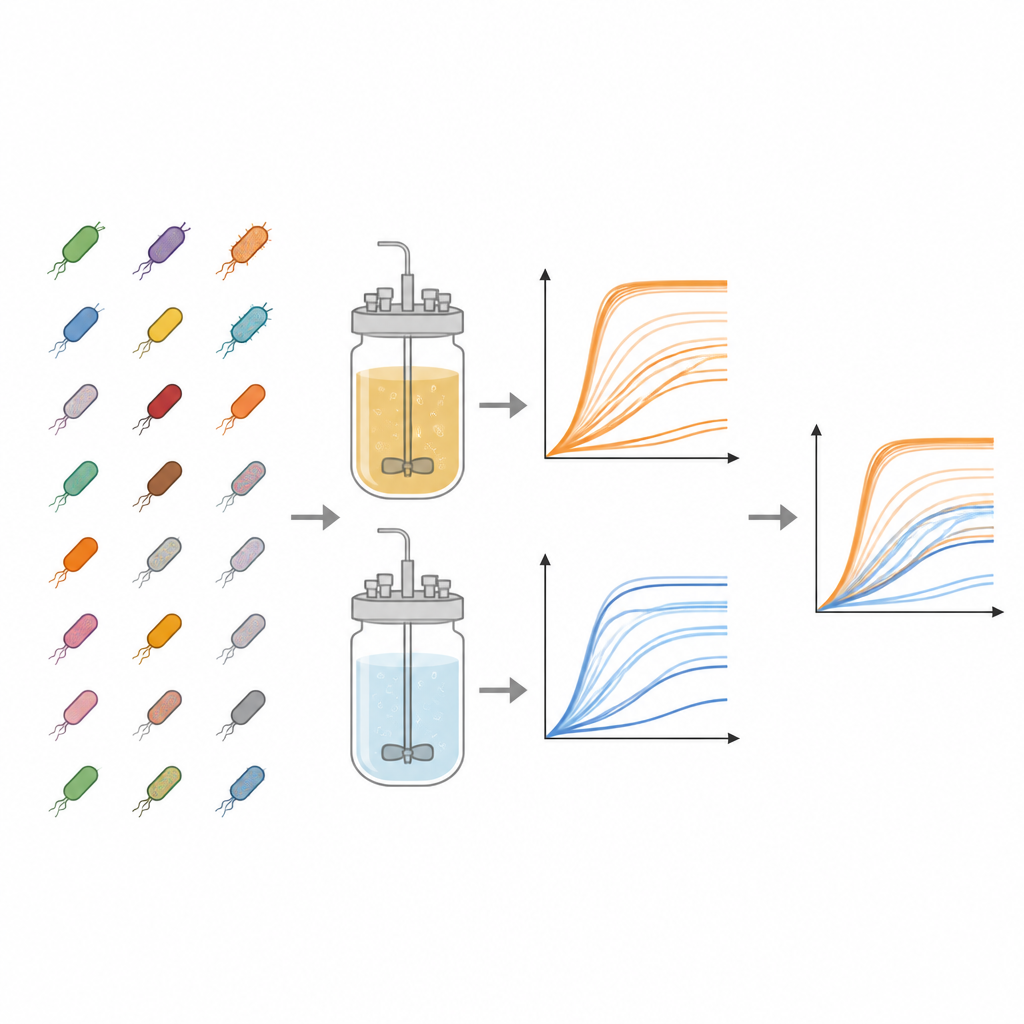
Suivi haute capacité de la croissance au fil du temps
Pour suivre la multiplication de chaque souche, l’équipe a utilisé des plaques en plastique standard à 96 puits, remplissant chaque puits de milieu et d’une petite quantité de bactéries congelées. Les plaques ont été incubées à une température proche de celle du corps avec agitation, tandis qu’une machine mesurait la turbidité de chaque puits toutes les 15 minutes pendant jusqu’à deux jours. La turbidité, lue sous forme de densité optique à 600 nanomètres, augmente à mesure que les cellules se multiplient, produisant une courbe de croissance montrant la latence, la croissance rapide et l’éventuel plateau. Pour chaque combinaison souche/milieu, les chercheurs ont réalisé trois expériences indépendantes, générant au total 23 454 courbes de croissance individuelles. Ils ont soustrait un signal de fond spécifique à chaque plaque pour nettoyer les données et ont stocké tous les points temporels dans des fichiers de tableurs accessibles.
Des courbes brutes à des descripteurs simples
Parce que les courbes de croissance sont riches mais complexes, les auteurs ont également calculé deux nombres résumés largement utilisés pour chaque courbe. Le premier est la capacité d’accueil, l’approximation de la turbidité maximale atteinte, qui reflète la densité maximale de la culture. Le second est le taux de croissance maximal, la pente la plus raide de la courbe, qui indique la vitesse d’expansion de la population durant sa phase la plus rapide. Ces valeurs ont été extraites par un programme Python directement à partir des mesures non lissées en utilisant de courtes fenêtres de points temporels consécutifs, et les chercheurs ont signalé les cas où des courbes incomplètes ou des données bruitées pourraient biaiser le résultat. De manière générale, la taille maximale de la population et le taux de croissance le plus élevé étaient supérieurs dans le bouillon riche que dans le milieu minimal, comme on pouvait s’y attendre d’un point de vue nutritionnel. 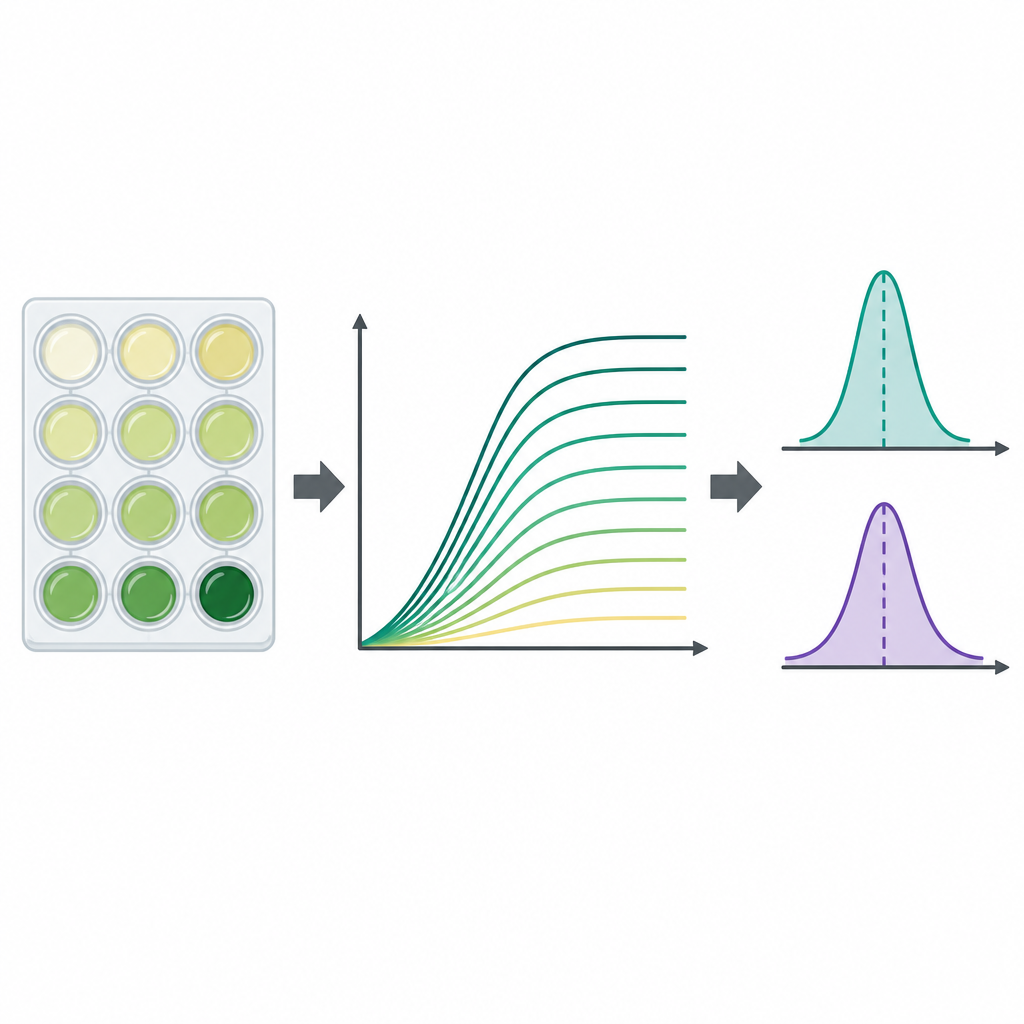
Contrôles de qualité et modalités de réutilisation des données
Les expériences à haut débit peuvent être sujettes à des erreurs subtiles, c’est pourquoi les auteurs ont quantifié avec soin la répétabilité de leurs mesures. Pour chaque souche et chaque milieu, ils ont comparé les trois réplicats et calculé la variation de la capacité d’accueil et du taux de croissance. Ils ont également inclus des indicateurs pour d’éventuels valeurs aberrantes et pour les courbes où des phases importantes ont pu être manquées à cause de la fenêtre d’enregistrement fixe. Toutes ces informations sont regroupées avec les fichiers de données principaux, permettant aux futurs utilisateurs de sélectionner les sous-ensembles qui correspondent le mieux à leurs propres critères de qualité. Le jeu de données est formaté pour être lisible par machine et est accompagné des noms de gènes, identifiants et grandes catégories fonctionnelles pour chaque gène supprimé.
Ce que cette ressource signifie pour les études à venir
Plutôt que de présenter une unique conclusion biologique, cet article fournit une carte partagée et bien documentée montrant comment des milliers de mutants d’E. coli croissent dans deux environnements contrastés. En rendant publics tous les points temporels et les indicateurs de fiabilité, les auteurs invitent d’autres équipes à réanalyser les courbes, tester de nouvelles méthodes mathématiques et relier le comportement de croissance à la fonction des gènes, aux réseaux métaboliques ou à d’autres couches de données cellulaires. Pour les non-spécialistes, le message principal est que la croissance bactérienne est façonnée conjointement par leurs gènes et leur environnement, et que disposer d’un jeu de données commun comme celui-ci facilite grandement l’étude et la comparaison de ces influences de manière cohérente.
Citation: Lao, Z., Ying, BW. Growth dynamics of 3,909 Escherichia coli single-gene knockouts in rich and minimal media. Sci Data 13, 717 (2026). https://doi.org/10.1038/s41597-026-07075-9
Mots-clés: croissance bactérienne, Escherichia coli, suppression de gènes, courbes de croissance, phénotypage microbien