Clear Sky Science · pt
Dinâmica de crescimento de 3.909 nocaute de gene único de Escherichia coli em meios ricos e mínimos
Por que acompanhar o crescimento bacteriano importa
Bactérias estão em todo lugar, do nosso intestino a fermentadores industriais, e seu sucesso depende de quão rápido e quão bem elas crescem. Mesmo para o conhecido organismo de laboratório Escherichia coli, os cientistas ainda carecem de registros detalhados e padronizados sobre como milhares de variantes genéticas diferentes crescem ao longo do tempo. Este artigo apresenta um grande conjunto de dados cuidadosamente organizado que captura como quase quatro mil linhagens de E. coli, cada uma com um gene ausente, crescem em condições de alimento rico e pobre. O recurso destina-se a ser uma base compartilhada que qualquer pessoa pode explorar para levantar novas questões sobre genes, ambientes e comportamento bacteriano.
Muitas linhagens mutantes, duas dietas muito diferentes
O trabalho centra-se na coleção Keio, uma biblioteca marcante de linhagens de E. coli na qual quase todos os genes não essenciais foram precisamente deletados. A partir dessa coleção, os autores examinaram 3.909 mutantes diferentes. Cada um foi cultivado em paralelo em dois tipos de meio líquido: um caldo nutritivo rico e um meio mínimo contendo apenas sais básicos, vitaminas e um único açúcar. Essas dietas contrastantes imitam um banquete versus uma ração de sobrevivência simples, permitindo aos pesquisadores ver como a falta de genes importa quando os recursos são abundantes em comparação com quando são escassos. 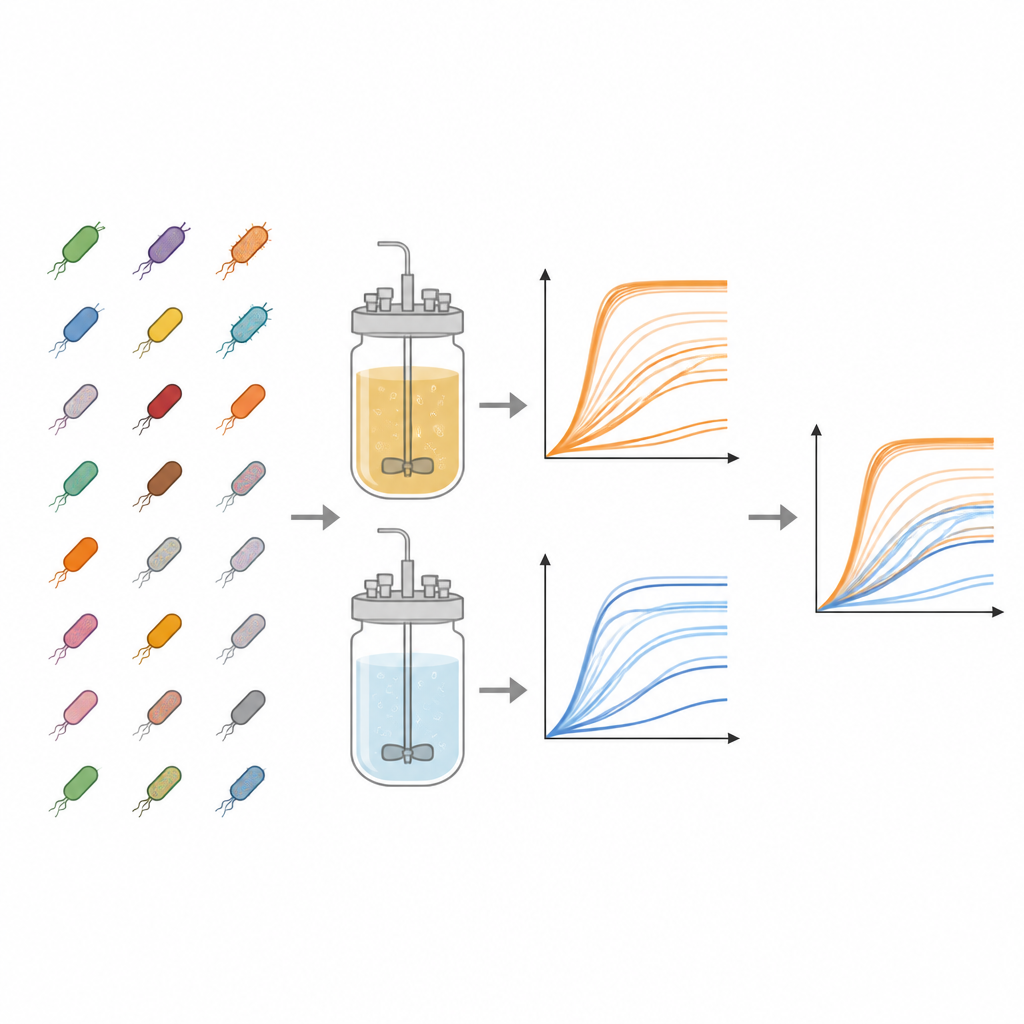
Monitoramento de alto rendimento do crescimento ao longo do tempo
Para acompanhar como cada linhagem se multiplicava, a equipe usou placas plásticas padrão com 96 pequenos poços, preenchendo cada poço com meio e uma pequena quantidade de bactéria congelada. As placas foram incubadas em temperatura semelhante à corporal com agitação, enquanto uma máquina media a turbidez de cada poço a cada 15 minutos por até dois dias. A turbidez, lida como densidade óptica a 600 nanômetros, aumenta à medida que as células se multiplicam, produzindo uma curva de crescimento que mostra latência, crescimento rápido e eventual saturação. Para cada combinação de linhagem e meio, os pesquisadores realizaram três experimentos independentes, gerando 23.454 curvas de crescimento individuais no total. Eles subtraíram um sinal de fundo específico da placa para limpar os dados e armazenaram todos os pontos no tempo em arquivos de planilha acessíveis.
Das curvas brutas a descritores simples
Como as curvas de crescimento são ricas, mas complexas, os autores também calcularam dois números-resumo amplamente usados para cada curva. Um é a capacidade de suporte, a turbidez máxima aproximada alcançada, que reflete quão denso o cultivo se torna. O outro é a taxa máxima de crescimento, a parte mais íngreme da curva, que indica quão rapidamente a população se expande durante sua fase mais rápida. Esses valores foram extraídos por um programa Python diretamente das medições não suavizadas usando pequenas janelas de pontos de tempo consecutivos, e os pesquisadores sinalizaram casos em que curvas incompletas ou dados ruidosos poderiam viésar o resultado. Em geral, tanto o tamanho máximo da população quanto a taxa de crescimento mais rápida foram maiores no caldo rico do que no meio mínimo, como se esperaria do ponto de vista nutricional. 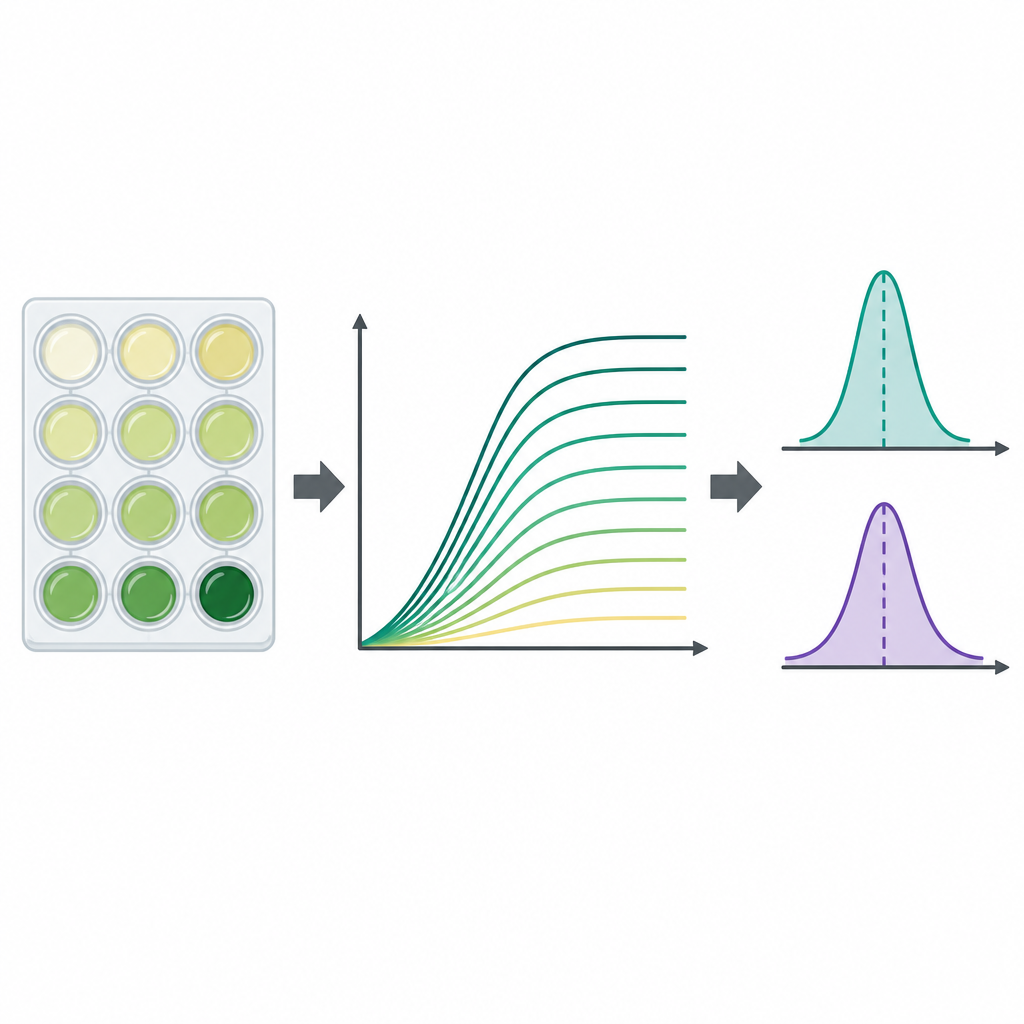
Verificações de qualidade e formas de reutilizar os dados
Experimentos de alto rendimento podem ser suscetíveis a erros sutis, portanto os autores quantificaram cuidadosamente quão repetíveis eram suas medições. Para cada linhagem e meio, compararam as três réplicas e calcularam quanto a capacidade de suporte e a taxa de crescimento variavam. Também incluíram marcadores para potenciais outliers e para curvas em que fases importantes podem ter sido perdidas devido à janela de registro fixa. Todas essas informações estão empacotadas com os arquivos principais de dados, permitindo que futuros usuários escolham os subconjuntos que melhor se ajustem aos seus próprios padrões de qualidade. O conjunto de dados está formatado para ser legível por máquina e é acompanhado por nomes de genes, identificadores e categorias funcionais amplas para cada gene deletado.
O que esse recurso significa para estudos futuros
Em vez de apresentar uma única afirmação biológica, este artigo entrega um mapa compartilhado e bem documentado de como milhares de mutantes de E. coli crescem em dois ambientes contrastantes. Ao tornar cada ponto no tempo e cada sinalização de confiabilidade publicamente disponíveis, os autores convidam outros a reanalisar as curvas, testar novos métodos matemáticos e conectar o comportamento de crescimento à função gênica, redes metabólicas ou outras camadas de dados celulares. Para não especialistas, a mensagem principal é que o crescimento bacteriano é moldado em conjunto pelos seus genes e pelo ambiente, e que ter um conjunto de dados comum como este facilita muito que muitos grupos estudem e comparem essas influências de maneira consistente.
Citação: Lao, Z., Ying, BW. Growth dynamics of 3,909 Escherichia coli single-gene knockouts in rich and minimal media. Sci Data 13, 717 (2026). https://doi.org/10.1038/s41597-026-07075-9
Palavras-chave: crescimento bacteriano, Escherichia coli, nocaute de genes, curvas de crescimento, fenotipagem microbiana