Clear Sky Science · it
Dinamicità di crescita di 3.909 delezioni a singolo gene di Escherichia coli in terreni ricchi e minimi
Perché è importante monitorare la crescita batterica
I batteri sono ovunque, dal nostro intestino ai fermentatori industriali, e il loro successo dipende da quanto velocemente e quanto bene crescono. Eppure, anche per il ben noto organismo da laboratorio Escherichia coli, mancano ancora registrazioni dettagliate e standardizzate di come migliaia di varianti genetiche crescano nel tempo. Questo articolo presenta un ampio dataset, organizzato con cura, che cattura come quasi quattromila ceppi di E. coli, ognuno privo di un singolo gene, crescono in condizioni di alimento ricco e povero. La risorsa è pensata come una base condivisa che chiunque può esplorare per porre nuove domande su geni, ambiente e comportamento batterico.
Molti ceppi mutanti, due diete molto diverse
Lo studio si concentra sulla collezione Keio, una libreria di riferimento di ceppi di E. coli in cui quasi tutti i geni non essenziali sono stati cancellati con precisione. Dagli esperimenti sono stati esaminati 3.909 diversi mutanti. Ognuno è stato coltivato in parallelo in due tipi di mezzo liquido: un brodo nutriente ricco e un mezzo minimo contenente solo sali di base, vitamine e un singolo zucchero. Queste diete contrastanti simulano un banchetto rispetto a una razione di sopravvivenza semplice, permettendo ai ricercatori di osservare quanto contano i geni mancanti quando le risorse sono abbondanti rispetto a quando sono scarse. 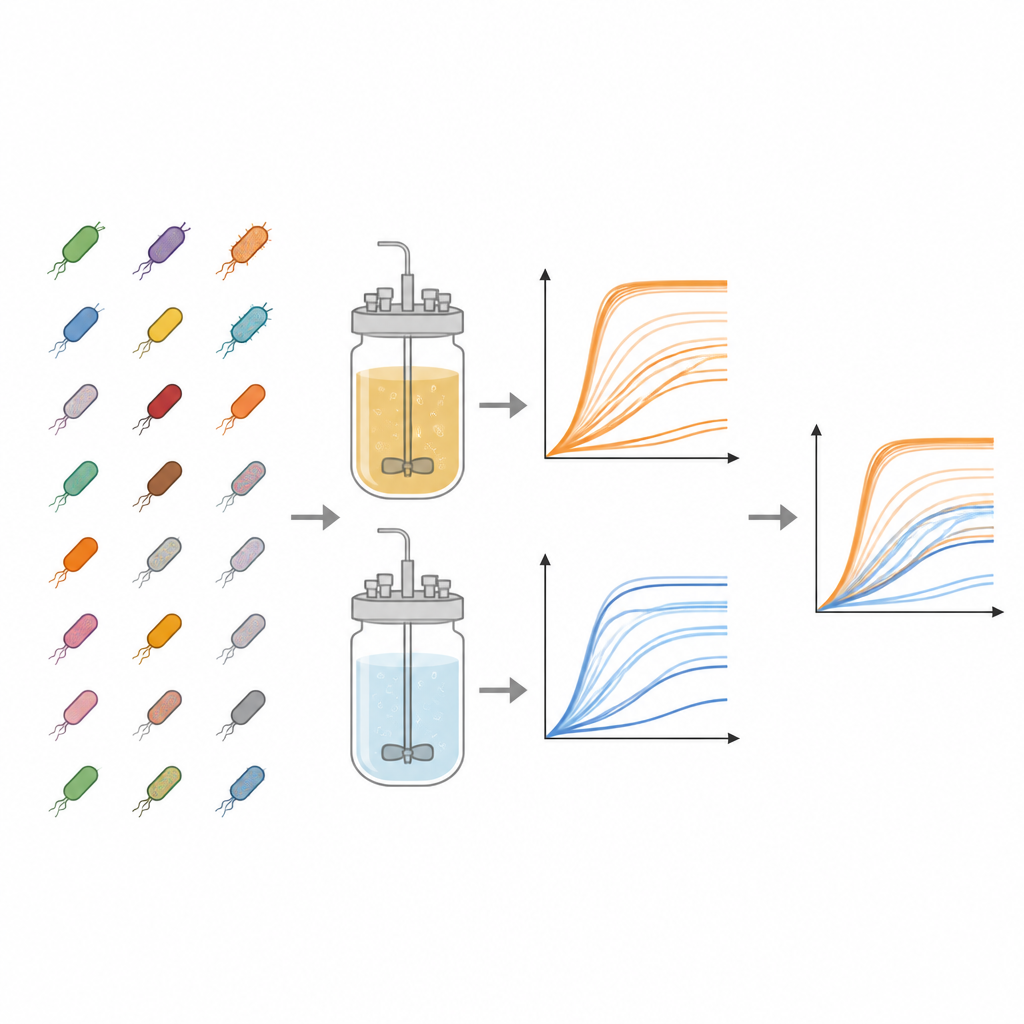
Monitoraggio ad alto rendimento della crescita nel tempo
Per seguire la moltiplicazione di ogni ceppo, il team ha usato piastre di plastica standard con 96 pozzetti, riempiendo ciascun pozzetto con il mezzo e una piccola quantità di batteri conservati. Le piastre sono state incubate a temperatura simile a quella corporea con agitazione, mentre una macchina misurava la torbidità di ogni pozzetto ogni 15 minuti per fino a due giorni. La torbidità, letta come densità ottica a 600 nanometri, aumenta con la moltiplicazione cellulare, generando una curva di crescita che mostra il ritardo iniziale, la crescita rapida e il raggiungimento del plateau. Per ogni combinazione di ceppo e mezzo i ricercatori hanno eseguito tre esperimenti indipendenti, generando in totale 23.454 curve di crescita individuali. Hanno sottratto un segnale di fondo specifico per piastra per pulire i dati e hanno memorizzato tutti i punti temporali in file di fogli di calcolo accessibili.
Dalle curve grezze a descrittori semplici
Poiché le curve di crescita sono ricche ma complesse, gli autori hanno anche calcolato due numeri di sintesi ampiamente usati per ogni curva. Il primo è la capacità portante, la torbidità massima approssimativa raggiunta, che riflette quanto densa diventa la coltura. Il secondo è il tasso di crescita massimo, la pendenza più ripida della curva, che indica la velocità di espansione della popolazione nella sua fase più rapida. Questi valori sono stati estratti da un programma Python direttamente dalle misurazioni non smussate usando brevi finestre di punti temporali consecutivi, e i ricercatori hanno segnalato i casi in cui curve incomplete o dati rumorosi potrebbero aver distorto il risultato. In generale, sia la dimensione massima della popolazione sia il tasso di crescita più rapido erano più elevati nel brodo ricco rispetto al mezzo minimo, come ci si aspetterebbe dal punto di vista nutrizionale. 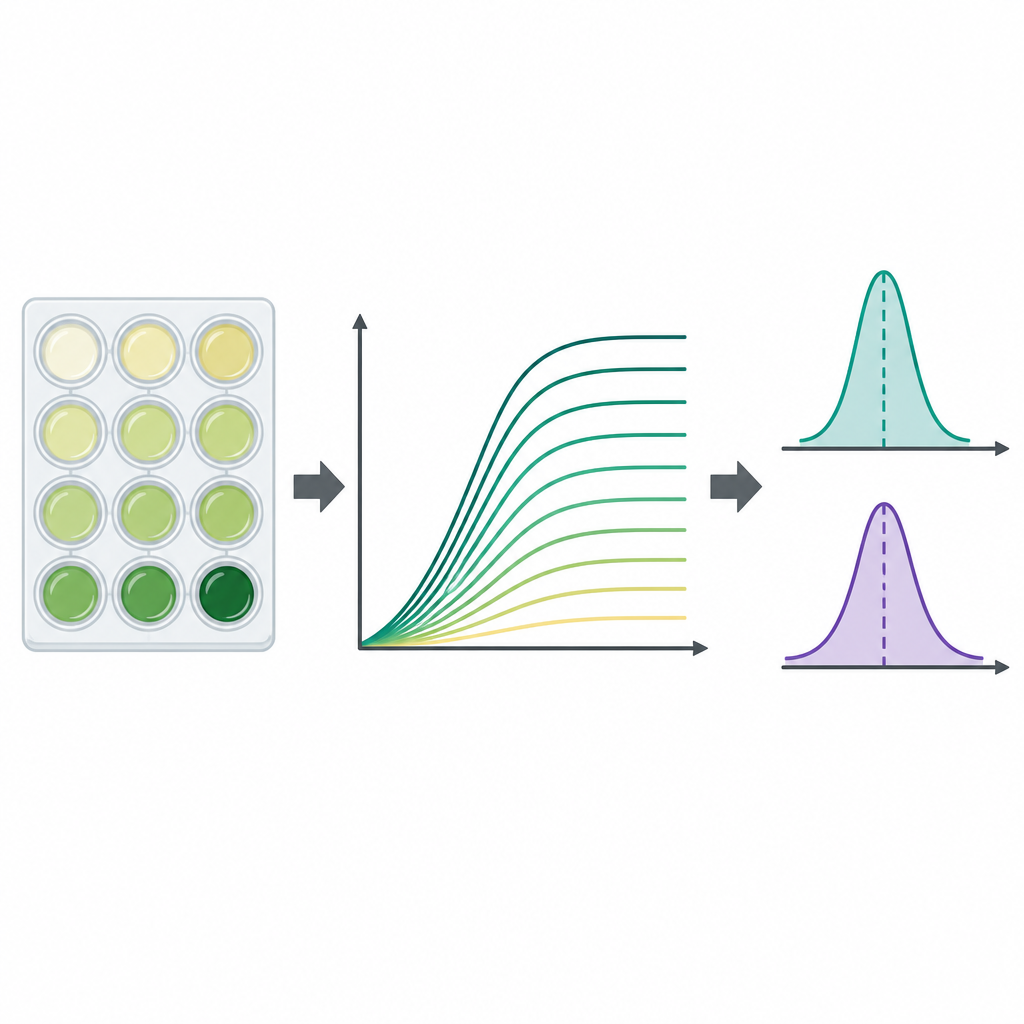
Controlli di qualità e modi per riutilizzare i dati
Gli esperimenti ad alto rendimento possono essere soggetti a errori sottili, quindi gli autori hanno quantificato con cura quanto fossero ripetibili le loro misure. Per ogni ceppo e mezzo hanno confrontato le tre repliche e calcolato quanto variassero la capacità portante e il tasso di crescita. Hanno inoltre incluso indicatori per potenziali outlier e per curve in cui fasi importanti potrebbero essere state perse a causa della finestra di registrazione fissa. Tutte queste informazioni sono fornite insieme ai file di dati principali, permettendo agli utilizzatori futuri di scegliere i sottoinsiemi che meglio si adattano ai propri standard di qualità. Il dataset è formattato per essere leggibile dalle macchine ed è accompagnato da nomi genici, identificatori e categorie funzionali ampie per ogni gene cancellato.
Cosa significa questa risorsa per studi futuri
Invece di proporre una singola affermazione biologica, questo articolo offre una mappa condivisa e ben documentata di come migliaia di mutanti di E. coli crescono in due ambienti contrastanti. Rendendo pubblici ogni punto temporale e ogni indicatore di affidabilità, gli autori invitano altri a rianalizzare le curve, testare nuovi metodi matematici e collegare il comportamento di crescita alla funzione genica, alle reti metaboliche o ad altri strati di dati cellulari. Per i non specialisti, il messaggio chiave è che la crescita dei batteri è determinata congiuntamente dai loro geni e dall'ambiente, e che disporre di un dataset comune come questo rende molto più semplice per molti gruppi studiare e confrontare tali influenze in modo coerente.
Citazione: Lao, Z., Ying, BW. Growth dynamics of 3,909 Escherichia coli single-gene knockouts in rich and minimal media. Sci Data 13, 717 (2026). https://doi.org/10.1038/s41597-026-07075-9
Parole chiave: crescita batterica, Escherichia coli, delezioni geniche, curve di crescita, fenotipizzazione microbica