Clear Sky Science · sv
HRCHY-CytoCommunity identifierar hierarkisk vävnadsorganisation i celltypers spatiala kartor
Hur celler bygger grannskap i våra vävnader
Våra organ är inte bara säckar med celler; de är noggrant ordnade städer där olika cell‑”grannar” samarbetar för att hålla oss vid liv och, vid sjukdom, ibland arbetar emot oss. Nya bild‑ och sekvenseringstekniker kan nu registrera var varje cell sitter i ett vävnadsskikt, tillsammans med vad den gör. Men att tolka denna förbluffande spatiala detalj är svårt. Denna studie introducerar HRCHY‑CytoCommunity, en beräkningsmetod som automatiskt återskapar hur celler grupperar sig i grannskap och större distrikt i friska organ och tumörer, och kopplar dessa mönster till patientutfall.
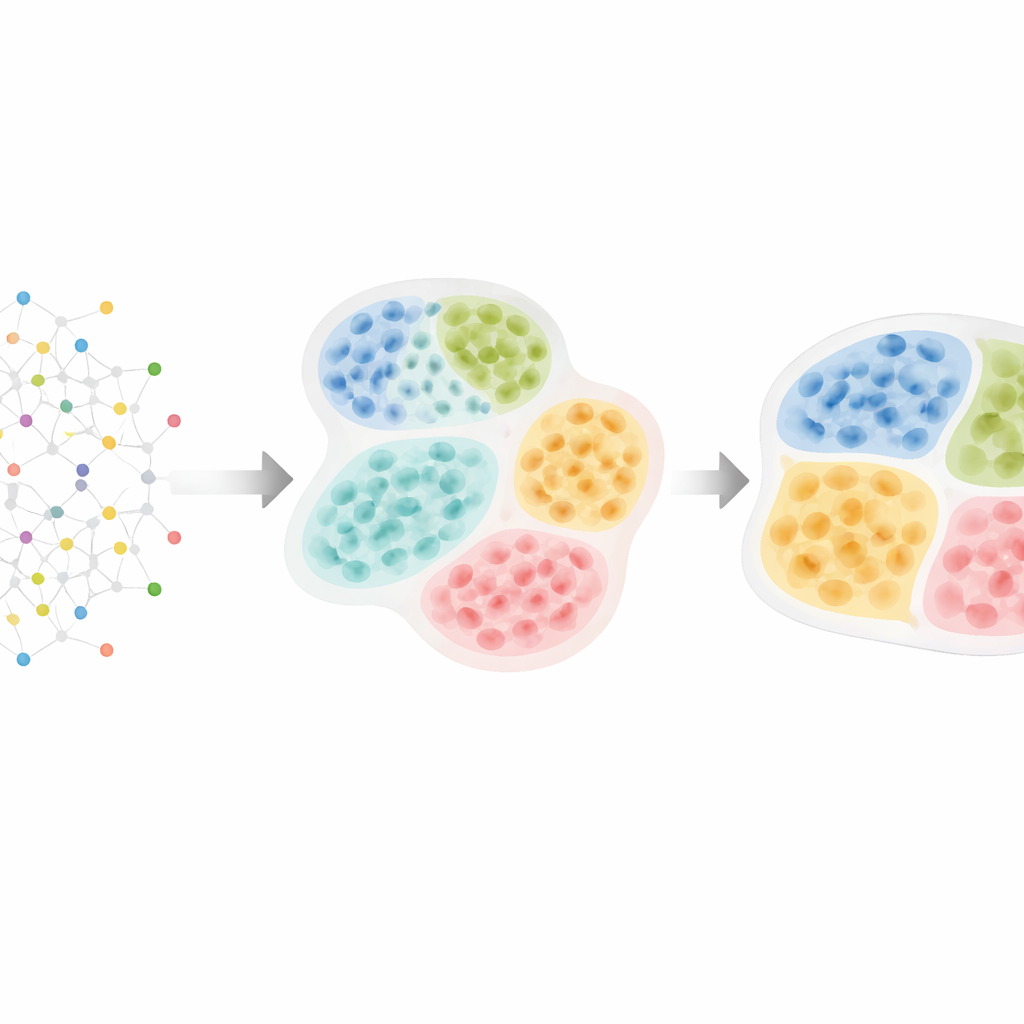
Från cellkartor till dold vävnadsstruktur
Moderna spatiala ”omics”‑tekniker kan mäta tusentals molekyler i tiotusentals eller hundratusentals celler samtidigt som deras exakta positioner i vävnaden bevaras. Forskare vet att celler organiserar sig i lager, zoner och fack—till exempel immunceller kontra cancerregioner i tumörer, eller distinkta kärnor i hjärnan. Dessa mönster är viktiga: tumörer där immunceller är åtskilda från cancerceller beter sig ofta annorlunda än de där de är inblandade, och speciella immunaggregat kallade tertiära lymfoida strukturer kan förutsäga bättre överlevnad i flera cancerformer. De flesta befintliga datorverktyg ignorerar dock antingen denna naturliga hierarki eller hittar strukturer på endast en nivå, vilket gör det svårt att se hur små cellulära grannskap passar in i större vävnadsdistrikt.
Ett nytt sätt att läsa cellulära grannskap
HRCHY‑CytoCommunity angriper denna utmaning genom att behandla en vävnad som ett nätverk av celler. Varje cell är en nod i en graf, kopplad till sina närmaste rumsliga grannar. Istället för att förlita sig direkt på råa gen‑ eller proteinmått använder metoden varje cells typ (såsom cancercell, T‑cell eller fibroblast) som huvudingång. Ett grafneuralnätverk lär sig sedan mönster för hur dessa celltyper ordnar sig. I ett steg grupperar det närliggande celler till finkorniga ”cellulära grannskap.” I ett andra steg samlar det dessa grannskap till grövre ”vävnadskompartments,” och säkerställer att varje cell tillhör exakt ett grannskap och att varje grannskap ligger tydligt inom ett enda kompartement. Särskilda träningsknep—som att beskära svaga kopplingar, tillsätta slumpmässigt brus och uppmuntra stabila, välbalanserade kluster—hjälper metoden att undvika bräckliga eller triviala grupperingarna.
Att hitta struktur över organ, tekniker och sjukdomar
Författarna testade HRCHY‑CytoCommunity på ett brett spektrum spatiala dataset från möss och människor, som omfattade både bildbaserade proteinkartor och sekvenseringsbaserade RNA‑kartor, och som spände över mjälte, hjärna, tarm och tumörer. I musmjlten återfann metoden klassiska strukturer som röd pulpa och lymfoida regioner, även när dessa regioner var uppdelade i frånkopplade fläckar. I kolorektal cancervävnad separerade den tydligt tumör från normala områden och framhävde distinkta grannskap vid tumörrkanter och kärnor. I musens hjärnregioner följde den noggrant kända, ofta små, kärnor och kortikala lager som många andra metoder suddade ihop, och hanterade mycket stora dataset med hundratusentals platser på bara några minuter. Ramverket fungerar också när varje mätt punkt innehåller blandningar av celltyper: genom att först uppskatta vilka celler som finns i varje punkt kan det fortfarande rekonstruera anatomiskt meningsfulla lager och subregioner.
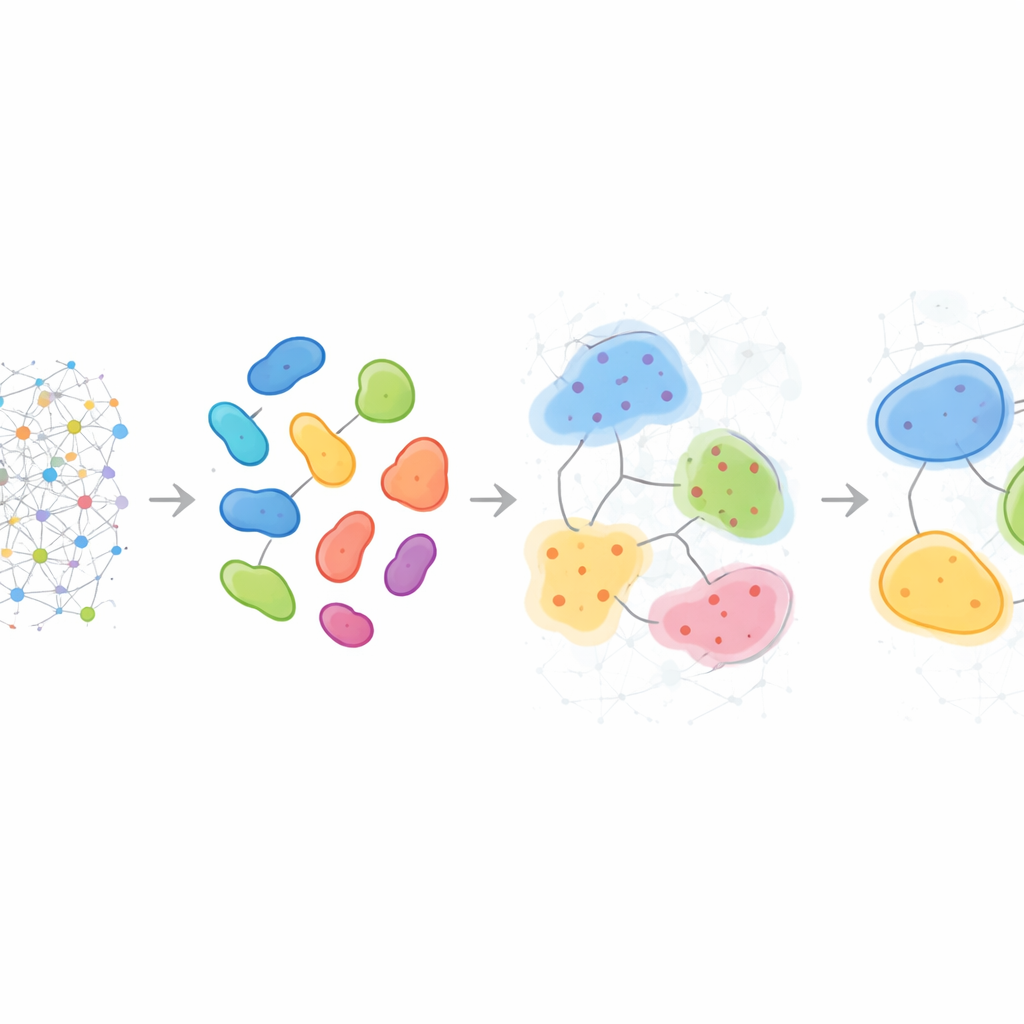
Mönster som skiljer sig mellan patienter
Utöver att beskriva enstaka prover kan HRCHY‑CytoCommunity justera grannskap och kompartement över många patienter för att definiera ett delat ”vokabulär” av multicellulära strukturer. I trippelnegativ bröstcancer fann metoden konsekvent breda immun‑rika och cancer‑rika kompartement, men de finare grannskapen inom dem skilde sig från person till person. Vissa tumörer innehöll unika kombinationer av makrofager, T‑celler och blodkärl, eller blandade cancer–neutrofilfickor, vilket avslöjade individualiserade mikroekosystem osynliga för enkla celltalsräkningar. När metoden tillämpades på en stor bröstcancer kohort hjälpte dessa flernivåstrukturer att stratifiera patienter efter överlevnad: ett kompartement rikt på en viss cancercellfenotyp markerade patienter med bättre utfall, medan vissa grannskap rika på fibroblaster eller specifika T‑cell‑ och makrofagblandningar flaggade grupper med betydligt sämre prognos, sannolikt återspeglande fysiska eller funktionella barriärer mot effektiv antitumörimmunitet.
Vad detta innebär för förståelse och behandling av sjukdom
Genom att omvandla komplexa spatiala kartor över celltyper till en tydlig hierarki av grannskap och distrikt erbjuder HRCHY‑CytoCommunity ett kraftfullt perspektiv på hur vävnader byggs upp och hur de bryts ner vid sjukdom. Metodens förmåga att fungera över olika experimentplattformar, hantera enorma dataset och ge fullständig, nästlad täckning av celler gör den till ett praktiskt verktyg för både grundläggande biologi och klinisk forskning. I cancer kan den avslöja mikroarkitekturer kopplade till patientöverlevnad och behandlingssvar; i friska organ kan den kartlägga hur specialiserade regioner samarbetar. I slutändan kan tillvägagångssätt som detta hjälpa läkare att läsa vävnadsorganisation lika rutinmässigt som de läser laboratorietester i dag, och därigenom vägleda mer precisa diagnoser och behandlingar.
Citering: Xie, R., Wang, Z., Liu, J. et al. HRCHY-CytoCommunity identifies hierarchical tissue organization in cell-type spatial maps. Nat Commun 17, 3312 (2026). https://doi.org/10.1038/s41467-026-70069-z
Nyckelord: spatial omics, vävnadsarkitektur, grafneuralnätverk, tumörmikromiljö, cellulära grannskap