Clear Sky Science · nl
HRCHY-CytoCommunity identificeert hiërarchische weefselorganisatie in ruimtelijke celtypemappen
Hoe cellen buurten vormen in onze weefsels
Onze organen zijn niet zomaar zakken met cellen; het zijn zorgvuldig gerangschikte steden waarin verschillende cel-“buren” samenwerken om ons in leven te houden en bij ziekte soms tegen ons werken. Nieuwe beeldvormings- en sequentietechnieken kunnen nu vastleggen waar elke cel zich bevindt in een weefseldoorsnede, samen met wat die cel aan het doen is. Maar die duizelingwekkende ruimtelijke details interpreteren is lastig. Deze studie introduceert HRCHY‑CytoCommunity, een computationele methode die automatisch reconstructies maakt van hoe cellen zich groeperen in buurten en grotere districten binnen gezonde organen en tumoren, en die deze patronen koppelt aan uitkomsten voor patiënten.
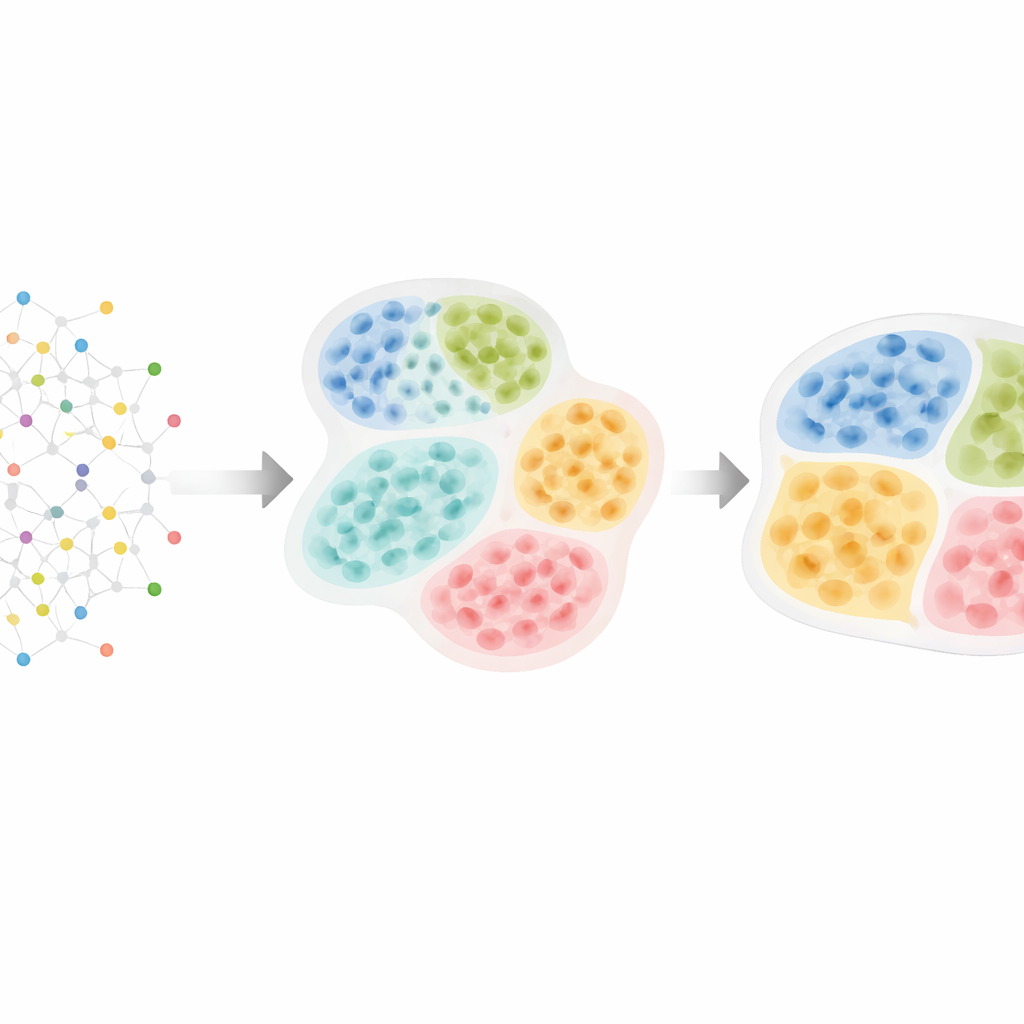
Van celkaarten naar verborgen weefselstructuur
Moderne ruimtelijke “omics”-technologieën kunnen duizenden moleculen meten in tienduizenden tot honderdduizenden cellen terwijl hun precieze locaties in het weefsel behouden blijven. Onderzoekers weten dat cellen zich organiseren in lagen, zones en compartimenten — bijvoorbeeld immuun- versus kankergedeeltes in tumoren, of verschillende kernen in de hersenen. Deze patronen zijn belangrijk: tumoren waarin immuuncellen gescheiden zijn van kankercellen gedragen zich vaak anders dan tumoren waarin ze door elkaar liggen, en speciale immuunaggregaten genaamd tertiaire lymfoïde structuren kunnen in verschillende kankers betere overleving voorspellen. Toch negeren de meeste bestaande computertools deze natuurlijke hiërarchie of vinden ze structuren slechts op één niveau, waardoor het moeilijk is te zien hoe kleine cellulaire buurten passen binnen grotere weefseldistricten.
Een nieuwe manier om cellulaire buurten te lezen
HRCHY‑CytoCommunity pakt deze uitdaging aan door een weefsel te behandelen als een netwerk van cellen. Elke cel is een knooppunt in een graaf, verbonden met zijn dichtstbijzijnde buren in de ruimte. In plaats van direct te vertrouwen op ruwe gen- of eiwitmetingen, gebruikt de methode het celtype van elke cel (zoals kankercel, T-cel of fibroblast) als belangrijkste invoer. Een graf-neuraal netwerk leert vervolgens patronen van hoe deze celtypes zich rangschikken. In een eerste stap groepeert het nabijgelegen cellen in fijnmazige “cellulaire buurten.” In een tweede stap combineert het deze buurten tot grovere “weefseldistricten,” waarbij wordt gegarandeerd dat elke cel precies tot één buurt behoort en elke buurt netjes binnen een enkel district valt. Speciale trainingstrucs — zoals het snoeien van zwakke verbindingen, toevoegen van willekeurige ruis en het aanmoedigen van stabiele, goed gebalanceerde clusters — helpen de methode om fragiele of triviale groeperingen te vermijden.
Structuur vinden over organen, technologieën en ziekten heen
De auteurs testten HRCHY‑CytoCommunity op een breed scala aan ruimtelijke datasets van muizen en mensen, met zowel beeldgebaseerde eiwitkaarten als sequentiegebaseerde RNA-kaarten, en inclusief milt, hersenen, darm en tumoren. In de muizenmilt herkende de methode klassieke structuren zoals het rode pulpa en lymfoïde gebieden, zelfs wanneer die regio’s in losse lapjes waren verdeeld. In colorectaal kankergewebe scheidde het zuiver tumor van normaal weefsel en benadrukte het verschillende buurten bij de tumorranden en -kernen. In muizenhersengebieden volgde het nauwkeurig bekende, vaak kleine kernen en corticale lagen die veel andere methoden samenvaagden, en het kon zeer grote datasets met honderden duizenden plekken in slechts enkele minuten verwerken. Het kader werkt ook wanneer elke gemeten plek mengsels van celtypes bevat: door eerst te schatten welke cellen in elke plek aanwezig zijn, kan het toch anatomisch betekenisvolle lagen en subregio’s reconstrueren.
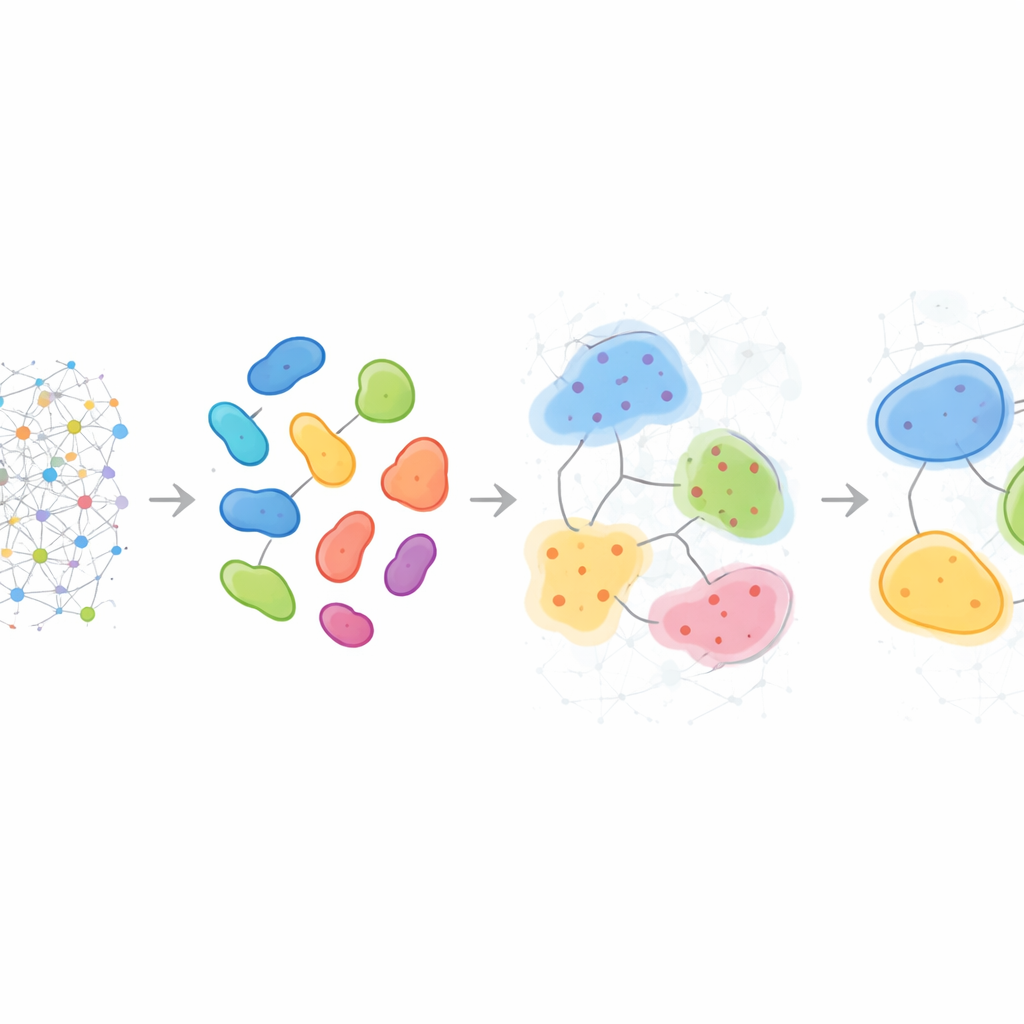
Patronen die verschillen van patiënt tot patiënt
Naast het beschrijven van individuele monsters kan HRCHY‑CytoCommunity buurten en districten over veel patiënten heen uitlijnen om een gedeelde “woordenschat” van multicellulaire structuren te definiëren. Bij triple-negatieve borstkanker vond de methode consequent brede immuunrijke en kankerrijke compartimenten, maar de fijnere buurten binnen deze compartimenten verschilden per persoon. Sommige tumoren bevatten unieke combinaties van macrofagen, T-cellen en bloedvaten, of gemengde kanker–neutrofiel pockets, waarmee geïndividualiseerde micro-ecologieën aan het licht kwamen die onzichtbaar blijven voor eenvoudige tellingen van celtypes. Toegepast op een grote borstkankercohort hielpen deze multiscale structuren patiënten te stratificeren op overleving: één compartiment verrijkt in een bepaald kankercelfenotype markeerde patiënten met betere uitkomsten, terwijl bepaalde buurten rijk aan fibroblasten of specifieke mengsels van T-cellen en macrofagen groepen met significant slechtere prognose aanduidden, waarschijnlijk weerspiegelend fysieke of functionele barrières voor effectieve anti-tumorimmuniteit.
Wat dit betekent voor begrip en behandeling van ziekte
Door complexe ruimtelijke kaarten van celtypes om te zetten in een heldere hiërarchie van buurten en districten biedt HRCHY‑CytoCommunity een krachtig perspectief op hoe weefsels worden opgebouwd en hoe ze in ziekte afbreken. De mogelijkheid van de methode om over verschillende experimentele platforms te werken, enorme datasets te verwerken en volledige, geneste dekking van cellen te leveren maakt het een praktische tool voor zowel fundamentele biologie als klinisch onderzoek. Bij kankers kan het micro-architecturen onthullen die gekoppeld zijn aan overleving en therapierespons; in gezonde organen kan het in kaart brengen hoe gespecialiseerde regio’s samenwerken. Uiteindelijk zouden benaderingen als deze artsen kunnen helpen om weefselorganisatie net zo routinematig te lezen als ze nu labtests lezen, wat leidend kan zijn tot preciezere diagnoses en behandelingen.
Bronvermelding: Xie, R., Wang, Z., Liu, J. et al. HRCHY-CytoCommunity identifies hierarchical tissue organization in cell-type spatial maps. Nat Commun 17, 3312 (2026). https://doi.org/10.1038/s41467-026-70069-z
Trefwoorden: ruimtelijke omics, weefselarchitectuur, graf-neurale netwerken, tumormicro-omgeving, cellulaire buurten