Clear Sky Science · it
HRCHY-CytoCommunity identifica l'organizzazione gerarchica dei tessuti nelle mappe spaziali dei tipi cellulari
Come le cellule costruiscono quartieri all'interno dei nostri tessuti
I nostri organi non sono semplici sacche di cellule; sono città accuratamente organizzate in cui diversi «vicini» cellulari si associano per mantenerci in vita e, nella malattia, talvolta agire contro di noi. Nuovi strumenti di imaging e sequenziamento possono ora registrare la posizione di ogni cellula in una sezione di tessuto, insieme a cosa stia facendo. Ma ricavare senso da questo dettagliato insieme spaziale è difficile. Questo studio presenta HRCHY‑CytoCommunity, un metodo computazionale che ricostruisce automaticamente come le cellule si raggruppano in vicinanze e in distretti più ampi all'interno di organi sani e tumori, e collega questi schemi agli esiti clinici dei pazienti.
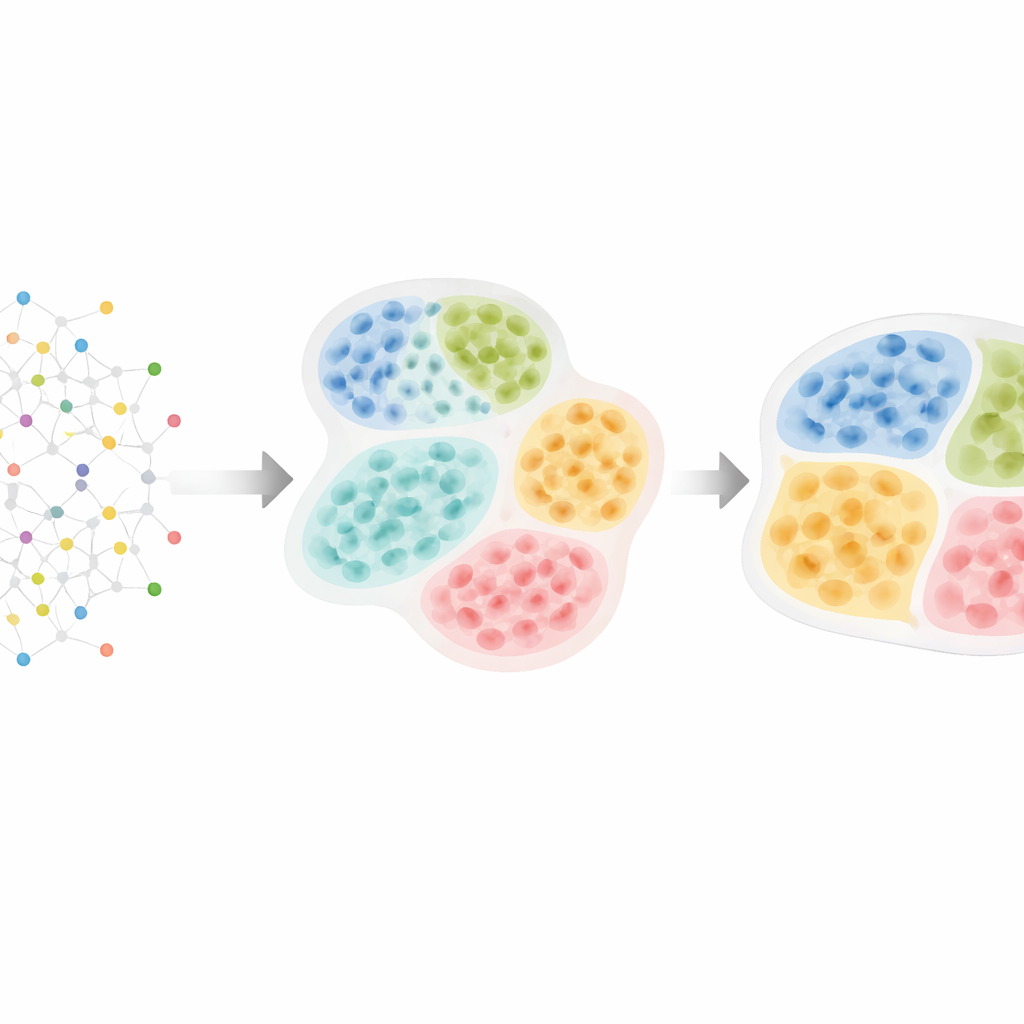
Dalle mappe cellulari alla struttura nascosta dei tessuti
Le moderne tecnologie «omiche» spaziali possono misurare migliaia di molecole in decine o centinaia di migliaia di cellule conservandone le esatte posizioni nel tessuto. I ricercatori sanno che le cellule si organizzano in strati, zone e compartimenti — per esempio regioni immunitarie versus tumorali nei tumori, o nuclei distinti nel cervello. Questi schemi contano: i tumori in cui le cellule immunitarie sono separate dalle cellule tumorali spesso si comportano diversamente rispetto a quelli in cui sono mescolate, e aggregati immunitari speciali chiamati strutture linfatiche terziarie possono prevedere una migliore sopravvivenza in diversi tumori. Tuttavia, la maggior parte degli strumenti computazionali esistenti o ignora questa gerarchia naturale o individua strutture a un solo livello, rendendo difficile vedere come le piccole vicinanze cellulari si inseriscano in distretti tessutali più grandi.
Un nuovo modo di leggere le vicinanze cellulari
HRCHY‑CytoCommunity affronta questa sfida trattando un tessuto come una rete di cellule. Ogni cellula è un nodo in un grafo, connesso ai suoi vicini spaziali più prossimi. Invece di fare affidamento direttamente sulle misure grezze di geni o proteine, il metodo usa il tipo cellulare di ciascuna cellula (ad esempio cellula tumorale, cellula T o fibroblasto) come input principale. Una rete neurale su grafi apprende quindi i modelli di come questi tipi cellulari si dispongono. In un primo passaggio raggruppa le cellule vicine in «vicinanze cellulari» a risoluzione fine. In un secondo passaggio aggrega queste vicinanze in «compartimenti tessutali» più grossolani, assicurando che ogni cellula appartenga esattamente a una vicinanza e che ogni vicinanza sia contenuta nettamente in un unico compartimento. Accorgimenti di addestramento — come il potare connessioni deboli, aggiungere rumore casuale e incoraggiare cluster stabili e ben bilanciati — aiutano il metodo a evitare raggruppamenti fragili o banali.
Individuare strutture attraverso organi, tecnologie e malattie
Gli autori hanno testato HRCHY‑CytoCommunity su un'ampia gamma di dataset spaziali di topi e umani, coprendo sia mappe proteiche basate su imaging sia mappe di RNA basate su sequenziamento, e comprendendo milza, cervello, intestino e tumori. Nella milza del topo, il metodo ha recuperato strutture classiche come la polpa rossa e le regioni linfoidi, anche quando tali regioni erano frammentate in chiazze disconnesse. Nel tessuto del cancro colorettale ha separato nettamente le aree tumorali da quelle normali e ha evidenziato vicinanze distinte ai margini e nei nuclei tumorali. Nelle regioni cerebrali dei topi ha tracciato accuratamente nuclei e strati corticali noti, spesso molto piccoli e che molti altri metodi sfumano insieme, e ha gestito dataset molto grandi contenenti centinaia di migliaia di punti in pochi minuti. Il framework funziona anche quando ogni spot misurato contiene miscele di tipi cellulari: stimando prima quali cellule sono presenti in ciascuno spot, può comunque ricostruire strati e sottoregioni con senso anatomico.
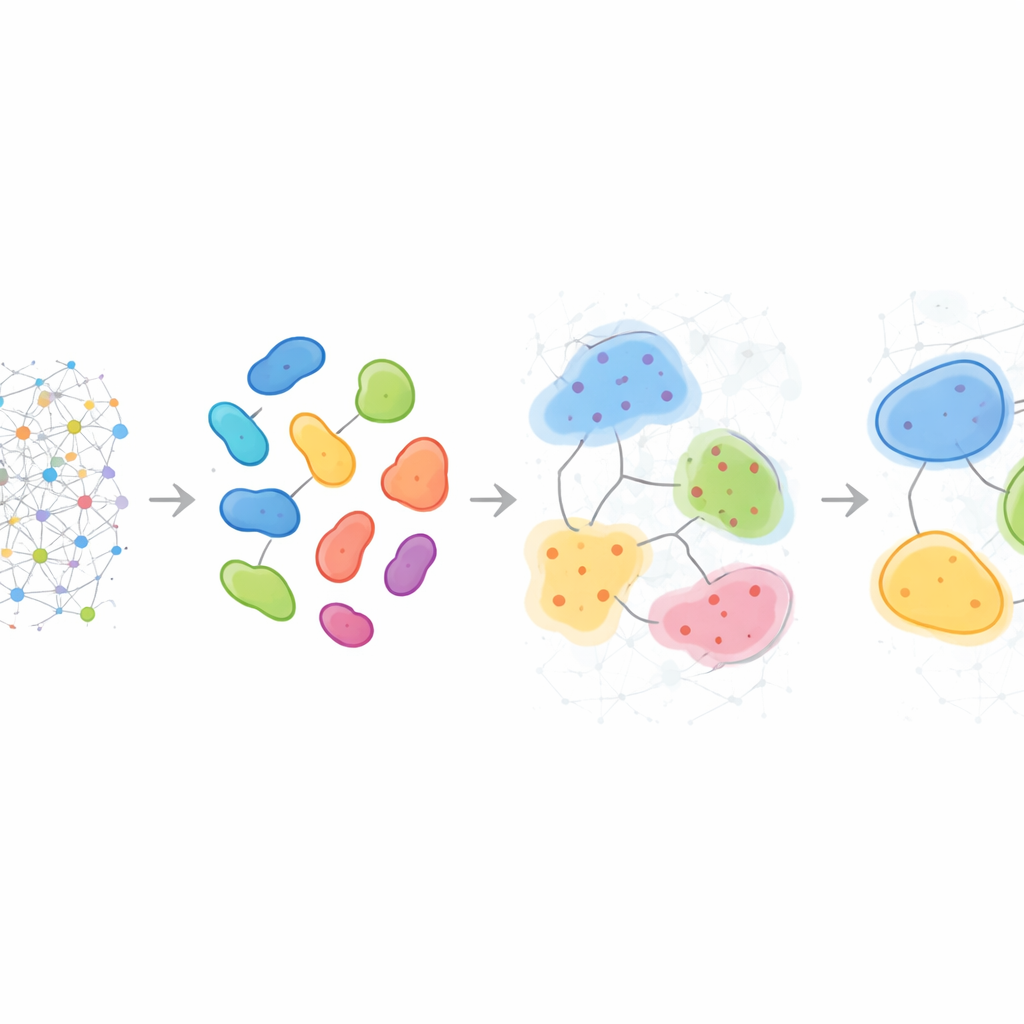
Schemi che variano da paziente a paziente
Oltre a descrivere singoli campioni, HRCHY‑CytoCommunity può allineare vicinanze e compartimenti attraverso molti pazienti per definire un «vocabolario» condiviso di strutture multicellulari. Nel carcinoma mammario triplo negativo, il metodo ha trovato in modo coerente ampi compartimenti ricchi di cellule immunitarie e compartimenti ricchi di cellule tumorali, ma le vicinanze più fini al loro interno differivano da persona a persona. Alcuni tumori contenevano combinazioni uniche di macrofagi, cellule T e vasi sanguigni, o tasche miste di cellule tumorali e neutrofili, rivelando micro‑ecologie individualizzate invisibili a semplici conteggi dei tipi cellulari. Applicato a una grande coorte di pazienti con cancro al seno, queste strutture multi‑scala hanno aiutato a stratificare i pazienti per sopravvivenza: un compartimento arricchito in un particolare fenotipo di cellule tumorali segnalava pazienti con esiti migliori, mentre certe vicinanze ricche di fibroblasti o di specifiche combinazioni di cellule T e macrofagi identificavano gruppi con prognosi significativamente peggiore, probabilmente riflettendo barriere fisiche o funzionali a un’efficace immunità anti‑tumorale.
Cosa significa per comprendere e trattare le malattie
Trasformando complesse mappe spaziali dei tipi cellulari in una chiara gerarchia di vicinanze e distretti, HRCHY‑CytoCommunity offre una lente potente su come i tessuti si costruiscono e come si deteriorano nella malattia. La capacità del metodo di funzionare su diversi piattaforme sperimentali, gestire dataset enormi e fornire una copertura completa e annidata delle cellule lo rende uno strumento pratico per la biologia di base e la ricerca clinica. Nei tumori può rivelare micro‑architetture legate alla sopravvivenza dei pazienti e alla risposta alla terapia; negli organi sani può mappare come regioni specializzate cooperano. In ultima analisi, approcci come questo potrebbero aiutare i medici a leggere l’organizzazione tissutale con la stessa routine con cui oggi interpretano gli esami di laboratorio, guidando diagnosi e trattamenti più precisi.
Citazione: Xie, R., Wang, Z., Liu, J. et al. HRCHY-CytoCommunity identifies hierarchical tissue organization in cell-type spatial maps. Nat Commun 17, 3312 (2026). https://doi.org/10.1038/s41467-026-70069-z
Parole chiave: omiche spaziali, architettura dei tessuti, reti neurali su grafi, microambiente tumorale, vicinanze cellulari