Clear Sky Science · pl
HRCHY-CytoCommunity identyfikuje hierarchiczną organizację tkanek na mapach przestrzennych typów komórek
Jak komórki tworzą sąsiedztwa w naszych tkankach
Nasze narządy to nie tylko zbiorniki z komórkami; to starannie ułożone miasta, w których różne „sąsiedztwa” komórkowe współpracują, by nas podtrzymywać, a w chorobie czasem działać przeciwko nam. Nowe narzędzia obrazowania i sekwencjonowania potrafią dziś zapisać, gdzie każda komórka leży w plaszczu tkanki oraz co robi. Nadmiar takich szczegółów przestrzennych jest jednak trudny do interpretacji. W tym badaniu wprowadzono HRCHY‑CytoCommunity, metodę obliczeniową, która automatycznie rekonstruuje, jak komórki grupują się w sąsiedztwa i większe dzielnice w zdrowych narządach i guzach, oraz łączy te wzorce z wynikami pacjentów.
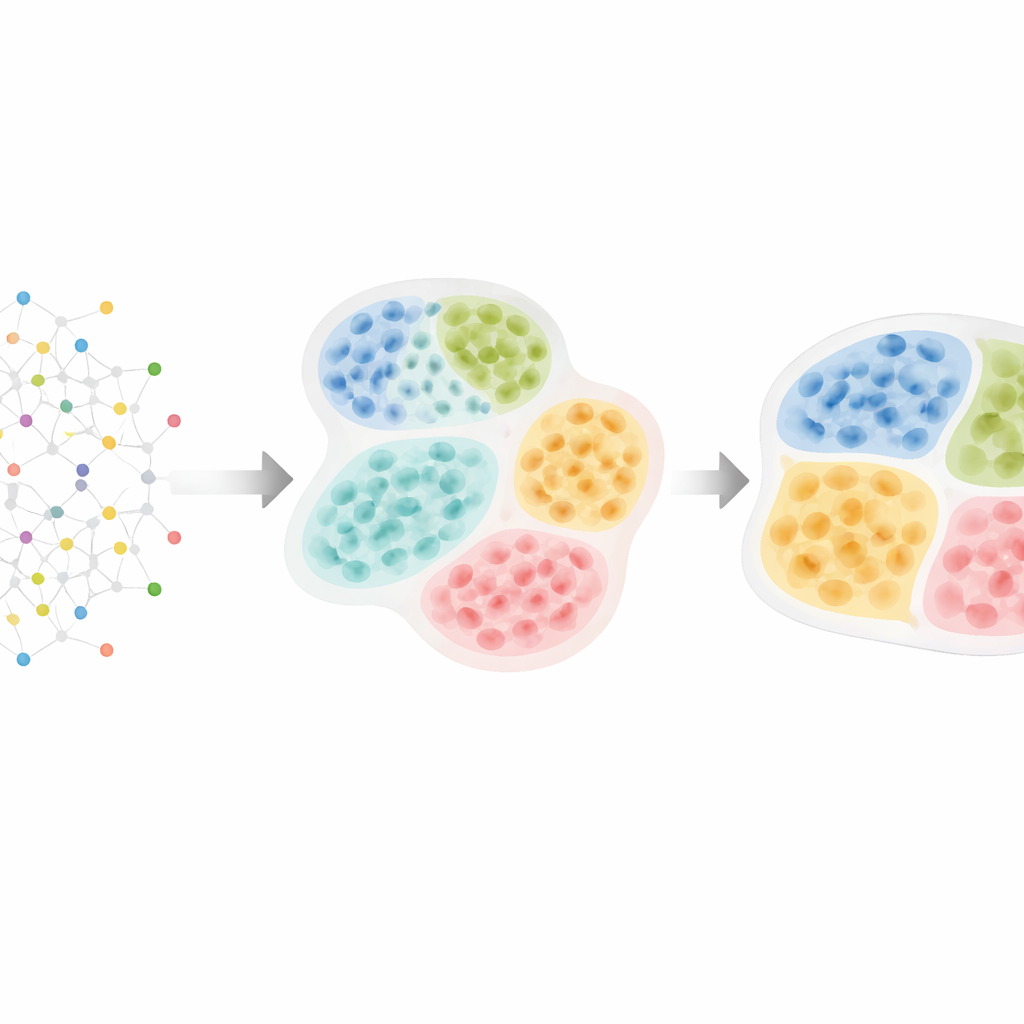
Od map komórek do ukrytej struktury tkanki
Nowoczesne technologie „omics” przestrzennego potrafią zmierzyć tysiące cząsteczek w dziesiątkach lub setkach tysięcy komórek, zachowując ich dokładne położenie w tkance. Badacze wiedzą, że komórki organizują się w warstwy, strefy i przegrody — na przykład obszary immunologiczne kontra nowotworowe w guzach, albo odrębne jądra w mózgu. Te wzory mają znaczenie: guzy, w których komórki odpornościowe są oddzielone od komórek nowotworowych, często zachowują się inaczej niż te, gdzie są wymieszane, a specjalne skupiska immunologiczne zwane trzeciorzędowymi strukturami limfatycznymi mogą przewidywać lepsze przeżycie w kilku nowotworach. Jednak większość istniejących narzędzi komputerowych albo ignoruje tę naturalną hierarchię, albo wykrywa struktury tylko na jednym poziomie, co utrudnia zobaczenie, jak małe sąsiedztwa komórkowe wpisują się w większe dzielnice tkanki.
Nowy sposób odczytywania sąsiedztw komórkowych
HRCHY‑CytoCommunity rozwiązuje ten problem, traktując tkankę jak sieć komórek. Każda komórka jest węzłem w grafie, połączonym z najbliższymi sąsiadami w przestrzeni. Zamiast polegać bezpośrednio na surowych pomiarach genów czy białek, metoda używa typu komórki (takiego jak komórka nowotworowa, limfocyt T czy fibroblast) jako głównego wejścia. Następnie grafowa sieć neuronowa uczy się wzorców układania się tych typów komórek. W jednym kroku grupuje pobliskie komórki w drobnoziarniste „sąsiedztwa komórkowe”. W drugim kroku pulije te sąsiedztwa w gruboziarniste „przegrody tkankowe”, zapewniając, że każda komórka należy do dokładnie jednego sąsiedztwa, a każde sąsiedztwo znajduje się czysto wewnątrz jednej przegrody. Specjalne sztuczki treningowe — takie jak przycinanie słabych połączeń, dodawanie losowego szumu i zachęcanie do stabilnych, dobrze zbalansowanych klastrów — pomagają metodzie unikać kruchego lub trywialnego grupowania.
Odnajdywanie struktury w różnych narządach, technologiach i chorobach
Autorzy przetestowali HRCHY‑CytoCommunity na szerokim zestawie danych przestrzennych od myszy i ludzi, obejmując zarówno mapy białkowe oparte na obrazowaniu, jak i mapy RNA oparte na sekwencjonowaniu, oraz obejmując śledzionę, mózg, jelito i guzy. W mysiej śledzionie metoda odtworzyła klasyczne struktury, takie jak czerwony miąższ i regiony limfoidalne, nawet gdy te regiony były rozbite na niepołączone fragmenty. W tkance raka jelita grubego wyraźnie oddzieliła obszary guza od tkanek prawidłowych i uwypukliła odrębne sąsiedztwa na krawędziach i w rdzeniach guza. W obszarach mózgu myszy dokładnie odwzorowała znane, często maleńkie, jądra i warstwy korowe, które wiele innych metod rozmywało, i poradziła sobie z bardzo dużymi zestawami danych zawierającymi setki tysięcy miejsc w ciągu zaledwie kilku minut. Ramy działają także wtedy, gdy każdy mierzony punkt zawiera mieszanki typów komórek: poprzez najpierw oszacowanie, które komórki są obecne w danym punkcie, nadal potrafi odtworzyć anatomicznie znaczące warstwy i podregiony.
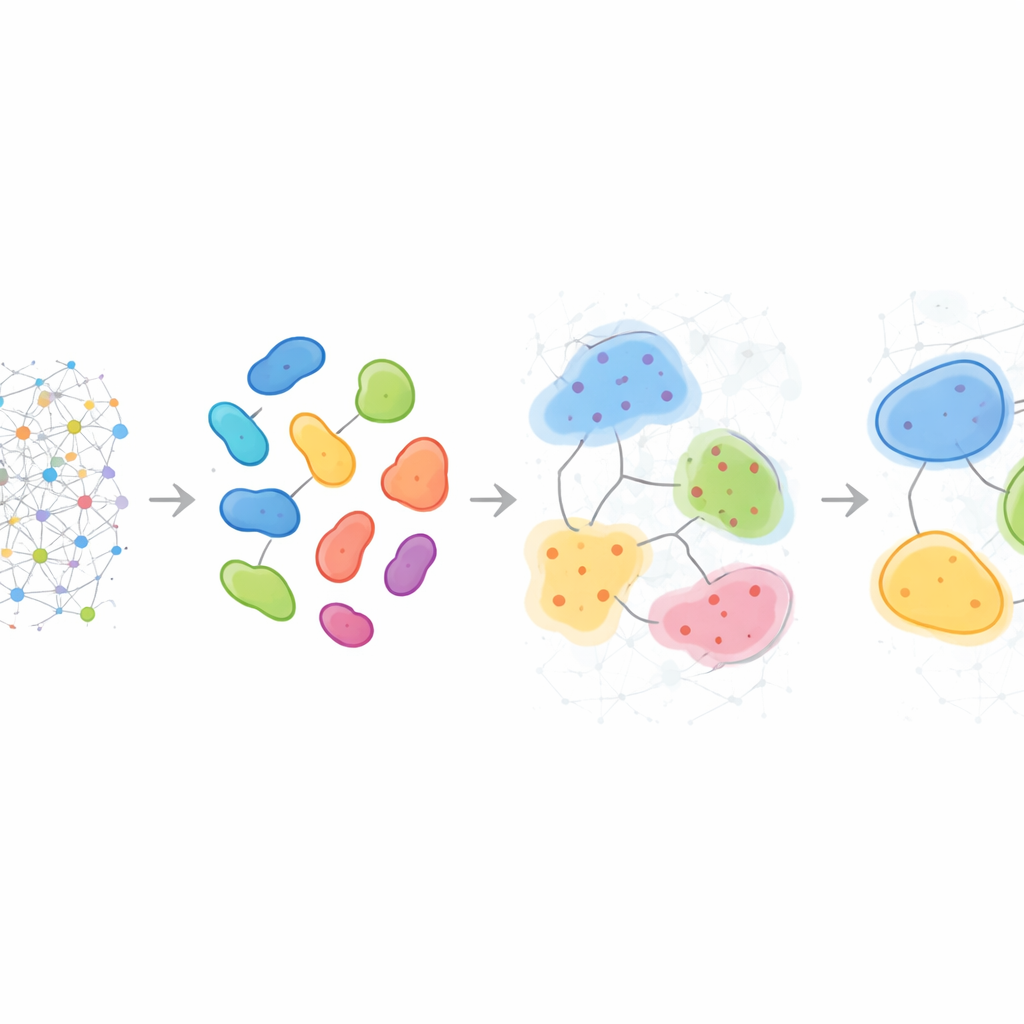
Wzorce różniące się między pacjentami
Ponad opisaniem pojedynczych próbek, HRCHY‑CytoCommunity potrafi wyrównać sąsiedztwa i przegrody między wieloma pacjentami, by zdefiniować wspólne „słownictwo” struktur wielokomórkowych. W raku piersi potrójnie ujemnym metoda konsekwentnie znajdowała szerokie przegrody bogate w komórki odpornościowe oraz przegrody bogate w komórki nowotworowe, jednak drobniejsze sąsiedztwa w ich obrębie różniły się między osobami. Niektóre guzy zawierały unikalne kombinacje makrofagów, limfocytów T i naczyń krwionośnych, albo mieszane kieszonki komórek nowotworowych i neutrofili, ujawniając zindywidualizowane mikroekologie niewidoczne przy prostym liczeniu typów komórek. Zastosowane do dużej kohorty raka piersi struktury wieloskalowe pomogły stratyfikować pacjentki pod względem przeżycia: jedna przegroda wzbogacona w określony fenotyp komórek nowotworowych oznaczała pacjentki z lepszymi wynikami, podczas gdy pewne sąsiedztwa bogate w fibroblasty lub specyficzne mieszanki limfocytów T i makrofagów wskazywały grupy z istotnie gorszą prognozą, co prawdopodobnie odzwierciedla bariery fizyczne lub funkcjonalne dla skutecznej odpowiedzi odporności przeciwnowotworowej.
Co to oznacza dla rozumienia i leczenia chorób
Przekształcając złożone mapy przestrzenne typów komórek w jasną hierarchię sąsiedztw i dzielnic, HRCHY‑CytoCommunity oferuje potężną soczewkę do badania, jak budowane są tkanki i jak rozpadają się w chorobie. Zdolność metody do działania w różnych platformach eksperymentalnych, obsługi ogromnych zestawów danych oraz dostarczania kompletnego, zagnieżdżonego pokrycia komórek czyni ją praktycznym narzędziem zarówno dla biologii podstawowej, jak i badań klinicznych. W nowotworach może ujawniać mikro‑architektury powiązane z przeżyciem pacjentów i odpowiedzią na terapię; w zdrowych narządach może mapować, jak wyspecjalizowane regiony współdziałają. Ostatecznie podejścia tego typu mogłyby pomóc lekarzom odczytywać organizację tkanki tak rutynowo, jak dziś odczytują wyniki badań laboratoryjnych, prowadząc do precyzyjniejszych diagnoz i terapii.
Cytowanie: Xie, R., Wang, Z., Liu, J. et al. HRCHY-CytoCommunity identifies hierarchical tissue organization in cell-type spatial maps. Nat Commun 17, 3312 (2026). https://doi.org/10.1038/s41467-026-70069-z
Słowa kluczowe: spatial omics, architektura tkanek, grafowe sieci neuronowe, mikrośrodowisko guza, sąsiedztwa komórkowe