Clear Sky Science · es
HRCHY-CytoCommunity identifica la organización tisular jerárquica en mapas espaciales de tipos celulares
Cómo las células construyen vecindarios dentro de nuestros tejidos
Nuestros órganos no son simplemente bolsas de células; son ciudades cuidadosamente organizadas donde distintos “vecinos” celulares colaboran para mantenernos vivos y, en la enfermedad, a veces actúan en nuestra contra. Nuevas herramientas de imagen y secuenciación pueden ahora registrar la ubicación de cada célula en una rebanada de tejido, junto con lo que está haciendo. Pero dar sentido a este abrumador detalle espacial es difícil. Este estudio presenta HRCHY‑CytoCommunity, un método computacional que reconstruye automáticamente cómo las células se agrupan en vecindarios y en distritos más amplios dentro de órganos sanos y tumores, y vincula estos patrones con los resultados clínicos de los pacientes.
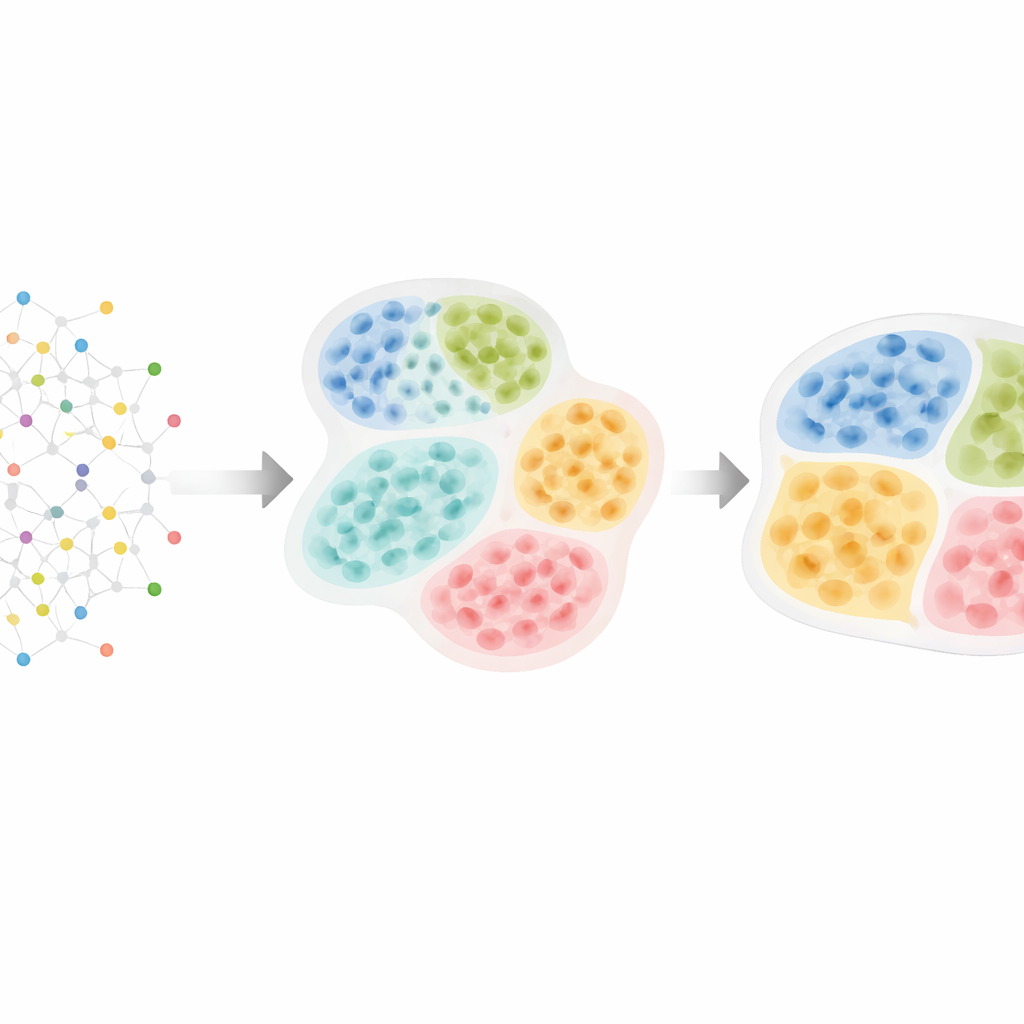
De mapas celulares a la estructura tisular oculta
Las tecnologías espaciales modernas de “ómica” pueden medir miles de moléculas en decenas o cientos de miles de células manteniendo sus ubicaciones exactas en el tejido. Los investigadores saben que las células se organizan en capas, zonas y compartimentos —por ejemplo, regiones inmunes frente a tumorales en los tumores, o núcleos distintos en el cerebro. Estos patrones son relevantes: los tumores con células inmunes segregadas de las células cancerosas suelen comportarse de forma diferente a aquellos donde están mezcladas, y agregados inmunes especiales llamados estructuras linfoides terciarias pueden predecir mejor supervivencia en varios cánceres. Sin embargo, la mayoría de las herramientas informáticas existentes o bien ignoran esta jerarquía natural o encuentran estructuras en un único nivel, lo que dificulta ver cómo los pequeños vecindarios celulares encajan en distritos tisulares más grandes.
Una nueva forma de leer los vecindarios celulares
HRCHY‑CytoCommunity afronta este reto tratando el tejido como una red de células. Cada célula es un nodo en un grafo, conectado con sus vecinos más cercanos en el espacio. En lugar de confiar directamente en las medidas crudas de genes o proteínas, el método utiliza el tipo celular de cada célula (como célula cancerosa, célula T o fibroblasto) como entrada principal. Una red neuronal de grafos aprende patrones de cómo se disponen estos tipos celulares. En un primer paso agrupa células cercanas en “vecindarios celulares” de fina resolución. En un segundo paso agrupa esos vecindarios en “compartimentos tisulares” más gruesos, garantizando que cada célula pertenezca exactamente a un vecindario y que cada vecindario se sitúe limpiamente dentro de un único compartimento. Trucos de entrenamiento especiales —como podar conexiones débiles, añadir ruido aleatorio y fomentar conglomerados estables y equilibrados— ayudan al método a evitar agrupamientos frágiles o triviales.
Encontrar estructura a través de órganos, tecnologías y enfermedades
Los autores probaron HRCHY‑CytoCommunity en una amplia gama de conjuntos de datos espaciales de ratones y humanos, cubriendo mapas de proteínas basados en imagen y mapas de ARN basados en secuenciación, y abarcando bazo, cerebro, intestino y tumores. En el bazo de ratón, el método recuperó estructuras clásicas como la pulpa roja y las regiones linfoides, incluso cuando esas regiones estaban fragmentadas en parches desconectados. En tejido de cáncer colorrectal, separó claramente áreas tumorales de normales y destacó vecindarios distintos en los bordes y núcleos tumorales. En regiones del cerebro de ratón, trazó con precisión núcleos y capas corticales conocidos, a menudo diminutos, que muchos otros métodos difuminaban, y manejó conjuntos de datos muy grandes con cientos de miles de puntos en apenas unos minutos. El marco también funciona cuando cada punto medido contiene mezclas de tipos celulares: al estimar primero qué células están presentes en cada punto, aún puede reconstruir capas y subregiones anatómicamente significativas.
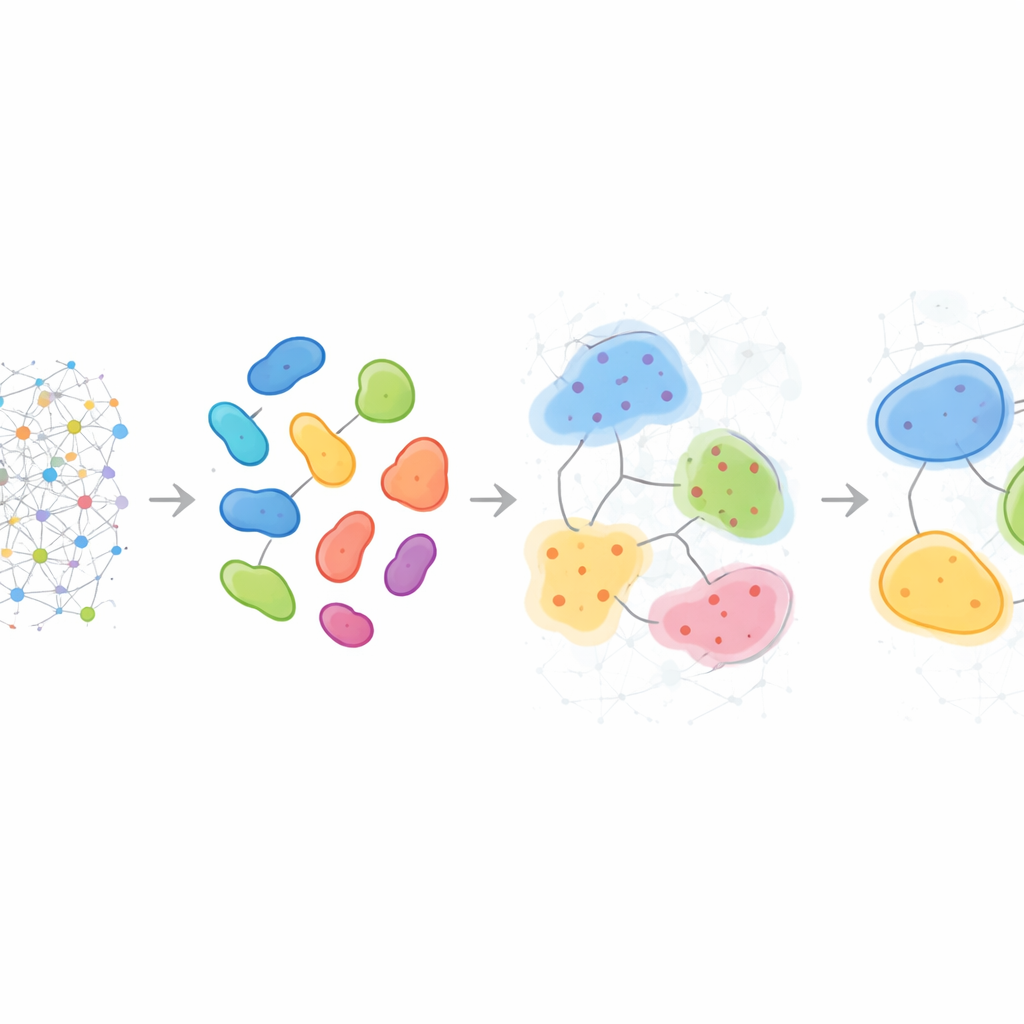
Patrones que difieren de un paciente a otro
Más allá de describir muestras individuales, HRCHY‑CytoCommunity puede alinear vecindarios y compartimentos entre muchos pacientes para definir un “vocabulario” compartido de estructuras multicelulares. En el cáncer de mama triple negativo, el método encontró de forma consistente compartimentos amplios ricos en células inmunes y compartimentos ricos en cáncer, aunque los vecindarios más finos dentro de ellos variaron entre personas. Algunos tumores contenían combinaciones únicas de macrófagos, células T y vasos sanguíneos, o bolsillos mixtos de células cancerosas y neutrófilos, revelando micro‑ecologías individualizadas invisibles a los simples recuentos de tipos celulares. Aplicado a una cohorte grande de cáncer de mama, estas estructuras multi‑escala ayudaron a estratificar a los pacientes por supervivencia: un compartimento enriquecido en un fenotipo celular canceroso particular marcó pacientes con mejores resultados, mientras que ciertos vecindarios ricos en fibroblastos o mezclas específicas de células T y macrófagos señalaron grupos con pronóstico significativamente peor, probablemente reflejando barreras físicas o funcionales a la inmunidad antitumoral efectiva.
Qué significa esto para entender y tratar la enfermedad
Al convertir mapas espaciales complejos de tipos celulares en una jerarquía clara de vecindarios y distritos, HRCHY‑CytoCommunity ofrece una lente potente sobre cómo se construyen los tejidos y cómo se descomponen en la enfermedad. La capacidad del método para funcionar en diferentes plataformas experimentales, manejar conjuntos de datos enormes y proporcionar cobertura completa y anidada de las células lo convierte en una herramienta práctica tanto para la biología básica como para la investigación clínica. En cánceres, puede revelar micro‑arquitecturas vinculadas a la supervivencia del paciente y a la respuesta a la terapia; en órganos sanos, puede cartografiar cómo cooperan las regiones especializadas. En última instancia, enfoques como este podrían ayudar a los médicos a leer la organización tisular con la misma rutina con que hoy interpretan análisis de laboratorio, guiando diagnósticos y tratamientos más precisos.
Cita: Xie, R., Wang, Z., Liu, J. et al. HRCHY-CytoCommunity identifies hierarchical tissue organization in cell-type spatial maps. Nat Commun 17, 3312 (2026). https://doi.org/10.1038/s41467-026-70069-z
Palabras clave: ómica espacial, arquitectura tisular, redes neuronales de grafos, microambiente tumoral, vecindarios celulares