Clear Sky Science · pt
HRCHY-CytoCommunity identifica organização tecidual hierárquica em mapas espaciais de tipos celulares
Como as células constroem vizinhanças dentro dos nossos tecidos
Nossos órgãos não são apenas sacos de células; são cidades cuidadosamente organizadas onde diferentes “vizinhos” celulares se juntam para nos manter vivos e, em doenças, às vezes agem contra nós. Novas ferramentas de imagem e sequenciamento agora podem registrar onde cada célula está em uma lâmina de tecido, juntamente com o que ela está fazendo. Mas entender esse detalhe espacial vertiginoso é difícil. Este estudo apresenta o HRCHY‑CytoCommunity, um método computacional que reconstrói automaticamente como as células se agrupam em vizinhanças e em distritos maiores dentro de órgãos saudáveis e tumores, e que relaciona esses padrões a desfechos de pacientes.
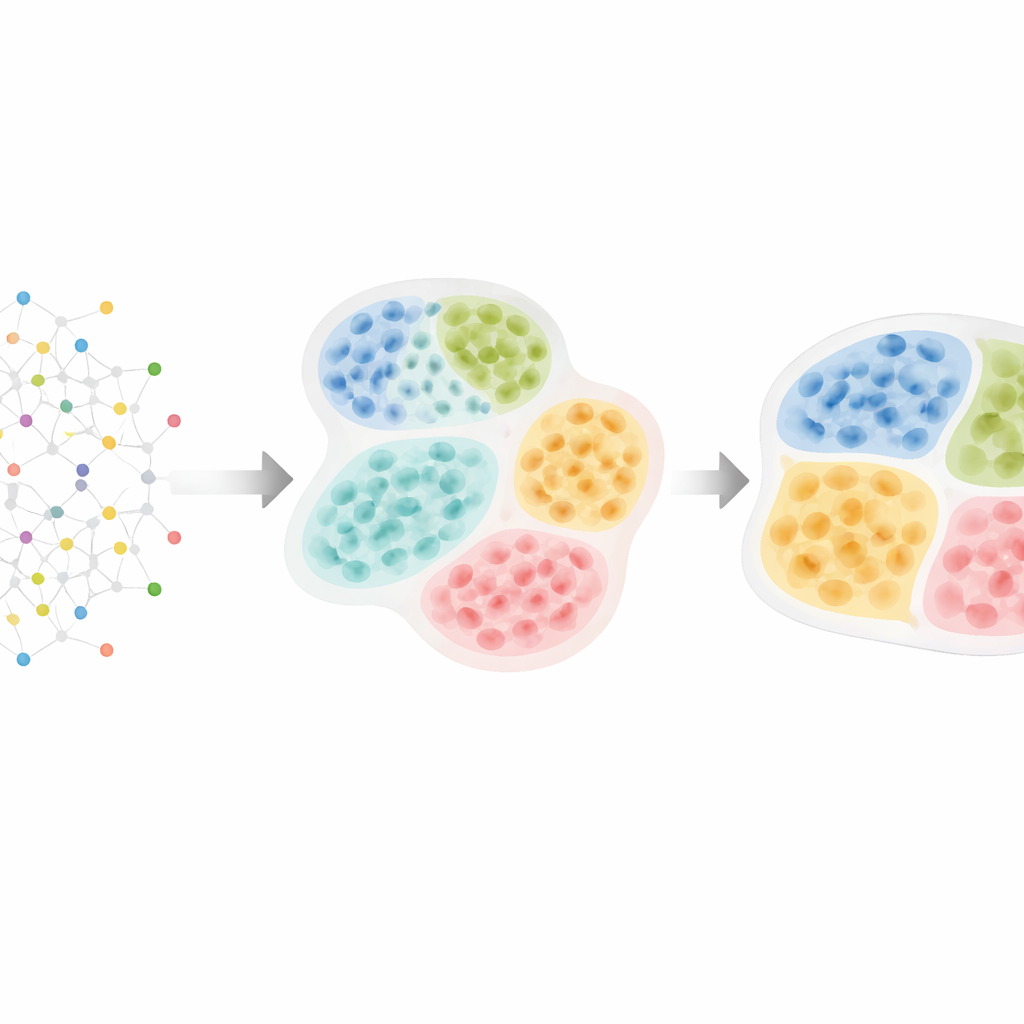
De mapas celulares à estrutura tecidual oculta
As modernas tecnologias de “ômicas” espaciais podem medir milhares de moléculas em dezenas ou centenas de milhares de células, preservando suas localizações exatas no tecido. Pesquisadores sabem que as células se organizam em camadas, zonas e compartimentos — por exemplo, regiões imunes versus cancerosas em tumores, ou núcleos distintos no cérebro. Esses padrões importam: tumores com células imunes segregadas das células cancerosas frequentemente se comportam de maneira diferente daqueles em que estão misturadas, e agregados imunes especiais chamados estruturas linfoides terciárias podem prever melhor sobrevida em vários cânceres. No entanto, a maioria das ferramentas computacionais existentes ou ignora essa hierarquia natural ou encontra estruturas em um único nível, dificultando ver como pequenas vizinhanças celulares se encaixam em distritos teciduais maiores.
Uma nova forma de ler vizinhanças celulares
O HRCHY‑CytoCommunity enfrenta esse desafio tratando o tecido como uma rede de células. Cada célula é um nó em um grafo, conectado aos seus vizinhos mais próximos no espaço. Em vez de depender diretamente das medidas brutas de genes ou proteínas, o método usa o tipo de cada célula (como célula cancerosa, célula T ou fibroblasto) como entrada principal. Uma rede neural gráfica então aprende padrões de como esses tipos celulares se organizam. Em um passo, agrupa células próximas em “vizinhanças celulares” de resolução fina. Em um segundo passo, agrega essas vizinhanças em “compartimentos teciduais” mais grossos, garantindo que cada célula pertença exatamente a uma vizinhança e que cada vizinhança esteja contida claramente em um único compartimento. Truques especiais de treinamento — como podar conexões fracas, adicionar ruído aleatório e incentivar agrupamentos estáveis e bem balanceados — ajudam o método a evitar agrupamentos frágeis ou triviais.
Encontrando estruturas através de órgãos, tecnologias e doenças
Os autores testaram o HRCHY‑CytoCommunity em uma ampla gama de conjuntos de dados espaciais de camundongos e humanos, cobrindo mapas de proteína baseados em imagem e mapas de RNA baseados em sequenciamento, e abrangendo baço, cérebro, intestino e tumores. No baço de camundongo, o método recuperou estruturas clássicas como a polpa vermelha e regiões linfoides, mesmo quando essas regiões estavam divididas em fragmentos desconectados. No tecido de câncer colorretal, separou claramente áreas tumorais de normais e destacou vizinhanças distintas nas bordas e nos núcleos do tumor. Em regiões do cérebro de camundongo, traçou com precisão núcleos e camadas corticais conhecidos, muitas vezes pequenos, que muitos outros métodos tendem a embaçar, e lidou com conjuntos de dados muito grandes contendo centenas de milhares de pontos em apenas alguns minutos. O framework também funciona quando cada ponto medido contém misturas de tipos celulares: ao primeiro estimar quais células estão presentes em cada ponto, ainda pode reconstruir camadas e sub-regiões com significado anatômico.
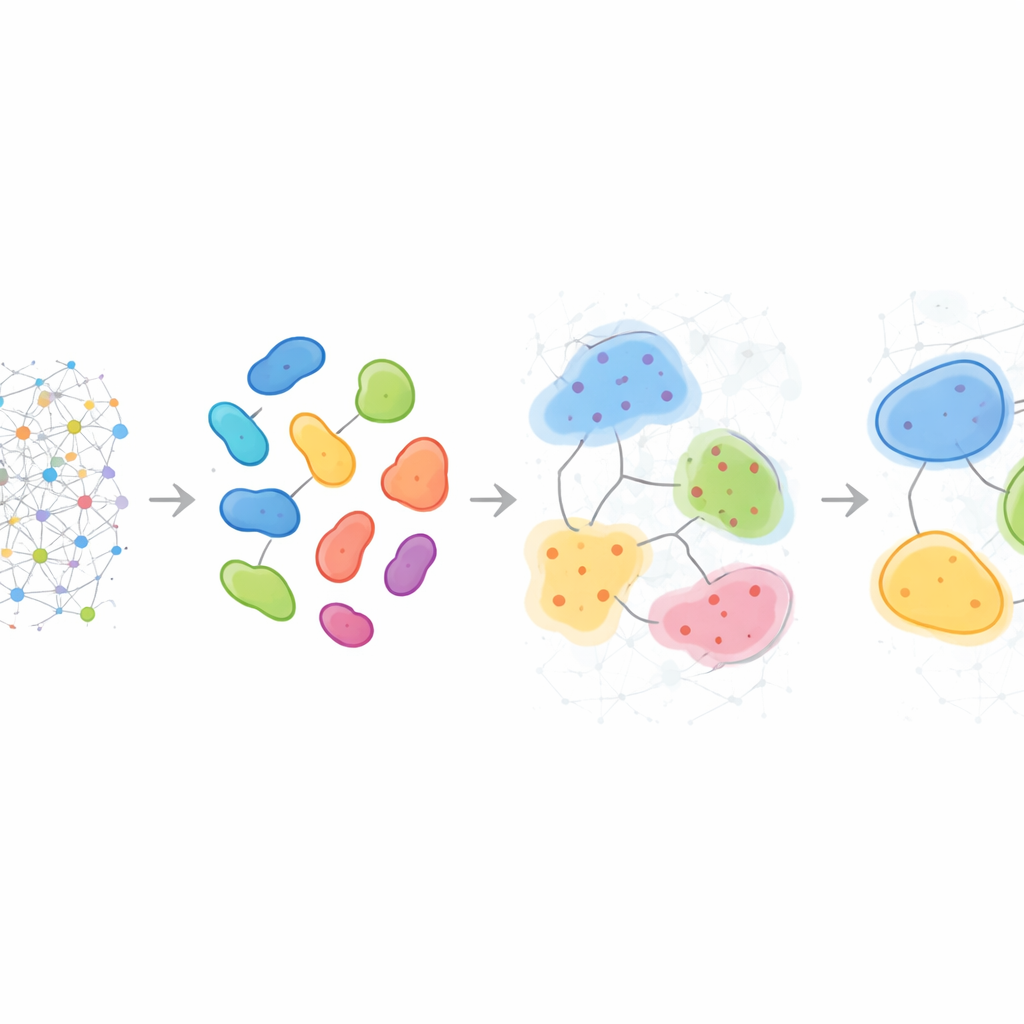
Padrões que diferem de paciente para paciente
Além de descrever amostras individuais, o HRCHY‑CytoCommunity pode alinhar vizinhanças e compartimentos entre muitos pacientes para definir um “vocabulário” compartilhado de estruturas multicelulares. No câncer de mama triplo‑negativo, o método encontrou de forma consistente compartimentos amplos ricos em células imunes e compartimentos ricos em células cancerosas, porém as vizinhanças mais finas dentro deles variaram de pessoa para pessoa. Alguns tumores continham combinações únicas de macrófagos, células T e vasos sanguíneos, ou bolsões mistos de câncer e neutrófilos, revelando microecologias individualizadas invisíveis a contagens simples de tipos celulares. Aplicado a uma grande coorte de câncer de mama, essas estruturas em múltiplas escalas ajudaram a estratificar pacientes por sobrevida: um compartimento enriquecido em um fenótipo particular de célula cancerosa marcou pacientes com melhores desfechos, enquanto certas vizinhanças ricas em fibroblastos ou em misturas específicas de células T e macrófagos sinalizaram grupos com prognóstico significativamente pior, provavelmente refletindo barreiras físicas ou funcionais à imunidade anti‑tumoral eficaz.
O que isso significa para entender e tratar doenças
Ao transformar mapas espaciais complexos de tipos celulares em uma hierarquia clara de vizinhanças e distritos, o HRCHY‑CytoCommunity oferece uma lente poderosa sobre como os tecidos são construídos e como se quebram na doença. A capacidade do método de funcionar em diferentes plataformas experimentais, lidar com conjuntos de dados enormes e fornecer cobertura completa e aninhada das células o torna uma ferramenta prática tanto para a biologia básica quanto para a pesquisa clínica. Em cânceres, pode revelar microarquiteturas ligadas à sobrevida e à resposta ao tratamento; em órgãos saudáveis, pode mapear como regiões especializadas cooperam. Em última instância, abordagens como esta podem ajudar médicos a ler a organização tecidual tão rotineiramente quanto leem exames laboratoriais hoje, orientando diagnósticos e tratamentos mais precisos.
Citação: Xie, R., Wang, Z., Liu, J. et al. HRCHY-CytoCommunity identifies hierarchical tissue organization in cell-type spatial maps. Nat Commun 17, 3312 (2026). https://doi.org/10.1038/s41467-026-70069-z
Palavras-chave: ômicas espaciais, arquitetura tecidual, redes neurais gráficas, microambiente tumoral, vizinhanças celulares